Clear Sky Science · pl
IL2Pepscan: Rama uczenia maszynowego do przewidywania peptydów indukujących IL-2 i ich identyfikacji w globalnych proteomach wirusów
Nauczanie układu odpornościowego za pomocą maleńkich fragmentów białek
Nowoczesne szczepionki i terapie przeciwnowotworowe coraz częściej polegają na precyzyjnym stymulowaniu układu odpornościowego zamiast na bezkrytycznym stosowaniu leków. W tym badaniu badacze analizują, jak niewielkie fragmenty białek, zwane peptydami, można dobierać tak, by uruchamiały silny komunikator immunologiczny — interleukinę‑2 (IL‑2). Korzystając z zaawansowanych modeli komputerowych, autorzy przeszukują zarówno znane dane immunologiczne, jak i katalogi białek tysięcy wirusów, aby znaleźć „igły” peptydowe w molekularnym stogu siana, które mogą pomóc w projektowaniu lepszych szczepionek i immunoterapii.
Dlaczego IL‑2 ma znaczenie dla zdrowia i chorób
IL‑2 to mała cząsteczka sygnalizacyjna, która działa jak czynnik wzrostu dla kluczowych komórek odpornościowych zwanych limfocytami T. Gdy te komórki po raz pierwszy natrafiają na zagrożenie — na przykład wirusa lub komórkę nowotworową — mogą wydzielić IL‑2, co pobudza limfocyty T do namnażania, specjalizacji i wytworzenia pamięci immunologicznej. IL‑2 pomaga też utrzymać komórki regulatorowe T, które zapobiegają temu, by układ odpornościowy atakował własne tkanki. Ze względu na tę dwojaką rolę IL‑2 stosowano jako lek w leczeniu nowotworów, takich jak czerniak, a także bada się jego zastosowanie w chorobach autoimmunologicznych. Jednak podawanie IL‑2 bezpośrednio może być obciążające dla pacjentów, dlatego rośnie zainteresowanie projektowaniem bezpiecznych peptydów, które skłonią organizm do wytwarzania IL‑2 w sposób bardziej kontrolowany i ukierunkowany.
Uczenie się „smaku” peptydów indukujących IL‑2
Badacze zaczęli od tysięcy sekwencji peptydowych, które już były testowane w eksperymentach laboratoryjnych i oznaczone jako indukujące IL‑2 lub nie. Oczyścili ten zbiór danych, usuwając duplikaty, nietypowe elementy budulcowe i peptydy zbyt krótkie lub zbyt długie, otrzymując ponad 6000 dobrze scharakteryzowanych przykładów. Analizując aminokwasy tworzące te peptydy, odkryli wyraźne różnice między obiema grupami. Peptydy indukujące IL‑2 miały tendencję do bycia bogatszymi w aminokwasy hydrofobowe, czyli odpychające wodę, takie jak leucyna i alanina, podczas gdy peptydy nieindukujące zawierały więcej reszt polarnych i naładowanych. Pewne krótkie wzorce, czyli motywy, takie jak „LEGS” i „ALEG”, pojawiały się wyłącznie w peptydach indukujących IL‑2, co sugeruje obecność sygnatur strukturalnych mogących wywoływać aktywację odpornościową.
Uczenie maszyn rozpoznawania wzorców wzmacniających odporność
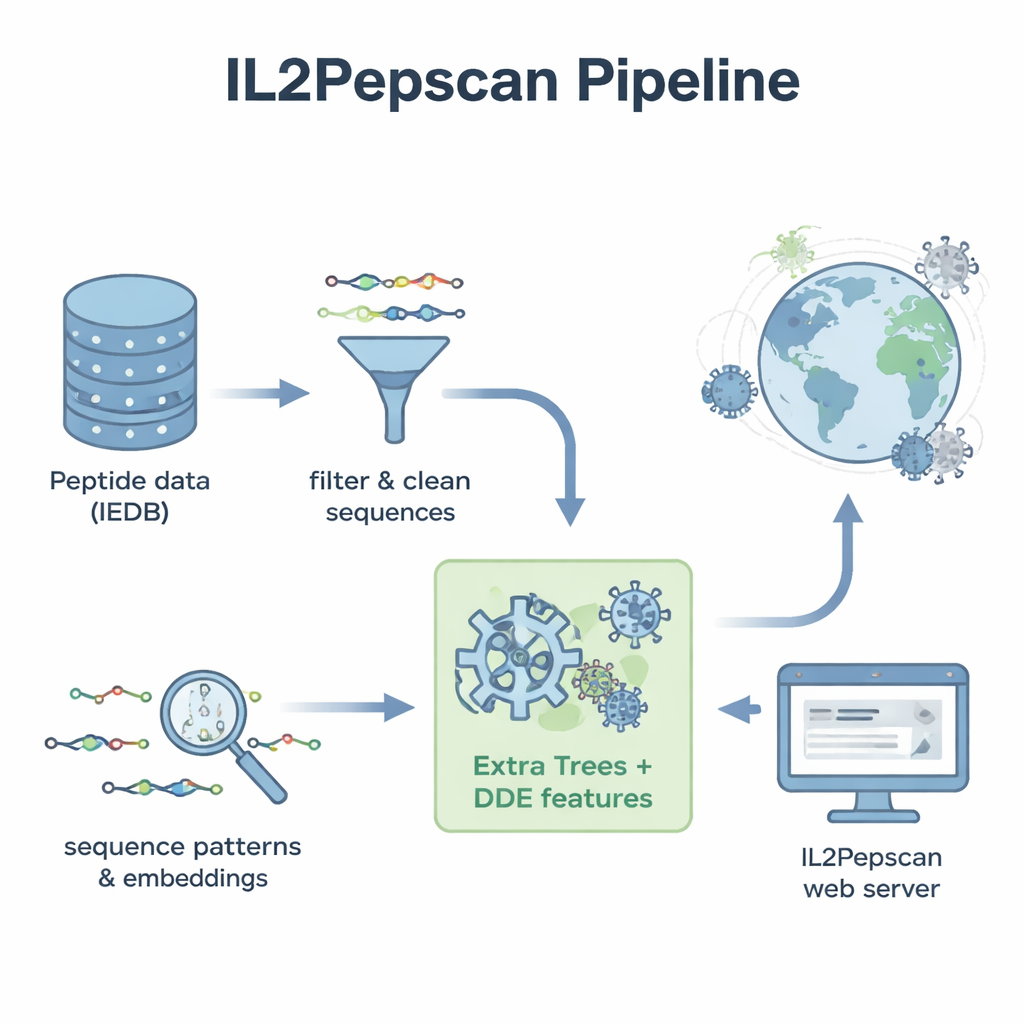
Aby przekształcić te wzorce w praktyczne narzędzie predykcyjne, zespół skonwertował każdy peptyd na opisy numeryczne odzwierciedlające jego skład i kolejność aminokwasów. Przetestowali szereg metod uczenia maszynowego — w tym popularne algorytmy, takie jak lasy losowe, maszyny wektorów nośnych i metody wzmacniania (boosted trees) — oraz architektury głębokiego uczenia często stosowane w zadaniach językowych i obrazowych. Wykorzystali też duży „model języka” białek o nazwie ProtBERT, pierwotnie trenowany na setkach milionów sekwencji białkowych, i dostroili go pod kątem rozpoznawania sygnałów związanych z IL‑2. Po rozległych testach z walidacją krzyżową i niezależnym zbiorem testowym wyróżnił się model Extra Trees w połączeniu z zestawem cech zwanym dipeptide deviation from expected mean (DDE). Model ten osiągnął niemal 80% dokładności i silny współczynnik korelacji, przewyższając kilka podejść głębokiego uczenia.
Skanowanie świata wirusów w poszukiwaniu ukrytych wyzwalaczy odporności
Uzbrojeni w najlepszy model, autorzy rozszerzyli poszukiwania. Zgromadzili referencyjne sekwencje białkowe z ponad 14 000 wirusów, podzielili te białka na około 156 milionów nakładających się peptydów i ocenili, które z nich model przewiduje jako potencjalnie indukujące IL‑2. Wśród kandydatów o najwyższych wynikach znalazły się peptydy z dobrze znanych rodzin wirusów, w tym flawiwirusów takich jak wirus Zachodniego Nilu, Zika, żółtej gorączki i wirus zapalenia wątroby typu C, a także z wirusów Influenzy i SARS‑CoV‑2. Wiele obiecujących peptydów pochodziło z białek otoczki lub nukleokapsydów wirusowych — tych samych typów białek, które w innych badaniach wykazywały zdolność wywoływania odpowiedzi IL‑2 u zwierząt. Model wskazał także potencjalne peptydy indukujące IL‑2 kodowane przez bakteriofagi, wirusy atakujące bakterie, co sugeruje jeszcze szerszy krajobraz sekwencji istotnych dla odporności.
Od algorytmu do narzędzia dostępnego dla wszystkich
Aby udostępnić swoje wyniki poza laboratorium obliczeniowym, autorzy stworzyli publiczny serwer internetowy o nazwie IL2Pepscan. Badacze mogą wkleić na stronie sekwencje peptydów lub białek, by oszacować ich potencjał do indukcji IL‑2, projektować nowe warianty poprzez mutacje pozycji, skanować całe białka w poszukiwaniu gorących miejsc lub wyszukiwać znane motywy związane z IL‑2. Chociaż badanie nie potwierdza jeszcze eksperymentalnie każdego przewidywanego peptydu, zgodność z istniejącymi wynikami laboratoryjnymi sugeruje, że IL2Pepscan może niezawodnie zawęzić listę kandydatów do dalszych testów. Dla osób niebędących specjalistami główny wniosek jest taki, że starannie wytrenowane algorytmy mogą przesiać ogromne zbiory danych biologicznych, aby wyodrębnić małe fragmenty białkowe, które w przyszłości mogą pomóc szczepionkom i immunoterapiom skłonić układ odpornościowy do silniejszej — i bardziej precyzyjnej — odpowiedzi.
Cytowanie: Arora, P., Abhigyan, R., Periwal, N. et al. IL2Pepscan: A machine learning framework for predicting IL-2 inducing peptides and their identification across global viral proteomes. Sci Rep 16, 6701 (2026). https://doi.org/10.1038/s41598-026-35977-6
Słowa kluczowe: interleukina-2, peptydowe szczepionki, uczenie maszynowe, proteom wirusowy, immunoterapia