Clear Sky Science · pl
Analiza strukturalna wiązania OCT4 z nukleosomami ludzkiego LIN28B
Jak komórki uzyskują dostęp do ukrytych instrukcji genetycznych
Każda komórka w twoim ciele zawiera tę samą sekwencję DNA, jednak tylko jej część jest wykorzystywana w danym typie komórek. Wiele z tej kontroli wynika z tego, jak DNA jest ciasno upakowane wokół białek zwanych histonami, tworząc struktury nazywane nukleosomami. Takie ciasne upakowanie może ukrywać kluczowe fragmenty DNA przed maszynerią komórkową odczytującą geny. Opisane tutaj badanie analizuje, w jaki sposób specjalne białko OCT4 potrafi odnaleźć i związać swoje docelowe DNA nawet wtedy, gdy jest ono owinięte i częściowo ukryte w nukleosomach — proces kluczowy dla tożsamości komórek macierzystych i reprogramowania komórkowego.
Dlaczego czynniki pionierskie są istotne dla komórek macierzystych
OCT4 należy do niewielkiej, lecz silnej grupy białek zwanych pionierskimi czynnikami transkrypcji. W odróżnieniu od większości białek wiążących DNA, czynnicy pionierskie potrafią wkroczyć w skondensowane, „wyłączone” regiony genomu i pomagać w uruchamianiu genów, odgrywając kluczową rolę w kształtowaniu tożsamości komórkowej oraz w reprogramowaniu komórek dorosłych do stanów podobnych do komórek macierzystych. OCT4 współdziała z partnerami takimi jak SOX2, KLF4 i c-MYC, by indukować pluripotencję — właściwość pozwalającą komórkom macierzystym przekształcić się niemal w każdy typ komórki. Zrozumienie, w jaki sposób OCT4 zaczepia się na DNA owiniętym w nukleosomy, jest niezbędne do rozszyfrowania mechanizmów zmiany losu komórek oraz do projektowania precyzyjniejszych metod manipulacji tożsamością komórkową w badaniach i medycynie.
Sprawdzanie, czy różnice między gatunkami mają znaczenie
Większość badań strukturalnych nukleosomów wykorzystuje histony pochodzące albo od żab (Xenopus laevis), albo od ludzi, ponieważ te białka są bardzo podobne, choć nie identyczne. Niewielkie różnice w sekwencjach aminokwasowych mogłyby teoretycznie zmieniać sposób, w jaki DNA jest nawinięte lub jak białka regulatorowe, takie jak OCT4, się z nim wiążą. W wcześniejszych pracach autorzy wykazali, że OCT4 wiąże specyficzną sekwencję regulatorową DNA z ludzkiego genu LIN28B, gdy to DNA jest owinięte w nukleosomy z histonów żabich. W nowym badaniu postawili proste, ale istotne pytanie: czy OCT4 zachowuje się tak samo, gdy nukleosomy zbudowane są z histonów ludzkich zamiast żabich?
Składanie i badanie nukleosomów LIN28B
Aby to sprawdzić, badacze odtworzyli nukleosomy w laboratorium, używając 182-parowej sekwencji DNA LIN28B oraz histonów pochodzących z człowieka lub żaby, złożonych metodą „powolnej dializy” naśladującą warunki panujące w komórce. Testy żelowe potwierdziły, że oba typy oktamerów histonowych efektywnie tworzyły nukleosomy. Następnie zbadali, jak te nukleosomy osadzają się na sekwencji LIN28B. Zarówno eksperymenty żelowe, jak i cięcie DNA z następnym sekwencjonowaniem (MNase-seq) wykazały, że DNA LIN28B może przyjmować wiele pozycji na rdzeniu histonowym, a to zachowanie nie zmienia się po ogrzaniu nukleosomów do temperatury ciała. Co kluczowe, pochodzenie histonów — żabie czy ludzkie — nie miało zauważalnego wpływu ani na pozycjonowanie DNA, ani na siłę wiązania OCT4.
Wizualizacja OCT4 na nukleosomie
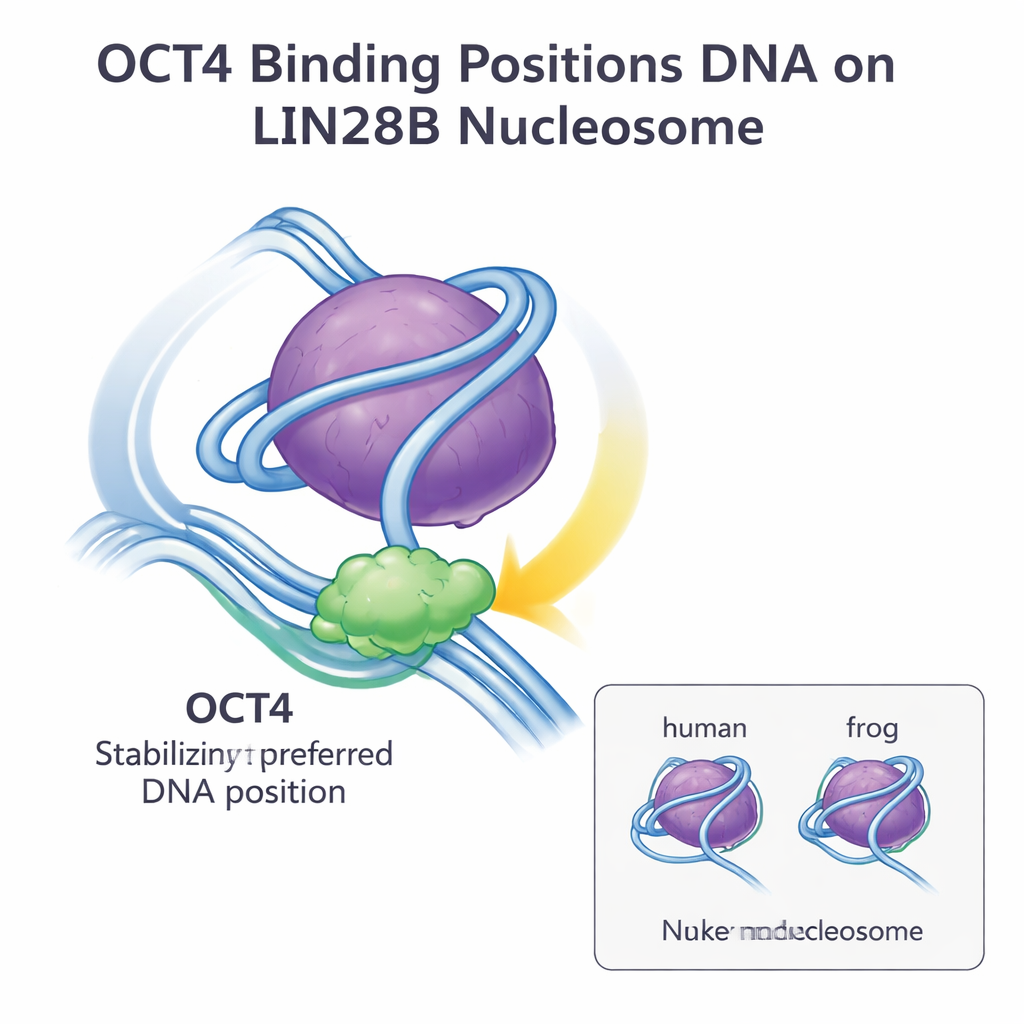
Zespół następnie użył krioelektronowej mikroskopii (cryo-EM), aby zobrazować strukturę OCT4 związanej z nukleosomami LIN28B zawierającymi ludzkie histony. Z około 15 000 cząstek odtworzyli trójwymiarową mapę o rozdzielczości około 6 angstremów. Obrazy pokazały, że obie domeny wiążące DNA w OCT4 stykają się z tym samym odsłoniętym fragmentem DNA w pobliżu punktu wejścia i wyjścia nukleosomu, tzw. regionu łącznikowego. To dokładnie to miejsce i orientacja, które wcześniej obserwowano, gdy OCT4 wiązał nukleosomy z histonami żabimi. Gdy starszy model dopasowano do nowej mapy cryo-EM, zgodność była doskonała, co wskazuje, że ogólna architektura kompleksu OCT4–nukleosom LIN28B jest zasadniczo identyczna dla obu gatunków.
Ogólna strategia otwierania chromatyny
Wspólnie te wyniki pokazują, że niewielkie różnice sekwencji między histonami żabimi i ludzkimi nie zmieniają tego, jak OCT4 rozpoznaje i wiąże nukleosom LIN28B. DNA LIN28B naturalnie lokuje się w kilku możliwych pozycjach na rdzeniu histonowym, ale wiązanie OCT4 wybiera i stabilizuje jedną preferowaną pozycję, czyniąc dodatkowe miejsca wiążące bardziej dostępnymi dla OCT4 i jego partnerów. Ta strategia „pozycjonowania i stabilizacji DNA” wydaje się ogólną metodą, dzięki której czynniki pionierskie uzyskują dostęp do zamkniętej chromatyny i sprzyjają kooperatywnemu wiązaniu innych regulatorów. Dla czytelnika niebędącego specjalistą najważniejszy wniosek jest taki, że podstawowy projekt nukleosomu oraz sposób, w jaki kluczowe białka regulatorowe, takie jak OCT4, z nim współdziałają, są wysoce konserwatywne między gatunkami — co wzmacnia przekonanie, że obserwacje z organizmów modelowych mogą wiarygodnie informować nasze rozumienie kontroli genów u ludzi i biologii komórek macierzystych.
Cytowanie: Sinha, K.K., Halic, M. Structural analysis of OCT4 binding to human LIN28B nucleosomes. Sci Rep 16, 5704 (2026). https://doi.org/10.1038/s41598-026-35959-8
Słowa kluczowe: czynniki pionierskie transkrypcji, OCT4, struktura nukleosomu, dostępność chromatyny, regulacja genów w komórkach macierzystych