Clear Sky Science · pl
Strukturalne, dysocjacyjne metody PCA do dekompozycji sygnałów neuroobrazowania o wysokiej wymiarowości
Rozplątywanie ukrytych sygnałów mózgu
Współczesne skany mózgu mogą rejestrować aktywność z setek tysięcy miejsc co sekundę, lecz przekształcenie tej lawiny liczb w jasne, znaczące sieci jest niezwykle trudne. Różne procesy mózgowe często nakładają się w przestrzeni i czasie, jak kilka stacji radiowych nadających na zbliżonych częstotliwościach. W artykule przedstawiono nowe narzędzia matematyczne, które pomagają wydzielić te splecione sygnały w sposób bardziej klarowny, obiecując ostrzejsze mapy funkcji mózgu zarówno dla badań podstawowych, jak i zastosowań klinicznych.
Dlaczego standardowe metody zawodzą
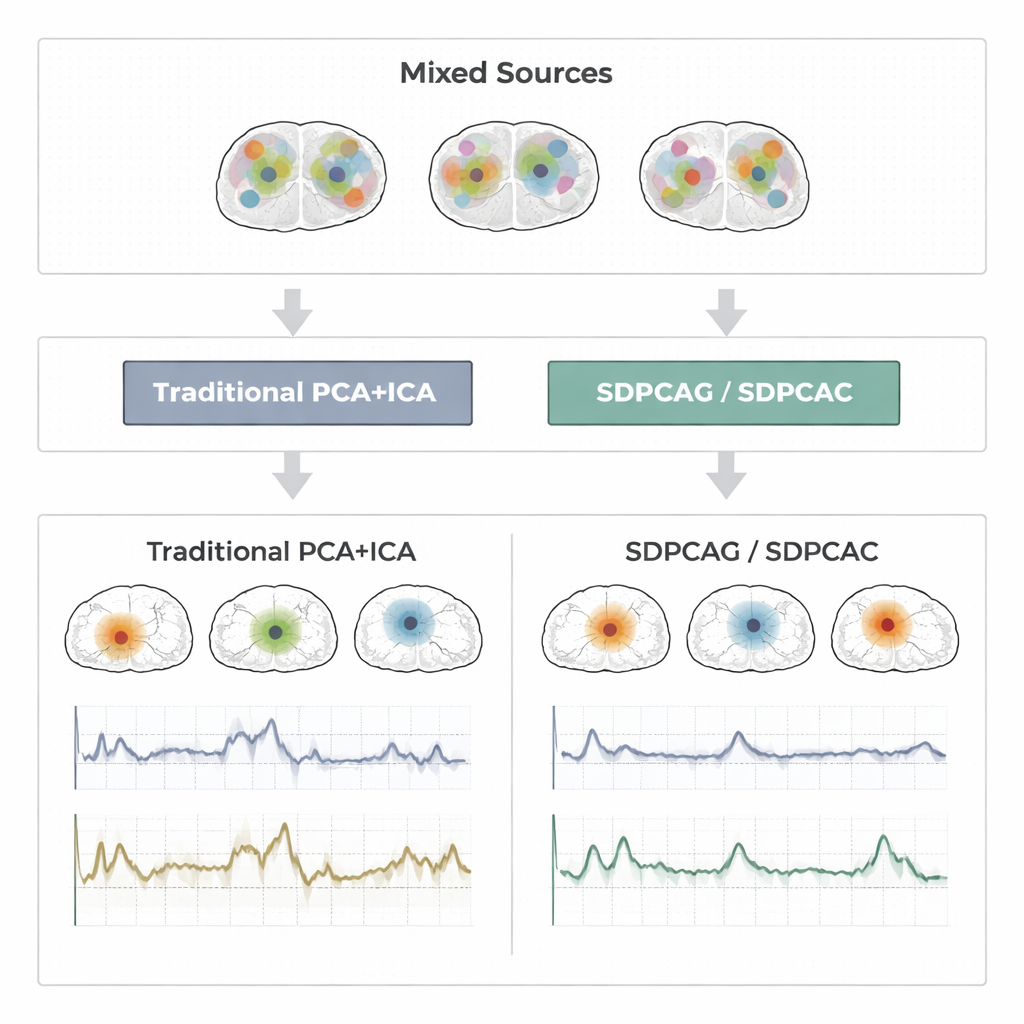
Przez dziesięciolecia badacze polegali na technikach zwanych analizą głównych składowych (PCA), rzadką PCA oraz analizą składowych niezależnych (ICA) do kompresji i separacji danych funkcjonalnego rezonansu magnetycznego (fMRI). PCA znajduje wzorce wyjaśniające większość zmienności w danych, ale każdy wzorzec miesza informacje niemal z każdego miejsca w mózgu, co utrudnia interpretację. Rzadka PCA próbuje to naprawić, zmuszając każdy wzorzec do używania tylko podzbioru lokalizacji, a ICA idzie dalej, zakładając statystyczną niezależność podstawowych sygnałów mózgowych. W praktyce jednak prawdziwe sieci mózgowe nakładają się i wzajemnie na siebie wpływają. Gdy to się dzieje, założenia o niezależności i rzadkości zawodzą. W efekcie powstają pofragmentowane mapy i zaszumione przebiegi czasowe, które przestają odpowiadać rzeczywistemu zachowaniu sieci mózgowych.
Nowy sposób rozdzielania sygnałów
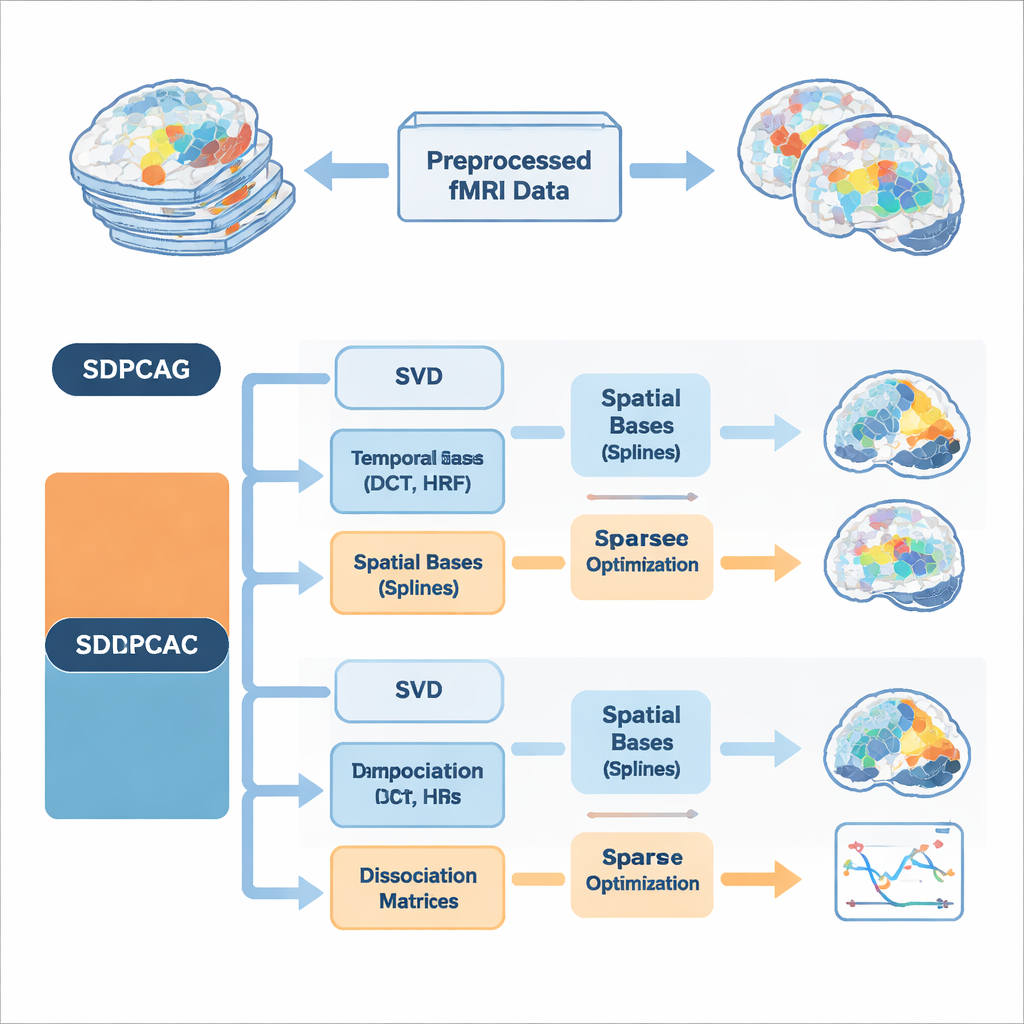
Autorzy proponują zintegrowane podejście nazwane strukturalną, dysocjacyjną PCA, zaimplementowane w dwóch algorytmach: SDPCAG i SDPCAC. Zamiast traktować przestrzeń i czas oddzielnie, metoda przekształca cały zestaw danych fMRI jednym, starannie zaprojektowanym rozkładem. Zaczyna się od standardowego rozkładu niskiego rzędu danych, a następnie wprowadza specjalne macierze „dysocjacji”, które przeważają i obracają jednocześnie mapy przestrzenne i przebiegi czasowe. Równocześnie komponenty te są reprezentowane za pomocą zestawów gładkich elementów bazowych: czasopodobnych fal cosinusowych, modeli hemodynamicznej odpowiedzi na aktywność neuronalną oraz gładkich krzywych przestrzennych zwanych funkcjami sklejanymi (spline). Ucząc się, jak łączyć te elementy przy wymuszaniu rzadkości — zachowując tylko najistotniejsze składniki — metoda potrafi rozdzielić nakładające się sieci bez narzucania nierealistycznej niezależności.
Wbudowanie wiedzy o mózgu od początku
Kluczową innowacją jest to, że algorytmy inkorporują wiedzę a priori o sygnałach mózgowych bezpośrednio w dekompozycji, zamiast oczyszczać wyniki później. Po stronie czasowej stosują dyskretne funkcje cosinusowe, aby zachęcać do gładkich przebiegów czasowych, oraz uwzględniają standardowe modele hemodynamicznej odpowiedzi — opóźnionego sygnału dotyczącego utlenowania krwi mierzonego przez fMRI. Po stronie przestrzennej bazy spline sprzyjają spójnym, ciągłym wzorom aktywacji zamiast rozrzuconych punktów. Dodatkowe ograniczenia limitują, ile funkcji bazowych czasowych i przestrzennych każdy komponent może użyć, co zmniejsza przeuczenie na szumie i odzwierciedla ideę, że prawdziwe sieci mózgowe są stosunkowo zwarte zarówno w przestrzeni, jak i w czasie. Przedstawione są dwie uzupełniające się strategie optymalizacji: SDPCAG aktualizuje całe macierze blokami, podczas gdy SDPCAC dopracowuje pojedynczy komponent w danym czasie, używając błędów resztkowych, kosztem nieco wyższych obliczeń za większą elastyczność dostosowań.
Testowanie metody
Aby ocenić skuteczność tych pomysłów, autorzy przeprowadzili obszerne testy na trzech typach danych: starannie zaprojektowanych syntetycznych sygnałach fMRI z znaną „prawdą”; eksperymencie motorycznym w układzie blokowym z projektu Human Connectome Project; oraz badaniu zdarzeń związanym z stukaniem palcem z niezależnego laboratorium. W tych warunkach porównali SDPCAG i SDPCAC z wiodącymi alternatywami łączącymi penalizowaną dekompozycję macierzy, rzadką PCA, ICA i uczenie słownikowe. Mierzyli, jak bardzo odzyskane przebiegi czasowe odpowiadają znanym wzorcom zadań, jak dobrze mapy przestrzenne pokrywają się z ustalonymi sieciami stanu spoczynku oraz jak dokładnie odzyskiwane są źródła przy różnych poziomach szumu. Nowe metody konsekwentnie generują czyściejsze, bardziej zlokalizowane mapy mózgu i mniej zaszumione szeregi czasowe, utrzymując silną wydajność nawet przy dużym zanieczyszczeniu danych. Jeden z algorytmów, SDPCAG, poprawia dokładność odzyskiwania źródeł o około 22% w porównaniu z silną metodą konkurencyjną, jednocześnie działając szybciej niż jego bardziej szczegółowy odpowiednik SDPCAC.
Znaczenie dla badań nad mózgiem
Mówiąc prosto, ta praca oferuje lepszy sposób „rozmieszania” sygnałów w danych fMRI. Poprzez wspólne modelowanie przestrzeni i czasu, użycie realistycznych priorytetów dotyczących zachowania aktywności mózgowej i przepływu krwi oraz wymuszanie przemyślanej rzadkości, SDPCAG i SDPCAC tworzą sieci mózgowe, które są zarówno ostrzejsze na obrazach, jak i wierniejsze względem ich podstawowych przebiegów czasowych. To może prowadzić do bardziej wiarygodnego wykrywania aktywacji związanych z zadaniem i precyzyjniejszego mapowania sieci stanu spoczynku, co z kolei wspiera badania nad schorzeniami takimi jak choroba Alzheimera, zaburzenia psychiatryczne i inne choroby mózgu. Choć wciąż jest miejsce na przyspieszenie i rozszerzenie podejścia — na przykład do badań wielooddziałowych czy multimodalnego obrazowania — stanowi ono istotny krok w kierunku przekształcania wysokowymiarowych danych skanowych w wiarygodne, interpretowalne obrazy działającego ludzkiego mózgu.
Cytowanie: Khalid, M.U., Nauman, M.M., Rehman, S.U. et al. Structured dissociative PCA methods for high dimensional neuroimaging signal decomposition. Sci Rep 16, 6911 (2026). https://doi.org/10.1038/s41598-026-35764-3
Słowa kluczowe: dekompozycja sygnału fMRI, rzadka PCA, mapowanie sieci mózgowych, ślepe rozdzielanie źródeł, łączność w stanie spoczynku