Clear Sky Science · pl
Różnorodność genetyczna Pseudomonas aeruginosa wyizolowanej z próbek klinicznych z wykorzystaniem markera molekularnego ISSR w szpitalu klinicznym trzeciego stopnia
Dlaczego szpitalne zarazki mają znaczenie dla nas wszystkich
Każdy, kto spędził czas w szpitalu — jako pacjent lub odwiedzający bliską osobę — liczy na to, że antybiotyki zadziałają, gdy są najbardziej potrzebne. Tymczasem niektóre drobnoustroje stają się tak odporne, że nawet najsilniejsze leki mają trudności, by je powstrzymać. Artykuł ten przygląda się jednemu z takich sprawców, bakterii o nazwie Pseudomonas aeruginosa, i pokazuje, jak naukowcy w indyjskim szpitalu zmapowali jej ukrytą różnorodność genetyczną, by lepiej zrozumieć, dlaczego tak trudno ją kontrolować.
Uparty zarazek we współczesnych szpitalach
Pseudomonas aeruginosa jest trudnym przeciwnikiem. Doskonale rozwija się w wilgotnych środowiskach — od przewodów respiratorów po opatrunki na rany — i atakuje szczególnie osoby o osłabionej odporności z powodu choroby, oparzeń czy długiego pobytu w szpitalu. Może wywoływać poważne infekcje płuc, krwi, dróg moczowych i ran. Szczególnie niebezpieczna jest jej zdolność do jednoczesnego opierania się wielu antybiotykom, co zmienia rutynowe zakażenia w zagrażające życiu kryzysy oraz zwiększa koszty leczenia i długość pobytów w szpitalu na całym świecie.
Przyglądanie się temu, co pod powierzchnią infekcji
Aby sprawdzić, jak różnorodny jest ten zarazek w obrębie jednego szpitala, badacze zebrali 100 próbek bakteryjnych z krwi, moczu, plwociny i wymazów z ran pobranych podczas rutynowej opieki w dużym szpitalu klinicznym we wschodnich Indiach. Skoncentrowali się na 18 szczepach opornych na wiele leków i przebadali, jak każdy reaguje na szeroki panel antybiotyków. Niepokojąco, ponad cztery z pięciu próbek były oporne na kluczowe leki, takie jak cefoperazon, meropenem i imipenem — leki często stosowane jako ostatnia linia obrony, gdy inne zawodzą. Kilka antybiotyków, w tym niektóre rzadziej używane, wciąż działało lepiej, co sugeruje pozostające, choć kurczące się, opcje leczenia. 
Odczytywanie „kodów kreskowych” bakterii
Policzenie, na które leki bakterie są odporne, to tylko połowa historii. Zespół chciał także wiedzieć, czy infekcje pochodzą od jednego skutecznego „superszczepu” rozprzestrzeniającego się w szpitalu, czy od wielu niespokrewnionych linii przybywających i ewoluujących niezależnie. W tym celu zastosowali podejście do znakowania DNA zwane ISSR, które uwydatnia odcinki kodu genetycznego leżące pomiędzy krótkimi powtórzeniami. Po amplifikacji w maszynie PCR i rozdziale na żelu te odcinki tworzą wzór prążków, który działa jak kod kreskowy dla każdego szczepu. Korzystając z 17 informatywnych starterów, badacze wygenerowali 95 odrębnych fragmentów DNA, a następnie porównali wzory we wszystkich 18 szczepach za pomocą narzędzi komputerowych grupujących podobne odciski palców.
Wiele odległych krewniaków, nie jeden superzarazek
Porównania genetyczne wykazały, że w szpitalu nie mieli do czynienia z jednym wymykającym się klonem. Zamiast tego szczepy podzieliły się na kilka odrębnych klastrów, ze współczynnikami podobieństwa od dość bliskich krewnych po bardzo odległych kuzynów. Niektóre izolaty, które zachowywały się podobnie w testach na leki, okazały się genetycznie różne, podczas gdy inne, spokrewnione, dzieliły elementy oporności. Wykresy głównych składowych i diagramy przypominające drzewa wzmacniały obraz współistnienia wielu linii w tej samej placówce, zamiast jednego dominującego szczepu rozprzestrzeniającego się po całym szpitalu. Tę różnorodność prawdopodobnie napędzają wymiana genów między bakteriami, mutacje i adaptacja pod ciągłą presją antybiotyków oraz układu odpornościowego człowieka. 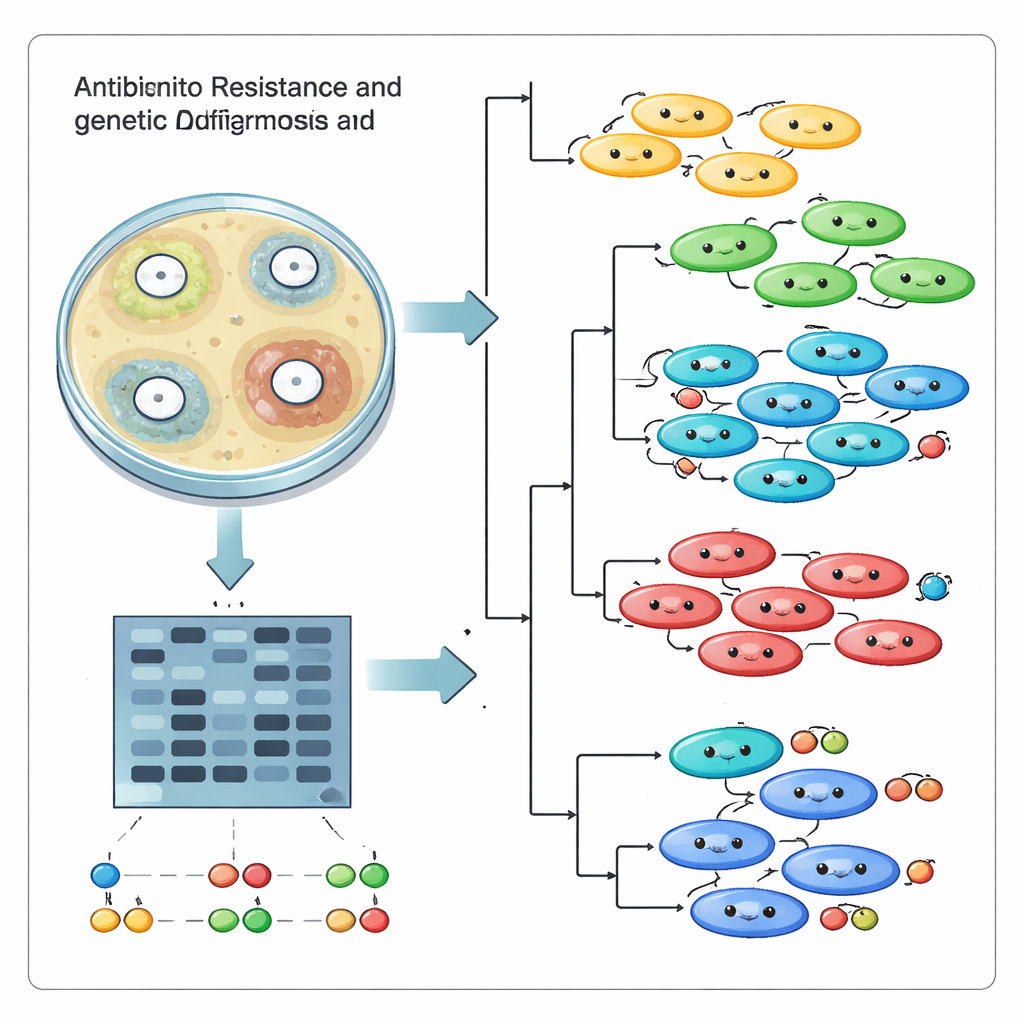
Co to oznacza dla pacjentów i szpitali
Dla szpitali te wyniki niosą jasny przekaz: śledzenie jedynie, które antybiotyki zawodzą, nie wystarcza. Ponieważ genetycznie różne szczepy mogą wykazywać podobne wzory oporności — a blisko spokrewnione mogą zachowywać się inaczej — zespoły medyczne potrzebują zarówno rutynowych testów wrażliwości na leki, jak i okresowego nadzoru genetycznego, by obserwować, jak populacja bakterii zmienia się w czasie. Metoda ISSR zastosowana tutaj jest stosunkowo prosta i niskokosztowa, co czyni ją atrakcyjną dla placówek o ograniczonych zasobach, chociaż autorzy podkreślają, że połączenie jej z bardziej szczegółowym sekwencjonowaniem całego genomu w przyszłych badaniach dałoby pełniejszy obraz.
Ukryty krajobraz, który wymaga czujności
Mówiąc wprost, badanie pokazuje, że w obrębie pojedynczego szpitala Pseudomonas aeruginosa to nie jeden wróg, lecz tłum spokrewnionych, lecz odrębnych sprawców, wielu już uzbrojonych przeciwko kilku antybiotykom. Mapując ten ukryty krajobraz różnorodności, naukowcy dostarczają narzędzi i wglądu, które mogą pomóc lekarzom wybierać lepiej ukierunkowane terapie, a zespołom kontroli zakażeń opracowywać mądrzejsze strategie powstrzymywania rozprzestrzeniania. Ciągłe monitorowanie tych wzorców genetycznych będzie niezbędne, by wyprzedzać tego adaptującego się zarazka i utrzymywać opiekę szpitalną bezpieczną dla pacjentów.
Cytowanie: Mishra, P., Sahoo, D. & Sahu, M.C. Genetic diversity of Pseudomonas aeruginosa isolated from clinical samples with ISSR molecular marker in a tertiary care teaching hospital. Sci Rep 16, 5315 (2026). https://doi.org/10.1038/s41598-026-35090-8
Słowa kluczowe: Pseudomonas aeruginosa, oporność na antybiotyki, infekcje szpitalne, różnorodność genetyczna, typowanie molekularne