Clear Sky Science · pl
Prawie kompletna biblioteka referencyjna 12S DNA dla ryb słodkowodnych Gujany Francuskiej, północny obszar Amazonii
Dlaczego ukryte ryby mają znaczenie
Rzeki na północnym krańcu Amazonii kryją zdumiewającą różnorodność ryb, z których wiele rzadko widują ludzie i które trudniej jest badać naukowcom. Tymczasem gatunki te są kluczowe dla sieci troficznych, rybołówstwa i zdrowia jednych z ostatnich wielkich lasów deszczowych świata. Niniejsze badanie podejmuje zaskakującą przeszkodę w poznaniu tego podwodnego życia: nie brak zaawansowanych narzędzi, lecz brak „książki telefonicznej”, która łączy anonimowe fragmenty DNA z rzeczywistymi gatunkami ryb. Tworząc niemal kompletną bibliotekę referencyjną DNA dla ryb słodkowodnych Gujany Francuskiej, autorzy otwierają potężne nowe sposoby monitorowania bioróżnorodności, śledzenia wpływów człowieka i wspierania ochrony w szerszym regionie Amazonii.
Odczytywanie rzek przez ślady
Zamiast łapać każdą rybę, współczesne badania mogą „czytać” rzeki, filtrując wodę i analizując drobne fragmenty materiału genetycznego, które zwierzęta pozostawiają, zwane środowiskowym DNA lub eDNA. Gdy te fragmenty są amplifikowane i sekwencjonowane, można je porównać z biblioteką referencyjną, by ujawnić, jakie gatunki występują. Jednak w megabioróżnorodnych tropikalnych systemach większość gatunków wciąż nie ma odpowiednich wpisów DNA, a powszechnie stosowane markery genetyczne bywają zbyt długie lub niewystarczająco specyficzne dla śladowych fragmentów w wodzie. Dla ryb krótkie odcinki genu 12S okazały się optymalnym wyborem: są na tyle krótkie, by dało się je odzyskać z zdegradowanego DNA, a jednocześnie zwykle wystarczająco różnicujące, by odróżnić blisko spokrewnione gatunki — jeśli tylko istnieje dobra biblioteka referencyjna.
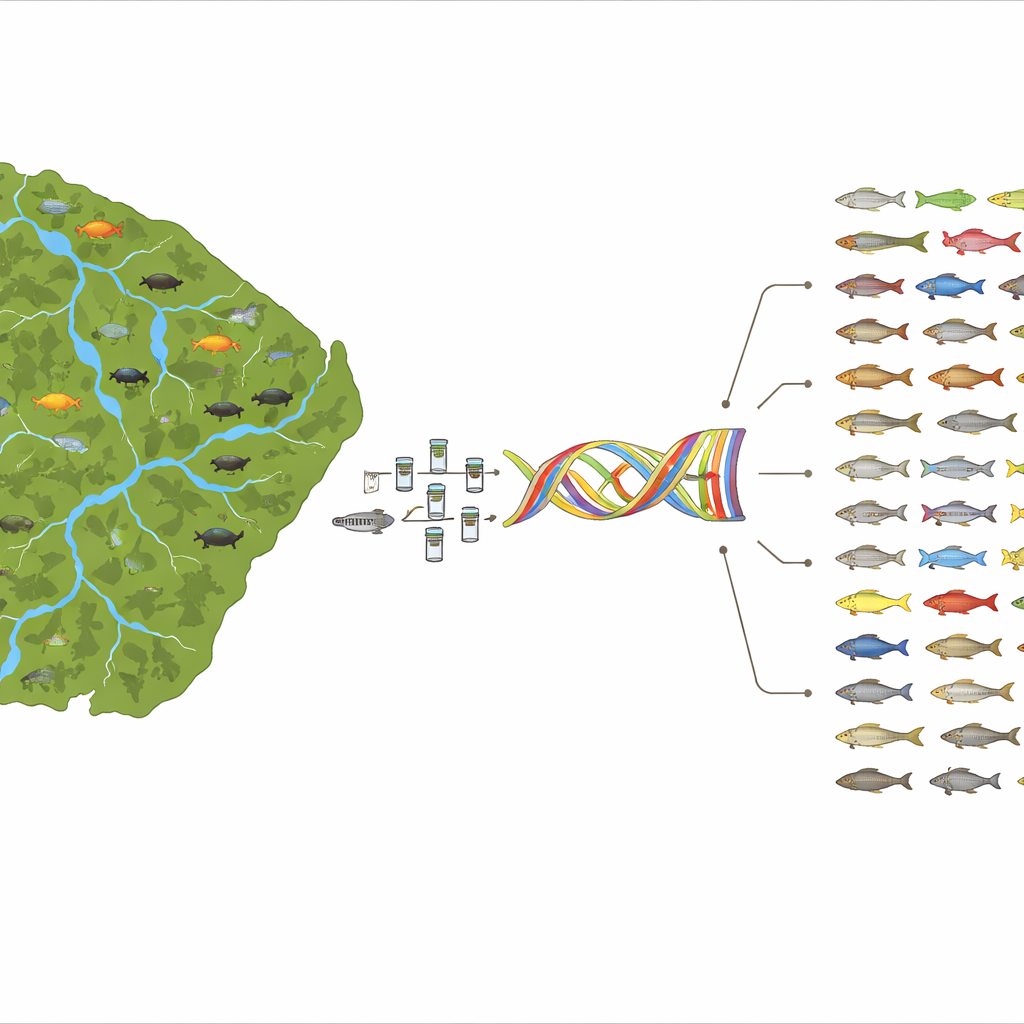
Budowanie katalogu genetycznego dzikiej granicy
Gujana Francuska, w przeważającej części porośnięte lasem terytorium na tarczy Gujańskiej między Brazylią a Surinamem, jest poprzecinana ośmioma głównymi zlewniami rzecznymi i rozległymi bagnami. Te wody kryją co najmniej 415 gatunków ryb słodkowodnych, z czego około jedna czwarta występuje tylko tam. W ciągu 15 lat i ponad 25 ekspedycji zespół pobierał próbki ryb w tych rzekach, używając sieci, pułapek i innych standardowych technik. Dla każdego złowionego osobnika pobierano mały fragment płetwy, konserwowano go w etanolu i później izolowano DNA w laboratorium. Wykorzystano też zbiory muzealne w Genewie, aby uzupełnić braki dla gatunków niezbędnych do badań terenowych. W sumie uzyskano sekwencje genu 12S dla 1557 okazów, reprezentujących 369 gatunków z 51 rodzin i wszystkich 16 rzędów ryb słodkowodnych znanych z Gujany Francuskiej — co stanowi pokrycie prawie 89% fauny ryb słodkowodnych regionu.
Sprawdzanie nazw i tożsamości w DNA
Przekształcenie tego bogactwa sekwencji w wiarygodną bibliotekę wymagało starannej kontroli jakości. Eksperci od ryb najpierw identyfikowali każdy okaz, korzystając z przewodników terenowych i, w razie potrzeby, konsultując się z taksonomistami-specjalistami. Badacze następnie sprawdzili, czy każdy gatunek odpowiada znanemu zasięgowi geograficznemu w rzekach Gujany Francuskiej, aby uniknąć pomyłek między podobnie wyglądającymi gatunkami. W końcu zbudowano filogenetyczne drzewo oparte na DNA, aby zobaczyć, czy okazy przypisane do tego samego gatunku grupują się razem, jak oczekiwano. Wszystkie sekwencje, które znalazły się poza przewidywaną grupą — co sugerowało błędne oznaczenie, zanieczyszczenie lub nierozstrzygnięte granice gatunkowe — zostały odrzucone. Zespół następnie skrócił pełne sekwencje 12S do konkretnych krótkich regionów celowanych przez dwa powszechnie stosowane zestawy starterów eDNA, często nazywane Teleo1 i 12S‑V5. Przetestowali, jak dobrze te krótsze „kody kreskowe” rozróżniają gatunki, stwierdzając, że Teleo1 potrafi przypisać około 95% sekwencji do poziomu gatunku, podczas gdy 12S‑V5 rozróżniało w przybliżeniu 83% na tym poziomie, a pozostałe sekwencje można było wiarygodnie przypisać do rodzaju lub rodziny.

Od lokalnych rzek do obrazu kontynentalnego
Chociaż biblioteka została zbudowana z myślą o Gujanie Francuskiej, wiele jej gatunków i linii jest współdzielonych z rzekami tropikalnej Ameryki Południowej. Porównując swoje wpisy z kontynentalną bazą danych występowania ryb słodkowodnych, autorzy pokazują, że ich sekwencje 12S obejmują około 6% wszystkich opisanych neotropikalnych gatunków ryb słodkowodnych, ale znacznie większą część wyższych jednostek taksonomicznych: około 23% rodzajów, 56% rodzin i 43% rzędów. Oznacza to, że nawet gdy dokładne dopasowanie do gatunku nie jest dostępne poza Gujaną Francuską, badania eDNA wciąż pozwalają wiarygodnie identyfikować obecność szerszych linii filogenetycznych, umożliwiając naukowcom badanie wzorców różnorodności funkcjonalnej — w jaki sposób różne typy ryb przyczyniają się do ról w ekosystemie — na rozległym obszarze.
Dlaczego ta biblioteka zmienia zasady gry
Dla czytelnika ogólnego najważniejsze jest to, że autorzy stworzyli brakującą książkę referencyjną, która pozwala naukowcom przetłumaczyć anonimowe ślady DNA w wodach Amazonii na konkretne gatunki ryb. Ich niemal kompletna biblioteka 12S dla Gujany Francuskiej umożliwia szybkie inwentaryzowanie społeczności rybnych na podstawie próbek wody, w tym gatunków rzadkich, skrytych czy zagrożonych, oraz monitorowanie, jak działania takie jak wylesianie i wydobycie złota przekształcają życie rzeczne. Poza granicami jednego terytorium biblioteka wzmacnia badania eDNA w całych Neotropikach, osadzając wiele grup ryb w starannie zweryfikowanym frameworku genetycznym. W regionie, gdzie tradycyjne badania są kosztowne i logistycznie trudne, to źródło przekształca same rzeki w czytelne archiwa bioróżnorodności, zwiększając szanse wykrywania zmian na czas, by chronić te ukryte światy słodkowodne.
Cytowanie: Brosse, S., Cuenot, Y., Condachou, C. et al. Near complete 12S DNA reference library for the freshwater fish of French Guiana, northern Amazonian region. Sci Data 13, 408 (2026). https://doi.org/10.1038/s41597-026-06811-5
Słowa kluczowe: środowiskowe DNA, ryby słodkowodne, Gujana Francuska, monitoring bioróżnorodności, genetyczna biblioteka referencyjna