Clear Sky Science · pl
Zbiór archeonów jelitowych ludzi z populacji estońskiej
Ukryty świat wewnątrz naszych jelit
Jelito człowieka zamieszkują biliony mikrobów, które pomagają trawić pokarm, kształtować nasz układ odpornościowy i wpływać na zdrowie w zaskakujący sposób. Większość badań koncentrowała się na bakteriach, ale inna grupa mikroskopijnego życia — archeony — pozostawała w dużej mierze w cieniu. Niniejsze badanie rzuca światło na tych pomijanych mieszkańców, tworząc szczegółowy katalog genomów archeonów od osób mieszkających w Estonii, dając naukowcom nową mapę tego ukrytego świata i narzędzia do badania, jak wpływa on na nasze ciało.
Dlaczego te mało znane mikroby mają znaczenie
Archeony to prastare formy życia, które pod mikroskopem trochę przypominają bakterie, ale różnią się zasadniczo. W jelicie ludzkim wiele archeonów wyspecjalizowało się w przekształcaniu wodoru i dwutlenku węgla w metan. Ich obecność została już powiązana z opóźnionym pasażem jelitowym, niektórymi formami zespołu jelita nadwrażliwego, otyłością, a nawet rakiem jelita grubego. Jednak dotychczas naukowcy dysponowali stosunkowo niewielką liczbą genomów referencyjnych do ich badania, a większość wiedzy pochodzi od niewielu dobrze poznanych gatunków. Ta luka utrudnia wykrycie wszystkich gatunków archeonów w jelicie danej osoby lub zrozumienie, jak mogą one przyczyniać się do zdrowia czy choroby.
Budowa biblioteki genomów dla całej populacji
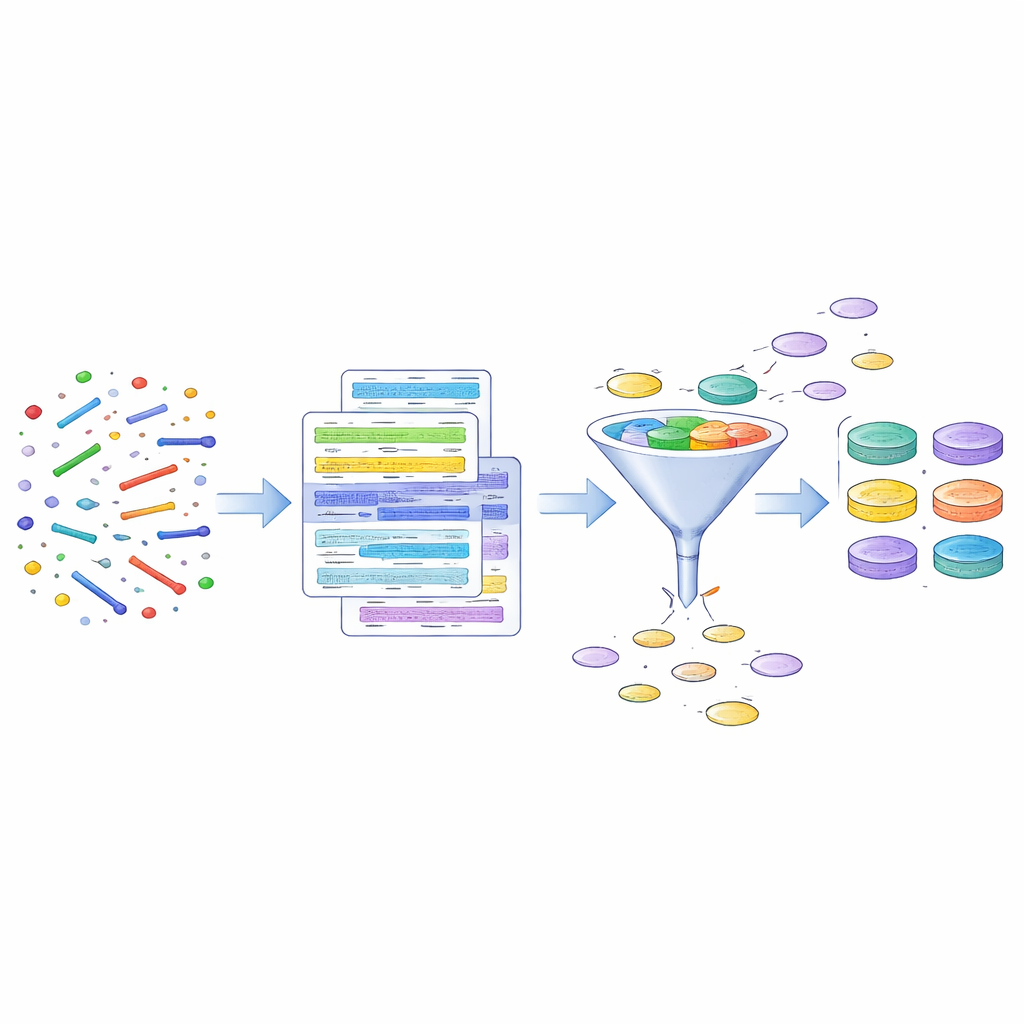
Badacze zaczęli od danych o mikrobiomie jelitowym pochodzących od 1 878 ochotników z kohorty estońskiego mikrobiomu, dużego badania zdrowotnego obejmującego osoby w różnym wieku i obu płci. Zamiast hodować mikroby w laboratorium, wykorzystali fragmenty DNA z próbek kału i komputerowo złożyli je w prawie kompletne genomy — metodę znaną jako metagenomika. Z ponad 84 000 zrekonstruowanych genomów wszystkich typów mikrobów skupili się na 316 początkowo zidentyfikowanych jako archeony. Po starannych kontrolach jakości zestaw ten zawęził się do 273 genomów archeonów, tworząc skuratorowaną kolekcję nazwaną „EstMB MAGdb Archaea-273”.
Oczyszczanie danych, aby uniknąć fałszywych odkryć
Rekonstrukcja genomów z surowych fragmentów DNA przypomina składanie na raz dziesiątek pociętych książek, a błędy mogą tworzyć chimery — fałszywe genomy zszyte z fragmentów, które do siebie nie należą. Aby tego uniknąć, zespół poszedł dalej niż standardowe miary jakości. Sprawdzili, jak kompletne są poszczególne genomy i ile zawierają zanieczyszczeń, ocenili ogólny rozmiar genomu oraz badali, czy mniejsze fragmenty w obrębie każdego genomu wskazują na spójne pochodzenie biologiczne. Usunięto podejrzane genomy, takie jak te o nieprawidłowo dużych rozmiarach lub niespójnych sygnałach taksonomicznych. Jeden uderzający przypadek dotyczył trzech genomów, które wydawały się należeć do bardzo nietypowej grupy archeonów rzadko spotykanej u ludzi; dalsze analizy wykazały, że prawdopodobnie były to artefakty techniczne, co podkreśla, jak łatwo błędy mogą przeniknąć do katalogów genomów.
Od setek genomów do kluczowych przedstawicieli
Aby ułatwić korzystanie z zasobu, autorzy pogrupowali 273 genomy w klastry na poziomie gatunku na podstawie podobieństwa ich sekwencji DNA. Proces ten wygenerował 21 odrębnych gatunków archeonów, a zespół wybrał po jednym dobrze złożonym, wysokiej jakości genomie, aby reprezentował każdy gatunek. Te 21 reprezentantów, zbiorczo nazwane „Archaea ESTrep-21”, mogą służyć jako panel referencyjny dla przyszłych badań. Wykorzystując te genomy jako wzorzec, badacze oszacowali następnie, jak powszechny jest każdy gatunek i jaką ma zwykle obfitość w populacji estońskiej. Kolekcja zawiera także wiele genomów dla niektórych gatunków, co otwiera możliwość badania drobnych różnic na poziomie szczepów — różnic, które ostatecznie mogą pomóc wyjaśnić, dlaczego ten sam gatunek bywa niegroźny u jednej osoby, a związany z chorobą u innej.
Co to oznacza dla przyszłych badań zdrowotnych
Dla osób niezaznajomionych z tematem najważniejszym wnioskiem jest to, że praca ta nie twierdzi, iż odkryto nowy drobnoustrój wywołujący choroby. Raczej dostarcza materiał referencyjny wysokiej jakości, na którym oprze się wiele przyszłych badań. Dzięki udostępnieniu oczyszczonej, dobrze udokumentowanej biblioteki genomów archeonów z jelita ludzkiego autorzy ułatwiają naukowcom na całym świecie dokładne wykrywanie tych mikrobów, porównywanie ich obecności między populacjami i łączenie konkretnych archeonów lub szczepów z cechami takimi jak nawyki jelitowe, waga czy ryzyko choroby. W podobny sposób jak dobra mapa pozwala podróżnikom nawigować po nieznanym terenie, estońska kolekcja genomów archeonów daje badaczom narzędzia do eksploracji dotąd słabo zbadanej części naszego wewnętrznego ekosystemu.
Cytowanie: Pantiukh, K., Org, E. Human gut archaea collection from Estonian population. Sci Data 13, 366 (2026). https://doi.org/10.1038/s41597-026-06742-1
Słowa kluczowe: mikrobiom jelitowy, archeony, metagenomika, zdrowie człowieka, katalog genomów