Clear Sky Science · pl
Złożenie genomu na poziomie chromosomów dla wciornastków morwowych Pseudodendrothrips mori (Thysanoptera: Thripidae)
Maleńkie szkodniki o dużym znaczeniu
Wciornastki morwowe są ledwie dłuższe niż ziarenko piasku, a jednak potrafią sprawić, że całe sady wyglądają na posrebrzone i chorowite, gdy nakłuwają liście i wysysają soki roślinne. Rolnicy mają problem z ich zwalczaniem, ponieważ rozmnażają się szybko, dobrze się ukrywają i często rozwijają odporność na pestycydy. To badanie dostarcza pierwszego szczegółowego planu genetycznego wciornastka morwowego, oferując potężne nowe narzędzie do zrozumienia, jak ten drobny szkodnik prosperuje — i jak można nim zarządzać w sposób bardziej zrównoważony.
Dlaczego mapować DNA owada uszkadzającego liście?
Wciornastki morwowe żywią się morwą i innymi roślinami, powodując zniekształcenia liści i spadek plonów. Ich małe rozmiary utrudniają badania: pojedynczy osobnik nie dostarcza wystarczająco dużo DNA ani RNA dla większości współczesnych metod sekwencjonowania, więc badacze muszą pracować ze starannie zgrupowanymi próbkami. Do tej pory brak kompletnego genomu odniesienia blokował głębsze pytania, takie jak to, jak owady te specjalizują się na określonych roślinach, jak tak szybko stają się odporne na środki chemiczne oraz jak ewoluują ich nietypowe systemy rozrodcze. Genom na poziomie chromosomów stanowi podstawę do badania wszystkich tych zagadnień — od biologii podstawowej po praktyczne metody zwalczania szkodników.
Budowa wysokiej jakości genomu z wielu maleńkich ciał
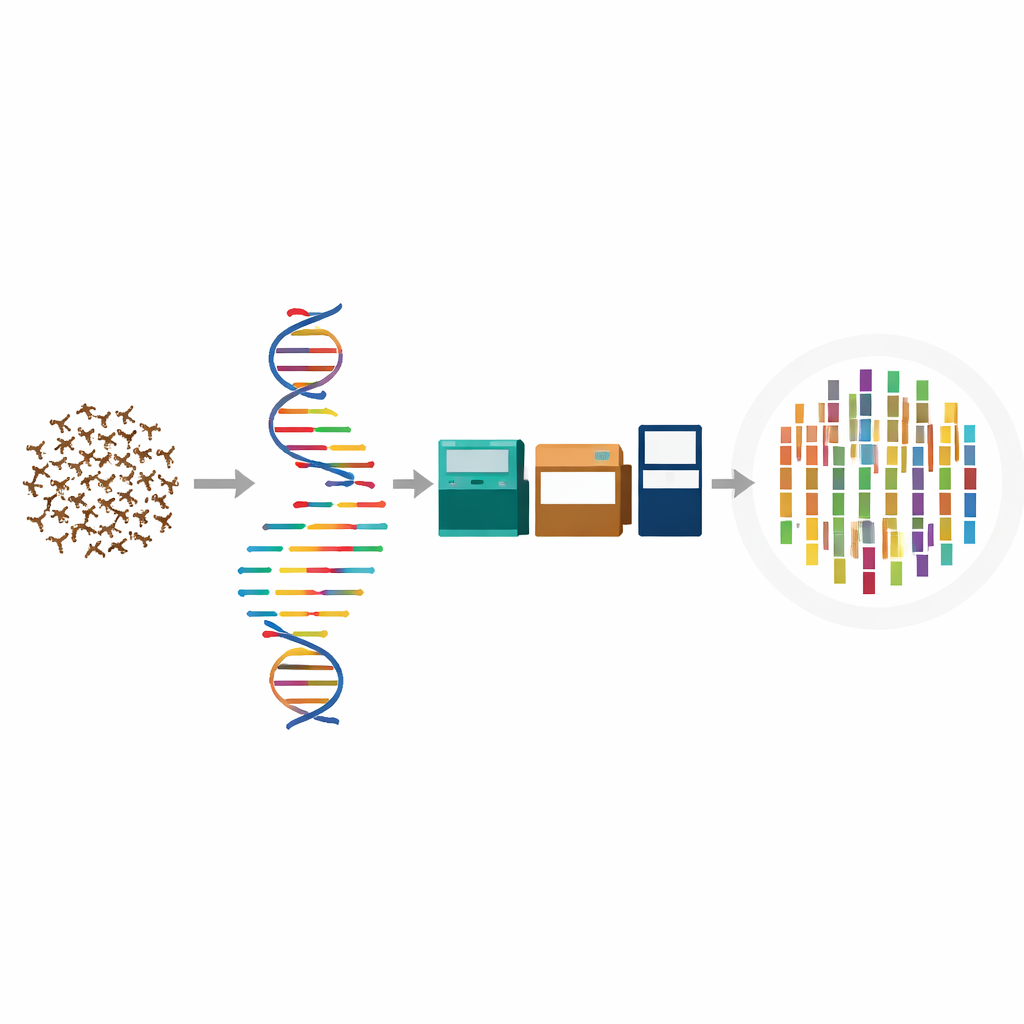
Aby pokonać problem skali, zespół zebrał setki dorosłych wciornastków z ogrodu morwowego w południowych Chinach i zgrupował je do różnych typów sekwencjonowania. Długie odcinki DNA odczytano technologią PacBio HiFi, która świetnie radzi sobie z pokrywaniem trudnych regionów genomu. Krótkie, bardzo dokładne fragmenty DNA z platformy Illumina posłużyły następnie do wygładzenia drobnych błędów. Trzeci typ danych, zwany Hi‑C, uchwycił sposób, w jaki kawałki DNA są składane i połączone wewnątrz jądra komórkowego, co pozwoliło badaczom ułożyć fragmenty w pełnej długości chromosomy. RNA z dodatkowych zgrupowanych wciornastków pomogło precyzyjnie określić miejsca początku i końca genów, tak aby złożony ciąg mógł zostać przekształcony w funkcjonalną mapę genetyczną.
Z porozrzucanych fragmentów do pełnych chromosomów
Wykorzystując te komplementarne strumienie danych, badacze złożyli genom o długości około 281 milionów liter DNA. Prawie całość tej sekwencji — ponad 98% — została zorganizowana w 19 długich struktur odpowiadających chromosomom owada. Miary jakości złożenia pokazują, że te odcinki są niezwykle ciągłe i dokładne jak na genom małego owada. Gdy zespół przeszukał tysiące standardowych genów owadzich oczekiwanych do wystąpienia pojedynczo w niemal każdym gatunku, znalazł około 98% z nich w całości, co jest mocnym sygnałem, że niewiele istotnych informacji zostało pominiętych. W porównaniu z innymi wciornastkami, których genomy zostały zsekwencjonowane, genom wciornastka morwowego ma podobny rozmiar, ale wyróżnia się kompletnością i starannością walidacji.
Ukryte powtórzenia i bogaty katalog genów
Następnie zespół przeszedł od surowej sekwencji do znaczenia biologicznego. Przeszukali genom pod kątem powtarzalnych fragmentów DNA, które mogą wpływać na ewolucję genów i przebudowy genomu w czasie. Około jedna piąta genomu wciornastka morwowego składa się z takich powtórzeń, z których wiele nie dało się dopasować do znanych rodzin, co sugeruje obecność linii charakterystycznych dla tej grupy owadów. Po zamaskowaniu tych regionów badacze połączyli dowody z białek znanych, danych RNA i predykcji komputerowych, aby zidentyfikować ponad 13 000 genów kodujących białka. Prawie wszystkie z tych genów można było przypisać prawdopodobnej funkcji porównując je z istniejącymi bazami danych, tworząc szeroki katalog molekularnych narzędzi, które ten szkodnik wykorzystuje do żerowania, detoksykacji chemikaliów roślinnych, reakcji na pestycydy i rozwoju.
Nowy zestaw narzędzi dla mądrzejszego zarządzania szkodnikami
Przekształcając trudnego do badania owada w jeden z najlepiej scharakteryzowanych genomów wciornastków do tej pory, ta praca kładzie podwaliny pod przyszłe przełomy. Dysponując wiarygodnym genomem odniesienia, naukowcy mogą teraz śledzić rozprzestrzenianie się populacji wciornastków morwowych, odkrywać sygnatury genetyczne odporności na pestycydy oraz poszukiwać słabych punktów w kluczowych szlakach biologicznych. Z czasem taka wiedza może wspierać bardziej ukierunkowane, przyjazne dla środowiska metody kontroli — od usprawnień w narzędziach monitorujących po strategie biologicznej kontroli — zmniejszając straty plonów przy ograniczonym stosowaniu chemikaliów o szerokim spektrum działania.
Cytowanie: Guan, DL., Li, YM., Zhang, SH. et al. A chromosome-level genome assembly for the mulberry thrips Pseudodendrothrips mori (Thysanoptera: Thripidae). Sci Data 13, 330 (2026). https://doi.org/10.1038/s41597-026-06697-3
Słowa kluczowe: wciornastki morwowe, złożenie genomu, szkodniki rolnicze, genomika owadów, odporność na pestycydy