Clear Sky Science · pl
Skład genomu Homatula variegata na poziomie chromosomów z dorzecza Jangcy
Mała rybka potrafiąca opowiedzieć wielką historię genetyczną
W wartkich, kamienistych potokach zasilających górny bieg Jangcy żyje niewielki, prążkowany babka zwana Homatula variegata. Ceniona jest zarówno na stół, jak i do akwariów domowych, jednak do tej pory niemal nic nie wiedziano o jej DNA. Niniejsze badanie dostarcza pierwszą niemal kompletną mapę genomu rozpisaną chromosom po chromosomie, otwierając drzwi do mądrzejszej ochrony, wydajniejszego hodowli i głębszego zrozumienia, jak życie przystosowuje się do zimnych, rwących górskich wód.
Po co mapować DNA skromnie wyglądającej ryby?
Choć ten babka osiąga zaledwie około 14 centymetrów, odgrywa nieproporcjonalnie dużą rolę w lokalnych ekosystemach rzecznych i regionalnej akwakulturze. Dobrze prosperuje w potokach średnich wysokości o żwirowym dnie i stałym nurcie, żywiąc się owadami, odpadkami organicznymi i małymi rybami. Ponieważ jest zarówno smaczna, jak i barwna, rośnie zainteresowanie jej hodowlą jako rodzimego gatunku ozdobnego i spożywczego. Jednak hodowanie i ochrona gatunku są znacznie trudniejsze bez precyzyjnego odniesienia genetycznego. Kompletny genom działa jak szczegółowa lista części i schemat połączeń, ujawniając geny kształtujące wzrost, kolor, odporność na choroby i zdolność radzenia sobie z szybkim, chłodnym nurtem. Do tej pory żaden z przedstawicieli tej gałęzi karpiowatych nie miał tak wysokiej jakości referencji, pozostawiając poważną lukę w genetyce ryb słodkowodnych.
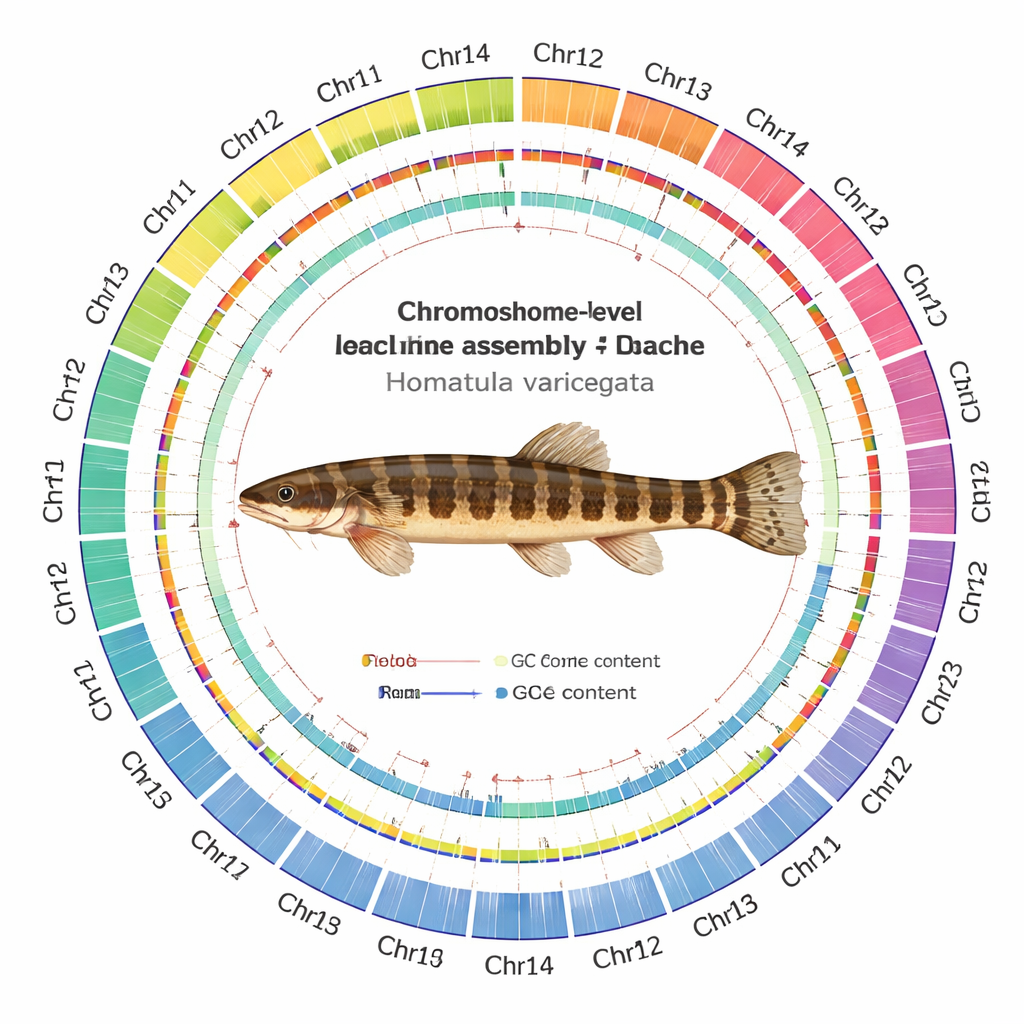
Budowa mapy DNA chromosom po chromosomie
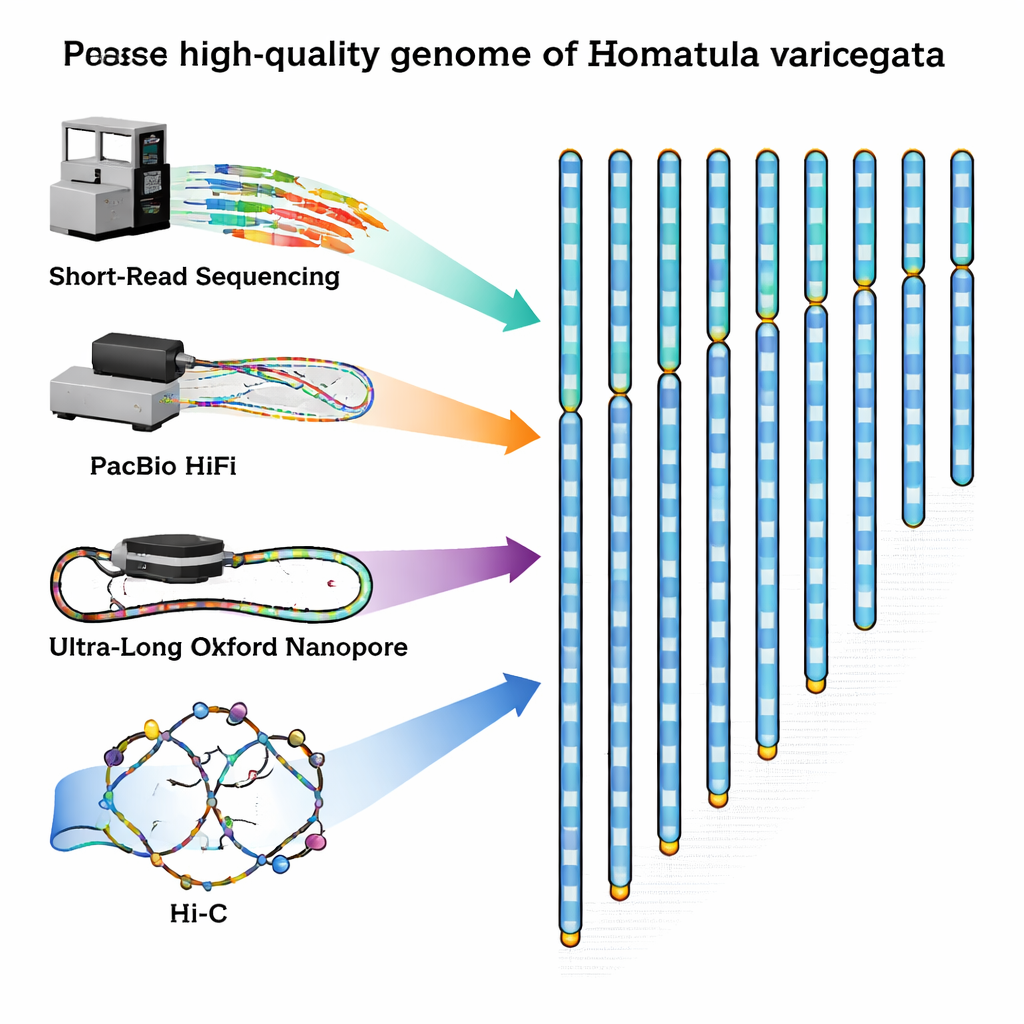
Aby wypełnić tę lukę, badacze schwytali zdrowego dorosłego samca z rzeki Qingyi, dopływu Jangcy, i ostrożnie wyizolowali DNA i RNA z jego krwi. Następnie połączyli kilka nowoczesnych metod sekwencjonowania, każdą o innych zaletach. Maszyny krótkiego odczytu firmy Illumina wygenerowały ogromną liczbę bardzo dokładnych fragmentów DNA. Technologia PacBio HiFi dostarczyła nieco dłuższe fragmenty o doskonałej dokładności, natomiast urządzenia Oxford Nanopore wygenerowały ultra-długie nici, które mogą rozciągać się przez trudne do rozszyfrowania, powtarzalne regiony. Na koniec metoda zwana Hi‑C uchwyciła sposób, w jaki nici DNA składują się i wchodzą ze sobą w interakcje w jądrze komórkowym, dostarczając trójwymiarowej mapy kontaktów, która pomaga łączyć fragmenty w pełne chromosomy we właściwej kolejności.
Co ujawnia nowy genom
Poprzez splecenie tych danych z nowoczesnym oprogramowaniem do składania i starannymi kontrolami jakości zespół opracował genom o długości 641 milionów liter DNA, uporządkowany w 24 chromosomy. Co godne uwagi, każdy chromosom został zmontowany jako pojedynczy, ciągły kawałek; w 22 z nich nie ma w ogóle luk, a w dwóch pozostałych występują tylko niewielkie przerwy. Udało się zidentyfikować 24 prawdopodobne centromery — centralne „pasy” każdego chromosomu — oraz wykryć większość ochronnych nagłówków telomerowych na końcach chromosomów. Naukowcy skatalogowali 24 479 genów kodujących białka i byli w stanie przypisać prawdopodobne funkcje około 93% z nich, porównując je z dużymi międzynarodowymi bazami danych. Zmapowali również krajobraz DNA powtarzalnego, stwierdzając, że ponad jedna czwarta genomu składa się z ruchomych elementów genetycznych, w szczególności transpozonów DNA, które mogą przeskakiwać po genomie i czasem napędzać ewolucję.
Testowanie jakości „pod maską”
Wysokopoziomowe liczby mają znaczenie tylko wtedy, gdy sama mapa jest wiarygodna. Zespół zatem poddał składanie serii testów. Odczyty ze wszystkich platform sekwencjonowania wyrównywały się do nowego genomu na bardzo wysokich poziomach, z równomiernym pokryciem większości chromosomów. Niezależne narzędzia liczące krótkie wzorce DNA sugerowały, że prawie cała oczekiwana zawartość sekwencji jest obecna, a standardowe testy kompletności genów wykazały, że zdecydowana większość uniwersalnych genów rybnych jest nienaruszona. Mapy kontaktów Hi‑C tworzyły czyste, kwadratowe wzory wzdłuż każdego chromosomu, z niewielkim rozproszonym sygnałem między nimi, co wskazuje, że segmenty są prawidłowo połączone, a nie pomieszane.
Od mapy DNA do realnego wpływu
Dla osoby niebędącej specjalistą ta praca może brzmieć jak triumf techniczny sam w sobie, ale jej implikacje są praktyczne i dalekosiężne. Posiadanie prawie kompletnego genomu Homatula variegata daje naukowcom punkt odniesienia, względem którego mogą porównywać populacje dzikie, śledzić różnorodność genetyczną i wykrywać oznaki inbredingu lub adaptacji lokalnej. Hodowcy mogą poszukiwać markerów DNA powiązanych z pożądanymi cechami, takimi jak szybki wzrost, odporność czy efektowna kolorystyka, przyspieszając selektywną hodowlę przy zachowaniu naturalnego charakteru gatunku. Ekolodzy mogą badać, jak ten babka wyewoluował, by żyć w chłodnych, szybko płynących potokach górskich — wnioski, które mogą również informować zarządzanie pokrewnymi gatunkami. Krótko mówiąc, genom na poziomie chromosomów przemienia skromną rybę rzeczną w potężny model do zrozumienia — i ochrony — bogactwa życia azjatyckich ekosystemów słodkowodnych.
Cytowanie: Tang, Y., Wu, Q., Wang, Y. et al. A chromosome level genome assembly of Homatula variegata from the Yangtze River basin. Sci Data 13, 303 (2026). https://doi.org/10.1038/s41597-026-06667-9
Słowa kluczowe: genom ryby, składanie chromosomowe, bioróżnorodność słodkowodna, genetyka akwakultury, pstrąg Jangcy (loach)