Clear Sky Science · pl
Kuratowany zasób genomów chemolitotroautotroficznych i genów markerowych do przewidywania szlaków fiksyzacji CO₂
Mikroby, które pomagają wyrównywać bilans węgla Ziemi
Ukryte w glebach, oceanach i środowiskach ekstremalnych, pewne mikroby potrafią budować własną biomasę, wykorzystując dwutlenek węgla (CO₂) jako główne źródło węgla. Te mikroskopijne „chemicy” odgrywają kluczową rolę w utrzymaniu równowagi cyklu węglowego Ziemi i mogą inspirować nowe metody wychwytywania przemysłowego CO₂. Do tej pory naukowcom brakowało jednak prostego, niezawodnego sposobu, by na podstawie DNA mikroba określić, jaką strategię fiksyzacji CO₂ stosuje. W tym badaniu przedstawiono kuratowany katalog genów oraz nowe narzędzie komputerowe, AutoFixMark, stworzone, by wypełnić tę lukę.
Wiele dróg przekształcania powietrza w biomasę
Nie wszystkie organizmy wiążą CO₂ w ten sam sposób. Mikroby rozwinęły co najmniej siedem naturalnych szlaków przekształcania CO₂ w materię organiczną. Niektóre, jak cykl Calvina–Bensona–Basshama powszechny u roślin i wielu bakterii, są dobrze znane; inne, na przykład redukcyjna ścieżka glicynowa odkryta dopiero w 2020 roku, są wciąż słabo zbadane. Te szlaki występują w różnych gałęziach drzewa życia i często wykorzystują podobne enzymy, co utrudnia rozróżnienie ich wyłącznie na podstawie sekwencji genomowej. Istniejące oprogramowanie potrafi przewidzieć szerokie możliwości metaboliczne, ale nie zostało zoptymalizowane ani gruntownie przetestowane pod kątem precyzyjnego wskazywania konkretnych dróg fiksyzacji CO₂.
Tworzenie czystej mapy referencyjnej mikroorganizmów wiążących CO₂
Badacze rozpoczęli od zebrania dwóch starannie sprawdzonych kolekcji genomów. Najpierw wybrali 15 dobrze poznanych mikroorganizmów, których szlaki fiksyzacji CO₂ zostały szczegółowo opisane. Organizmy referencyjne, obejmujące kilka grup bakterii i archeonów, posłużyły jako wzorce do zdefiniowania kluczowych enzymów rzeczywiście wyróżniających każdy szlak. Następnie stworzyli zestaw testowy składający się z 347 genomów chemolitotroautotroficznych — mikroorganizmów, które pozyskują energię z substancji nieorganicznych i budują biomasę z CO₂. Każdy genom w tym większym zbiorze został ręcznie powiązany z konkretnymi szlakami fiksyzacji CO₂ na podstawie literatury, co dostarczyło solidnego zestawu prawdy do testowania przewidywań.
Geny markerowe i proste reguły zamiast czarnych skrzynek
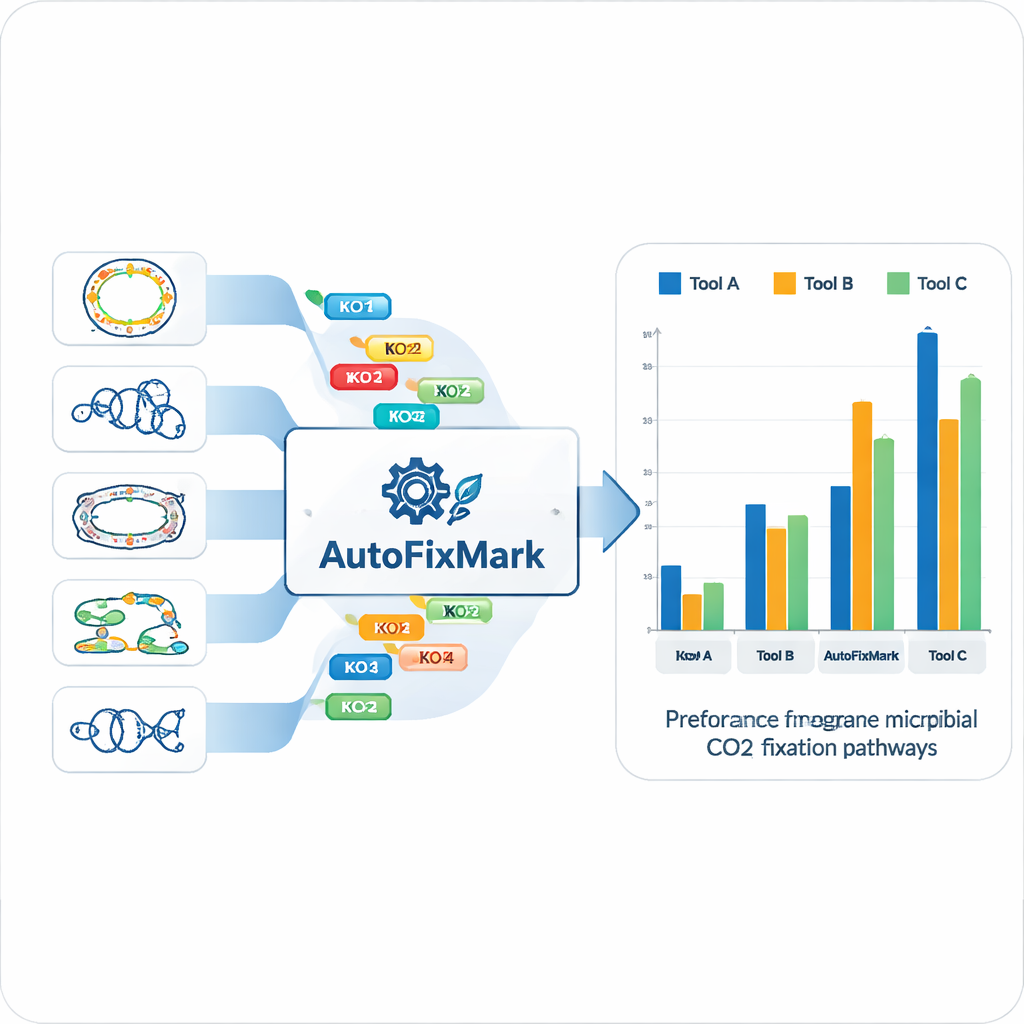
Wykorzystując 15 genomów referencyjnych, zespół zidentyfikował „geny markerowe” dla każdego z siedmiu szlaków fiksyzacji CO₂ i przypisał je do znormalizowanych identyfikatorów KEGG Orthology (KO). Zamiast polegać na nieprzejrzystym uczeniu maszynowym, zakodowali przejrzyste reguły opisujące, jak te markery się łączą. Niektóre reakcje mogą być realizowane przez dowolny z kilku alternatywnych enzymów, co obsługuje reguła „one_of”. Inne wymagają kompleksów wieloskładnikowych i muszą zawierać „all_of” określony zestaw KO. Dla redukcyjnej ścieżki glicynowej, gdzie nie wszystkie komponenty są w pełni poznane, narzędzie stosuje reguły „at_least”, które wymagają obecności minimalnej liczby podjednostek. Te reguły logiczne są zapisane w formacie JSON czytelnym dla maszyn i stanowią rdzeń bazy wiedzy AutoFixMark.
Lekki program, który przewyższa uznane oprogramowanie
AutoFixMark to niewielki, oparty na regułach program napisany w Pythonie. Przyjmuje na wejściu listę identyfikatorów KO dla genów w genomie mikroba, zwykle wygenerowaną przez oddzielne narzędzie KofamScan, a następnie sprawdza, które reguły markerów są spełnione dla każdego z siedmiu szlaków. Autorzy porównali AutoFixMark z dwoma powszechnie używanymi narzędziami do anotacji metabolicznej, METABOLIC i gapseq, używając swojego zestawu testowego 347 genomów. Wszystkie trzy narzędzia dobrze radziły sobie z klasycznymi szlakami, takimi jak cykl Calvina, redukcyjny cykl kwasu trójkarboksylowego oraz ścieżka Wood–Ljungdahla. Jednak AutoFixMark wyraźnie przewyższał pozostałe w przypadku nowszych lub rzadszych szlaków, takich jak cykl 3-hydroksypropionowy/4-hydroksymaślanowy, cykl dikarboksylanowy/4-hydroksymaślanowy oraz redukcyjna ścieżka glicynowa — niektóre z nich w ogóle nie są objęte konkurencyjnym oprogramowaniem.
Znaczenie wyników dla badań klimatu i ekologii
Kuratowane zbiory genów, program AutoFixMark oraz pełna kolekcja genomów testowych są publicznie dostępne. Oznacza to, że badacze mogą teraz przesiewać zarówno izolowane mikroby, jak i złożone genomowe rekonstrukcje z metagenomów, aby sprawdzić, jakie strategie fiksyzacji CO₂ mają genetyczne predyspozycje wykorzystywać. Autorzy podkreślają, że AutoFixMark przewiduje potencjał genetyczny, a nie to, czy dany szlak jest aktywny w warunkach rzeczywistych. Wiele z tych szlaków biochemicznych może działać odwrotnie, w zależności od bilansu energetycznego komórki. Mimo to posiadanie solidnej, przejrzystej metody identyfikacji mikroorganizmów wiążących CO₂ pomoże naukowcom mapować, gdzie i jak życie usuwa węgiel z atmosfery, ukierunkować eksperymenty nad nowymi szlakami oraz wspierać projektowanie przyszłych biotechnologii opartych na CO₂.
Cytowanie: Kawashima, S., Okabeppu, Y., Miyazawa, S. et al. A curated resource of chemolithoautotrophic genomes and marker genes for CO₂ fixation pathway prediction. Sci Data 13, 121 (2026). https://doi.org/10.1038/s41597-026-06655-z
Słowa kluczowe: mikrobowa fiksyzacja węgla, metabolizm autotroficzny, annotacja genomu, chwytanie CO2, metagenomika