Clear Sky Science · pl
Adnotowany zbiór danych wybarwień Grama z dodatnich posiewów krwi
Dlaczego szybkie odpowiedzi w przypadku zakażeń są ważne
Kiedy bakterie lub grzyby trafiają do krwiobiegu, każda godzina bez odpowiedniego leczenia może decydować o życiu i śmierci. Lekarze polegają na szybkim badaniu laboratoryjnym zwanym barwieniem Grama, by rozpoznać typ drobnoustroju i dobrać wczesne antybiotyki. Jednak odczytywanie tych preparatów mikroskopowych to zadanie wymagające doświadczenia, wykonywane ręcznie, zajmujące czas i podatne na różnice między technikami. Niniejsze badanie opisuje nowy, starannie adnotowany zbiór obrazów prawdziwych szkiełek z posiewów krwi ze szpitala, stworzony po to, by pomóc komputerom uczyć się automatycznego odczytu barwień Grama i wspierać szybszą, bardziej niezawodną opiekę.
Przekształcanie prawdziwych szkiełek szpitalnych w dane
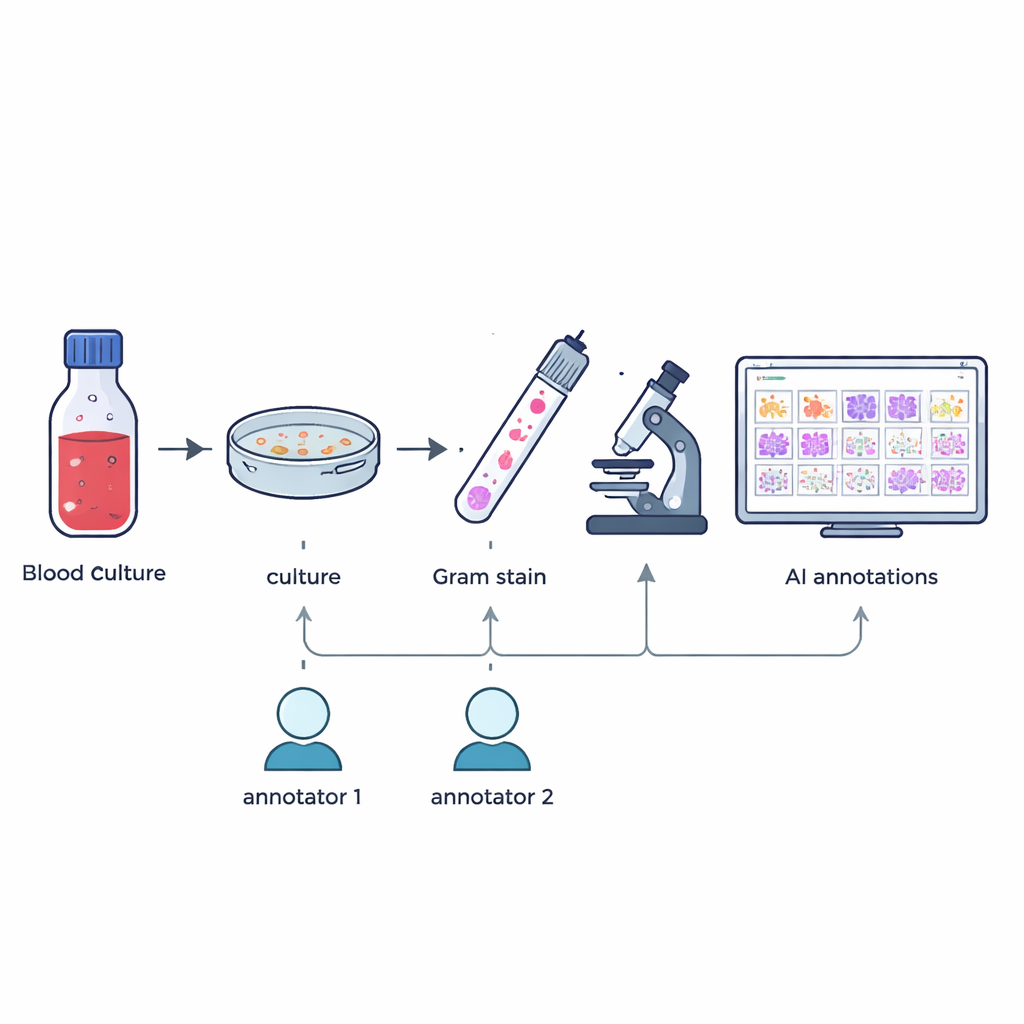
Naukowcy zgromadzili 57 różnych gatunków bakterii i grzybów wyhodowanych z dodatnich butelek posiewów krwi pobranych w ramach codziennej pracy szpitala. Od stycznia do maja 2024, gdy posiew sygnalizował dodatni wynik, personel przygotowywał rozmazy barwione Grama na szkiełkach i potwierdzał dokładny gatunek za pomocą wysokoprecyzyjnej identyfikacji metodą MALDI-TOF. Nie zmieniając rutynowych procedur ani nie pobierając dodatkowych próbek, zespół wykonywał następnie cyfrowe obrazy o wysokiej rozdzielczości typowych pól widzenia pod mikroskopem olejowym 100×, co dało 505 dużych kolorowych obrazów odzwierciedlających to, co technicy widzą w praktyce.
Staranna etykietacja drobnych kształtów
Aby zbudować użyteczny zestaw szkoleniowy dla sztucznej inteligencji, trzeba dokładnie wiedzieć, gdzie w każdym obrazie znajduje się każdy drobnoustrój. Dwóch doświadczonych techników mikrobiologii niezależnie rysowało ramki wokół pojedynczych komórek mikroorganizmów lub ich skupisk na każdym obrazie, kierując się wyłącznie tym, co widzieli pod mikroskopem. Niestandardowe oprogramowanie porównało obie serie oznaczeń: ramki wystarczająco zachodzące na siebie zostały scalone, a niezgodności lub sporne przypadki oznaczono do przeglądu. Starszy ekspert z ponad 20-letnim doświadczeniem ręcznie przeanalizował te przypadki. Ten wieloetapowy proces dał 7 528 sprawdzonych adnotacji wyróżniających dwoinki/ziarenkowce (komórki okrągłe), pałeczki (komórki cylindryczne) oraz grzyby, przy jednoczesnym wykluczeniu obiektów częściowych lub wątpliwych.
Co zawiera zbiór danych
Gotowy zasób łączy kilka warstw informacji. Wszystkie 505 obrazów udostępniono jako pliki JPEG o wysokiej rozdzielczości, a finalne, zweryfikowane przez ekspertów ramki zapisano w standardowym formacie COCO JSON powszechnie używanym w badaniach nad widzeniem komputerowym. Dodatkowe pliki łączą każdy obraz z gatunkiem drobnoustroju, informacją o tym, czy jest Gram-dodatni czy Gram-ujemny, jego ogólną grupą morfologiczną, rodzajem fiolki posiewowej, z której pochodzi, oraz czasem, po jakim posiew stał się dodatni. Ponieważ każdy obraz zawiera tylko jeden gatunek, wszystkie ramki w danym obrazie mają te same cechy biologiczne. Użytkownicy mogą wybrać między jednym dużym plikiem adnotacji a oddzielnymi plikami dla każdego obrazu, a dołączony prosty skrypt w Pythonie pozwala wizualizować dowolny obraz z nałożonymi ramkami.
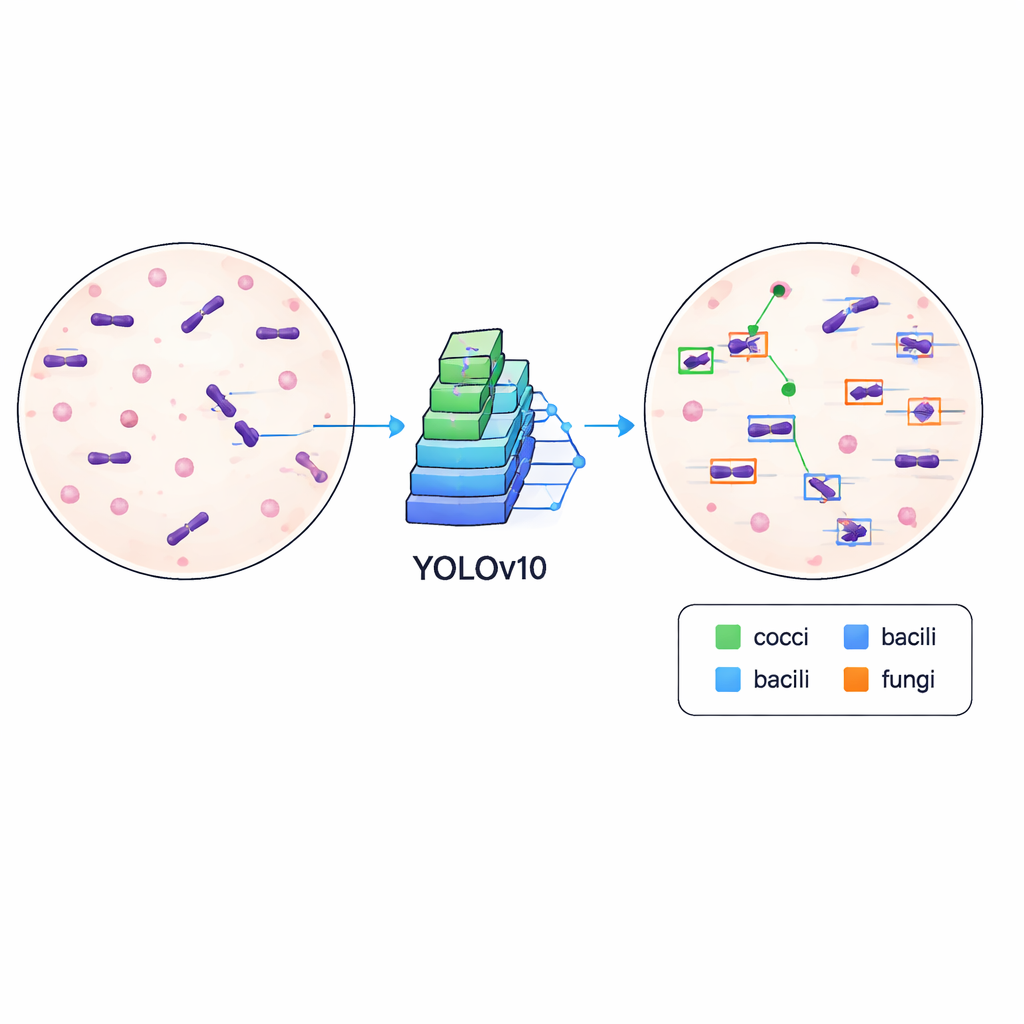
Nauczanie komputerów wykrywania drobnoustrojów
Aby pokazać, że zbiór danych jest nie tylko uporządkowany, ale i praktyczny, autorzy przeszkolili nowoczesny algorytm wykrywania obiektów znany jako YOLOv10 do lokalizowania i klasyfikowania drobnoustrojów na obrazach. Dane podzielono na zestawy treningowe i walidacyjne, a model trenowano przez 500 epok na wydajnej karcie graficznej, śledząc, jak dobrze uczy się rysować dokładne ramki i rozróżniać typy komórek. Wytrenowany system osiągnął średnią precyzję (mAP) około 84,6% przy standardowym progu dopasowania, co wskazuje, że potrafi niezawodnie lokalizować i opisywać drobnoustroje pomimo zmienności wyglądu preparatów, w tym różnic w intensywności barwienia, zanieczyszczeniach tła i ostrości.
Jak można wykorzystać ten zasób
Ponieważ dane są zgodne z powszechnymi formatami, można je włączyć do wielu istniejących pipeline’ów widzenia komputerowego. Badacze mogą najpierw szkolić system, który odróżnia prawdziwe drobnoustroje od zanieczyszczeń, pomagając laboratoriom odfiltrowywać fałszywie dodatnie sygnały posiewów. Mogą też grupować drobnoustroje według ogólnych kształtów, co odpowiada potrzebom klinicystów w ramach wczesnego, tzw. „poziomu 1” raportu kierującego wstępnym doborem antybiotyków. Bardziej ambitnym celem jest rozróżnianie poszczególnych gatunków na podstawie subtelnych wskazówek wizualnych. Autorzy wskazują ograniczenia: niektóre komórki są skupione, część szkiełek pochodzi z pojedynczego źródła dla danego gatunku, a ostrość może się różnić — tak jak w rzeczywistości. Mimo to każda uwzględniona ramka została starannie sprawdzona, co czyni zbiór danych wiarygodnym punktem wyjścia.
Co to oznacza dla pacjentów
Mówiąc prosto, ta praca przekształca rutynowe preparaty z posiewów krwi w wspólne pole do nauki dla inteligentnego oprogramowania. Udostępniając publicznie zarówno obrazy, jak i adnotacje ekspertów, badanie obniża barierę dla zespołów na całym świecie, by budować i testować narzędzia AI potrafiące szybko i konsekwentnie czytać barwienia Grama. Choć takie systemy nie zastąpią mikrobiologów, mogą pomóc szybciej wykrywać groźne zakażenia, zmniejszać błędy interpretacyjne i wspierać lepsze stosowanie antybiotyków. Dla pacjentów może to oznaczać szybsze i bardziej precyzyjne leczenie wtedy, gdy jest to najważniejsze.
Cytowanie: Yi, Q., Gou, X., Zhu, R. et al. An annotated dataset of Gram stains from positive blood cultures. Sci Data 13, 294 (2026). https://doi.org/10.1038/s41597-026-06651-3
Słowa kluczowe: zakażenia krwi, barwienie Grama, zbiór danych obrazów medycznych, sztuczna inteligencja, diagnostyka mikrobiologiczna