Clear Sky Science · pl
Pierwszy montaż i anotacja genomu na poziomie chromosomów zagrożonego słodkowodnego płaszczka kolcowego (Fontitrygon garouaensis) z Afryki
Rzadki mieszkaniec rzeki zyskuje genomowe światło reflektorów
W mętnych rzekach Afryki Zachodniej żyje niezwykła płaszczka, która dokonała tego, czego prawie żadna z jej krewnych — rekinów i płaszczek — nie zrobiła: osiedliła się na stałe w słodkiej wodzie. Ta gładka słodkowodna płaszczka, Fontitrygon garouaensis, jest również gatunkiem zagrożonym i słabo zbadanym. Artykuł stojący za tą notą przedstawia pierwszy kompletny, na poziomie chromosomów, mapę jej DNA, dając potężne narzędzie do zrozumienia, jak tak starożytna morska linia przystosowała się do życia w rzekach i jak można ją lepiej chronić.
Dlaczego ta płaszczka ma znaczenie
Rekiny i płaszczki należą do jednej z najstarszych gałęzi drzewa filogenetycznego kręgowców, oddzielając się od przodków ryb kostnoszkieletowych setki milionów lat temu. Mimo ich ewolucyjnego znaczenia, ich genomy pozostają słabo zmapowane, zwłaszcza u gatunków żyjących w afrykańskich wodach. Fontitrygon garouaensis jest szczególnie wyjątkowa: to jedyna znana płaszczka w pełni przystosowana do afrykańskich systemów słodkowodnych, wykazująca charakterystyczne cechy morfologiczne, takie jak zredukowany lub brakujący rząd kolców na grzbiecie. Ponieważ przejście z zasolonych mórz do słodkich rzek jest rzadkie i stanowi duże wyzwanie fizjologiczne dla rekinów i płaszczek, ten gatunek oferuje naturalny eksperyment na temat tego, jak zwierzęta przekształcają swoją biologię, by radzić sobie w nowych środowiskach.
Budowanie genetycznej mapy odniesienia
Aby odczytać plan genetyczny płaszczki, badacze pobrali jedną dorosłą samicę z rzeki Niger w Nigerii i uzyskali wysokiej jakości DNA i RNA z kilku tkanek. Następnie zastosowali „hybrydową” strategię łączącą trzy nowoczesne podejścia sekwencjonowania. Sekwencjonowanie krótkimi odczytami Illumina dostarcza ogromnej liczby drobnych fragmentów DNA, sekwencjonowanie długimi odczytami PacBio HiFi generuje znacznie dłuższe i bardziej ciągłe odcinki, a sekwencjonowanie Hi-C rejestruje, jak DNA składa się i wchodzi w interakcje w jądrze komórkowym. Splatając te zbiory danych za pomocą wyspecjalizowanego oprogramowania, zespół złożył genom o długości około 4,19 miliarda liter DNA, zorganizowany w 41 fragmentów na poziomie chromosomów — porównywalny rozmiarem z niektórymi z największych znanych genów rekinów.
Co ujawnia genom
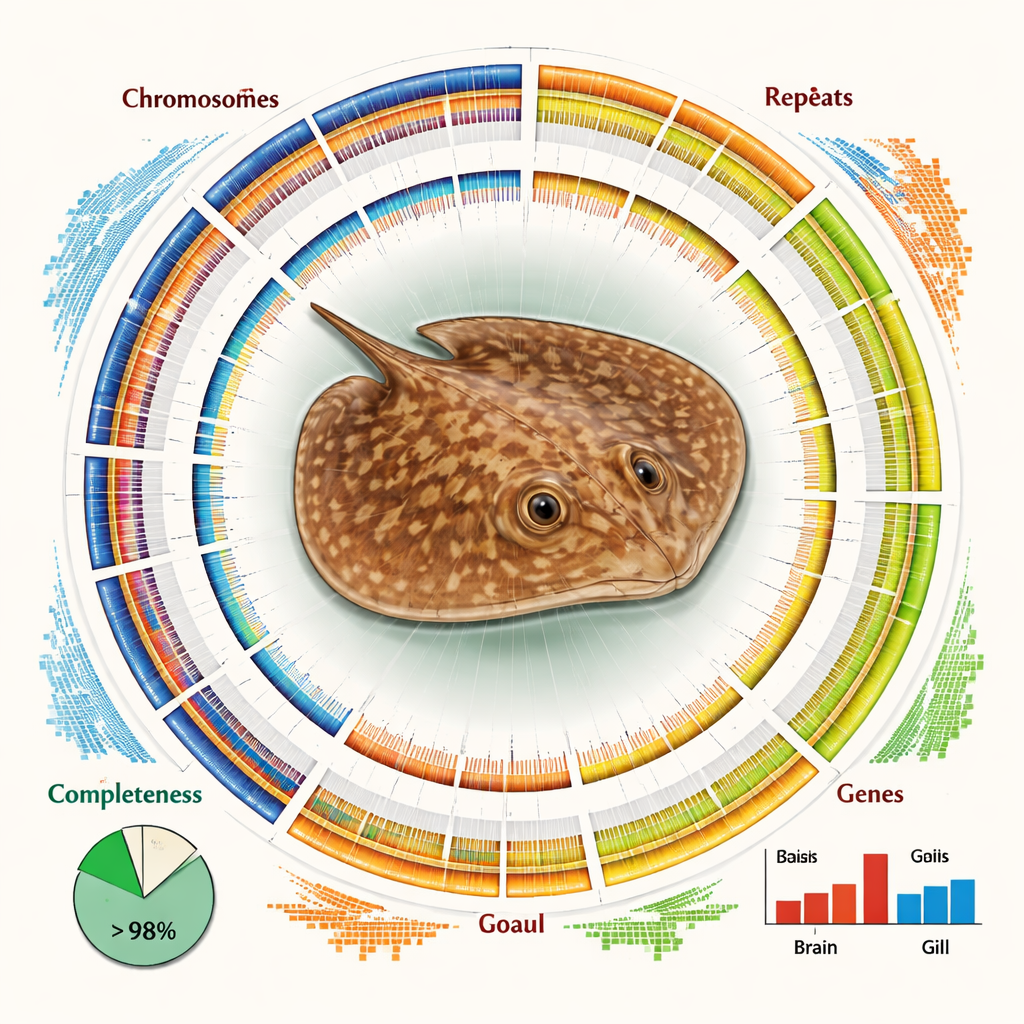
Gotowy montaż jest zarówno duży, jak i niezwykle kompletny. Niezależne kontrole jakości wykazują, że ponad 93 procent oczekiwanych rdzeniowych genów kręgowców jest obecnych i nienaruszonych, a ponad 84 procent całej sekwencji DNA zostało pewnie przypisane do konkretnych chromosomów. Genom jest zdominowany przez DNA powtarzalny — odcinki sekwencji występujące wielokrotnie — stanowiące około dwóch trzecich jego długości. Wiele z tych powtórzeń należy do ruchomych elementów genetycznych, takich jak LINE i LTR, które kopiowały się i wstawiały w całym genomie w przebiegu ewolucji. Pomimo tej złożoności badacze zidentyfikowali niemal 30 000 genów kodujących białka i mogli przypisać prawdopodobne funkcje ponad 98 procentom z nich, korzystając z międzynarodowych baz danych białek i szlaków metabolicznych.
Wskazówki dotyczące życia w słodkiej wodzie i ewolucji
Dysponowanie mapą na poziomie chromosomów pozwoliło zespołowi na więcej niż tylko katalogowanie genów. Porównując chromosomy płaszczki z chromosomami spokrewnionych rekinów i płaszczek, odkryli historię strukturalnych przetasowań — pęknięć, fuzji i przestawień całych segmentów chromosomów — które wyróżniają tę linię. Zmiany te mogły przyczynić się do ukształtowania unikalnych cech gatunku i jego niszy ekologicznej. Autorzy zbadali także aktywność genów w dwóch kluczowych tkankach: skrzelach, które pośredniczą w oddychaniu i równowadze soli z otaczającą wodą, oraz mózgu. Stwierdzili wyraźne różnice w aktywacji genów, przy czym geny skrzeli są wzbogacone w szlaki związane z wykorzystaniem energii i metabolizmem tłuszczów, co sugeruje biochemiczne dostosowania niezbędne do przetrwania w słodkiej wodzie.
Nowa podstawa dla działań ochronnych
U podstaw tej pracy leży przekształcenie mało znanej, zagrożonej płaszczki rzecznej w jeden z najlepiej scharakteryzowanych kostnoszkieletowych ryb chrzęstnych na poziomie DNA. Dla niespecjalistów oznacza to, że naukowcy mają teraz szczegółowy podręcznik odniesienia dla tego gatunku — od chromosomów po pojedyncze geny. To odniesienie może kierować przyszłymi badaniami nad tym, jak gatunek radzi sobie ze zmieniającą się jakością wody, jak zorganizowane są jego populacje wzdłuż rzek oraz jak jest spokrewniony z innymi płaszczkami. Co równie ważne, dostarcza podstaw genomowych do planowania ochrony, oferując nowe sposoby monitorowania różnorodności genetycznej, identyfikacji odrębnych populacji wartych ochrony oraz zrozumienia, jak ta rzadka specjalistka słodkowodna może reagować na trwające presje środowiskowe.
Cytowanie: Nneji, L.M., Oladipo, S.O., Oyebanji, O.O. et al. First Chromosome-level Genome Assembly and Annotation of an Endangered Freshwater Stingray (Fontitrygon garouaensis) from Africa. Sci Data 13, 302 (2026). https://doi.org/10.1038/s41597-026-06646-0
Słowa kluczowe: słodkowodna płaszczka kolcowa, montaż genomu, ewolucja elasmobranchów, genomika ochrony, różnorodność rzek Afryki