Clear Sky Science · pl
Skład genomu na poziomie chromosomów u ważki kamiennej Rhopalopsole triangulispina Mo i Li, 2025 (Plecoptera: Leuctridae)
Dlaczego mały owad z potoku ma znaczenie
W wartko płynących górskich potokach na całym świecie drobne, delikatne owady zwane ważkami kamiennymi cicho sygnalizują, jak zdrowa jest woda. Ich młode stadia, czyli nimfy, są tak wrażliwe na zanieczyszczenia, że ich obecność często oznacza czysty i dobrze natleniony ciek. Mimo tej ekologicznej roli naukowcy dotąd zaskakująco mało wiedzieli o szczegółowym składzie genetycznym wielu ważek kamiennych. Niniejsze badanie dostarcza wysokiej jakości, na poziomie chromosomów mapę DNA jednego z takich gatunków, Rhopalopsole triangulispina, otwierając nowe możliwości zrozumienia ich ewolucji i wykorzystania w ochronie ekosystemów słodkowodnych.
Życie w czystej, szybko płynącej wodzie
Ważki kamienne z nadrodziny Nemouroidea należą do jednych z najbardziej zróżnicowanych i licznych grup tych owadów, zamieszkując zimne, czyste strumienie, jeziora i stawy — często ukryte wśród kamieni lub osadów. Ich nimfy zależą od dobrej jakości wody: temperatura, poziom tlenu, zanieczyszczenia chemiczne, a nawet rodzaj dna koryta mogą decydować o tym, czy gatunek przetrwa, czy zniknie. Z uwagi na tę wrażliwość, naukowcy używają ich jako naturalnych „czujników środowiskowych” przy ocenie stanu rzek i potoków. W obrębie Nemouroidea rodzina Leuctridae i rodzaj Rhopalopsole są szczególnie powszechne w azjatyckich regionach górskich, w tym w Chinach, gdzie opisano ponad 60 gatunków Rhopalopsole. Pomimo tej różnorodności brakowało jednak map referencyjnych genomu, zwłaszcza w pełni opisywanych genomów, co ograniczało możliwości badania ich ewolucji i stosowania narzędzi genomowych w monitoringu jakości wód.
Budowanie mapy genetycznej od podstaw
Aby wypełnić tę lukę, badacze zebrali dorosłe osobniki Rhopalopsole triangulispina w chronionym rezerwacie górskim w południowych Chinach. Po starannym zachowaniu materiału wyizolowali wysokiej jakości DNA i RNA (cząsteczkę odzwierciedlającą aktywność genów). Wykorzystując kilka zaawansowanych technologii sekwencjonowania, uzyskali różne obrazy genomu: bardzo dokładne, długie odczyty DNA (PacBio HiFi), ogromne liczby krótkich odczytów (Illumina) oraz specjalne dane pokazujące, jak fragmenty DNA są składane i wchodzą ze sobą w interakcje wewnątrz jądra komórkowego (Hi-C). Razem te typy danych pozwoliły zespołowi złożyć materiał genetyczny w długie, ciągłe sekwencje, a następnie użyć informacji Hi-C do uporządkowania ich w 13 struktur przypominających chromosomy, zwanych pseudochromosomami.
Co ujawnia genom
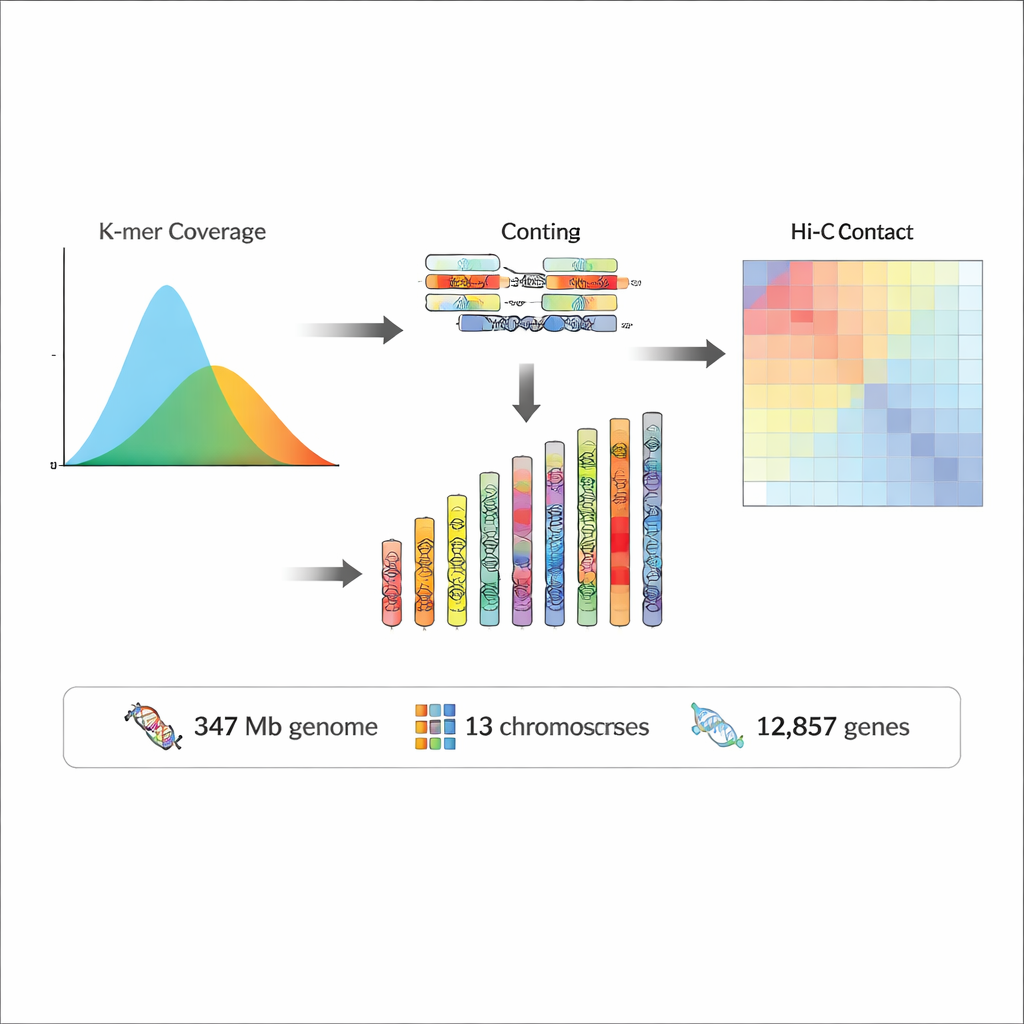
Gotowy genom ma około 347 milionów „liter” DNA, z prawie 97% materiału umieszczonego na 13 pseudochromosomach. Kontrole jakości wykazały, że montaż jest zarówno bardzo kompletny, jak i niezwykle dokładny, z szacowanymi wskaźnikami błędów poniżej jednej na dziesięć milionów nukleotydów oraz z ponad 95% wszystkich odczytów sekwencji odtwarzających się na nim. Niemal połowę genomu stanowi DNA powtarzalny — odcinki pojawiające się wielokrotnie, często odzwierciedlające ruchome elementy genetyczne, czyli „skaczące geny”, które kształtowały genom w toku ewolucji. Na tej podstawie zespół przewidział 12 857 genów kodujących białka oraz ponad 2 400 genów RNA niekodujących białek, w tym cząsteczki zaangażowane w budowę rybosomów, przetwarzanie RNA i kierowanie produkcją białek. Porównując te geny z dużymi międzynarodowymi bazami danych, badacze mogli przypisać prawdopodobne funkcje większości z nich i powiązać wiele z znanymi ścieżkami biologicznymi.
Nowe źródło danych dla ewolucji i ekologii
Ponad katalogowaniem genów, ten genom pełni rolę podręcznika referencyjnego dla przyszłych badań. Naukowcy mogą teraz badać, które geny pomagają ważkom kamiennym przystosować się do zimnej, szybko płynącej wody, jak reagują na poziomie molekularnym na zanieczyszczenia lub zmiany klimatu oraz jak różne linie ważek kamiennych są ze sobą spokrewnione. Do tej pory większość prac ewolucyjnych nad Nemouroidea opierała się na cechach morfologicznych, DNA mitochondrialnym lub fragmentach genów. Ten kompletny, opatrzony anotacjami genom oferuje znacznie bogatszą i precyzyjniejszą podstawę do odtwarzania drzewa genealogicznego ważek i porównywania genomów między owadami, w tym takimi o bardzo odmiennych trybach życia. Ponieważ wszystkie surowe dane i anotacje są publicznie dostępne, badacze z całego świata mogą ponownie analizować informacje, integrować je z innymi zbiorami danych i tworzyć nowe narzędzia do biomonitoringu.
Od planu DNA do czystszych potoków
Dla osób niebędących specjalistami kluczowe przesłanie jest takie, że mamy teraz szczegółowy, na poziomie chromosomów plan genomu gatunku ważki kamiennej, który pełni rolę pierwszej linii obrony zdrowia wód słodkowodnych. Ten genom pomoże naukowcom zrozumieć, jak te owady żyją i się adaptują, prześledzić ich głęboką historię ewolucyjną oraz opracować bardziej czułe, oparte na DNA metody wykrywania ich w rzekach i potokach. W praktyce oznacza to lepsze systemy wczesnego ostrzegania przed zanieczyszczeniem i zmianami środowiskowymi. Odkrywając genetyczne podstawy małego owada z górskich strumieni, praca ta w ostatecznym rozrachunku przyczynia się do ochrony czystej wody, od której zależą ludzie i ekosystemy.
Cytowanie: Lin, A., Cao, J., Murányi, D. et al. Chromosome-level genome assembly of the stonefly Rhopalopsole triangulispina Mo and Li, 2025 (Plecoptera: Leuctridae). Sci Data 13, 292 (2026). https://doi.org/10.1038/s41597-026-06631-7
Słowa kluczowe: genom ważki kamiennej, biowskaźniki środowisk wodnych, skład na poziomie chromosomów, ewolucja owadów, środowiskowe DNA