Clear Sky Science · pl
Metabarkodowanie i dane metagenomiczne wzdłuż wodnych gradientów środowiskowych na wybrzeżach Francji i Chile
Ukryte życie w zmieniających się morzach
Wzdłuż światowych wybrzeży, od spokojnych lagun po spektakularne fiordy, mikroorganizmy nieustannie dostosowują się do zmieniających się warunków. Te maleńkie organizmy napędzają cykle węgla i składników odżywczych, które leżą u podstaw rybołówstwa, jakości wód, a nawet klimatu. Wiele wód przybrzeżnych, zwłaszcza złożone środowiska takie jak laguny i fiordy, było jednak słabo zbadanych na poziomie genetycznym. Niniejsze badanie miało to zmienić, tworząc bogaty, otwarty zbiór danych o mikroorganizmach przybrzeżnych z Francji i Chile, oferując nowe spojrzenie na to, jak życie morskie reaguje na ciągłe zmiany środowiskowe.
Wybrzeża jako naturalne laboratoria testowe
Wody przybrzeżne rzadko są stałe. Ulewne deszcze, dopływ rzek, parowanie i pływy potrafią przemieszczać temperaturę i zasolenie w krótkich odległościach i w krótkim czasie. Dostępność składników odżywczych dla mikroskopijnych alg może gwałtownie rosnąć lub spadać, a działalność człowieka wprowadza dodatkowe zakłócenia. Taka zmienność tworzy mozaikę siedlisk, które selekcjonują różne społeczności mikroorganizmów i sprzyjają nowym adaptacjom. Aby uchwycić tę złożoność, badacze pobrali próbki w 26 lokalizacjach wzdłuż wybrzeży Francji i Chile, obejmując laguny, estuaria, fiordy, porty, plaże, wody przybrzeżne oraz jedno stanowisko przybrzeżne otwartego morza. Niektóre miejsca we Francji były odwiedzane co miesiąc przez rok, aby śledzić sezonowość, podczas gdy miejsca w Chile pobrano w południowej jesieni, co dało szeroki przekrój kontrastujących światów przybrzeżnych. 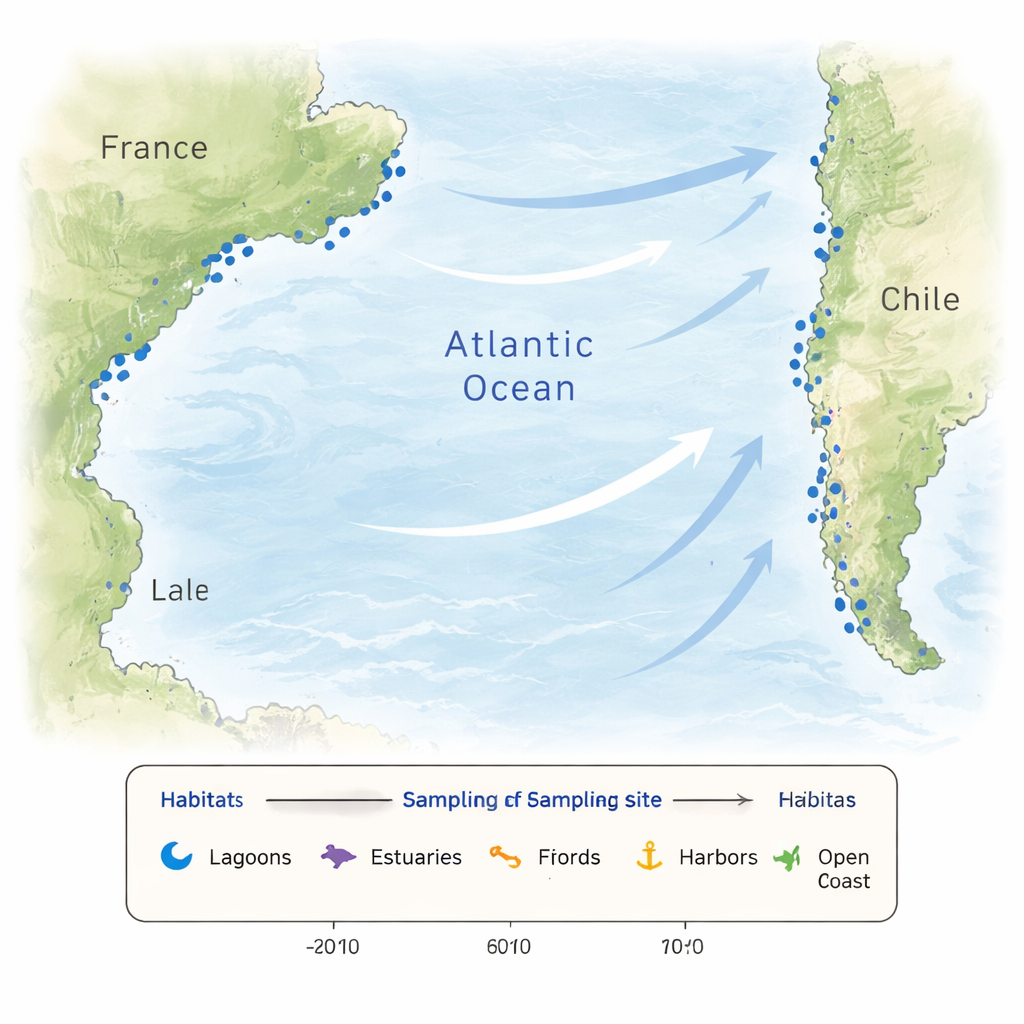
Z wiader wody do genetycznych odcisków palców
Na każdym stanowisku zespół pobierał duże objętości wody morskiej, głównie z oświetlonej strefy powierzchniowej, ale także z głębszych warstw w wybranych fiordach i wodach przybrzeżnych otwartego morza. Mierzono podstawowe warunki środowiskowe, takie jak temperatura, zasolenie i składniki odżywcze, oraz wskaźniki aktywności biologicznej, jak chlorofil (proxy dla alg), rozpuszczone związki organiczne, produkcja bakterii i oddychanie. W laboratorium mikroorganizmy skoncentrowano na drobnych filtrach i wyizolowano ich DNA. Jeden zestaw testów skupił się na standardowym genie markerowym (16S rRNA), który działa jak kod kreskowy do identyfikacji bakterii i archeonów. Podejście metabarkodowania ujawniło ponad 53 000 odrębnych wariantów DNA i wykazało, że niektóre próbki dzieliły zaledwie trzy warianty, co podkreśla, jak bardzo różnić się mogą sąsiednie społeczności.
Odbudowa genomów z genetycznej zupy
Drugi kierunek analiz był bardziej ambitny: shotgunowa metagenomika, w której całe DNA w próbce jest sekwencjonowane jednocześnie. Z użyciem zaawansowanych metod składania i binowania zespołowi udało się zrekonstruować 1 372 szkicowe genomy, znane jako metagenomowo złożone genomy (MAGy). Wiele z tych genomów nie dawało się dopasować do znanych gatunków, a tylko około 4% odpowiadało formalnie opisanym gatunkom mikrobów. W niektórych grupach, na przykład u bakterii i archeonów przystosowanych do nietypowych warunków, ponad połowa przewidywanych białek nie miała znanej funkcji. Badacze zbudowali także ogromny katalog genów liczący ponad 23 miliony nieredundantnych genów, stwierdzając, że około 31% nie miało odpowiedników w głównych bazach referencyjnych. Wskazuje to na głębokie zasoby nieopisanej biologii zasiedlające wody przybrzeżne.
Ekstremalne siedliska, nowe narzędzia
Niektóre stanowiska, zwłaszcza hipersłone laguny we Francji, wyróżniały się jako ogniska genetycznej nowości. Tam poziomy zasolenia wahały się od niemal normalnej wody morskiej do ponad dwukrotnie większego zasolenia niż ocean w ciągu zaledwie kilku miesięcy. Takie stresujące warunki mogą sprzyjać tzw. mikroorganizmom ekstremotolerancyjnym wyposażonym w enzymy działające w wysokiej soli lub w podwyższonej temperaturze. Takie enzymy są coraz bardziej pożądane w zastosowaniach przemysłowych: w detergentach, biopaliwach, oczyszczaniu zanieczyszczeń i przetwórstwie żywności. Łącząc szczegółowe pomiary środowiskowe z danymi genów i genomów, ten zbiór danych pomaga wskazać, gdzie najprawdopodobniej znaleźć takie nietypowe organizmy i narzędzia biochemiczne. 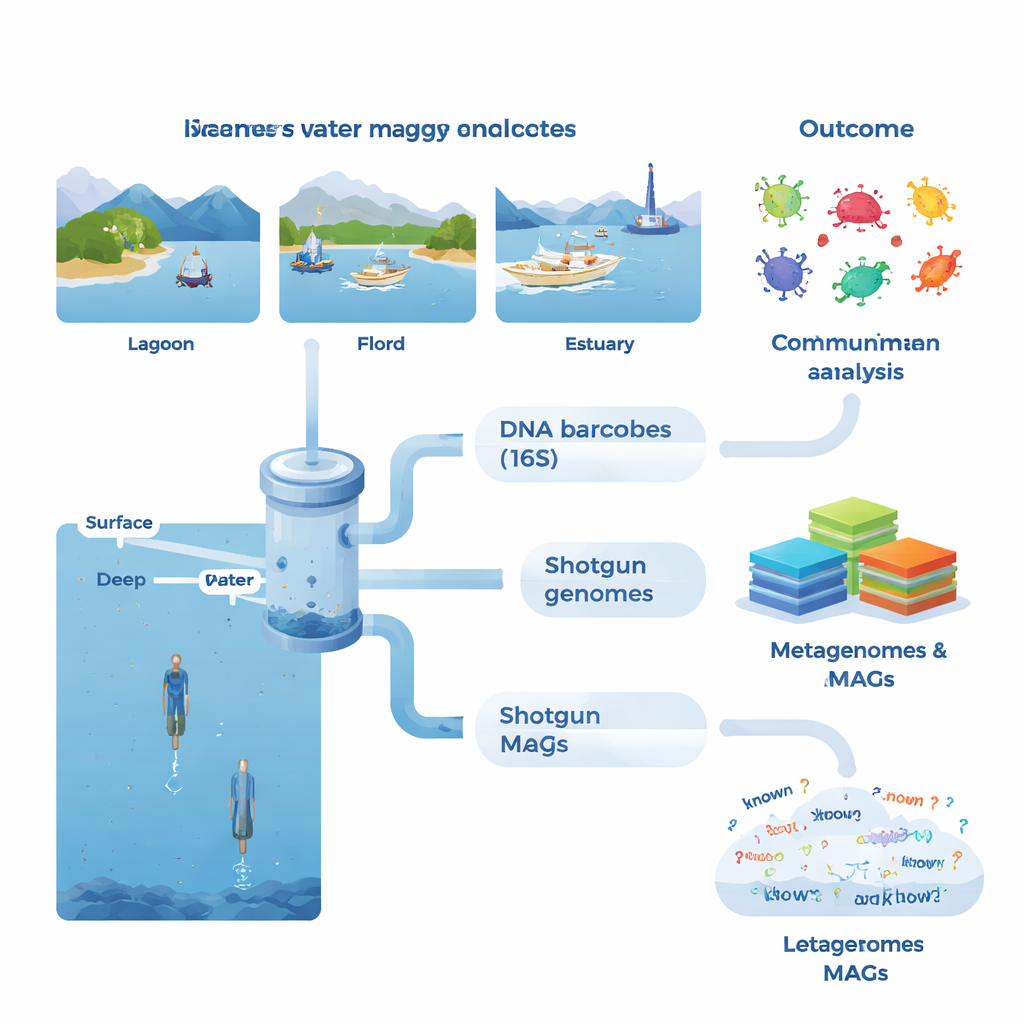
Publiczne zasoby dla przyszłości oceanu
Zamiast przedstawiać jedno odkrycie, ta praca dostarcza starannie zweryfikowany, otwarty zasób, który inni naukowcy mogą eksplorować. Wszystkie sekwencje DNA, rekonstrukcje genomów, katalogi genów i pomiary środowiskowe są publicznie zarchiwizowane, wraz z kodem komputerowym użytym do ich przetworzenia. Dla osób nietechnicznych kluczowy przekaz jest taki, że mikroorganizmy przybrzeżne są zarówno różnorodne, jak i pełne niespodzianek, szczególnie w niedocenianych środowiskach jak laguny i fiordy. Gdy badacze wykorzystają te dane, będą lepiej przygotowani, by zrozumieć, jak mikroskopijne życie wzdłuż naszych brzegów reaguje na ocieplenie, zanieczyszczenia i zaburzenia — oraz by wykorzystać nowatorskie geny, które mogą przynieść korzyści biotechnologii i zarządzaniu środowiskiem.
Cytowanie: Maeke, M.D., Hassenrück, C., Aguilar-Muñoz, P. et al. Metabarcoding and metagenomic data across aquatic environmental gradients along the coasts of France and Chile. Sci Data 13, 29 (2026). https://doi.org/10.1038/s41597-026-06572-1
Słowa kluczowe: mikrobiomy przybrzeżne, metagenomika, laguny i fiordy, bioróżnorodność morska, środowiskowe DNA