Clear Sky Science · pl
SEA CDM: Wspólny model danych Study-Experiment-Assay i bazy danych do integracji i analizy danych między dziedzinami
Dlaczego porządkowanie danych laboratoryjnych ma znaczenie dla nas wszystkich
Współczesna medycyna opiera się na górach danych eksperymentalnych — od badań nad szczepionkami i badań zakażeń po genomikę nowotworów. Te dane często jednak są zamknięte w niekompatybilnych formatach, co utrudnia naukowcom łączenie wyników i dostrzeganie ważnych wzorców, na przykład kto najlepiej reaguje na szczepionkę lub dlaczego niektórzy mają więcej skutków ubocznych. Ten artykuł opisuje nowy sposób organizowania i łączenia różnorodnych eksperymentów biomedycznych, dzięki któremu badacze mogą zadawać bogatsze pytania i szybciej uzyskiwać bardziej wiarygodne odpowiedzi, które ostatecznie wpływają na to, jak zapobiegamy i leczymy choroby.
Wspólny język dla eksperymentów
Różne grupy badawcze i bazy danych często opisują swoje badania po swojemu, nawet gdy zajmują się bardzo podobnymi zagadnieniami. Jedna baza może koncentrować się na badaniach szczepionek, inna na aktywności genów w pojedynczych komórkach, a jeszcze inna na wynikach klinicznych — każda używa innych etykiet i struktur. Study–Experiment–Assay Common Data Model, w skrócie SEA CDM, oferuje prostą wspólną „gramatykę” dla tych wysiłków. Dzieli każdy projekt biomedyczny na trzy powiązane kroki: ogólne badanie, które stawia pytanie; eksperymenty przeprowadzane na ludziach lub zwierzętach; oraz assaye — takie jak badania krwi czy pomiary ekspresji genów — które generują wyniki. Wokół tych kroków model standaryzuje też kluczowe elementy, takie jak kto lub co było badane, jakie próbki pobrano, jakie leczenia zastosowano i jakie analizy przeprowadzono. 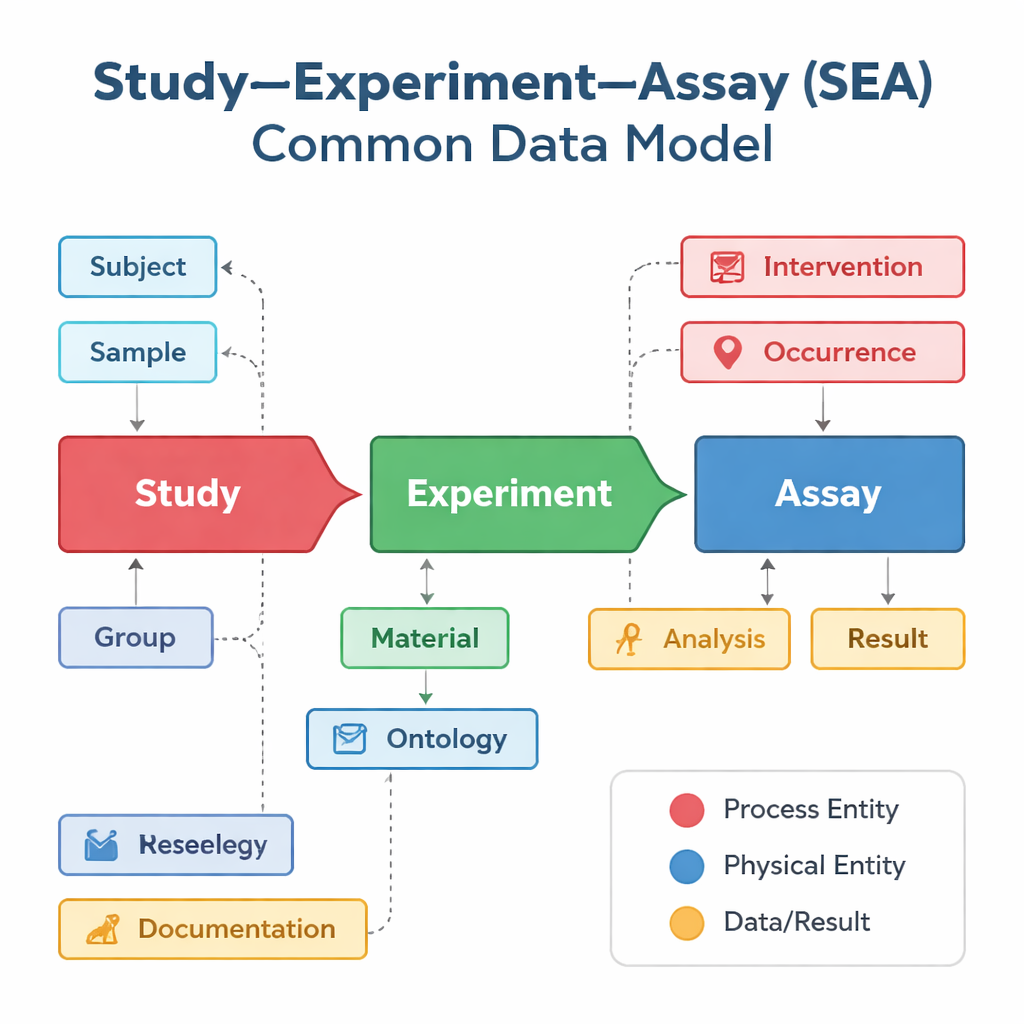
Ontologie: zamiana etykiet w wiedzę
Proste wyrównanie nagłówków kolumn nie wystarczy; ta sama koncepcja może być nazywana różnie w różnych miejscach. SEA CDM opiera się na kuratorowanych słownikach zwanych ontologiami, aby upewnić się, że „szczepionka przeciw grypie”, „trójwalentna inaktywowana szczepionka przeciw grypie” i nazwa handlowa typu „Fluzone” są rozpoznawane jako powiązane pojęcia. Te ontologie są uporządkowane jak drzewa rodzinne terminów medycznych i biologicznych. Ponieważ SEA CDM przypisuje oficjalny identyfikator z ontologii do każdej zmiennej — na przykład choroby, typu komórki czy szczepionki — komputery mogą automatycznie podążać za tymi drzewami, odnajdywać wszystkie relewantne rekordy, a nawet wywnioskować powiązania. Na przykład krótkie zapytanie może wydobyć każde badanie, które używało dowolnej trójwalentnej szczepionki przeciw grypie spośród setek nazwanych produktów, umożliwiając potężne wyszukiwania semantyczne, wykraczające daleko poza proste dopasowanie słów kluczowych. 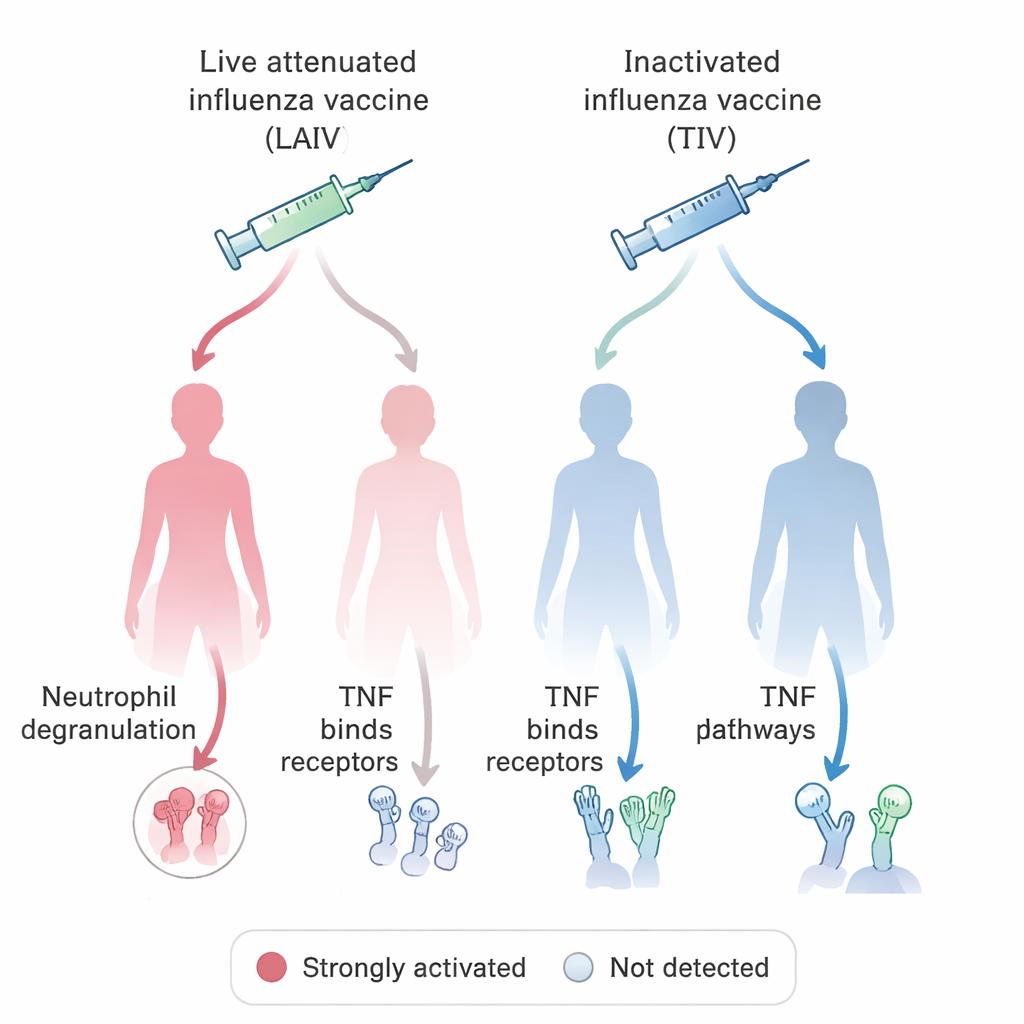
Z porozrzucanych plików do połączonych baz danych
Aby przetestować swój model w praktyce, autorzy zbudowali rodzinę baz danych i narzędzi pod wspólną nazwą OSEAN. Przekształcili trzy duże publiczne zasoby do struktury SEA CDM: ImmPort, który przechowuje metadane badań odpowiedzi immunologicznej; VIGET, który łączy badania szczepionek z danymi o aktywności genów; oraz CELLxGENE, koncentrujący się na pomiarach pojedynczych komórek. Za pomocą niestandardowych potoków przetworzyli dziesiątki oryginalnych tabel i formatów plików do spójnego zestawu tabel SEA CDM lub węzłów grafu. Pozwoliło to przechowywać ponad tysiąc badań związanych z odpornością, ponad dwa miliony próbek oraz liczne opisy szczepionek, chorób i metod laboratoryjnych w jednej spójnej ramie, którą można przeszukiwać tym samym oprogramowaniem.
Co zjednoczone dane mogą ujawnić o szczepionkach i różnicach związanych z płcią
Dysponując tym zharmonizowanym systemem, zespół postawił pytanie biologiczne o bezpośrednim znaczeniu medycznym: jak różne szczepionki przeciw grypie stymulują układ odpornościowy u kobiet i mężczyzn? Poprzez zapytania do bazy OSEAN opartej na VIGET i zastosowanie prostych reguł określających, co uznać za „stymulowany” gen, zidentyfikowali setki genów, których aktywność wzrosła po szczepieniu zarówno szczepionkami żywymi atenuowanymi (z osłabionym wirusem), jak i inaktywowanymi, „zabitymi” szczepionkami. Następnie porównali szlaki, w które te geny są zaangażowane, rozdzielając dane według płci. Jednym z uderzających wzorców były neutrofile — typ białych krwinek, które atakują mikroby, uwalniając toksyczne ziarnistości — oraz sygnalizacja przez TNF, kluczową cząsteczkę zapalną. W większości grup szczepienie przeciw grypie było związane ze znakami degranulacji neutrofili, lecz ten znak był nieobecny u kobiet, które otrzymały żywą atenuowaną szczepionkę. Natomiast sygnalizacja związana z TNF była szczególnie widoczna u tych kobiet, ale nie w odpowiadających im grupach męskich. Te obserwacje korespondują z badaniami na zwierzętach sugerującymi, że zachowanie neutrofili i odpowiedzi na szczepionki może różnić się systematycznie między samcami a samicami.
Budowanie ekosystemu dla przyszłych odkryć
Autorzy twierdzą, że prawdziwa siła SEA CDM polega na uczynieniu danych biomedycznych bardziej FAIR — odnajdywalnymi, dostępnymi, interoperacyjnymi i możliwymi do ponownego użycia. Nadając eksperymentom wspólną strukturę i przywiązując każdą istotną etykietę do jasno zdefiniowanego terminu ontologicznego, ich system znacznie ułatwia łączenie danych z różnych źródeł, śledzenie sposobu postępowania z próbkami i odtwarzanie analiz. Studium przypadku grypy pokazuje, że nawet stosunkowo proste zapytania, uruchomione na zharmonizowanej bazie danych, mogą ujawnić subtelne, specyficzne dla płci wzorce odpowiedzi na szczepionkę, które mogą wpływać na dawkowanie lub wybór szczepionki. W miarę jak kolejne zasoby będą przyjmować ten wspólny model i towarzyszące mu narzędzia, badacze będą lepiej przygotowani do łączenia tropów między chorobami, technologiami i populacjami, przekształcając rozfragmentowane zbiory danych w prawdziwy integracyjny ekosystem biodanych.
Cytowanie: Huffman, A., Yeh, FY., Hur, J. et al. SEA CDM: Study-Experiment-Assay Common Data Model and Databases for Cross-Domain Data Integration and Analysis. Sci Data 13, 238 (2026). https://doi.org/10.1038/s41597-026-06558-z
Słowa kluczowe: integracja danych, ontologia biomedyczna, odpowiedź na szczepionkę, różnice związane z płcią, graf wiedzy