Clear Sky Science · pl
Budowa złożonych i różnorodnych sekwencji DNA z wykorzystaniem trójramiennych złączeń DNA
Tworzenie nowych genetycznych opowieści
Nowoczesna biologia potrafi czytać i edytować DNA z oszałamiającą szybkością, jednak rzeczywiste pisanie długich, specjalnie zaprojektowanych sekwencji genetycznych wciąż pozostaje w tyle. Ta luka spowalnia wszystko, od projektowania nowych leków po tworzenie bardziej ekologicznych materiałów. W tym badaniu przedstawiono „Sidewinder” — nową metodę łączenia fragmentów DNA, która ma uczynić tworzenie skomplikowanych, szytych na miarę genów tak niezawodnym i skalowalnym, jak ich odczytywanie.
Dlaczego składanie DNA wymaga przemyślenia
Każda komórka funkcjonuje dzięki DNA, długiemu łańcuchowi chemicznych liter kodujących instrukcje życia. Naukowcy potrafią chemicznie wytwarzać tylko krótkie odcinki DNA, więc dłuższe geny muszą być składane z wielu małych kawałków, jak zdania złożone z pociętych słów. Istniejące metody korzystają z dopasowujących się końców tych fragmentów, które kierują, które elementy ze sobą łączą. Jednak te dopasowujące się końcówki stają się częścią końcowego DNA, co oznacza, że nie można ich swobodnie optymalizować pod kątem bezbłędnego składania bez jednoczesnej zmiany samego genu. W miarę jak projekty stają się dłuższe i bardziej złożone, ten wrodzony kompromis prowadzi do większej liczby błędów, niższych wydajności i praktycznych ograniczeń tego, co da się zbudować.
Boczna ścieżka, która prowadzi bez zostawiania śladu
Sidewinder rozwiązuje ten problem, dodając trzeci pomocniczy łańcuch DNA, który nigdy nie pojawia się w produkcie końcowym. Fragmenty DNA są przygotowane z dwoma cechami na końcach: krótkimi „toeholdami”, które ostatecznie utworzą bezszwowe połączenie, oraz dłuższymi „kodami kreskowymi” zaprojektowanymi tylko po to, aby rozpoznawać właściwych partnerów. Po zmieszaniu w kontrolowanej temperaturze kody kreskowe sąsiednich fragmentów odnajdują się i owijają w tymczasową boczną helisę, tworząc trójramienne złącze, które przyciąga dopasowane toeholdy na miejsce. Enzym następnie łączy główne fragmenty DNA. Na koniec pomocnicze kody kreskowe są usuwane, pozostawiając czystą, ciągłą sekwencję bez dodatkowych blizn czy oznaczeń. 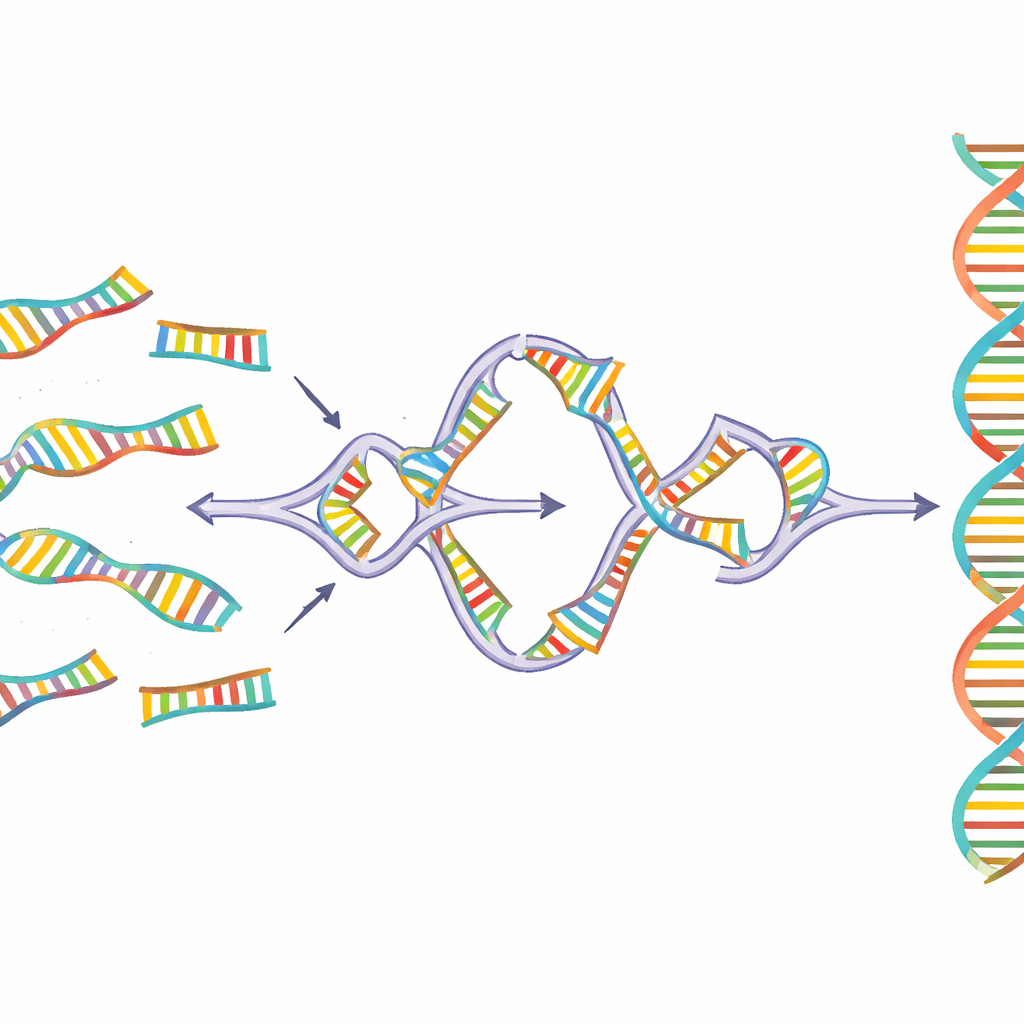
Od kilkunastu fragmentów do trudnych genów
Aby pokazać możliwości Sidewinder, autorzy zbudowali konstrukty DNA z 5, 10, 20, a nawet 40 oddzielnych fragmentów w jednej reakcji. Konkurencyjne, najnowocześniejsze metody załamywały się już po kilku fragmentach, dając złożone mieszaniny lub całkowicie zawodząc, podczas gdy Sidewinder konsekwentnie dawał pojedynczy, prawidłowo oznaczony produkt. Sekwencjonowanie długich odczytów potwierdziło, że w teście z 40 fragmentami ponad 96% odczytów stanowiły prawdziwe produkty Sidewinder i każdy z nich był złożony we właściwej kolejności. Zespół następnie przetestował metodę na sekwencjach w „trybie trudnym”: ludzki gen o bardzo wysokiej zawartości nukleotydów G i C oraz fragment białka przypominający jedwab, bogaty w powtórzenia. Takie sekwencje często pokonują standardowe metody montażu, ponieważ mają skłonność do samoprzylegania w mylący sposób. Sidewinder nadal generował niemal idealne zespoły, nawet gdy wszystkie skrzyżowania celowo dzieliły ten sam toehold — coś, co byłoby niemal niemożliwe do kontrolowania za pomocą starszych technik.
Wiele genów naraz i oceany wariantów
Dzięki temu, że kody kreskowe Sidewinder jednoznacznie definiują, kto może się parować z kim, wiele genów można zbudować w tej samej probówce bez krzyżowego zanieczyszczenia. Badacze wymieszali fragmenty trzech różnokolorowych markerów białkowych i zmontowali je w jednej reakcji. Przy użyciu odpowiednich starterów mogli selektywnie amplifikować dowolny pojedynczy gen lub mieszankę, a sekwencjonowanie wykazało, że nieprawidłowe skrzyżowania między projektami były niezwykle rzadkie. 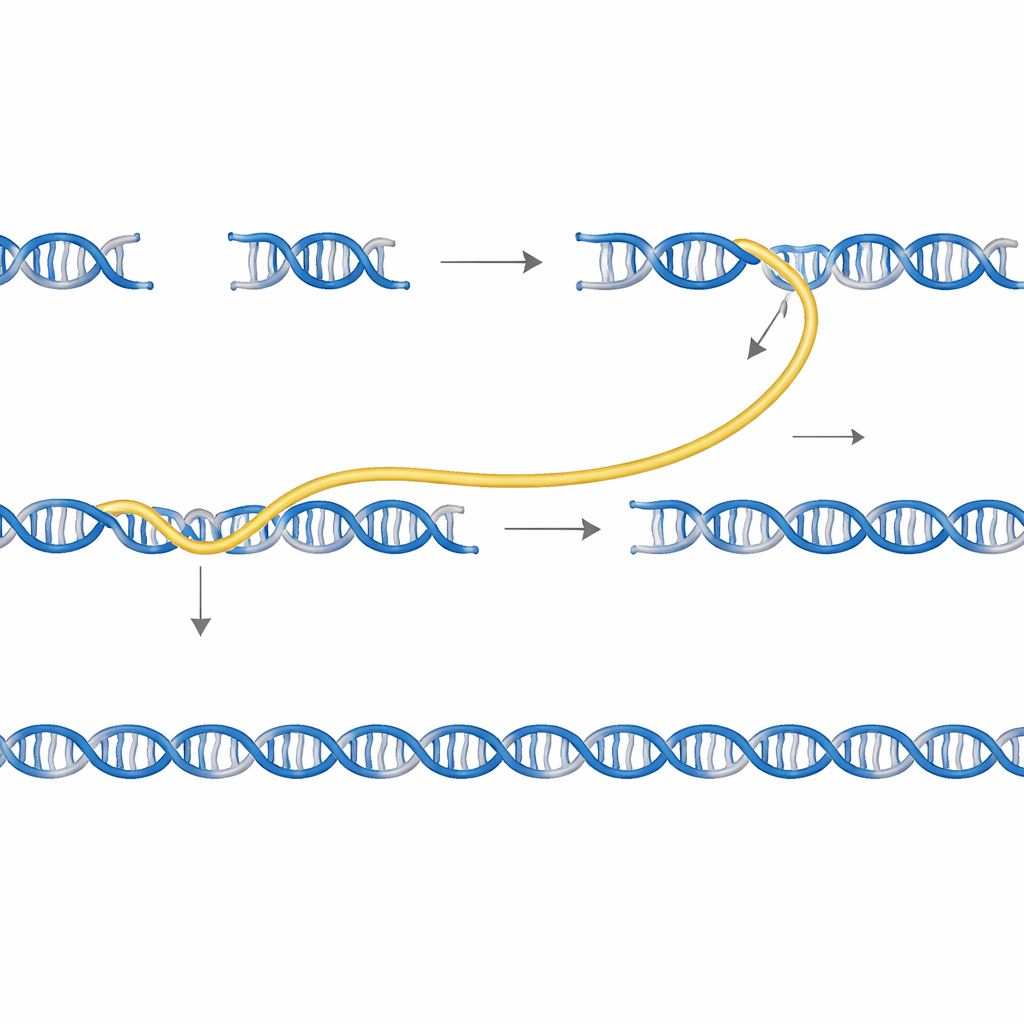
Co to oznacza dla przyszłej inżynierii biologicznej
Kluczowe osiągnięcie Sidewinder polega na oddzieleniu „instrukcji montażu” od końcowej historii DNA. Przenosząc informacje prowadzące na usuwalny boczny łańcuch, naukowcy mogą projektować złącza niezwykle specyficzne i niezawodne, bez konieczności kompromisu dla samego genu. W efekcie otrzymujemy uniwersalny sposób budowy długich, trudnych i silnie zróżnicowanych sekwencji DNA z dokładnością dorównującą, a w niektórych aspektach przewyższającą, jakość wyjściowych fragmentów. W miarę jak narzędzia, takie jak sztuczna inteligencja, coraz częściej proponują odważne nowe projekty genetyczne, techniki takie jak Sidewinder mogą stać się niezbędne do zamiany tych projektów w rzeczywiste molekuły stosowane w medycynie, materiałach, rolnictwie i innych dziedzinach.
Cytowanie: Robinson, N.E., Zhang, W., Ghosh, R. et al. Construction of complex and diverse DNA sequences using DNA three-way junctions. Nature 651, 491–500 (2026). https://doi.org/10.1038/s41586-025-10006-0
Słowa kluczowe: składanie DNA, biologia syntetyczna, biblioteki genów, nanotechnologia DNA, inżynieria białek