Clear Sky Science · pl
Metagenomika wskazuje na współdziałanie mikrobiomu i szlaków funkcjonalnych w chorobie Parkinsona
Historia jelitowo‑mózgowa kryjąca się za dobrze znaną chorobą
Choroba Parkinsona jest najbardziej kojarzona z drżeniami i spowolnieniem ruchów, ale początki mogą leżeć daleko od mózgu — głęboko w jelitach. Wiele osób z Parkinsonem boryka się z zaparciami i innymi problemami trawiennymi wiele lat przed pojawieniem się pierwszych objawów ruchowych. W badaniu tym sprawdzono, czy rozległa społeczność drobnoustrojów żyjących w naszych jelitach oraz szlaki chemiczne, jakich używają, różnią się u osób z chorobą Parkinsona w porównaniu ze zdrowymi dorosłymi. Analizując materiał genetyczny z próbek kału, badacze poszukiwali wzorców, które pewnego dnia mogłyby pomóc przewidywać, wyjaśniać lub nawet zapobiegać tej powszechnej chorobie mózgu.
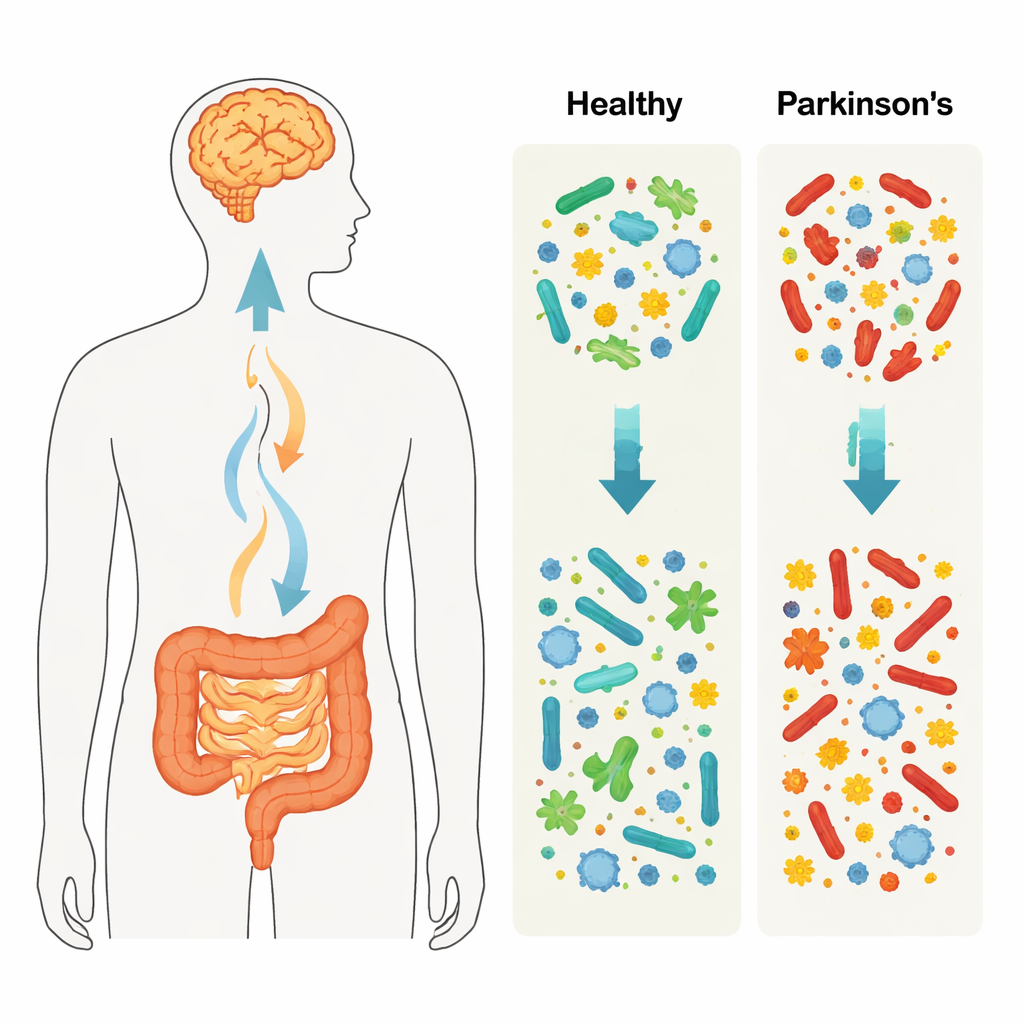
Kogo badano i co mierzono
Badacze porównali próbki kału od 55 dorosłych mieszkańców Ameryki Północnej z chorobą Parkinsona z próbkami od 42 zdrowych dorosłych pochodzących z istniejącego badania publicznego. Zamiast skupiać się na kilku wybranych mikroorganizmach, zastosowali sekwencjonowanie całych genomów, które obejmuje DNA bakterii, wirusów, grzybów, eukariontów jednokomórkowych oraz geny odpowiadające za ich metabolizm. Pozwoliło to zadać dwa podstawowe pytania: jakie organizmy są obecne i do czego genetycznie są zdolne? Równolegle do spisu mikrobiologicznego zespół użył standardowych miar ekologicznych, aby opisać, jak zróżnicowana i równomiernie zbalansowana jest społeczność jelitowa każdej osoby.
Zmiany w bakteryjnych mieszkańcach jelit
Na najszerszym poziomie jelita osób z chorobą Parkinsona zawierały inną proporcję głównych grup bakterii niż jelita zdrowych kontrolnych uczestników. Dwie duże grupy, Firmicutes i Actinobacteria, były relatywnie bardziej liczne w Parkinsonie, podczas gdy Bacteroidetes i niektóre bakterie niezaklasyfikowane występowały rzadziej. Osoby z Parkinsonem miały bardziej równomierne społeczności bakteryjne — żaden pojedynczy typ nie dominował — lecz w rzeczywistości gospodarzy było mniej odrębnych gatunków. Przy analizie na bardziej szczegółowych poziomach taksonomicznych zidentyfikowano dziesiątki konkretnych linii bakteryjnych różniących się między grupami, kreśląc obraz rozległej, lecz subtelnej przebudowy ekosystemu jelitowego w chorobie Parkinsona.
Wirusy, grzyby i inni ukryci gracze
Zespół przyjrzał się także poza bakteriami — wirusom je infekującym (fagom), wirusom DNA w ogóle oraz grzybom i protistom. Zestaw fagów u pacjentów z Parkinsonem wykazywał wyraźne różnice w składzie rodzinnym i różnorodności w porównaniu ze zdrowymi dorosłymi, co sugeruje, że wirusowi drapieżnicy bakterii jelitowych też są przearanżowani. Inne wirusy DNA i grzyby również pokazały odrębne ogólne wzorce społeczności między grupami, chociaż ich bezwzględne poziomy były niskie i bardzo zróżnicowane między osobami. Protisty występowały skąpo i w przybliżeniu podobnie, przy czym jeden powszechny mieszkaniec jelit, Blastocystis, pojawiał się częściej w próbkach osób z Parkinsonem, ale bez silnego wsparcia statystycznego. Razem te obserwacje sugerują, że z Parkinsonem mogą wiązać się zmiany wielokrólowe w jelitach, a nie tylko przesunięcia wśród bakterii.
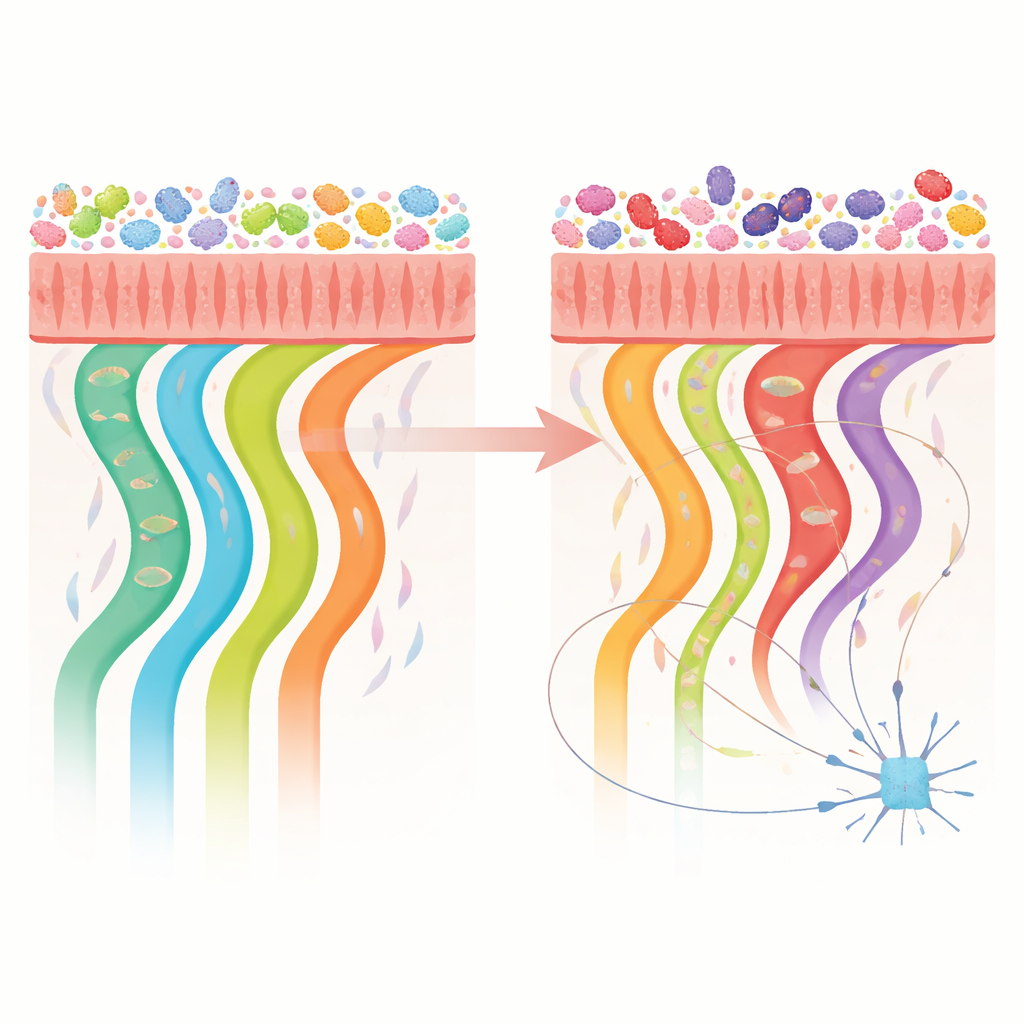
Zmiany w szlakach aktywności mikrobiologicznej
Ponad tym, kto tam jest, badanie badało, do czego mikroby jelitowe są zdolne. Łącząc geny z danych sekwencyjnych z znanymi szlakami biochemicznymi, badacze odkryli, że osoby z Parkinsonem miały szerszy i bardziej równomiernie rozłożony zestaw funkcji mikrobiologicznych. Kilka szlaków wyróżniało się jako szczególnie wzbogacone. Należały do nich drogi związane z produkcją energii, spalaniem tłuszczów i recyklingiem składników ścian komórkowych bakterii, a także szlaki generujące molekuły związane z obroną antyoksydacyjną i metabolizmem puryn. Inne wiązały się z przetwarzaniem tRNA, rodzaju cząsteczki, która może dawać małe fragmenty badane jako biomarkery w chorobach neurodegeneracyjnych. Chociaż badanie nie mierzyło faktycznie wytwarzanych substancji chemicznych, potencjał genetyczny do tych aktywności był wyraźnie inny w jelitach osób z Parkinsonem.
Co to może oznaczać, a czego jeszcze nie dowodzi
Autorzy podkreślają, że ich praca ma charakter eksploracyjny i wiąże się z zastrzeżeniami. Grupa porównawcza zdrowych pochodziła z innego badania, w którym stosowano inne metody laboratoryjne, a szczegółowe informacje o stylu życia i diecie nie były dostępne, więc część różnic może odzwierciedlać czynniki techniczne lub środowiskowe, a nie samą chorobę Parkinsona. Rzadkie wykrywanie niektórych organizmów oraz brak bezpośrednich pomiarów produktów ubocznych mikrobiologii ograniczają, jak daleko można łączyć wyniki z objawami czy postępem choroby. Uczestnicy badania z Parkinsonem byli także w większości biali, wysoko wykształceni i relatywnie zamożni, co może nie odzwierciedlać szerszej populacji pacjentów.
Dlaczego te wyniki są ważne na przyszłość
Pomimo tych ograniczeń badanie wzmacnia ideę, że choroba Parkinsona jest powiązana ze zmianami w ekosystemie jelitowym i jego produkcie chemicznym. Odmienne wzorce bakterii, fagów, grzybów i szlaków metabolicznych sugerują, że środowisko jelitowe w Parkinsonie jest przebudowane w złożony sposób, który może wpływać na stan zapalny, stres oksydacyjny i przetwarzanie molekuł powiązanych ze zdrowiem mózgu. Dla laika wniosek jest taki, że Parkinson może nie być wyłącznie chorobą mózgu, lecz częścią zaburzenia obejmującego całe ciało, które rozpoczyna się częściowo w jelitach. Przyszłe, bardziej szczegółowe badania łączące genetykę, pomiary chemiczne i dane kliniczne w różnych grupach będą potrzebne, aby przekształcić te mikrobiologiczne odciski palców w wiarygodne narzędzia do wcześniejszego wykrywania lub nowych strategii leczenia.
Cytowanie: Park, S.J., Özdinç, B.E., Coker, K.G. et al. Metagenomics indicates an interplay of the microbiome and functional pathways in Parkinson’s disease. npj Parkinsons Dis. 12, 60 (2026). https://doi.org/10.1038/s41531-026-01271-5
Słowa kluczowe: choroba Parkinsona, mikrobiom jelitowy, metagenomika, oś jelita–mózg, metabolizm mikrobiologiczny