Clear Sky Science · pl
TONSOKU zapobiega tworzeniu się dużych duplikacji tandemowych i ogranicza aktywację punktu kontrolnego ATR–WEE1
Gdy naprawa DNA zawodzi u roślin
Nasze genomy, podobnie jak genomy upraw i nowotworów, są nieustannie narażone na uszkodzenia podczas kopiowania DNA. Zazwyczaj systemy naprawcze dyskretnie usuwają problemy, zanim wyrządzą szkody. W tym badaniu przyjrzano się efektom braku jednego z takich systemów opartego na białku zwanym TONSOKU (TSK) w małej chwastowej roślinie wykorzystywanej w badaniach. Wynik to zaskakujący wzrost dużych duplikacji DNA i nietypowe wzory wzrostu — wnioski, które mają znaczenie zarówno dla hodowli roślin, jak i zrozumienia chorób ludzkich.
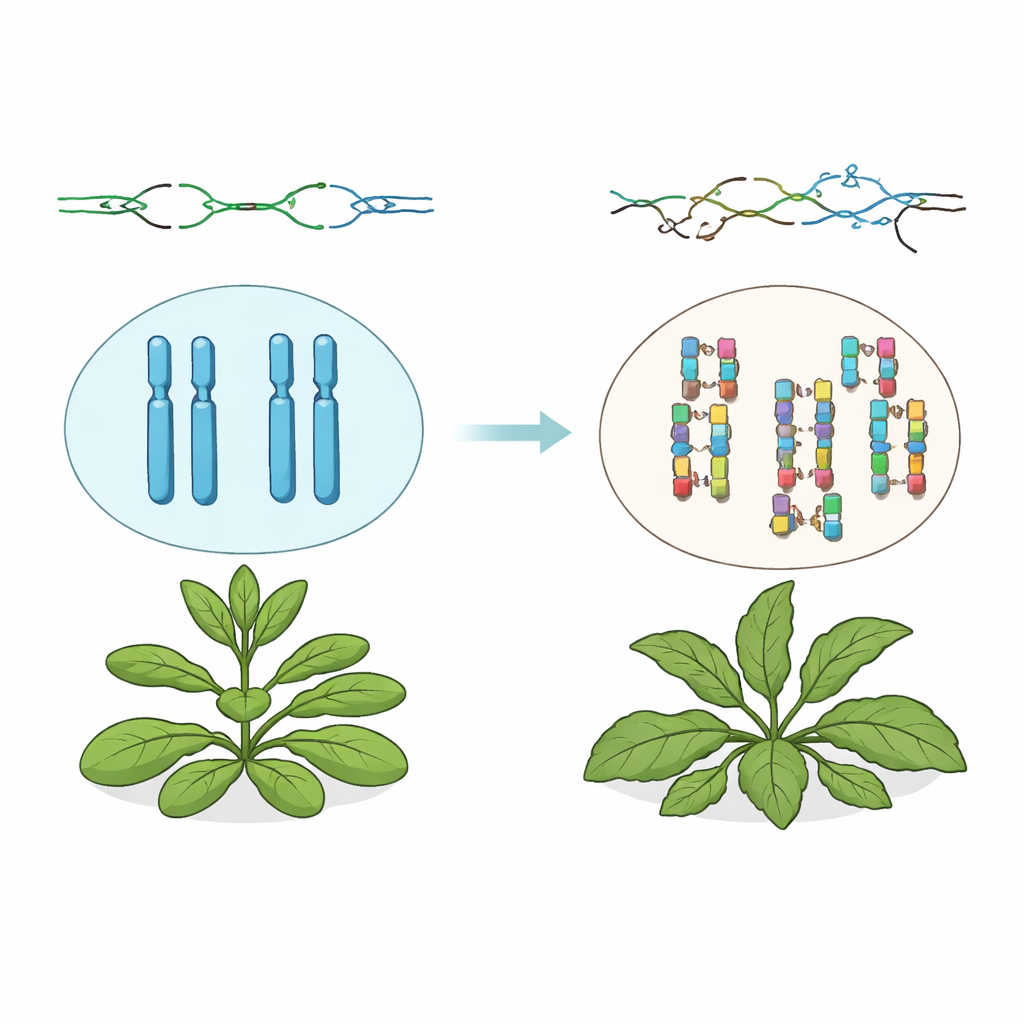
Nakładają się dodatkowe kopie DNA
Naukowcy pracowali z Arabidopsis thaliana pozbawionymi funkcjonalnego genu TSK. Chociaż rośliny te są zdolne do życia i rozmnażania, ich genomy opowiadają dramatyczną historię. Przy użyciu sekwencjonowania całego genomu zespół odkrył, że podczas gdy drobne mutacje utrzymują się na zbliżonym poziomie, duże odcinki DNA były często kopiowane podwójnie — tzw. duplikacje tandemowe. Dodane fragmenty miały rozmiary od poniżej tysiąca nukleotydów do niemal półtora miliona, często zwiększając całkowity rozmiar genomu o około 7 procent. Wiele z tych duplikacji było unikalnych dla poszczególnych roślin, co wskazuje, że powstają one wielokrotnie i niezależnie w trakcie wzrostu roślin i między pokoleniami.
Duplikacje przebudowują geny i ich aktywność
Te dodatkowe segmenty DNA to nie pusty ładunek. Gdy w skopiowanych regionach znajdują się geny, mają one tendencję do wyższej aktywności, po prostu dlatego, że jest ich więcej kopii. Łącząc sekwencjonowanie DNA z pomiarami RNA (odczytem aktywności genów), badacze wykazali, że geny w obrębie duplikowanych regionów często produkują wielokrotnie więcej RNA niż ich odpowiedniki w normalnych roślinach. Ten wzrost może się rozlewać i wpływać także na geny poza strefami duplikacji. Z upływem czasu zmiany liczby kopii mogą w znaczący sposób modyfikować cechy — zjawisko od dawna wykorzystywane w udomowianiu roślin i często obserwowane w ludzkich nowotworach.
Awaryjna ścieżka naprawcza tworzy uszkodzenia
Aby ustalić, jak powstają te duplikacje, zespół przyjrzał się końcom skopiowanych segmentów. Wzory, które zaobserwowano, odpowiadały odciskom palców awaryjnej ścieżki naprawy DNA zwanej theta-mediated end joining, zależnej od enzymu znanego jako polimeraza theta. Gdy zwykły, wysoko precyzyjny system naprawy zależny od TSK zawodzi, ta zapasowa ścieżka wkracza, by załatać przerwane DNA. Wykorzystuje przy tym drobne dopasowane sekwencje jako „klej”, co łatwo prowadzi do skopiowania fragmentu DNA dwukrotnie. Mapowanie optyczne bardzo długich cząsteczek DNA potwierdziło, że dodatkowe fragmenty siedzą tuż obok swoich pierwotnych odpowiedników na chromosomach, tworząc prawdziwe duplikacje tandemowe, a nie oddzielne kręgi DNA.
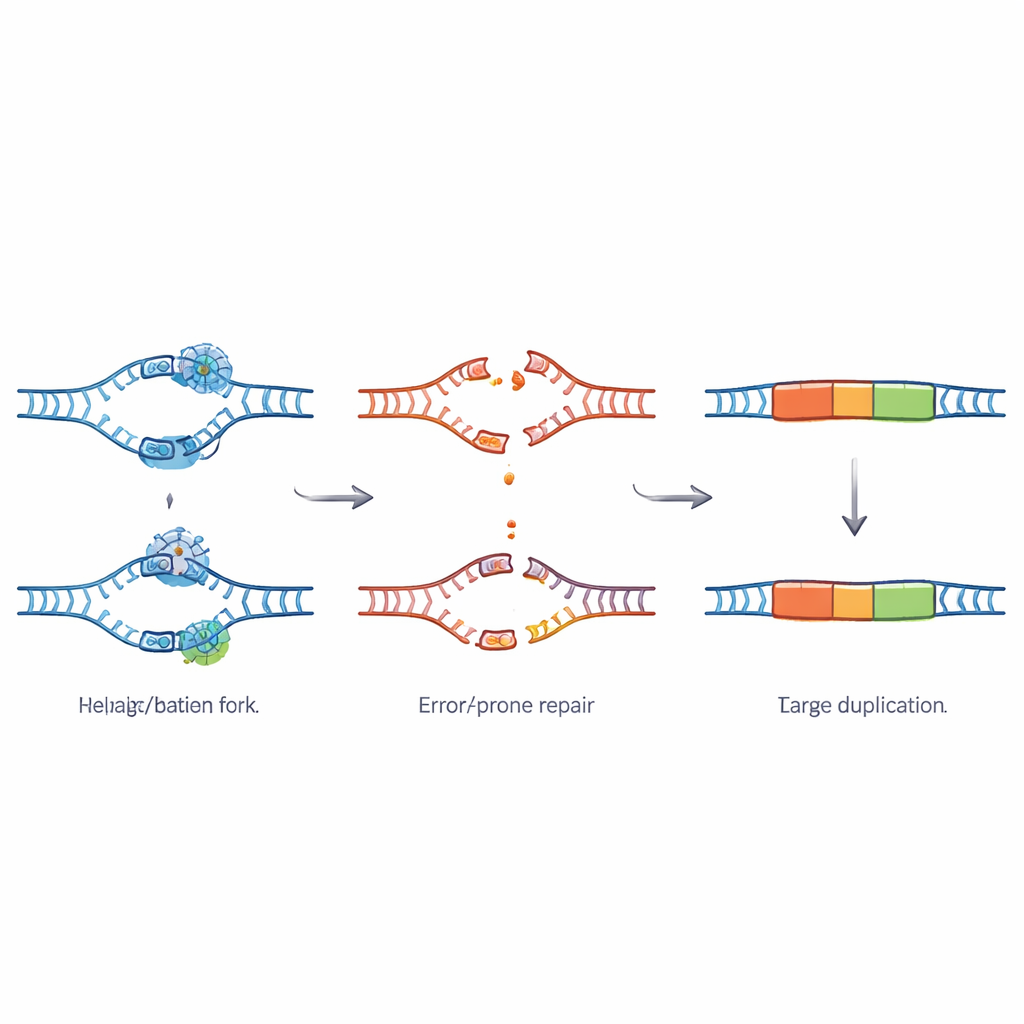
Gorące punkty stresu w genomie
Regiony z duplikacjami nie są rozmieszczone losowo. Mają tendencję do występowania w częściach genomu, które replikują się późno podczas podziału komórkowego i które są upakowane w gęste, powtarzalne DNA zwane heterochromatyną. Obszary te obfitują w specyficzne motywy powtarzalne i w ruchome elementy DNA, które są znane z tego, że sprawiają problemy maszynerii kopiującej DNA. Granice wokół miejsc duplikacji wykazują też oznaki przewlekłego stresu: zawierają więcej naturalnej zmienności, dłuższe ciągi powtórzeń, więcej elementów transpozonowych i więcej miejsc zapoczątkowania replikacji niż typowe regiony. Wszystko to wskazuje, że są to ogniska, w których kopiowanie DNA często się zatrzymuje lub załamuje, zwłaszcza przy braku TSK.
Od uszkodzonego DNA do roślin o dziwnych kształtach
Arabidopsis bez TSK nie tylko noszą „blizny” w genomie; wyglądają też osobliwie. Wiele wykazuje skręcone wzory liści i kwiatów, grube lub rozszczepione łodygi oraz nietypowe rozgałęzienia. Badacze sprawdzili, czy te widoczne dziwactwa wynikają z samych duplikacji, czy z alarmowej reakcji komórki na trwające uszkodzenia DNA. Wyłączając kluczowych graczy w odpowiedzi rośliny na uszkodzenia DNA — białka wykrywające zatrzymanie replikacji i zatrzymujące cykl komórkowy — w dużej mierze przywrócili normalny kształt roślin, choć duplikacje nadal powstawały. To pokazuje, że defekty rozwojowe wynikają głównie z przewlekłej aktywacji odpowiedzi na uszkodzenia DNA, a nie bezpośrednio z dodatkowych kopii DNA.
Dlaczego to ma znaczenie poza jednym chwastem
Ta praca ujawnia wcześniej ukrytą drogę, dzięki której mogą powstawać duże duplikacje DNA, gdy zawodzi konserwowany szlak naprawczy, łącząc stres repilkacyjny, podatną na błędy naprawę i widoczne zmiany w morfologii organizmu. Podobne białka TONSOKU-podobne i systemy naprawcze występują u zwierząt, w tym u ludzi. W niektórych nowotworach genomy są usiane dużymi duplikacjami tandemowymi o rozmiarach zadziwiająco podobnych do tych obserwowanych u omawianych roślin i są silnie zależne od tego samego szlaku wykrywania stresu, który badali autorzy. Zrozumienie, jak utrata funkcji podobnych do TSK przesuwa równowagę od stabilnego utrzymania DNA w kierunku wymykającej się kontroli duplikacji, może zatem rzucić światło zarówno na inżynierię nowych cech roślin, jak i na ewolucję oraz odpowiedź na leczenie niektórych guzów.
Cytowanie: Thomson, G., Poulet, A., Huang, YC. et al. TONSOKU prevents the formation of large tandem duplications and restrains ATR–WEE1 checkpoint activation. Nat Commun 17, 2874 (2026). https://doi.org/10.1038/s41467-026-70906-1
Słowa kluczowe: stabilność genomu, duplikacje tandemowe, stres podczas replikacji DNA, szlaki naprawy DNA, rozwój roślin