Clear Sky Science · pl
TONSL zapobiega tandemowym duplikacjom zależnym od polimerazy theta poprzez naprawę ukierunkowaną przez chromatynę
Kiedy DNA tworzy niebezpieczne dodatkowe kopie
Każda komórka musi kopiować swoje DNA z zadziwiającą dokładnością, a mimo to nasze genomy wciąż ulegają uszkodzeniom, które mogą przestawiać chromosomy. Jedną z szczególnie istotnych zmian jest „duplikacja tandemowa”, w której fragment DNA zostaje skopiowany i wstawiony tuż obok swojego oryginalnego miejsca. Takie dodatkowe kopie mogą sprzyjać ewolucji, dostarczając materiału genowego do powstawania nowych funkcji, ale w nowotworach często napędzają niekontrolowany wzrost. W badaniu tym ujawniono, jak białko o nazwie TONSL pomaga komórkom unikać tych ryzykownych duplikacji, odkrywając ukrytą barierę ochronną, która wydaje się być wspólna dla zwierząt i roślin. 
Dodatkowe kopie: korzystne dla ewolucji, ryzykowne dla zdrowia
Duże, powtarzające się odcinki DNA ustawione obok siebie, znane jako duplikacje tandemowe, należą do najczęstszych zmian strukturalnych w złożonych genomach. Mogą podwoić całe geny, co czasami umożliwia przez długie okresy ewolucyjne pojawianie się nowych funkcji. Jednak gdy naukowcy badają zdrowe tkanki, znajdują bardzo niewiele świeżych duplikacji tandemowych, co sugeruje, że komórki aktywnie ich zapobiegają. W wielu nowotworach te duplikacje są jednak liczne, przekształcając genom na dużą skalę. Tajemnicą pozostawało, w jaki sposób normalne komórki zwykle naprawiają pęknięcia DNA, nie tworząc przypadkowo tak dużych skopiowanych fragmentów.
Odkrycie ukrytego strażnika genomu
Aby odnaleźć naturalnych obrońców przed tymi zdarzeniami duplikacyjnymi, badacze zwrócili się ku malutkiej nicieni Caenorhabditis elegans, którą można namnażać i sekwencjonować w dużych ilościach. Ponowna analiza kolekcji około 2000 mutagenezowanych szczepów robaków pozwoliła zidentyfikować kilka linii z nieoczekiwanie dużą liczbą duplikacji tandemowych. Wspólnym mianownikiem w tych szczepach była uszkodzona pojedyncza sekwencja genu, nazwana tnsl-1, kodująca białko TONSL. Gdy zespół celowo wyłączył ten gen i hodował robaki przez wiele pokoleń, ich genomy kumulowały duplikacje tandemowe w stałym tempie, mniej więcej po jednej na pokolenie, rozrzucone po wszystkich chromosomach. Co zaskakujące, organizmy pozostały w dużej mierze zdrowe, co pokazuje, że genom może po cichu gromadzić wiele dużych duplikacji bez natychmiastowego załamania.
Szybko dzielące się komórki tworzą małe duplikacje, wolno dzielące się — duże
Bliższa analiza wykazała, że nowe duplikacje występowały w dwóch głównych przedziałach wielkości: jeden skupiał się wokół dziesiątek tysięcy par zasad, a drugi wokół kilkuset tysięcy. Zespół wysunął hipotezę, że tempo podziałów komórkowych może kształtować, jak duża stanie się duplikacja. Zarodki robaków dzielą się bardzo szybko, z cyklami komórkowymi trwającymi około 20 minut, podczas gdy komórki linii zarodkowej (dającej początek jajom i plemnikom) dzielą się znacznie wolniej. Dzięki starannie zaprojektowanym krzyżówkom genetycznym i sekwencjonowaniu całego genomu potomstwa, badacze mogli określić, kiedy powstawały duplikacje. Stwierdzili, że małe duplikacje powstawały podczas szybkich, wczesnych podziałów embrionalnych, podczas gdy duże pojawiały się później w wolniej dzielącej się linii zarodkowej. Wskazuje to na model, w którym długość czasu dostępnego na naprawę DNA i kopiowanie determinuje, jak daleko proces kopiowania napędzany pęknięciem może postępować, zanim zostanie zamknięty.
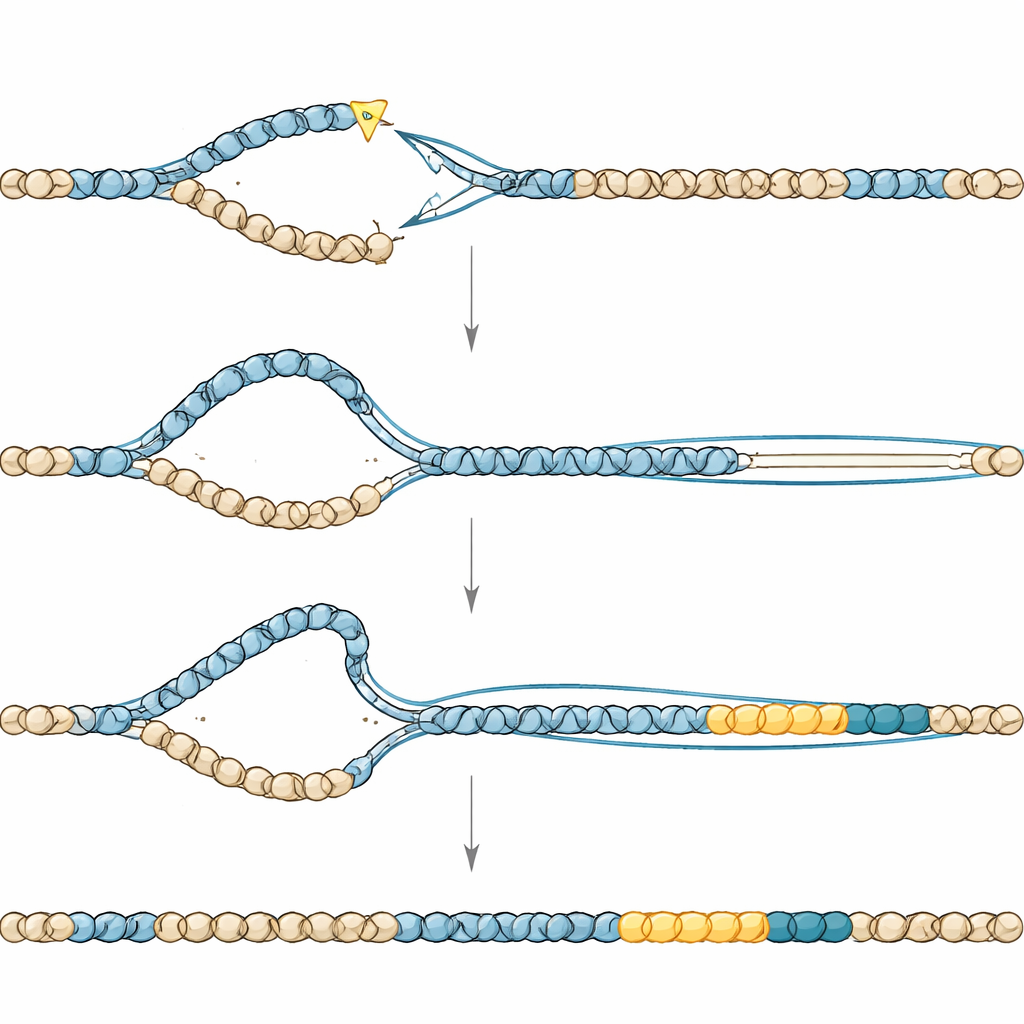
Jak wadliwa maszyna naprawcza buduje duplikacje
Miejsca łączenia skopiowanych fragmentów z oryginalnym DNA nosiły ślady specjalistycznej, podatnej na błędy ścieżki naprawczej zwanej łączeniem końców zależnym od polimerazy theta. Gdy wyłączono kluczowy enzym tej ścieżki, duplikacje niemal zniknęły, ale robaki zapłaciły wysoką cenę w płodności, co sugeruje, że ta sama ścieżka jest też potrzebna do ratowania pękniętych chromosomów, gdy brakuje TONSL. Inne eksperymenty wskazały na drugiego wykonawcę — proces przypominający „replicację indukowaną przez pęknięcie” (break-induced replication), w którym złamany koniec DNA używa nienaruszonego wzorca do skopiowania dużych odcinków sekwencji. Usunięcie helikazy sprzyjającej takim dalekosiężnym kopiowaniom zmniejszyło rozmiar duplikacji, nie zatrzymując ich całkowicie, co wzmocniło koncepcję, że przedłużona, słabo kontrolowana synteza DNA leży u podstaw tych zdarzeń.
Chromatyna jako cichy reżyser naprawy
Wiadomo, że TONSL wiąże określone chemiczne modyfikacje na białkach opakowujących świeżo zreplikowane DNA, co sugeruje, że pomaga odbudować chromatynę — strukturę, która owija i organizuje DNA — zaraz po replikacji. Autorzy wprowadzili subtelną zmianę w białku robaka osłabiającą to wiązanie z chromatyną. Robaki niosące tę pojedynczą zamianę aminokwasu wciąż tworzyły duplikacje, ale mniej i mniejsze, co wskazuje, że przyczepność TONSL do świeżej chromatyny bezpośrednio powstrzymuje wymkniętą się syntezę DNA w miejscach naprawy. W jego nieobecności pośrednie produkty naprawy mogą rozciągać się zbyt daleko, zanim zostaną w końcu zszyte przez podatną na błędy ścieżkę łączenia, pozostawiając zduplikowany blok zamiast czystej naprawy.
Wspólna obrona od robaków po rośliny
Aby sprawdzić, czy ta ochronna rola jest zachowana w innych organizmach, zespół przebadał mutant rośliny modelowej Arabidopsis thaliana pozbawiony zbliżonego białka TONSOKU. Już po kilku pokoleniach rośliny te zgromadziły uderzającą liczbę dużych duplikacji tandemowych, zwiększając rozmiar genomu w przybliżeniu o jeden procent na pokolenie — olbrzymia zmiana w skali ewolucyjnej. Miejsca łączeń DNA ponownie nosiły charakterystyczne krótkie nakładki i insercje związane z tą samą podatną na błędy ścieżką naprawczą, co sugeruje, że robaki i rośliny używają głęboko zachowanego systemu ukierunkowanego przez chromatynę, aby odsuwać pęknięcia związane z replikacją od wyników sprzyjających duplikacjom.
Co to oznacza dla nowotworów i stabilności genomu
Mówiąc najprościej, praca ta pokazuje, że TONSL i jego roślinny kuzyn działają jako kontrolerzy jakości siedzący na skrzyżowaniu kopiowania DNA i naprawy. Pomagając właściwie odbudować chromatynę po pęknięciu, utrzymują procesy naprawcze krótkimi i uporządkowanymi, zapobiegając temu, by długie odcinki DNA były kopiowane dwa razy z rzędu. Bez tej kontroli komórki nadal naprawiają pęknięcia, ale robią to przez nadmierne wydłużanie i następnie grubiańskie ponowne łączenie DNA, pozostawiając po sobie duplikacje tandemowe. Ponieważ podobne wzory duplikacji obserwuje się w kilku nowotworach ludzkich, w tym w guzach z defektami czynników związanych z replikacją, zrozumienie roli TONSL może ostatecznie pomóc wyjaśnić, dlaczego niektóre nowotwory nabywają tak silnie przekształcone genomy i zasugerować nowe drogi przewidywania lub wpływania na to, jak ich DNA będzie się zmieniać pod wpływem terapii.
Cytowanie: van Schendel, R., Romeijn, R., Kralemann, L.E.M. et al. TONSL suppresses polymerase theta-dependent tandem duplications through chromatin-guided repair. Nat Commun 17, 2875 (2026). https://doi.org/10.1038/s41467-026-70905-2
Słowa kluczowe: stabilność genomu, duplikacje tandemowe, naprawa DNA, chromatyna, TONSL