Clear Sky Science · pl
SMART: przestrzenna agregacja multi-omiczna z użyciem grafowych sieci neuronowych i uczenia metryk
Postrzeganie tkanek jako map sąsiedztw
Nasze ciało składa się z tętniących życiem sąsiedztw komórkowych, gdzie geny, białka i upakowanie DNA współdziałają w precyzyjnych lokalizacjach. Nowe mikroskopy i narzędzia sekwencjonowania potrafią obecnie odczytywać wiele z tych warstw molekularnych bezpośrednio w cienkich przekrojach tkanki, lecz przekształcenie tego potoku wielowarstwowych, przestrzennych danych w przejrzyste obrazy organizacji narządów stanowi ogromne wyzwanie obliczeniowe. W tym badaniu przedstawiono SMART — metodę komputerową, która pomaga naukowcom łączyć te złożone sygnały w szczegółowe mapy, pokazujące, gdzie żyją różne wspólnoty komórkowe i jak są rozmieszczone.
Dlaczego mapowanie sąsiedztw komórkowych jest trudne
Nowoczesne technologie „przestrzennych multi-omik” mogą mierzyć jednocześnie kilka rodzajów informacji molekularnej — takich jak RNA, białka powierzchniowe komórek oraz dostępność chromatyny — zachowując przy tym dokładne położenie każdego pomiaru w przekroju tkanki. Każdy rodzaj omiki daje inną perspektywę zachowania komórek, ale są one zaszumione, mają wysoką wymiarowość i nie układają się naturalnie w bezpośrednią zgodność. Ponadto komórki tego samego typu nie zawsze tworzą zwarte skupiska; mogą występować jako porozrzucane „wyspy” w obrębie narządu. Istniejące narzędzia programowe często albo pomijają układ przestrzenny, nadmiernie upraszczają relacje między omikami, albo mają trudności z obsługą bardzo dużych zbiorów danych, jakie potrafią wygenerować nowe instrumenty.
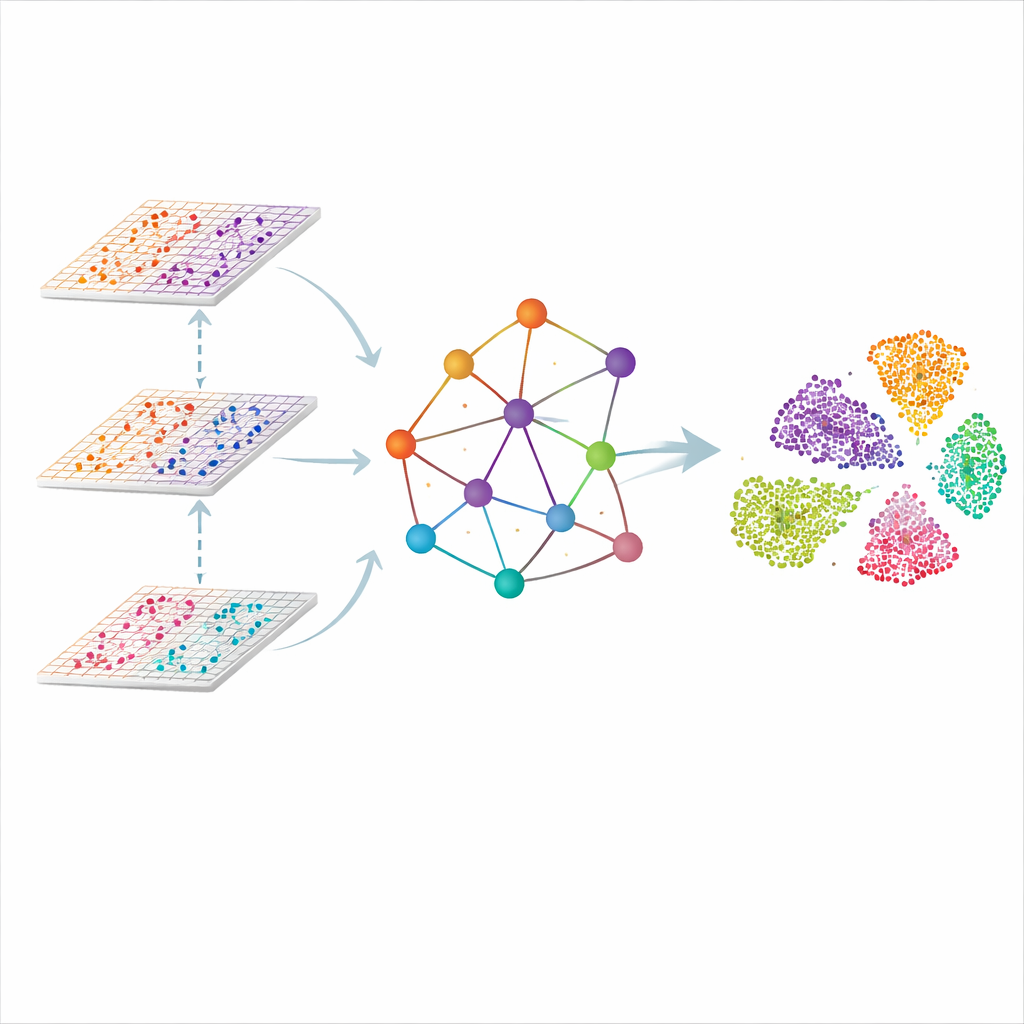
Graf tkanki, a nie tylko lista komórek
SMART podchodzi do problemu, traktując każde miejsce pomiaru w tkance jako punkt w sieci. Sąsiednie miejsca są łączone, tworząc graf przestrzenny, a odczyty molekularne z każdej omiki są najpierw skompresowane do mniejszego zestawu skoordynowanych cech, które wychwytują ogólne wzorce zamiast pojedynczych genów. Specjalny rodzaj sieci neuronowej zaprojektowany dla grafów przekazuje informacje wzdłuż krawędzi, pozwalając każdemu punktowi „słuchać” sąsiadów przy jednoczesnym śledzeniu wkładu poszczególnych omik. Rezultatem jest wspólna, niskowymiarowa reprezentacja, w której podobne regiony tkanki — takie jak odrębne warstwy mózgu czy strefy w węźle chłonnym — naturalnie grupują się razem.
Nauczanie modelu, co powinno być podobne
Samodzielne podążanie za fizycznymi sąsiadami nie wystarcza, ponieważ komórki tego samego typu mogą być od siebie odległe. SMART dodaje drugi składnik zapożyczony z systemów rozpoznawania twarzy: uczenie metryczne z użyciem tripletów. Dla każdego punktu metoda automatycznie znajduje inny punkt o bardzo podobnych wzorcach molekularnych („pozytywny”) oraz taki, który jest wyraźnie różny („negatywny”). Następnie dostosowuje wewnętrzną reprezentację tak, by pozytywne przykłady przyciągać bliżej, a negatywne odpychać dalej, nawet jeśli są od siebie daleko na preparacie tkankowym. Ta „przeciwstawna” operacja działa równolegle z krokiem rekonstrukcji, który wymusza, by SMART zachował kluczowe szczegóły każdej warstwy omiki, równoważąc ciągłość przestrzenną z molekularną specyfiką.
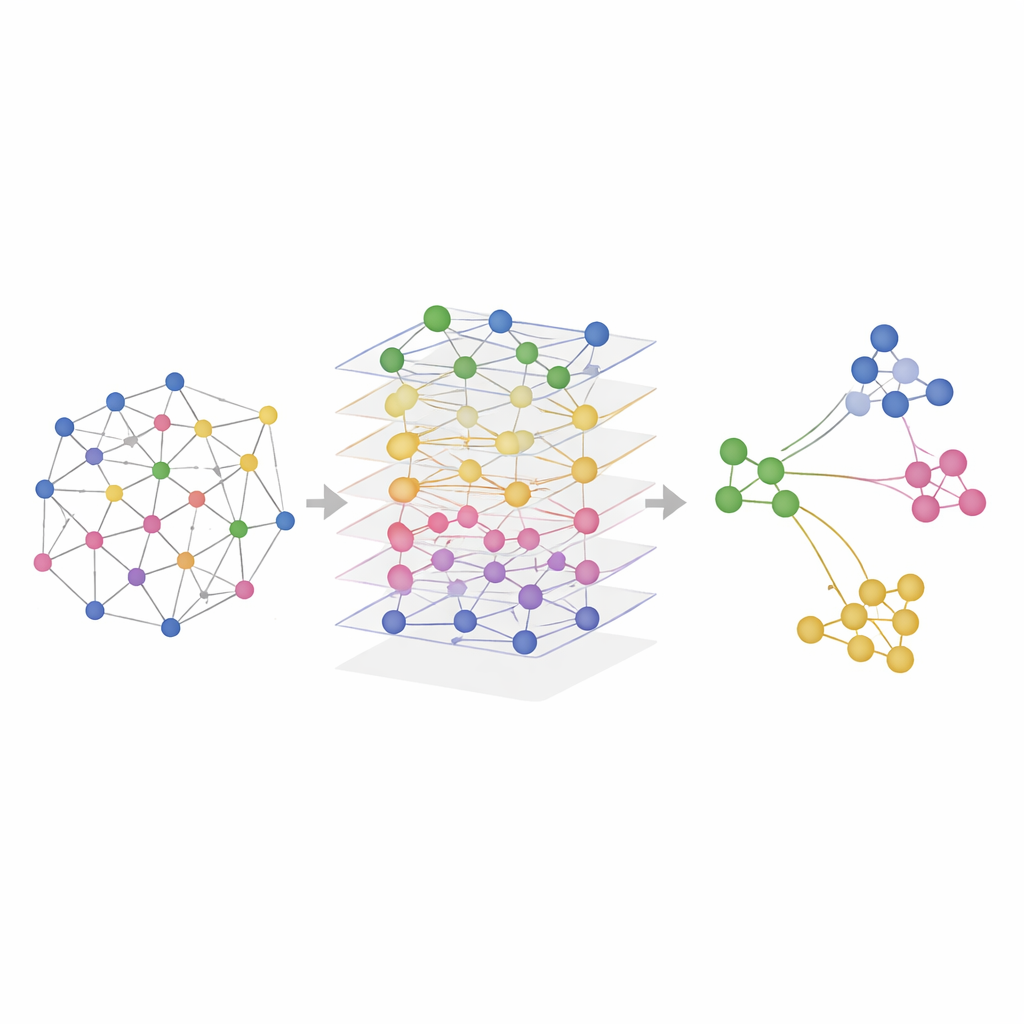
Testowanie SMART na rzeczywistych tkankach
Naukowcy przetestowali SMART zarówno na danych symulowanych, jak i na eksperymentach mierzących kombinacje RNA, białek i dostępności chromatyny w mózgach myszy, śledzionach myszy, ludzkich węzłach chłonnych i migdałkach. W kontrolowanych symulacjach, gdzie prawdziwe regiony przestrzenne były znane, SMART najdokładniej odtworzył wzorce zgodne z ground truth i zachował relacje obecne w każdej warstwie omiki. W rzeczywistych zbiorach danych SMART konsekwentnie identyfikował drobne struktury anatomiczne — takie jak specyficzne rejony mózgu czy strefy komórek odpornościowych w narządach limfoidalnych — ostrzej niż konkurencyjne metody, przy jednoczesnym utrzymaniu niskich wymagań obliczeniowych. Powiązana wersja, nazwana SMART-MS, rozszerza te pomysły na wiele przekrojów tkanki, wyrównując plastry z tego samego narządu i korygując techniczne różnice między eksperymentami.
Szybkie mapy dla kolejnej fali biologii przestrzennej
Mówiąc prosto, SMART to silnik do tworzenia map dla nowej generacji atlasów molekularnych. Poprzez połączenie modelowania w stylu sieciowym układu tkanki z wbudowanym poczuciem tego, co należy uznać za „podobne”, potrafi przemienić ogromne, nieuporządkowane zbiory przestrzennych pomiarów multi-omicznych w spójne mapy sąsiedztw organów. Umożliwia to badaczom łatwiejsze dostrzeganie, gdzie występują konkretne typy komórek i mikrośrodowiska, jak zmieniają się w czasie rozwoju lub choroby oraz jak łączą się nowe technologie eksperymentalne. W miarę jak dane przestrzenne będą rosnąć pod względem rozmiaru i złożoności, narzędzia takie jak SMART i SMART-MS będą kluczowe dla przekształcania surowych pomiarów w biologiczne wnioski.
Cytowanie: Du, Z., Chen, Q., Huang, W. et al. SMART: spatial multi-omic aggregation using graph neural networks and metric learning. Nat Commun 17, 2876 (2026). https://doi.org/10.1038/s41467-026-70821-5
Słowa kluczowe: przestrzenne multi-omiki, grafowe sieci neuronowe, mikrośrodowisko tkankowe, integracja danych, biologia pojedynczych komórek