Clear Sky Science · pl
Przeprojektowanie genów międzygatunkowych z wykorzystaniem informacji o ortologach i modelowania generatywnego
Dlaczego przeprojektowanie genów między gatunkami ma znaczenie
Nowoczesna biotechnologia często wymaga przenoszenia genów z jednego mikroorganizmu do innego, aby wytwarzać leki, enzymy lub narzędzia do oczyszczania środowiska. Tymczasem gen, który sprawnie funkcjonuje w swoim macierzystym mikrobie, może słabo działać w nowym gospodarzu i produkować niewiele białka. W tym artykule przedstawiono nowy system sztucznej inteligencji, OrthologTransformer, który uczy się od samej ewolucji, by przepisywać geny tak, by „brzmiały” jak rodzimy gen w innym gatunku, zwiększając ich wydajność i otwierając nowe możliwości dla technologii ekologicznych i przemysłu.
Ograniczenia dzisiejszych trików dostrajania genów
Przez dekady naukowcy polegali na strategii zwanej optymalizacją kodonów, aby pomóc obcym genom działać w nowych gospodarzach. Idea jest prosta: kod genetyczny ma wiele trzy-literowych „kodonów”, które kodują ten sam aminokwas, a różne gatunki preferują różne kodony. Tradycyjne narzędzia zamieniają rzadkie kodony na preferowane, nie zmieniając sekwencji aminokwasowej białka. Często to pomaga, ale pomija wiele innych cech istotnych dla działania genu, takich jak fałdowanie RNA, sygnały regulacyjne czy czas produkcji białka. W niektórych przypadkach nadmierna optymalizacja kodonów może wręcz obniżyć wydajność białka. Natura rozwiązuje adaptację międzygatunkową w znacznie bogatszy sposób: spokrewnione geny w różnych gatunkach, zwane ortologami, często wykazują zmiany aminokwasowe i niewielkie insercje lub delecje, a także zamiany kodonów, zachowując jednocześnie ogólną funkcję.
Nauka odgrywek natury w przepisaniu genów
OrthologTransformer traktuje przeprojektowanie genów jak rodzaj tłumaczenia językowego: mając sekwencję DNA z jednej bakterii, „tłumaczy” ją na to, jak ten gen prawdopodobnie wyglądałby w innym gatunku. Model opiera się na architekturze Transformer używanej we współczesnych narzędziach językowych, ale tutaj operuje na kodonach zamiast na słowach. Trenuje się go na milionach naturalnie sparowanych genów ortologicznych z ponad dwóch tysięcy gatunków bakterii, z dodatkowymi tokenami informującymi, z którego i na który gatunek dokonuje się konwersja. Widząc, jak ewolucja już wyważyła funkcję i adaptację do gospodarza, system uczy się, kiedy wystarczą proste zamiany kodonów, a kiedy tolerowane są subtelne zmiany aminokwasowe lub korekty długości. W testach obejmujących 45 gatunków bakterii i setki kombinacji źródło–cel, przeprojektowane przez AI geny bardziej przypominały rodzime ortologi celu niż zarówno konwencjonalna optymalizacja kodonów, jak i wiodący neuronowy optymalizator kodonów, przy jednoczesnym zachowaniu wysokiego podobieństwa na poziomie białka. 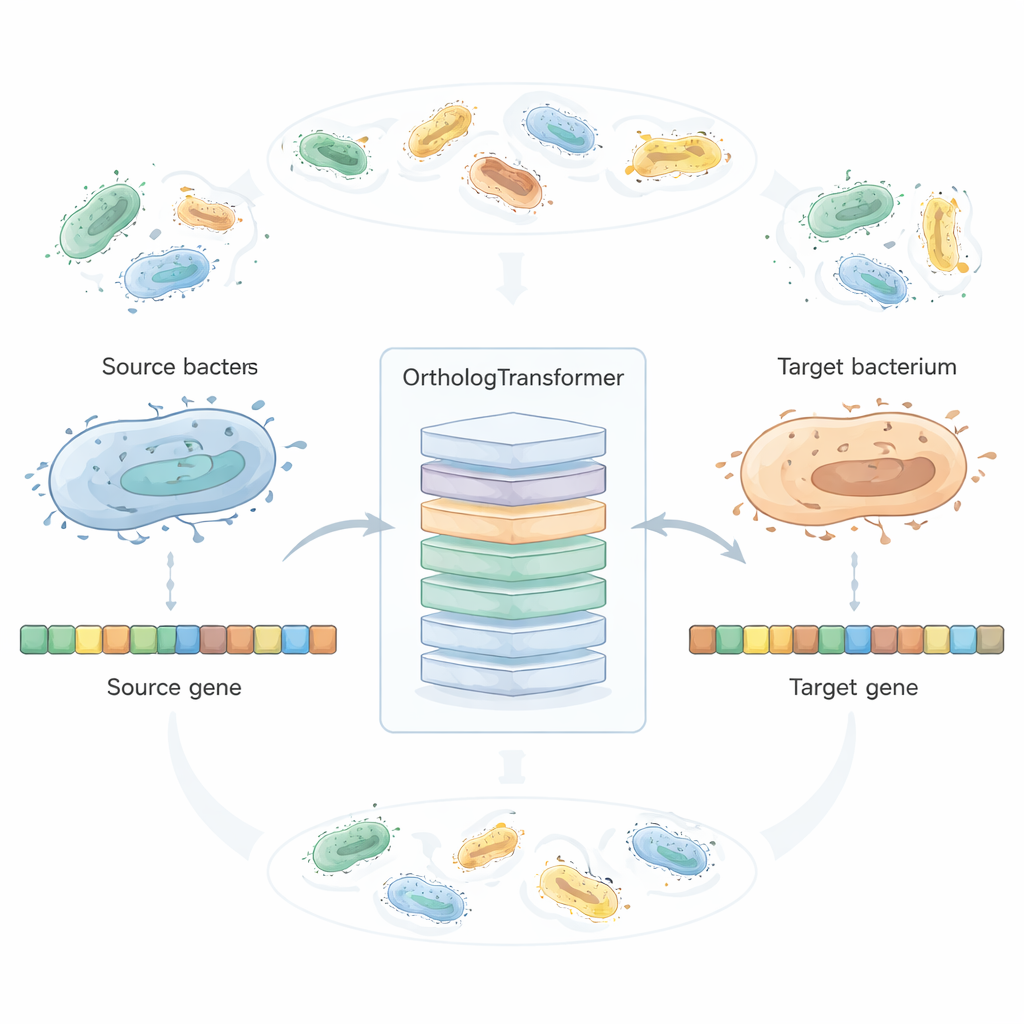
Wykorzystanie zaprojektowanych przez AI enzymów jedzących plastik
Aby pokazać, że to nie tylko trik obliczeniowy, zespół skupił się na PETazie, enzymie z bakterii Ideonella sakaiensis, który potrafi rozkładać tworzywo PET, stosowane w większości butelek. Ideonella rośnie wolno i nie nadaje się idealnie do zastosowań przemysłowych, więc badacze poprosili OrthologTransformer o przepisanie genu PETazy dla szybciej rosnącego gospodarza, Bacillus subtilis. Wygenerowali panel dwunastu przeprojektowanych wariantów genu, eksplorując różne ustawienia szkolenia i dodatkową procedurę poszukiwania, która przesuwała sekwencje w stronę bakteryjnego składu DNA charakterystycznego dla Bacillusa oraz korzystnych struktur RNA. Pomimo że niektóre warianty zawierały wiele zmian w DNA i kilka substytucji aminokwasowych, modele komputerowe przewidywały zachowanie rdzennego kształtu 3D enzymu. Gdy te projekty zbudowano i przetestowano w żywych komórkach Bacillusa, kilka z nich produkowało duże ilości wydzielanej PETazy, a wszystkie wykazały mierzalną aktywność rozkładu plastiku.
Projekt AI, który przewyższa standardową optymalizację
Wyjątkowy okazał się jeden z zaprojektowanych przez AI wariantów o nazwie AI-L2. Komórki Bacillusa niosące ten gen wydzielały szczególnie duże ilości PETazy i generowały w przybliżeniu trzykrotnie więcej produktu rozkładu plastiku niż jakikolwiek inny szczep w siedmiodniowym teście, oraz około dziesięciokrotnie więcej niż typowe kontroly z optymalizacją kodonów, mierzony po produktach reakcji. Zdjęcia mikroskopowe filmów PET wystawionych na działanie komórek AI-L2 ujawniły głębokie zagłębienia i dziury tam, gdzie plastik został zjedzony, znacznie bardziej dramatyczne niż w innych warunkach. Szczegółowe testy enzymu wykazały, że wersja PETazy AI-L2 nie tylko była produkowana bardziej wydajnie, ale też szybciej przetwarzała substrat, dając wyższą efektywność katalityczną niż enzymy pierwotne i z optymalizacją kodonów. Równoległy eksperyment w Escherichia coli pokazał, że wersja PETazy zaprojektowana przez OrthologTransformer, nawet gdy zmieniała jedynie użycie kodonów, a nie sekwencję aminokwasową, nadal przewyższała gen zoptymalizowany metodą opartą na częstotliwości kodonów, co podkreśla, że model wychwytuje subtelne, specyficzne dla gospodarza preferencje, które tradycyjne metody pomijają. 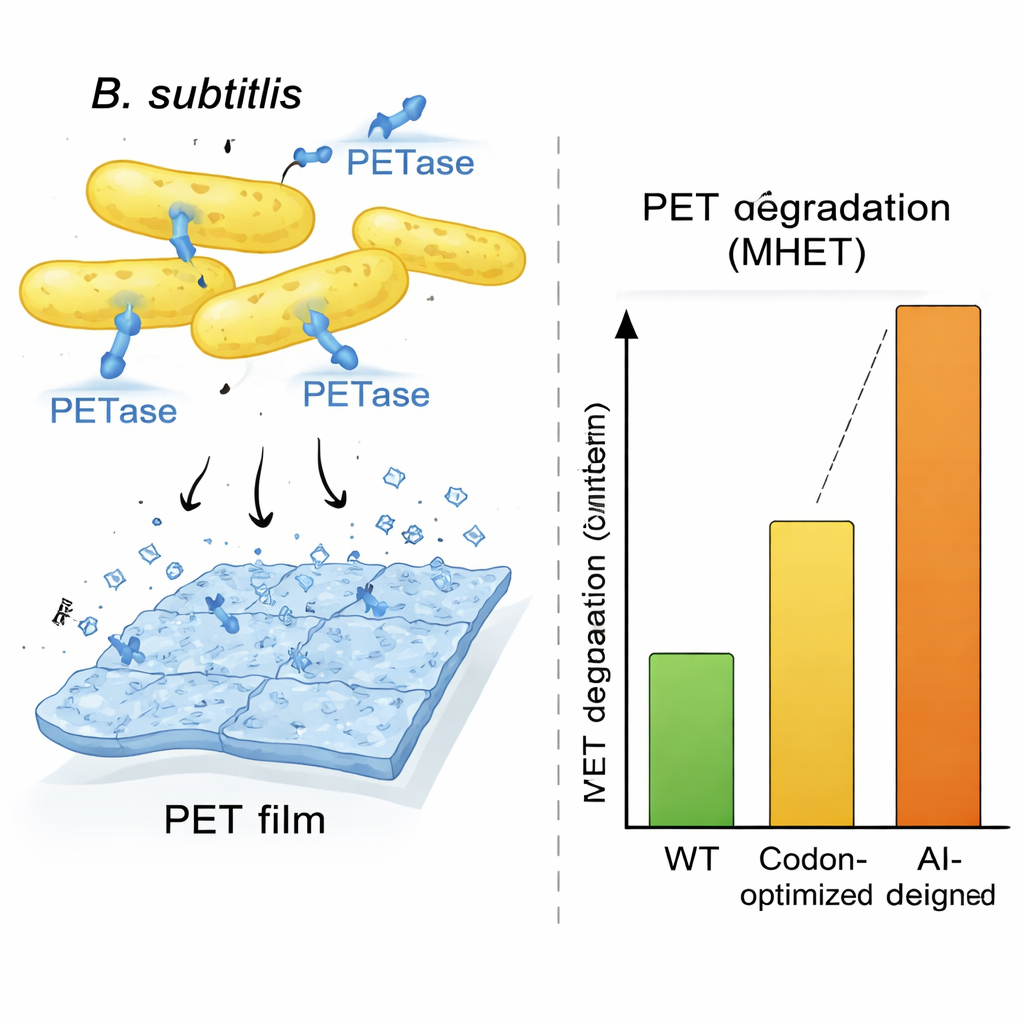
Co to oznacza dla przyszłej biologii i technologii
Mówiąc prościej, OrthologTransformer działa jak ekspert-tłumacz, który nie tylko przepisuje „ortografię” genu dla nowego mikroba, lecz także wprowadza drobne, inspirowane ewolucją poprawki do samego „zdania”, gdy wie, że będą bezpieczne lub korzystne. Ucząc się bezpośrednio z tego, jak geny naturalnie adaptowały się w tysiącach gatunków bakterii, może proponować przeprojektowane DNA, które działa lepiej w nowych gospodarzach niż projekty ograniczone do zamiany kodonów. Udane stworzenie silniejszego enzymu rozkładającego plastik w Bacillus subtilis sugeruje, że takie prowadzone przez AI przeprojektowanie genów może przyspieszyć rozwój biokatalizatorów przemysłowych, mikroorganizmów do oczyszczania środowiska, a w przyszłości nawet terapii genowych, pomagając organizmom czytać i wykorzystywać obce geny tak, jakby były własne.
Cytowanie: Akiyama, M., Tashiro, M., Huang, Y. et al. Cross-species gene redesign leveraging ortholog information and generative modeling. Nat Commun 17, 2120 (2026). https://doi.org/10.1038/s41467-026-69966-0
Słowa kluczowe: przeprojektowanie genów, biologia syntetyczna, geny ortologiczne, AI w biotechnologii, enzymy degradowania plastiku