Clear Sky Science · pl
Nieliniowy indeks selekcji genomowej przyspiesza wielowymaiarową poprawę plonów
Mądrzejsza hodowla dla głodniejszego świata
W miarę jak rośnie liczba ludności na świecie, a klimat staje się mniej przewidywalny, hodowcy roślin muszą szybciej niż kiedykolwiek poprawiać równocześnie kilka cech upraw — takich jak plon, wysokość i czas kwitnienia. W tym artykule przedstawiono nowe narzędzie matematyczne, które pomaga hodowcom osiągnąć to zadanie, wykorzystując informacje DNA w bardziej realistyczny sposób, uwzględniając nie tylko indywidualne efekty genów, lecz także ich wzajemne interakcje. Podejście to obiecuje przyspieszyć tworzenie lepszych odmian kukurydzy i pszenicy bez konieczności pomiaru każdej rośliny w polu.
Dlaczego łączenie wielu cech jest takie trudne
Hodowców rzadko interesuje tylko jedna cecha. Na przykład chcą wyższych plonów ziarna, ale też niższych, bardziej odpornych roślin, które kwitną we właściwym czasie. Klasyczne „indeksy selekcyjne” łączą kilka cech w jedną ocenę służącą do porządkowania roślin. Tradycyjnie te indeksy zakładają, że każda cecha przyczynia się prostoliniowo i że efekty różnych cech się dodają. Rzeczywista biologia jest bardziej złożona: cechy wzajemnie na siebie wpływają i mogą istnieć punkty optymalne, gdzie „więcej” nie oznacza lepiej. Ignorowanie tych nieliniowych interakcji może spowalniać postęp genetyczny, a nawet kierować hodowlę w niewłaściwą stronę.
Od prostych linii do elastycznych krzywych
Wcześniejsze narzędzia genomowe pozwalały hodowcom korzystać z markerów DNA rozmieszczonych w całym genomie do przewidywania, jak dobre będą potomstwo danej rośliny, co doprowadziło do tzw. liniowych indeksów selekcji genomowej. Działają one dobrze, gdy efekty genów są głównie addytywne. Autorzy rozszerzają bardziej elastyczną, starszą ideę — kwadratowy fenotypowy indeks selekcyjny, który już uwzględniał wyrazy kwadratowe i interakcje między cechami — na erę danych genomowych. Ich nowe narzędzie, nazwane Kwadratowym Genomicznym Indeksem Selekcyjnym (QGSI), wykorzystuje przewidywane genomowe wartości hodowlane i łączy je przy pomocy wyrazów liniowych oraz krzywych (kwadratowych). Pozwala to indeksowi uchwycić złożone wzorce, takie jak interakcje gen–gen i optymalne kombinacje cech, nawet gdy pomiary polowe nie są dostępne w każdym cyklu.
Testowanie nowego indeksu
Aby sprawdzić, czy ta dodatkowa złożoność się opłaca, badacze porównali QGSI z liniowymi i kwadratowymi indeksami korzystającymi wyłącznie z danych polowych oraz z liniowymi indeksami genomowymi, które używają DNA, lecz pozostają proste. Przeprowadzili symulacje komputerowe hodowli kukurydzy przez 10 cykli selekcji i przeanalizowali także dwa rzeczywiste zbiory danych kukurydzy oraz pięć zbiorów pszenicy z międzynarodowych programów hodowlanych. Testowano dwie metody przewidywania wartości genetycznej z DNA: standardowy model addytywny i bardziej elastyczny model jądrowy Gaussa, który może wychwycić subtelne interakcje genów. W tych warunkach QGSI konsekwentnie dawał większe odpowiedzi selekcyjne — czyli większą ogólną poprawę cech — niż indeksy liniowe i zazwyczaj przewyższał także kwadratowy indeks fenotypowy.
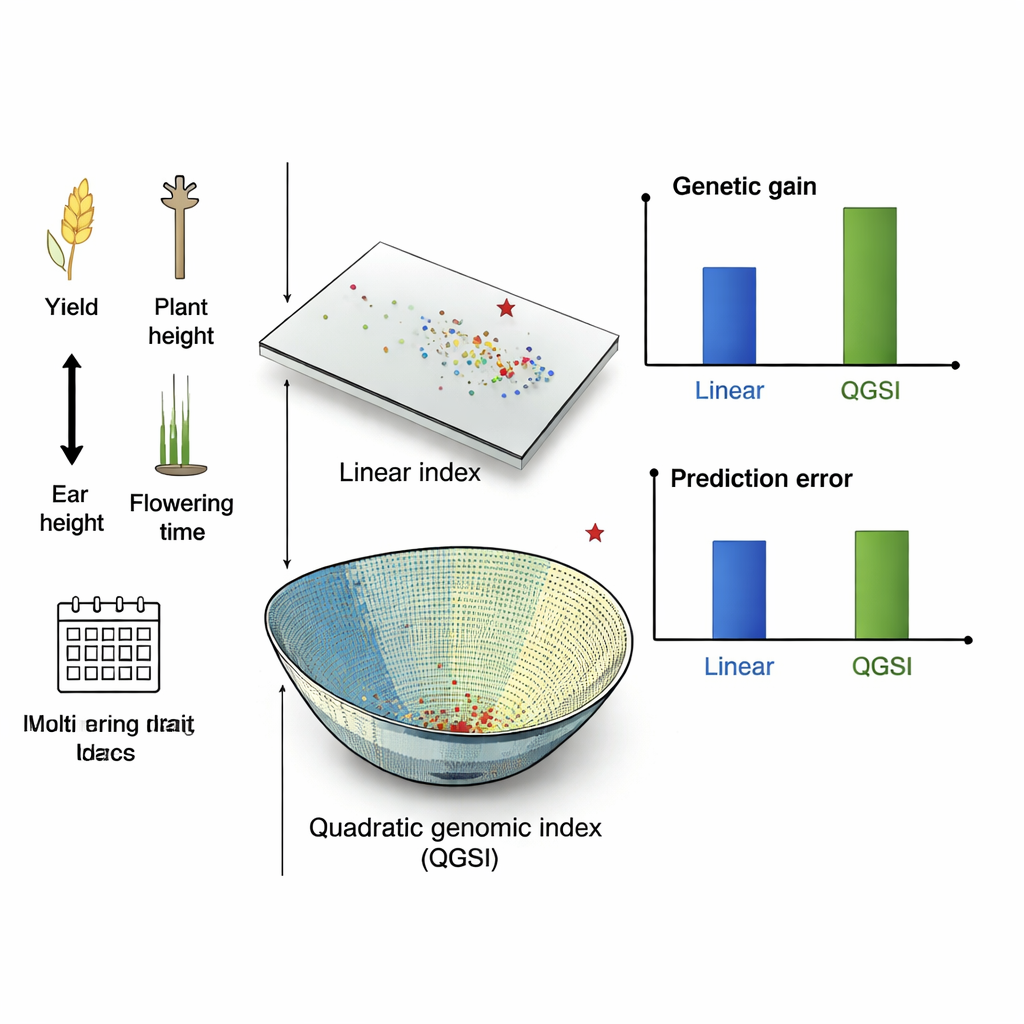
Lepsze zyski, mniej błędów, większa równowaga
W symulowanych cyklach kukurydzy QGSI zapewnił najwyższe zyski, wyprzedzając zarówno liniowe indeksy genomowe, jak i kwadratowe indeksy oparte jedynie na pomiarach polowych. Miało to też tendencję do niższego błędu predykcji, co oznacza, że jego oceny były bardziej wiarygodnym przewodnikiem przy wyborze rodziców. W rzeczywistych populacjach kukurydzy z Meksyku i Zimbabwe QGSI osiągnął o 80–90% wyższe zyski niż liniowe indeksy genomowe przy równoczesnej poprawie kilku cech. W próbach pszenicy prowadzonych w różnych warunkach nawadniania i opadów wzór był podobny: indeksy kwadratowe przewyższały liniowe, a połączenie QGSI z modelem jądrowym Gaussa przyniosło najsilniejsze i najbardziej stabilne ulepszenia między środowiskami, zwłaszcza dla plonu ziarna przy utrzymaniu wysokości roślin i czasu kwitnienia w akceptowalnych zakresach.
Co to oznacza dla przyszłych upraw
Dla osób nietechnicznych kluczowy przekaz jest taki, że hodowcy mają teraz bardziej realistyczny system ocen, który odzwierciedla, jak geny i cechy rzeczywiście ze sobą oddziałują, zamiast zmuszać je do prostoliniowego modelu. Autorzy zalecają stosowanie kwadratowego fenotypowego indeksu, gdy w początkowych etapach dostępne są jedynie dane polowe, a przejście na QGSI po uzyskaniu danych genomowych i wprowadzeniu szybkich cykli selekcji. Dzięki lepszemu uchwyceniu nieliniowych zależności genetycznych QGSI może przyspieszyć wielowymaiarową poprawę upraw i pomóc dostarczyć nowe odmiany kukurydzy i pszenicy o wyższych plonach, większej odporności i lepszym przystosowaniu do trudnych warunków.
Cytowanie: Jesús Cerón-Rojas, J., Montesinos-López, O.A., Montesinos-López, A. et al. Nonlinear genomic selection index accelerates multi-trait crop improvement. Nat Commun 17, 1991 (2026). https://doi.org/10.1038/s41467-026-69890-3
Słowa kluczowe: selekcja genomowa, hodowla roślin, kukurydza, pszenica, poprawa wielu cech