Clear Sky Science · pl
Warianty alleliczne genów Avr w wysoce zjadliwych szczepach wyjaśniają ciężkie epidemie rdzy łodyg pszenicy
Dlaczego rdza pszenicy ma znaczenie dla wszystkich
Rdza łodyg pszenicy to wiekowa choroba upraw, która może ogołocić pola z plonów i zagrozić światowym zapasom żywności. W ciągu ostatnich dwóch dekad pojawiły się nowe, wyjątkowo agresywne formy tego grzyba, które spowodowały poważne epidemie w Afryce i Europie, omijając odmiany pszenicy hodowane pod kątem odporności. W badaniu postawiono podstawowe, lecz kluczowe pytanie: co dokładnie zmieniło się w tych nowych szczepach grzyba, co pozwoliło im przełamać obronę pszenicy i rozprzestrzeniać się tak szeroko?
Jak rośliny i grzyby toczą molekularne chowanego
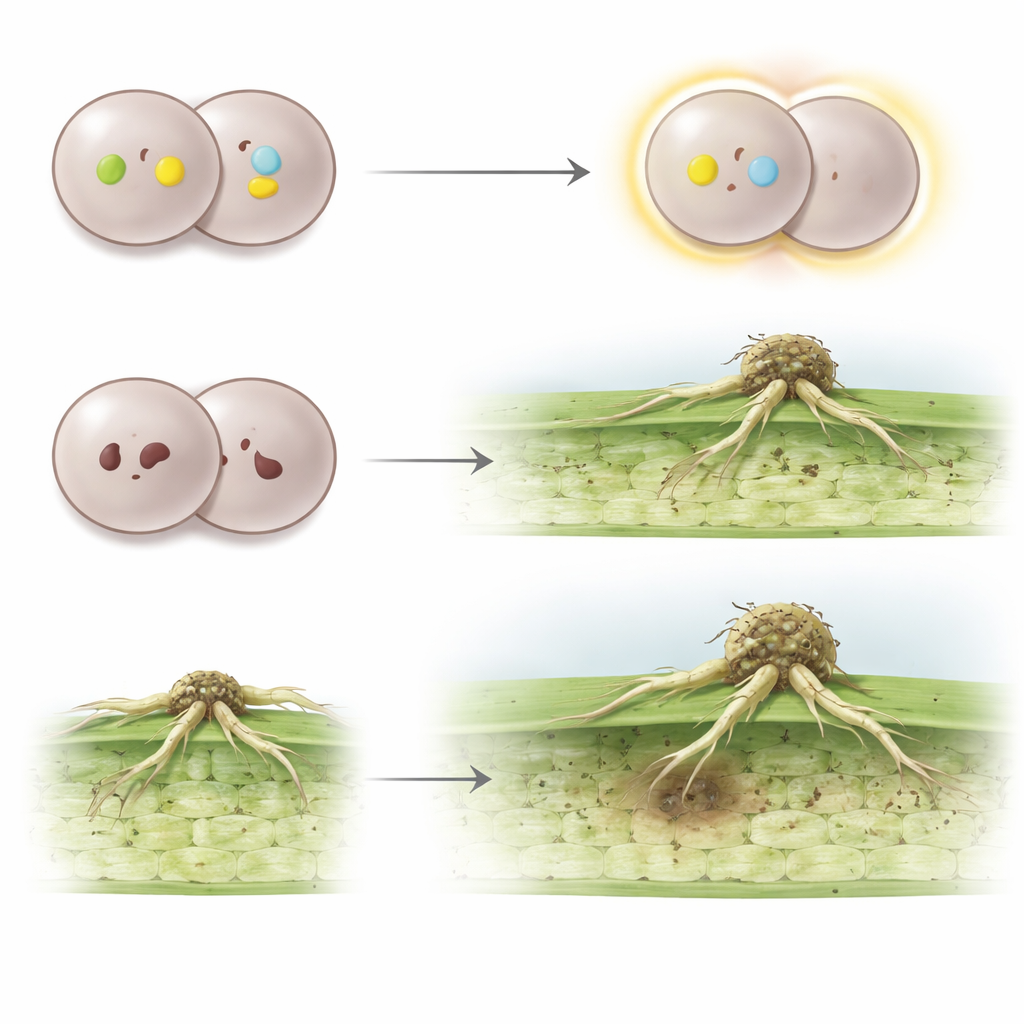
Pszenica broni się za pomocą genów odporności, które rozpoznają specyficzne cząsteczki produkowane przez najeżdżające grzyby. Gdy gen odporności wykryje jedną z tych grzybowych cząsteczek, wywoływana jest reakcja immunologiczna, która zatrzymuje infekcję. Grzyb z kolei nosi odpowiadające „geny awirulencji”, które kodują właśnie te cząsteczki, które roślina próbuje rozpoznać. Jeśli grzybowa cząsteczka jest obecna i nienaruszona, odmiana pszenicy z dopasowanym genem odporności może zablokować chorobę. Jeśli jednak grzyb usunie lub zmieni tę cząsteczkę, może obejść system nadzoru rośliny. Cykliczne pojawianie się nowych ras rdzy odzwierciedla tę genetyczną wojnę zbrojeń między genami awirulencji grzyba a genami odporności pszenicy.
Odczytywanie genomu grzyba chromosom po chromosomie
Grzyb wywołujący rdzę łodyg jest nietypowy, ponieważ każdy osobnik nosi dwa odrębne jądra komórkowe, z których każde zawiera pełny genom. Utrudnia to ustalenie, które wersje genów awirulencji występują. Autorzy wykorzystali zaawansowane sekwencjonowanie długich odczytów DNA oraz trójwymiarowe mapowanie chromosomów, aby uzyskać kompletne mapy genomów, jądro po jądrze, dla dwóch szczepów epidemicznych: ETH2013‑1, odpowiedzialnego za dużą epidemię w Etiopii w 2013 roku, oraz ITA2018‑1, należącego do linii, która rozprzestrzeniła się po Europie po pierwszym wybuchu na Sycylii w 2016 roku. Wykazali, że cztery jądra z tych dwóch izolatów tworzą cztery unikalne „haplotypy” genomowe, różne od wcześniej badanych szczepów referencyjnych, co daje znacznie jaśniejszy obraz różnorodności genetycznej grzyba i jego drzewa rodowego.
Wskazanie zmian genowych stojących za ostatnimi epidemiami
Mając te kompletne genomy, zespół systematycznie przeanalizował znane geny awirulencji powiązane z ważnymi genami odporności pszenicy. Sklasyfikowali dziesiątki wariantów sekwencji, w tym zmiany liczby kopii genów, subtelne mutacje zmieniające pojedynczy aminokwas oraz przypadki, w których gen został całkowicie usunięty. Przy użyciu kombinacji testów na komórkach roślinnych, roślin modelowych oraz systemu dostarczania opartego na wirusie sprawdzili, czy każdy wariant grzyba jest wciąż rozpoznawany przez odpowiadający mu gen odporności pszenicy. W sumie funkcjonalnie scharakteryzowali 22 nowe warianty genów awirulencji. Pozwoliło im to wyjaśnić na poziomie molekularnym, dlaczego niektóre linie rdzy mogą infekować określone odmiany pszenicy, podczas gdy inne nie.
Jak jeden brakujący gen pomógł szczepowi opanować Europę
Jednym z uderzających odkryć jest rasa znana jako TTRTF, która spowodowała śmiertelną epidemię na Sycylii, a później stała się szeroko rozpowszechniona w Europie. W wielu polach z pszenicą durum rosnące odmiany miały gen odporności zwany Sr13b, który miał je chronić. Naukowcy odkryli, że włoski szczep epidemiczny ma czyste usunięcie odpowiadającego genu awirulencji, AvrSr13, w obu swoich jądrach. Bez tego genu grzyb przestaje produkować charakterystyczną cząsteczkę, którą system odporności oparty na Sr13 ma wykrywać, co pozwala TTRTF infekować pszenicę z Sr13b bez przeszkód. Ten sam szczep nosi także zmodyfikowaną formę innego genu awirulencji, AvrSr35, co wyjaśnia jego zdolność do ominięcia drugiego genu odpornościowego, Sr35.
Budowanie genetycznego atlasu, by wyprzedzać rdzę
Ponad wyjaśnieniem ostatnich epidemii, badanie tworzy „atlas genów Avr” dla grzyba rdzy łodyg: mapę odniesienia, która łączy konkretne warianty genów awirulencji z ich zachowaniem wobec kluczowych genów odporności pszenicy. Ten atlas można wykorzystać do interpretacji sekwencji DNA zbieranych ze spór rdzy w terenie oraz do przewidywania, na podstawie samej sekwencji, które odmiany pszenicy mogą być zagrożone. Dla hodowców roślin i zespołów monitorujących choroby oznacza to, że mogą wybierać geny odporności, których dominujące populacje rdzy wciąż nie potrafią ominąć, i szybko wykrywać pojawienie się nowych, bardziej niebezpiecznych wariantów.
Co to oznacza dla ochrony przyszłych zbiorów
Mówiąc prosto, praca ta pokazuje dokładnie, jak niedawne szczepy rdzy rozpracowały genetyczne zamki niektórych z najlepszych systemów ochronnych pszenicy. Dzięki ujawnieniu, które grzybowe klucze uległy zmianie, a które roślinne zamki wciąż działają, badanie dostarcza mapy drogowej do projektowania odmian pszenicy o dłużej utrzymującej się odporności oraz do używania przenośnych narzędzi DNA do śledzenia niebezpiecznych typów rdzy, gdy przemieszczają się po świecie. Ostatecznie zrozumienie tych molekularnych szczegółów to praktyczny krok w kierunku zabezpieczenia zbiorów pszenicy wobec ewoluującego patogenu.
Cytowanie: Spanner, R.E., Henningsen, E.C., Langlands-Perry, C. et al. Allelic variation of Avr genes in highly virulent strains explains severe wheat stem rust epidemics. Nat Commun 17, 2718 (2026). https://doi.org/10.1038/s41467-026-69508-8
Słowa kluczowe: rdza łodyg pszenicy, odporność roślin, geny awirulencji, sekwencjonowanie genomu, monitoring chorób upraw