Clear Sky Science · pl
Odkrycie peptydów przeciwdrobnoustrojowych celujących w Acinetobacter baumannii za pomocą wstępnie wytrenowanego i dopracowanego potrójnego procesu uczenia się na małej liczbie próbek
Dlaczego to ma znaczenie dla zdrowia codziennego
Infekcje oporne na leki rosną tak szybko, że do połowy wieku mogą zabijać więcej osób rocznie niż nowotwory. Jednym z najbardziej niepokojących sprawców jest Acinetobacter baumannii — odporny na leczenie drobnoustrój szpitalny, który ignoruje wiele antybiotyków i często zakaża pacjentów podłączonych do respiratorów. W badaniu tym pokazano, jak naukowcy połączyli sztuczną inteligencję z eksperymentami laboratoryjnymi, aby szybko odkryć nowe, niewielkie kandydaty leków, które mogą zabijać tę bakterię przy znacznie mniejszym uszkodzeniu organizmu niż nasze obecne leki ostatniej szansy.
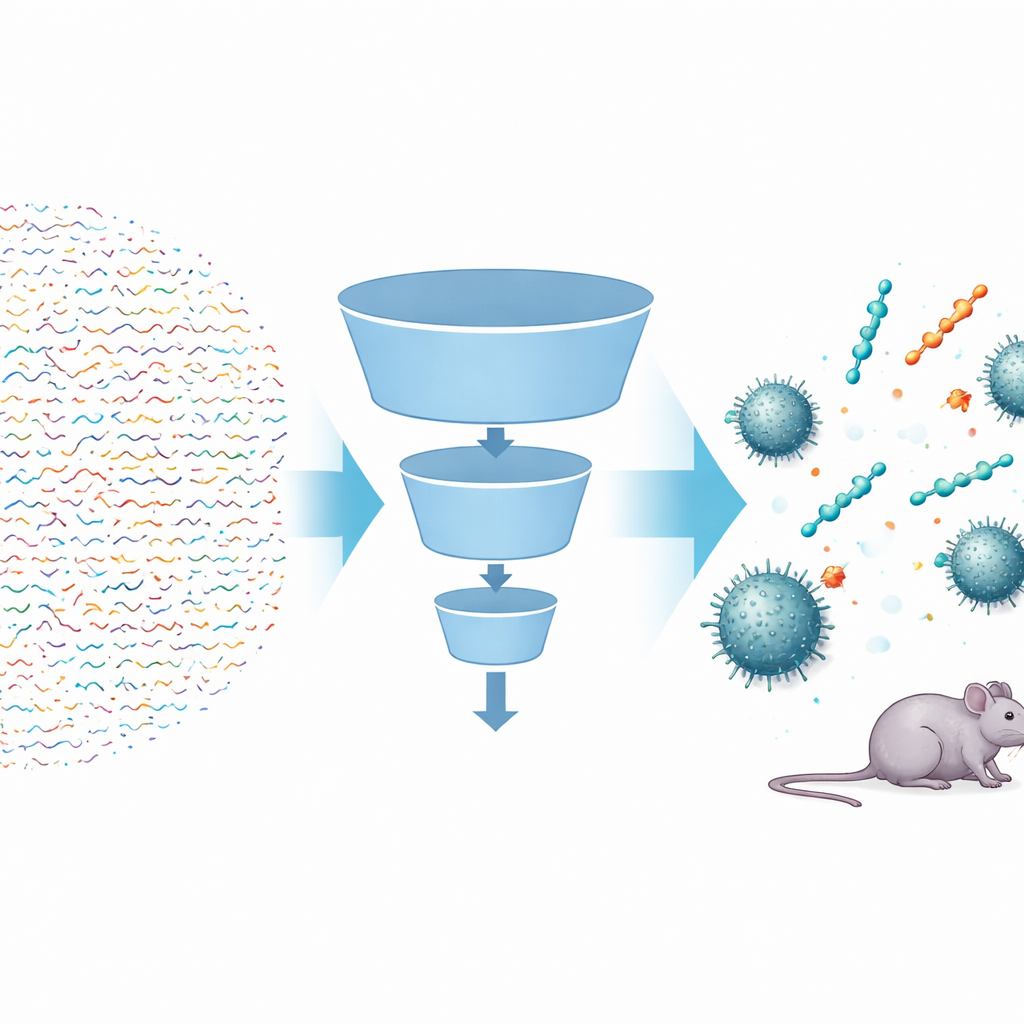
Szpitalny superbakter, którego trudno zabić
Acinetobacter baumannii to bakteria Gram-ujemna, która rozwija się na oddziałach intensywnej terapii, szczególnie u pacjentów korzystających z respiratorów. Jej wytrzymała zewnętrzna powłoka i szybko ewoluujące geny czynią ją odporną na wiele standardowych antybiotyków. Obecnie jedną z niewielu pozostałych opcji jest lek zwany polymyksyną B, ale może on poważnie uszkadzać nerki, a bakteria może nadal rozwijać oporność. Równocześnie obiecującą klasą są krótkie fragmenty białek zwane peptydami przeciwdrobnoustrojowymi; badano je przeciw innym mikrobom, lecz bardzo niewiele z nich działa specyficznie i skutecznie przeciw A. baumannii. Tradycyjne metody prób i błędów są po prostu zbyt wolne i kosztowne, by przesiać astronomicznie dużą liczbę możliwych krótkich sekwencji peptydowych.
Wykorzystanie inteligentnych algorytmów do przeszukania ogromnej przestrzeni
Naukowcy zbudowali wieloetapowy proces oparty na sztucznej inteligencji, nazwany FSLSMEP, aby przeskanować całe biblioteki krótkich peptydów — o długościach sześciu, siedmiu lub ośmiu reszt — obejmujące dziesiątki miliardów kandydatów. Problem polegał na tym, że mieli tylko 148 znanych peptydów działających przeciw A. baumannii, co jest stanowczo za mało dla standardowych metod uczenia maszynowego. Aby to obejść, zaczęli od potężnego modelu wstępnie wytrenowanego, który „przeczytał” już setki milionów naturalnych sekwencji białkowych i nauczył się ogólnych reguł dotyczących zachowania takich cząsteczek. Następnie dopracowali ten model w dwóch etapach: najpierw na większym zbiorze peptydów aktywnych przeciw spokrewnionej bakterii Pseudomonas aeruginosa, a ostatecznie na skąpych danych o A. baumannii. W trakcie tego procesu trzy powiązane moduły — jeden do odróżniania prawdopodobnych od nieprawdopodobnych peptydów, drugi do ich rankingowania i trzeci do szacowania siły działania — działały jak kolejne filtry w lejkowatym systemie.
Od przewidywań komputerowych do sukcesów w probówce
Po wstępnym odrzuceniu najmniej obiecujących peptydów przy użyciu prostych reguł chemicznych, zespół wprowadził do swojej procedury niemal cztery miliony kandydatów. Klasyfikator odrzucił większość sekwencji, które nie wyglądały na przeciwdrobnoustrojowe; model rankingowy faworyzował te, których cechy sugerowały silną aktywność; a model regresyjny przewidywał minimalne stężenie leku potrzebne do zahamowania wzrostu bakterii. Z sześćdziesięciu czterech milionów heksapeptydów system zaproponował zaledwie dziesięć najlepszych kandydatów. Po syntezie i testach laboratoryjnych dziewięć z nich wykazało rzeczywistą aktywność przeciwbakteryjną — co jest imponującym wskaźnikiem trafień w odkrywaniu leków. Te same wytrenowane modele zastosowano później, bez ponownego trenowania, do znacznie większych przestrzeni heptapeptydów i oktapeptydów, z których badacze wybrali kolejne wysoko ocenione sekwencje do testów. Ponownie większość okazała się aktywna, w tym heptapeptydy tak silne jak polymyksyna B przeciw niektórym szczepom.
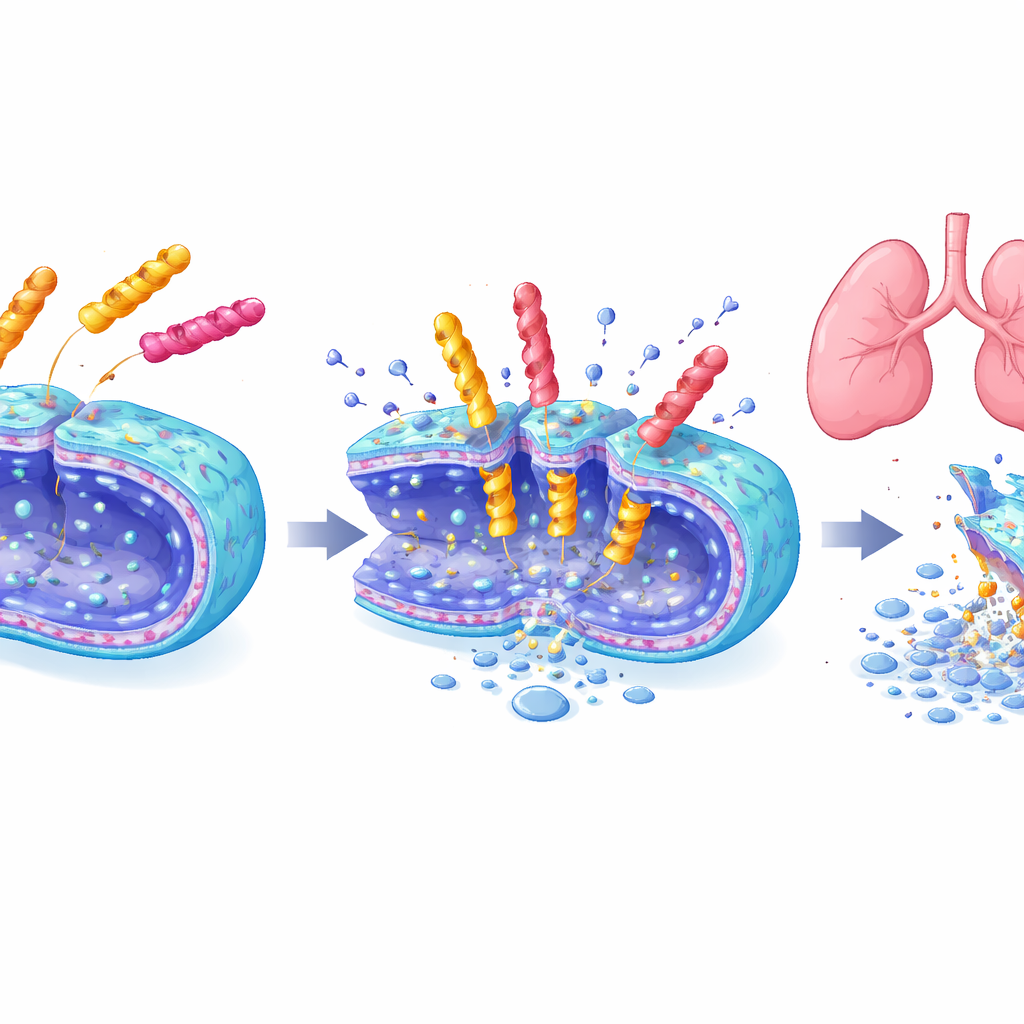
Silne środki o łagodniejszym działaniu
Trzy prowadzące peptydy — po jednym z bibliotek sześciu, siedmiu i ośmiu reszt — zbadano szczegółowo. Szybko eliminowały populacje A. baumannii w ciągu minut do godzin, uszkadzały błony bakteryjne widoczne w mikroskopii elektronowej i działały też przeciw kilku innym groźnym mikrobom. Jednocześnie powodowały niewielkie szkody w hodowanych komórkach ssaczych i w czerwonych krwinkach, w przeciwieństwie do niektórych istniejących peptydów przeciwdrobnoustrojowych. W długoterminowych testach ekspozycji bakterie nie rozwijały łatwo oporności na te nowe cząsteczki, podczas gdy oporność na polymyksynę B rosła szybko. Co najistotniejsze, w modelu myszy z zapaleniem płuc inhalacyjna dawka heptapeptydu EME7(7) oczyściła zakażenie płuc równie skutecznie jak polymyksyna B, ale nie uszkodziła nerek, podczas gdy polymyksyna B wywołała wyraźne uszkodzenia nerek i wzrost markerów stresu nerkowego we krwi.
Co to oznacza dla przyszłych leków
Ta praca pokazuje, że starannie zaprojektowany proces AI potrafi przekształcić maleńki, niepełny zbiór danych w potężny silnik odkrywania nowych peptydów przeciwdrobnoustrojowych. Poprzez połączenie szerokiego wstępnego trenowania, etapowego dopracowywania i wielowarstwowego filtrowania, badacze efektywnie przeszukali całe biblioteki krótkich peptydów i znaleźli kandydatów, którzy zarówno zwalczają groźny szpitalny superbakter, jak i wydają się bezpieczniejsi dla organów wewnętrznych. Ta sama strategia powiodła się również w znajdowaniu peptydów aktywnych przeciw grzybowi Candida albicans, co sugeruje, że można ją ponownie wykorzystać do poszukiwania wielu innych typów terapeutycznych peptydów. Dla pacjentów podejście to może ostatecznie przełożyć się na nowe leki leczące uporczywe infekcje bez ciężkich skutków ubocznych i szybkiego rozwoju oporności, które nękają dzisiejsze antybiotyki ostatniej linii.
Cytowanie: Huang, J., Zhang, W., Wang, A. et al. Discovery of antimicrobial peptides targeting Acinetobacter baumannii via a pre-trained and fine-tuned few-shot learning-based pipeline. Nat Commun 17, 2475 (2026). https://doi.org/10.1038/s41467-026-69306-2
Słowa kluczowe: peptydy przeciwdrobnoustrojowe, oporność na antybiotyki, Acinetobacter baumannii, odkrywanie leków przy użyciu uczenia maszynowego, few-shot learning