Clear Sky Science · pl
Heterogeniczne wielokrotne kopie wariantów blaCTX-M na tej samej plazmidzie zwiększają adaptacyjność ewolucyjną w klinicznym szczepie Klebsiella pneumoniae
Dlaczego to ma znaczenie dla współczesnej medycyny
Infekcje oporne na antybiotyki stanowią rosnące zagrożenie w szpitalach na całym świecie, a lekarze coraz częściej polegają na lekach ostatniej szansy, aby ratować pacjentów. To badanie wyjaśnia, jak powszechna bakteria szpitalna, Klebsiella pneumoniae, może wykorzystać subtelny trik genetyczny, by przetrwać silne kombinacje antybiotyków zaprojektowane, by przezwyciężyć oporność. Odkrycie tej strategii pomaga wyjaśnić, dlaczego niektóre infekcje nawracają mimo agresywnego leczenia — i daje wskazówki, jak lekarze mogą wyprzedzać bakterie.
Drobnoustrój szpitalny pod presją
Historia zaczyna się na oddziale intensywnej terapii, gdzie dwóch pacjentów zostało zakażonych niemal identycznymi szczepami K. pneumoniae. Jeden szczep był łatwy do wyleczenia współczesną parą leków ceftazydym/awibaktam, podczas gdy drugi wykazywał silną oporność. Porównania genetyczne wykazały, że oba szczepy nosiły tę samą szeroką rodzinę enzymów opornościowych, nazywanych β-laktamazami, na wspólnej plazmidzie — małym, ruchomym kółku DNA w bakterii. Jednak w szczepie opornym jeden z tych enzymów uległ subtelnej zmianie, a wariant nazwany CTX-M-249 pozwolił bakterii zignorować kombinację leków, która powinna ją zabić.
Mała zmiana, duże konsekwencje
Bardziej szczegółowe testy biochemiczne wykazały, że CTX-M-249 wymienia jeden rodzaj ochrony na inny. Zwykła wersja, CTX-M-65, doskonale rozkłada niektóre antybiotyki, takie jak cefotaksym, ale pozostaje wrażliwa na inhibitor awibaktam. CTX-M-249, zmieniony zaledwie w dwóch pozycjach białka, staje się skuteczny wobec ceftazydymu w połączeniu z awibaktamem, lecz traci dużą część swej siły przeciwko cefotaksymowi. Na papierze wygląda to na klasyczny kompromis ewolucyjny: zyskanie jednej obrony przy osłabieniu innej. Tymczasem kliniczny szczep uniknął tej wady, nosząc kilka blisko spokrewnionych kopii genu jednocześnie, co pozwalało różnym wersjom enzymu współistnieć w tej samej linii bakteryjnej.
Wiele kopii, wiele opcji
Wykorzystując sekwencjonowanie długich odczytów i precyzyjne metody zliczania, badacze odkryli, że plazmid w szczepie opornym zawierał dwa odrębne miejsca blaCTX-M, z których jedno mogło występować w wielu, nieco różnych wersjach. Przy braku nacisku lekom, około połowy populacji nosiło starszą wersję CTX-M-65, prawie połowa niosła CTX-M-249, a niewielka część miała formy pośrednie. Gdy bakterie były narażone na rosnące dawki ceftazydymu/awibaktamu, zarówno liczba kopii genu, jak i udział CTX-M-249 gwałtownie wzrastały. Czasem następowało to przez zwiększenie liczby plazmidów na komórkę; przy wyższych stężeniach leku sama plazmidia zaczynała tworzyć krótkie tandemowe powtórzenia genu oporności. W praktyce bakterie używały duplikacji DNA jak pokrętła, które mogły przykręcać lub odkręcać, aby dopasować się do otaczających antybiotyków.
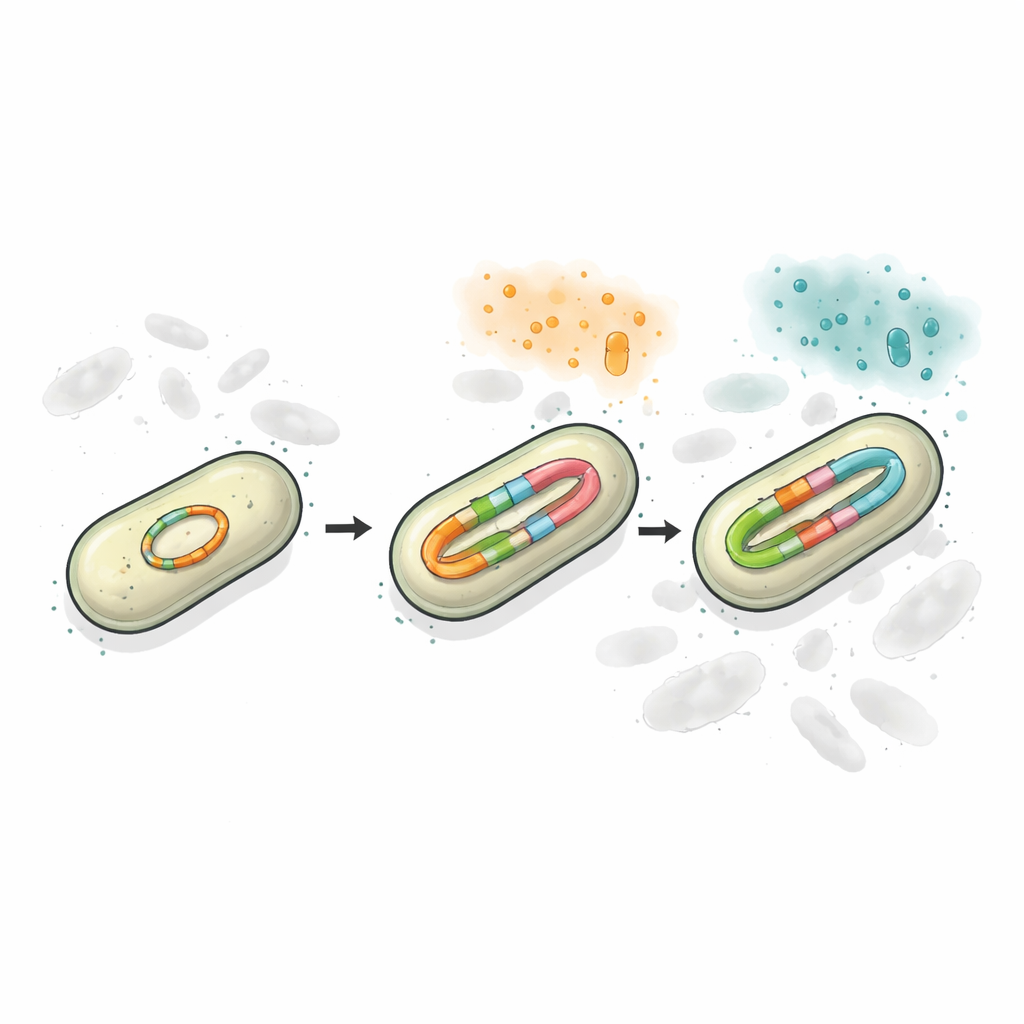
Utrzymywanie różnorodności na jednym kręgu DNA
Aby sprawdzić, jak to ustawienie wpływa na przeżywalność, zespół zbudował uproszczone modele laboratoryjne, w których bakterie nosiły albo jedną wersję oporności, dwie wersje na oddzielnych plazmidach, albo obie wersje zakodowane razem na jednej plazmidzie. Po wystawieniu na działanie dwóch różnych cefalosporyn systemy mieszane przewyższały szczepy z pojedynczym genem, ponieważ przynajmniej jedna wersja enzymu radziła sobie z każdym z leków. Jednak konfiguracja, w której obie warianty genu znajdowały się na tej samej plazmidzie, okazała się najstabilniejsza. Gdy antybiotyki były podawane przez kilka dni lub zmieniano je z jednego leku na inny, komórki z dwiema oddzielnymi plazmidami często traciły jedną z nich, poświęcając część swojej ochrony. W przeciwieństwie do tego „dwie w jednej” plazmidzie była dziedziczona jako pakiet, zachowując obie opcje oporności nawet gdy narzucała krótkoterminowy koszt wzrostu.
Szerzej: wzorzec w groźnych bakteriach
Modele matematyczne odtworzyły te eksperymenty, pokazując, że powyżej pewnych poziomów antybiotyku bakterie z jedną plazmidą niosącą wiele wariantów oporności ostatecznie dominują w mieszanych populacjach. Naukowcy następnie przeszukali tysiące genomów K. pneumoniae pochodzących ze szpitali, gospodarstw, żywności i środowiska. Często znajdowali wiele, nieco różnych kopii kluczowych genów oporności — szczególnie w izolatach klinicznych od ludzi, które są narażone na duże obciążenie lekami. To sugeruje, że wbudowywanie „wielokrotnej heterogeniczności” w plazmidy nie jest rzadką osobliwością, lecz powszechną taktyką, której bakterie używają, aby zabezpieczyć się przed zmieniającymi się terapiami.
Co to znaczy dla pacjentów i leczenia
Dla osoby niebędącej specjalistą główny przekaz jest taki, że niektóre bakterie nie noszą po prostu pojedynczego genu oporności; noszą rodziny powiązanych wersji zebranych na tym samym ruchomym elemencie DNA, co daje im elastyczne narzędzia przeciw różnym lekom. Takie ustawienie pozwala im utrzymywać oporność przez długi czas, nawet gdy lekarze zmieniają terapie, i pomaga wyjaśnić, dlaczego niektóre infekcje są tak trudne do wyleczenia. Jednocześnie badanie pokazuje, że starannie dobrane kombinacje leków — na przykład łączenie ceftazydymu/awibaktamu z cefotaksymem — mogą wykorzystać słabości tego systemu i stłumić nawet silnie uzbrojone szczepy. Zrozumienie, jak bakterie konstruują i wykorzystują te wielokrotne plazmidy, jest zatem kluczowe dla projektowania mądrzejszych strategii antybiotykowych i spowalniania postępu oporności.
Cytowanie: Weng, R., Zhu, J., Wu, X. et al. Heterogeneous multicopy of blaCTX-M variants on the same plasmid enhances evolutionary adaptability in clinical Klebsiella pneumoniae. Nat Commun 17, 2460 (2026). https://doi.org/10.1038/s41467-026-69266-7
Słowa kluczowe: oporność na antybiotyki, Klebsiella pneumoniae, plazmidy, beta-laktamazy, terapia wielolekowa