Clear Sky Science · pl
PRICE: bezpośrednie i odporne wykrywanie mikroRNA z rozdzielczością pojedynczego nukleotydu
Dlaczego drobne komunikaty genetyczne mają znaczenie
W każdej komórce krąży chmara drobnych cząsteczek RNA zwanych mikroRNA, które precyzyjnie regulują, które geny są włączane, a które wyciszane. Zmiana zaledwie jednej „litery” w tych krótkich cząsteczkach może przesunąć równowagę w stronę zdrowia lub choroby, w tym nowotworów. Lekarze i badacze chcieliby odczytywać te subtelne różnice bezpośrednio z krwi lub tkanek, ale obecne metody bywają wolne, kosztowne i niewystarczająco precyzyjne, by niezawodnie wychwycić zmianę pojedynczej litery. W artykule przedstawiono nową technikę laboratoryjną nazwaną PRICE, która obiecuje prostsze i dokładniejsze odczytywanie tych mikroskopijnych błędów w mikroRNA, otwierając możliwości wcześniejszego wykrywania raka i lepszego monitorowania zachowania guzów.
Nowy sposób rozróżniania podobnych cząsteczek
MikroRNA są wyjątkowo krótkie, co utrudnia ich rozróżnianie, gdy sekwencje różnią się tylko jednym składnikiem. Wiele obecnych narzędzi, takich jak PCR czy sekwencjonowanie RNA, dobrze liczy mikroRNA ogólnie, ale ma problemy, gdy dwie wersje są prawie identyczne, albo wymaga skomplikowanego przygotowania próbek i drogich urządzeń. Autorzy łączą dwa silne pomysły, by to przezwyciężyć: programowalny „nożycowy” enzym z rodziny CRISPR oraz syntetyczne, DNA‑podobne fragmenty zwane peptydowymi kwasami nukleinowymi (PNA). Enzym CRISPR Cas13a może zostać zaprogramowany do rozpoznania konkretnego RNA, a gdy znajdzie cel, zaczyna ciąć pobliskie cząsteczki reporterskie, powodując jasny sygnał fluorescencyjny. PNA natomiast to krótkie nici, które wiążą się wyjątkowo mocno z dopasowanymi sekwencjami RNA, ale nagle tracą przyczepność, jeśli choć jedna litera jest niezgodna.
Jak działa metoda PRICE
W systemie PRICE PNA działają jak selektywne blokery, które wyciszają wszystko, czego badacze nie chcą widzieć. Dla określonego mikroRNA zespół projektuje zestaw PNA blokujących, które idealnie pasują do wszystkich „błędnych” wersji — tych z niepożądanymi zmianami pojedynczych liter — jednocześnie celowo niedopasowując się do wybranego docelowego RNA. Gdy próbka biologiczna (surowica, komórki lub tkanka) jest zmieszana z tymi PNA, niecelowe mikroRNA zostają silnie związane i skutecznie zamaskowane. Prawdziwy cel pozostaje niezwiązany i wolny, by wchodzić w interakcję z kompleksem Cas13a, który został uprzednio zaprogramowany przewodnikowym RNA rozpoznającym to mikroRNA. Tylko ten niezablokowany cel może przełączyć Cas13a w aktywny tryb cięcia, co z kolei rozcina fluorescencyjne molekuły reporterskie i generuje silne, łatwe do zmierzenia świecenie.
Dostrajanie precyzji do pojedynczej litery
Autorzy systematycznie badali, jak projektować PNA blokery tak, by były na tyle mocne, by chwycić niepożądane mikroRNA, a jednocześnie na tyle słabe, by zignorować pożądane, różniące się tylko jedną literą. Odkryli, że kluczowe są dwa reguły podobne do kwestii temperatury: PNA powinno tworzyć stabilny duet z niechcianym mutantem w temperaturach równych lub wyższych od temperatury ciała, ale tworzyć znacznie słabszy duet z celem, który rozpada się przy temperaturach dużo niższych. Korzystając z tych zasad, wsparte prostym modelem predykcyjnym, zbudowali PNA, które redukują fałszywe sygnały pochodzące od mutantów mikroRNA o ponad 70 procent, jednocześnie pozostawiając prawdziwy sygnał praktycznie nietknięty. Co ważne, dodane PNA nie zmniejszały ogólnej czułości: PRICE wciąż wykrywało mikroRNA w stężeniach rzędu kilkudziesięciu femtomoli, porównywalnie z najlepszymi testami opartymi na amplifikacji, ale bez dodatkowych kroków kopiowania.
Zastosowanie testu w próbkach nowotworowych
Aby pokazać, że PRICE to coś więcej niż teoria, zespół skupił się na rodzinie mikroRNA let‑7, która odgrywa istotną rolę w biologii nowotworów. Wykazali, że PRICE potrafi wyodrębnić docelowe mikroRNA z mieszanin zawierających wiele niemal identycznych członków rodziny i może nawet wykrywać rzadkie warianty stanowiące zaledwie 5 procent próby. Badacze sięgnęli następnie po rzeczywisty materiał kliniczny: linie komórkowe raka wątroby, biopsje tkankowe i surowicę pacjentów. Zarówno w tkance nowotworowej, jak i we krwi, PRICE konsekwentnie wykrywało obniżone poziomy konkretnych mikroRNA let‑7 u pacjentów w porównaniu z grupami kontrolnymi bez nowotworu, zgodnie z wcześniejszymi badaniami. W bezpośrednim porównaniu ze standardowym RT‑qPCR, PRICE wykazało co najmniej porównywalną, a często lepszą zdolność rozróżniania przypadków nowotworowych od nienowotworowych, szczególnie w próbkach surowicy o niskim obfitości, gdzie wyniki PCR stawały się zszumione.
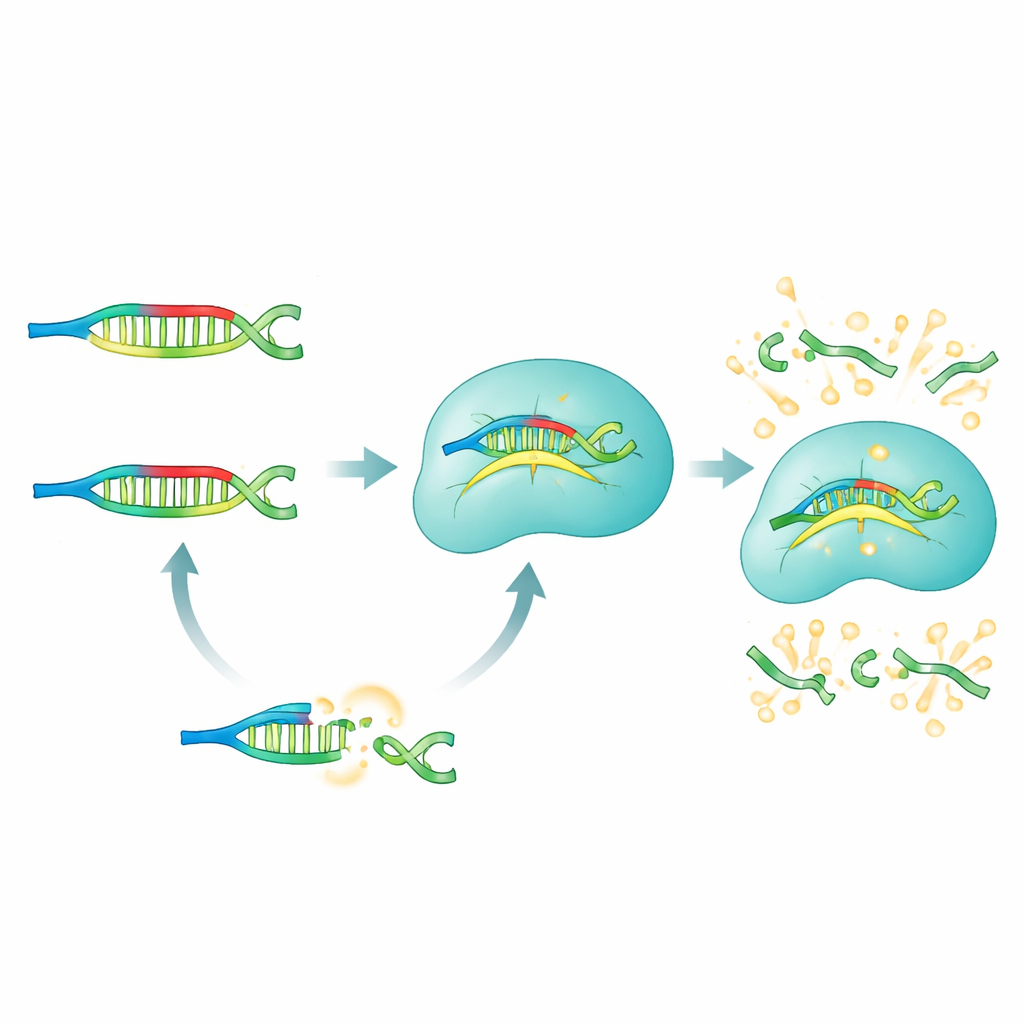
Dlaczego to ma znaczenie dla przyszłej diagnostyki
W istocie, praca ta pokazuje, że możliwe jest bezpośrednie odczytywanie różnic pojedynczych liter w drobnych regulatorowych RNA w praktyczny, skalowalny sposób. Pozwalając PNA blokować niechciane podobne sekwencje i powierzając ostateczny odczyt enzymowi CRISPR, PRICE oferuje elastyczne narzędzie do projektowania testów, które można łatwo przeprogramować przez wymianę panelu blokerów i przewodnikowego RNA. Poza rakiem wątroby i rodziną let‑7, ta sama strategia może zostać rozszerzona na wiele innych chorób, w których mają znaczenie niewielkie zmiany w RNA, a nawet na warianty DNA w połączeniu z pokrewnymi enzymami CRISPR. Autorzy pokazują również kompaktowy, wielokanałowy czytnik zdolny do uruchamiania assayów PRICE poza dużymi laboratoriami centralnymi, sugerując przyszłe testy przy łóżku pacjenta. Jeśli zostanie dalej rozwinięty, PRICE może stać się praktycznym sposobem monitorowania subtelnych przesunięć genetycznych sygnalizujących raka i inne choroby na długo przed pojawieniem się objawów.
Cytowanie: Wang, B., Zhou, S., Zhang, X. et al. PRICE: direct and robust detection of microRNAs at single-nucleotide resolution. Nat Commun 17, 2647 (2026). https://doi.org/10.1038/s41467-026-69181-x
Słowa kluczowe: diagnostyka mikroRNA, CRISPR Cas13a, peptydowe kwasy nukleinowe, wariant pojedynczego nukleotydu, biomarkery raka wątroby