Clear Sky Science · pl
FidlTrack: wysokowiernościowe śledzenie pojedynczych cząstek uwzględniające strukturę rozwiązuje wewnątrzkomórkowy ruch molekularny w organellach monitorujących przetwarzanie APP
Obserwacja pojedynczych cząsteczek wewnątrz żywych komórek
W każdej komórce niezliczone cząsteczki nieustannie się poruszają, zderzają, wiążą i rozdzielają. Współczesne mikroskopy potrafią śledzić pojedyncze cząsteczki jedna po drugiej, obiecując wgląd w to, jak działa życie na najdrobniejszych skalach. Jednak gdy wiele cząsteczek porusza się szybko w ciasnych, krętych przestrzeniach, takich jak siateczka śródplazmatyczna czy mitochondria, ich trajektorie splatają się i łatwo je błędnie zinterpretować. W artykule tym przedstawiono FidlTrack — nowe podejście do uporządkowania tych splątanych danych, dzięki któremu badacze mogą ufać obserwowanyym ścieżkom pojedynczych cząsteczek w czasie rzeczywistym.
Dlaczego śledzenie drobnych ruchów jest tak trudne
Śledzenie pojedynczych cząstek polega na podążaniu za tym samym jasnym punktem przez wiele klatek filmu. Na stosunkowo płaskiej powierzchni komórki, gdzie cząsteczki poruszają się wolno i są od siebie odseparowane, jest to wykonalne. W głębi komórki natomiast dyfuzja przebiega znacznie szybciej, a cząsteczki gromadzą się w wąskich, pętlowych rurkach i płatach. Między kolejnymi klatkami ten sam punkt mógł przemieścić się znacznie, a w pobliżu może znajdować się kilka identycznych punktów. Tradyjne oprogramowanie musi „zgadywać”, który punkt w następnej klatce odpowiada tej samej cząsteczce, a te przypuszczenia łatwo bywają błędne. Co gorsza, poprawne i błędne ścieżki mogą wyglądać bardzo podobnie, więc trudno jest ocenić, którym fragmentom danych można ufać.
Projektowanie eksperymentów dla wiarygodnych danych
Naukowcy najpierw zbudowali realistyczny symulator generujący filmy z „prawdziwą prawdą” ruchu dyfundujących cząsteczek, gdzie rzeczywiste trajektorie są znane. Wykorzystali te syntetyczne zbiory danych, aby systematycznie przetestować, jak kluczowe czynniki wpływają na wiarygodność śledzenia: jak szybko poruszają się cząsteczki, ile ich pojawia się w każdym obrazie, jak często zbierane są klatki oraz jak daleko cząsteczka może przeskoczyć między klatkami. Na tej podstawie stworzyli mapy pokazujące, dla danej sytuacji, które ustawienia maksymalizują odsetek poprawnie odtworzonych ruchów. Mapy te ujawniają, że dla wolno poruszających się cząsteczek przy umiarkowanych zagęszczeniach śledzenie może być bardzo wiarygodne, lecz dla szybko poruszających się cząsteczek przy wysokich zagęszczeniach błędy szybko narastają, a dodawanie kolejnych cząsteczek przestaje poprawiać użyteczną informację.
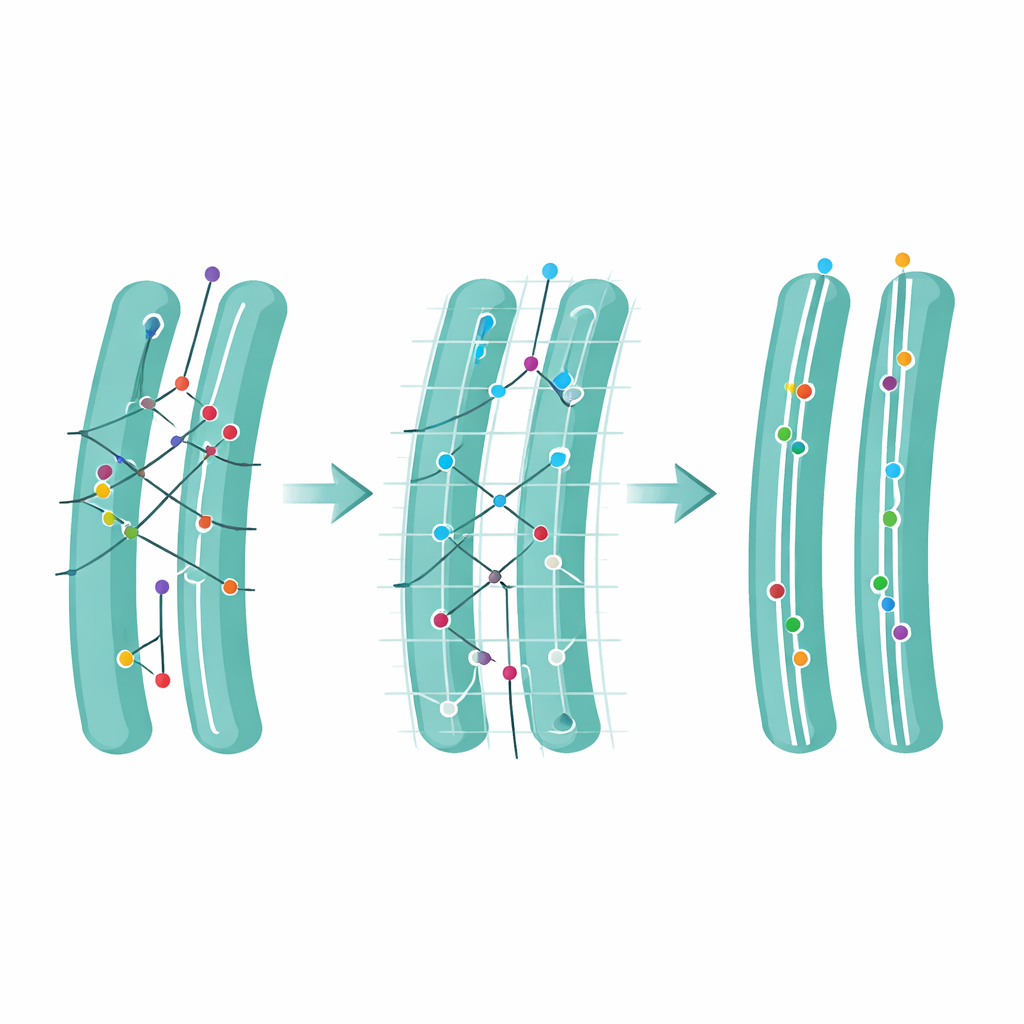
Wykrywanie i wycinanie wątpliwych skoków
Następnie zespół zajął się subtelnym, lecz silnym pojęciem: niejednoznacznością. Ruch nazywa się niejednoznacznym, gdy w zasięgu znajduje się więcej niż jeden możliwy kolejny punkt, zmuszając algorytm do wyboru między kilkoma prawdopodobnymi połączeniami. Na podstawie symulacji autorzy wykazali, że duża część błędów śledzenia wynika z takich niejednoznacznych kroków. Zdefiniowali Wskaźnik Niejednoznaczności, który zlicza, jak często występują takie sytuacje, a następnie zbadali, co się dzieje, gdy po śledzeniu usunąć wszystkie niejednoznaczne kroki. Takie przycinanie poświęca część danych i skraca trajektorie, ale radykalnie zwiększa ogólną wiarygodność pozostałych danych i poprawia oszacowania prędkości ruchu cząsteczek. Po zastosowaniu do rzeczywistych filmów markerów w siateczce śródplazmatycznej niejednoznaczność była wyższa w zatłoczonych rejonach wokół jądra komórkowego, a usuwanie niejednoznacznych połączeń oczyszczało te obszary bez szkody dla prostszych regionów.
Pozwolenie architekturze komórki kierować śledzeniem
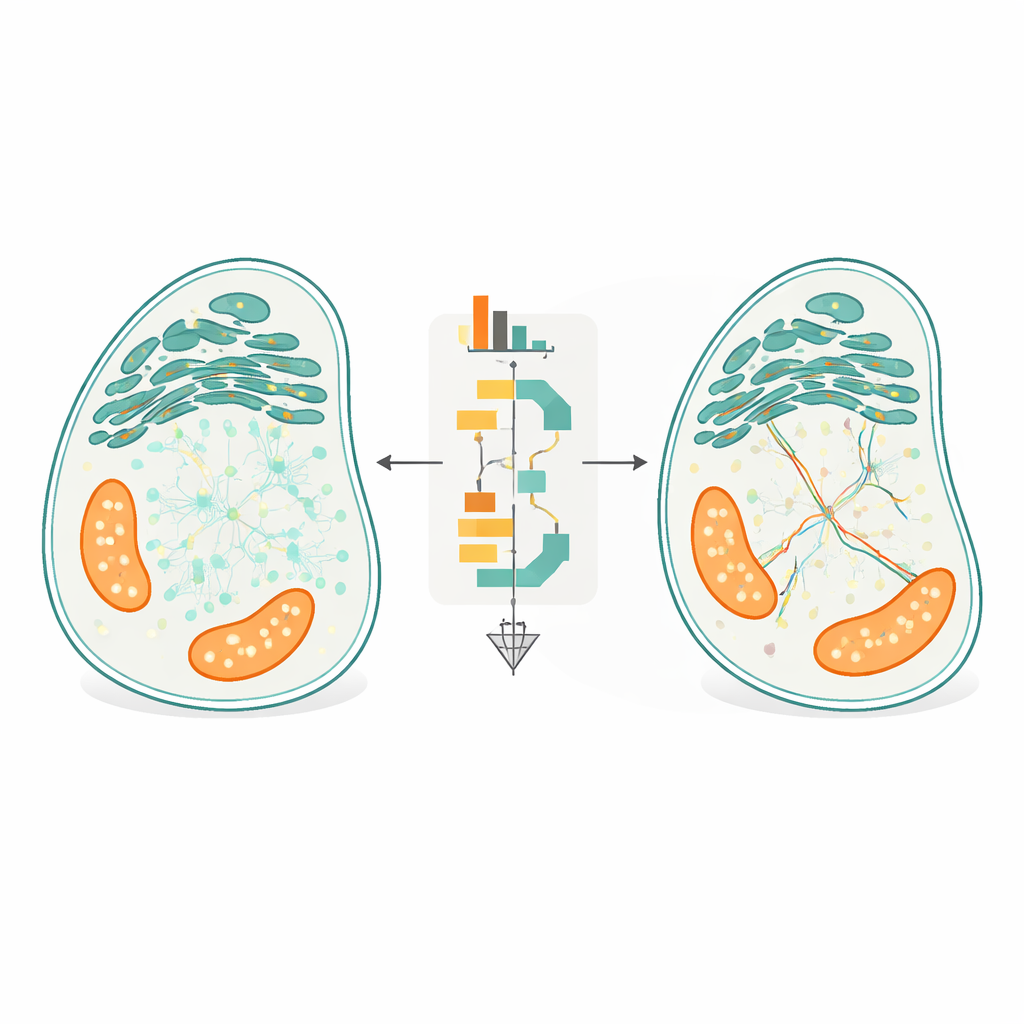
Centralną innowacją FidlTrack jest śledzenie „świadome struktury”. Zamiast traktować każdy punkt jako poruszający się w pustej przestrzeni, metoda wykorzystuje obrazy wewnętrznej architektury komórki — takie jak zarysy siateczki śródplazmatycznej, mitochondriów czy cienkich wypustek neuronalnych — by ograniczyć, gdzie cząsteczki realistycznie mogą się przemieszczać. Obraz organelli jest konwertowany na graf połączonych pikseli, a odległości mierzone są wzdłuż tego grafu, a nie liniami prostymi przez przestrzeń. Połączenia, które wymagałyby od cząsteczki przeskoczenia przez przerwę między dwoma oddzielnymi tubulami, mogą być w ten sposób oznaczone jako niemożliwe i odrzucone. W symulacjach ciasno upakowanych rurek oraz w rzeczywistych nagraniach procesów neuronalnych i organelli, ta świadomość strukturalna zmniejszyła liczbę niejednoznacznych połączeń nawet o połowę i zwiększyła ilość wiarygodnych, niejednoznacznych danych o ruchu wielokrotnie.
Ujawnianie ukrytych zachowań komórek i zdarzeń istotnych dla chorób
Wyposażeni w te narzędzia — zoptymalizowane ustawienia, filtrowanie niejednoznaczności i świadomość struktury — autorzy ponownie przeanalizowali kilka pytań biologicznych, które wcześniej były poza zasięgiem. W siateczce śródplazmatycznej mogli wyraźnie śledzić, jak białka poruszają się wchodząc w interakcje z miejscami wyjścia kierującymi ładunek ku aparatu Golgiego, odróżniając krótkie „przeloty” od dłuższych zatrzymań. Zarejestrowali rzadkie momenty, kiedy związane z Alzheimerem białko APP jest cięte przez enzym BACE1, widoczne jako nagłe przejście z wolnego ruchu przytwierdzonego do błony do szybszej swobodnej dyfuzji. Śledzili też zaprojektowane cząsteczki przypominające przeciwciała w ER i na podstawie zmian w ich ruchu wnioskowali, kiedy były związane z celem, a kiedy swobodnie dryfowały. W tych różnych przypadkach FidlTrack odzyskiwał bardziej wiarygodne trajektorie i wyostrzał różnice, które standardowe śledzenie albo rozmywało, albo zaniżało.
Co to znaczy dla przyszłej biologii komórki
Dla osób niebędących specjalistami kluczowy przekaz jest taki: nie wszystkie ścieżki pojedynczych cząsteczek są takie same — niektórym można ufać, inne wprowadzają w błąd, a dotychczas trudno było je odróżnić. FidlTrack oferuje praktyczne, otwarte narzędzie do zmierzenia, jak wiarygodny jest dany zbiór danych, oraz do poprawy tej wiarygodności przez dostrojenie ustawień eksperymentalnych, usunięcie niejednoznacznych kroków i użycie geometrii samej komórki jako przewodnika. Dzięki temu można z większą pewnością obserwować, jak cząsteczki przemierzają zawiłe wnętrze komórki, oraz wykrywać rzadkie lub subtelne zdarzenia — od sortowania białek po procesy związane z chorobami — które wcześniej były zagłuszone przez szum.
Cytowanie: Parutto, P., Yuan, Y., Davì, V. et al. FidlTrack: high-fidelity structure-aware single particle tracking resolves intracellular molecular motion in organelles sensing APP processing. Nat Commun 17, 2639 (2026). https://doi.org/10.1038/s41467-026-69067-y
Słowa kluczowe: śledzenie pojedynczych cząstek, dynamika wewnątrzkomórkowa, struktura organelli, ruch białek, choroba Alzheimera