Clear Sky Science · pl
Wielokrajowa analiza genomowa podkreśla regionalne rozprzestrzenianie się cholery w Afryce
Dlaczego śledzenie zarazków przez granice ma znaczenie
Cholera wciąż powoduje zachorowania i śmierć dziesiątek tysięcy osób rocznie w Afryce, a wciąż pozostają podstawowe pytania o to, jak zaczynają się ogniska, jak przemieszczają się między krajami i dlaczego nawracają. To badanie łączy naukowców i zespoły służb zdrowia publicznego z siedmiu afrykańskich państw, aby śledzić bakterię wywołującą cholerę poprzez odczytywanie jej kodu genetycznego. Porównując setki genomów bakteryjnych, badacze pokazują, jak ostatnie fale cholery przemieszczały się przez granice, jakie typy szczepów krążą w poszczególnych miejscach i jak ta wiedza może ulepszyć działania mające zapobiegać przyszłym epidemiom.
Kontynentalne spojrzenie na cholerę
Aby wyjść poza rozproszone raporty przypadków, Africa Centres for Disease Control and Prevention zainicjowało współpracę nazwaną Konsorcjum Genomiki Cholery w Afryce (CholGEN). Laboratoria w Kamerunie, Demokratycznej Republice Konga, Malawi, Mozambiku, Nigerii, Ugandzie i Zambii zsekwencjonowały 763 wysokiej jakości genomy bakterii Vibrio cholerae O1, głównie z lat 2019–2024. To największy zestaw genomów cholery kiedykolwiek wygenerowany na samym kontynencie afrykańskim. Umieszczając te nowe genomy obok prawie 1 800 wcześniej zsekwencjonowanych próbek z Afryki i Azji, zespół mógł odtworzyć, jak niedawne afrykańskie ogniska wpisują się w trwającą globalną pandemię cholery.
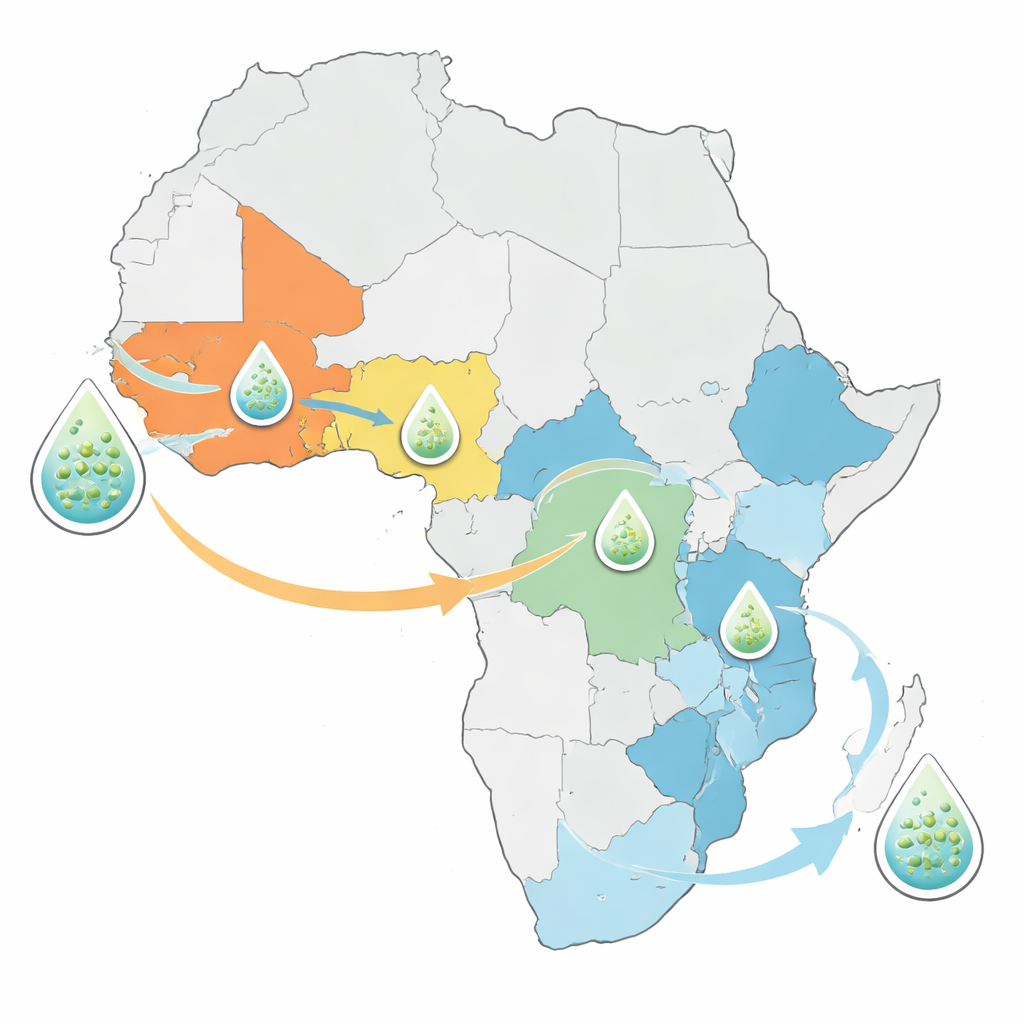
Stare szczepy, nowe trasy
Analiza wykazała, że szczepy cholery powodujące dzisiejsze afrykańskie ogniska nie stanowią całkowicie nowego zagrożenia. Zamiast tego wszystkie nowo zsekwencjonowane bakterie wywodzą się z wcześniej znanych introdukcji linii siódmej pandemii cholery, która po raz pierwszy dotarła do Afryki z Azji w 1970 roku. Kraje zachodniej i centralnej Afryki, takie jak Nigeria, Kamerun i Demokratyczna Republika Konga, mają zwykle zdominowanie przez jedną lub dwie długo utrzymujące się linie, które przetrwały przez dekady. Kraje wschodniej i południowej Afryki z kolei gromadzą mieszankę kilku linii jednocześnie. Jedna linia, nazwana AFR15, rozprzestrzeniła się szczególnie szybko w ostatnich latach i powiązana jest z nietypowo dużymi ogniskami w Malawi, Zambii i sąsiednich krajach, a także z epidemiami w częściach Bliskiego Wschodu i Azji Południowej.
Gdy wielkość ognisk nie wynika z genów
Mogłoby się wydawać, że gwałtowny rozrost AFR15 wynika z istotnych zmian genetycznych czyniących go bardziej niebezpiecznym lub lepiej unikającym leczenia. Jednak gdy badacze porównali tempo i wzorce mutacji w kilku aktywnych liniach, nie znaleźli wyraźnych różnic. Bakterie ewoluowały w podobnym tempie, a rodzaje mutacji i dotknięte geny wyglądały podobnie między liniami. Ogólne profile genów odpowiedzialnych za oporność na antybiotyki również były w przeważającej mierze stabilne w czasie i między krajami. Głównym wyjątkiem była Uganda, gdzie bakterie nabyły duży mobilny element DNA zwany plazmidem, który niesie wiele genów oporności, prawdopodobnie przywieziony wraz ze szczepami powiązanymi z ogniskami w Jemenie i Libanie. Nawet w takim przypadku badanie nie wykazało nowych genów, które same w sobie wyjaśniałyby surowość niedawnych afrykańskich ognisk.
Ukryte podróże ujawnione dzięki lepszemu próbkowaniu
Ponieważ genomy bakteryjne noszą zapis miejsc, w których znajdowano blisko spokrewnione szczepy, zespół mógł wnioskować, jak często cholera przekracza granice. Wykryli wiele przykładów międzynarodowego rozprzestrzeniania się między sąsiednimi krajami, w tym powtarzające się wymiany między Zambią a Demokratyczną Republiką Konga. Jednak przy bliższym spojrzeniu okazało się, że statystyczne sygnały skoków transgranicznych były najsilniejsze w latach i regionach o intensywnym próbkowaniu. Sugeruje to, że rzeczywiste ruchy cholery są częstsze niż ujawniają obecne dane; wiele zdarzeń transmisji prawdopodobnie pozostaje niezauważonych po prostu dlatego, że nikt nie sekwencjonuje bakterii w tych miejscach lub w tych okresach. Aby to uwzględnić, autorzy opracowali ramy szacujące, ile nowej informacji kraj może zyskać dzięki sekwencjonowaniu dodatkowych próbek, uwzględniając różnorodność genetyczną, liczbę introdukcji i istniejące dane.
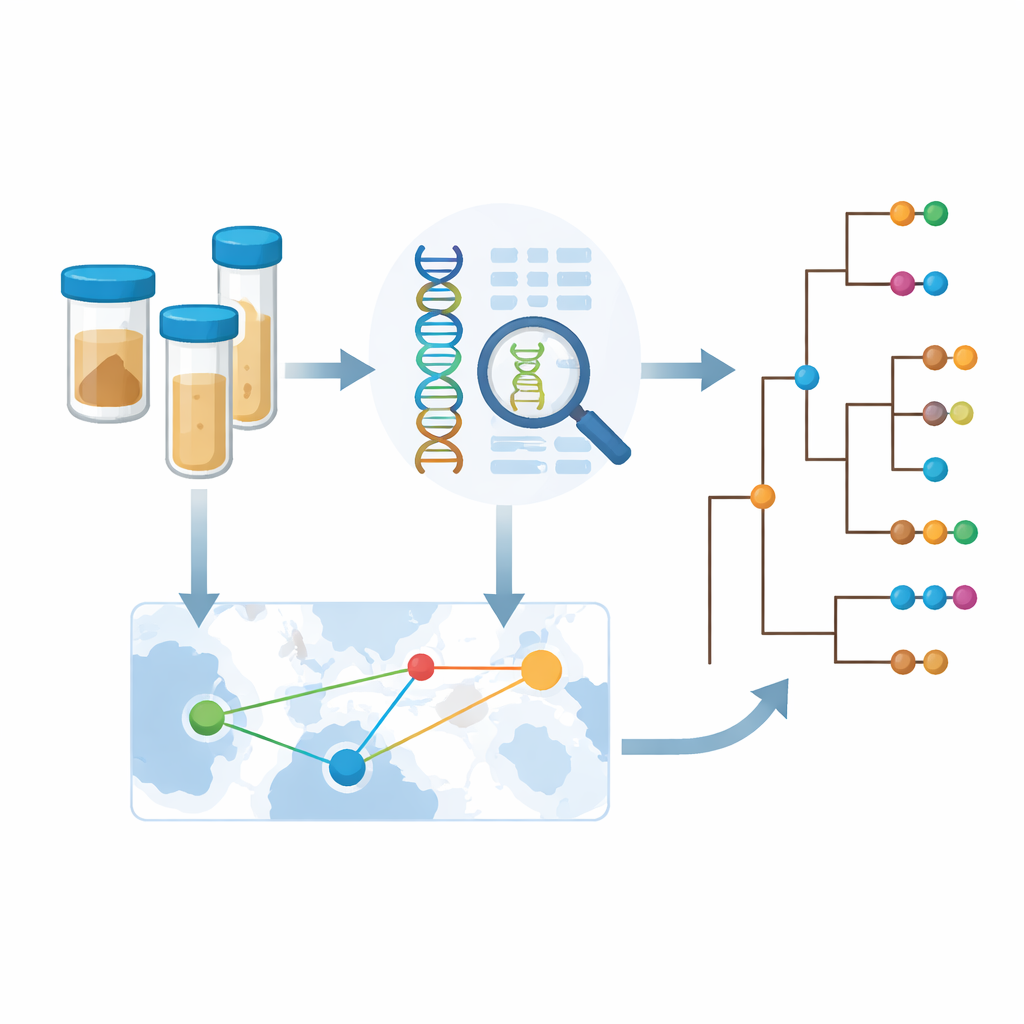
Wykorzystanie genomiki do kierowania skuteczniejszymi działaniami kontrolnymi
Badanie konkluduje, że dla dzisiejszej cholery w Afryce istotniejsze od dramatycznych zmian w samej bakterii jest to, jak i gdzie choroba się rozprzestrzenia. Wnioski przemawiają za rutynowym, regionalnie koordynowanym nadzorem genomowym, aby kraje sąsiednie mogły wcześniej wykrywać wspólne ogniska, śledzić ich źródła i celować w interwencje takie jak kampanie szczepień, poprawa wody i sanitacji oraz działania przygraniczne z większą efektywnością. Poprzez budowanie zdolności sekwencjonowania w afrykańskich laboratoriach służb zdrowia publicznego i dzielenie się danymi przez granice, inicjatywy takie jak CholGEN dostarczają praktycznego modelu wykorzystania nowoczesnej genetyki do przybliżenia ambitnego celu wyeliminowania cholery jako zagrożenia dla zdrowia publicznego do 2030 roku.
Cytowanie: Mboowa, G., Matteson, N.L., Tanui, C.K. et al. Multicountry genomic analysis underscores regional cholera spread in Africa. Nat Commun 17, 2539 (2026). https://doi.org/10.1038/s41467-026-68642-7
Słowa kluczowe: cholera, nadzór genomowy, Africa, transmisja transgraniczna, oporność na antybiotyki