Clear Sky Science · pl
Model języka genomowego łagodzi artefakty chimeryczne w bezpośrednim sekwencjonowaniu RNA metodą nanopore
Dlaczego oczyszczanie odczytów RNA ma znaczenie
Nasze komórki nieustannie odczytują instrukcje genetyczne zapisane w RNA, a nowe technologie sekwencjonowania pozwalają naukowcom obserwować ten proces z niespotykaną dotąd szczegółowością. Jednym z najpotężniejszych narzędzi jest bezpośrednie sekwencjonowanie RNA metodą nanopore, które potrafi odczytać całe cząsteczki RNA za jednym razem — ale wprowadza też błędy, które mogą przypominać łamanie i ponowne składanie genów w sposób, który w rzeczywistości nie występuje. W tym badaniu przedstawiono DeepChopper, narzędzie programowe działające jak model języka dla genomów, które usuwa te błędy, tak by badacze mogli ufać danym RNA.
Gdy sekwenator tworzy fałszywe zlepki genów
Nowoczesne urządzenia nanopore przeciągają pojedyncze nici RNA przez mikroskopijne pory i odczytują ich sekwencję bezpośrednio. Ma to duże zalety w porównaniu ze starszymi metodami, na przykład zachowuje modyfikacje chemiczne i pozwala uchwycić pełnej długości transkrypty w jednym odczycie. Jednak proces opiera się również na krótkich pomocniczych fragmentach zwanych adapterami, które są przyłączane do cząsteczek RNA podczas przygotowania biblioteki. Czasem dwie lub więcej cząsteczek RNA zostają przypadkowo połączone poprzez te adaptery, tworząc tzw. chimery — hybrydowe cząsteczki, które wyglądają jak fuzje różnych genów. Standardowe narzędzia analityczne mogą błędnie interpretować te techniczne pozostałości jako prawdziwe zdarzenia biologiczne, na przykład powiązane z rakiem fuzje genów czy nietypowe sposoby składania, prowadząc do mylących wyników.
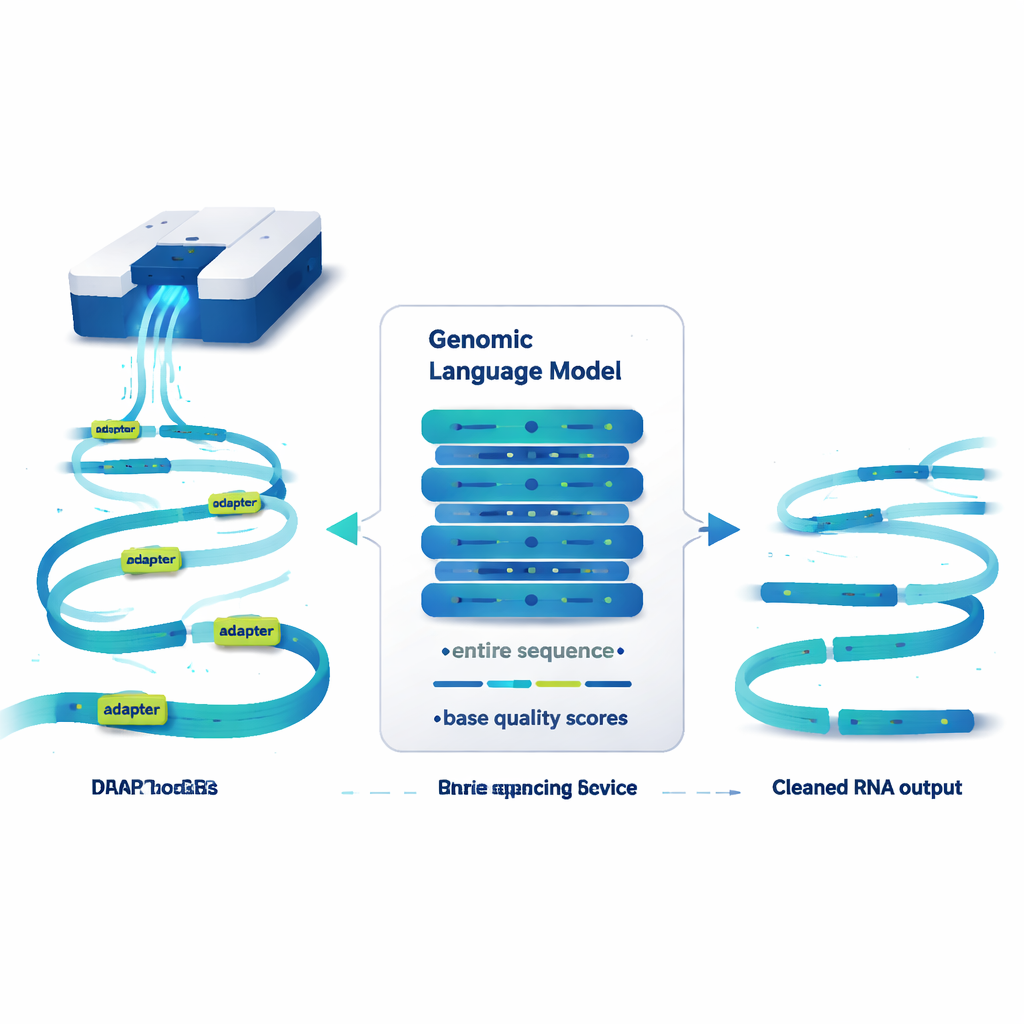
Model języka, który czyta genomy, nie zdania
DeepChopper traktuje sekwencje genetyczne podobnie jak tekst i wykorzystuje pomysły z dużych modeli językowych. Zamiast słów czyta sekwencje RNA literka po literce, wraz z oceną jakości dla każdej pozycji, która wskazuje wiarygodność odczytu. Zbudowany na zwartej architekturze HyenaDNA, potrafi skanować do 32 000 nukleotydów naraz — wystarczająco długo, by objąć praktycznie każdą ludzką cząsteczkę RNA. Dla każdej pozycji DeepChopper estymuje, czy ta baza jest częścią prawdziwej sekwencji RNA, czy częścią adaptera. Krok dopracowujący następnie wygładza te przewidywania, tak by adaptery były oznaczane jako ciągłe bloki, a nie rozproszone punkty.
Usuwanie złych złączy bez wyrzucania danych
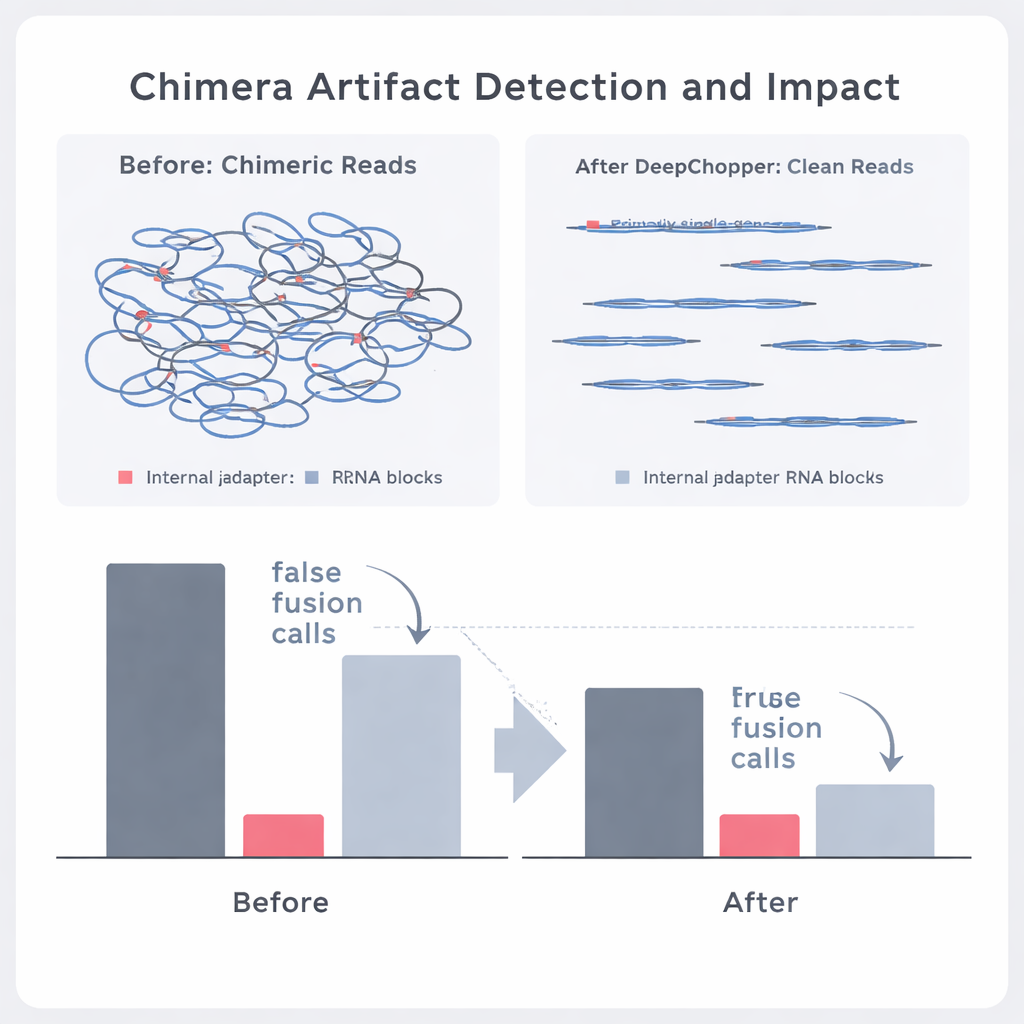
Gdy DeepChopper znajdzie adaptery wewnątrz odczytu, robi coś istotnego: zamiast odrzucać cały odczyt, „tnie” go w miejscach adapterów i zachowuje auténtyczne fragmenty. Dzięki temu sztuczna fuzja dwóch RNA może zostać rozdzielona z powrotem na oryginalne części. W testach na milionach odczytów nanopore z różnych ludzkich linii komórkowych nowotworowych i komórek macierzystych DeepChopper znacznie przewyższał istniejące narzędzia do przycinania adapterów, które nie były projektowane z myślą o tym trybie bezpośredniego sekwencjonowania RNA. Na syntetycznych benchmarkach poprawnie rozpoznawał adaptery z ponad 99% precyzją i czułością, a jednocześnie skalował się wydajnie do zbiorów danych zawierających ponad 20 milionów odczytów z wykorzystaniem procesorów graficznych.
Oddzielanie prawdziwych fuzji genów od miraży sekwencjonowania
Autorzy sprawdzili następnie, czy DeepChopper potrafi odróżnić rzeczywiste zdarzenia biologiczne od artefaktów w prawdziwych danych nowotworowych. Porównując bezpośrednie odczyty RNA z odpowiadającymi im zestawami danych uzyskanymi niezależnymi metodami (takimi jak sekwencjonowanie cDNA zarówno na platformach Oxford Nanopore, jak i PacBio), mogli oznaczyć, które pozorne chimery były potwierdzone przez inne technologie, a które nie. DeepChopper zmniejszył liczbę niepotwierdzonych wyrównań chimerycznych nawet o 62–91%, jednocześnie znacząco zwiększając udział tych potwierdzonych przez inne metody. Również zredukował liczbę podejrzanych zgłoszeń fuzji genów o niemal 90%, w szczególności tych obejmujących geny rybosomalne, które okazały się częstymi artefaktami. Równocześnie prawdziwe zdarzenia fuzji wspierane przez krótkodystansowe sekwencjonowanie RNA zostały zachowane.
Lepsza chemia pomaga — ale artefakty pozostają
Oxford Nanopore niedawno wprowadził zaktualizowany zestaw do sekwencjonowania (RNA004), zaprojektowany częściowo w celu zmniejszenia technicznych artefaktów. DeepChopper zastosowano „od razu” do danych z tej nowej chemii i wciąż wykrył, że niewielka lecz istotna część odczytów zawierała wewnętrzne adaptery i chimeryczne złącza. Nawet bez dodatkowego uczenia model skrócił liczbę artefaktów chimerycznych o około jedną piątą; po dopracowaniu na nowych danych działał nieco lepiej, zachowując równocześnie autentyczne sygnały. We wszystkich użytych chemiiach i typach komórek korekta tych artefaktów pozwoliła narzędziom dalszego przetwarzania wykryć znacznie więcej transkryptów pełnej długości i wariantów alternatywnych, dając jaśniejszy obraz krajobrazu RNA komórki.
Co to oznacza dla przyszłych badań RNA
Dla osób niezajmujących się specjalistycznie tematem kluczowy wniosek jest taki: nie każde zaskakujące powiązanie RNA zgłoszone przez sekwenator jest prawdziwą biologiczną obserwacją — część to błędy wprowadzane przez samą technologię. DeepChopper działa jak wysoko wyszkolony redaktor tekstu dla danych RNA z nanopore, wykrywając charakterystyczne sekwencje adapterów łączące niepowiązane cząsteczki i wycinając je z precyzją pojedynczej zasady. Efektem są czyściejsze, bardziej wiarygodne mapy tego, które cząsteczki RNA występują w komórce i jak są złożone. W miarę jak laboratoria coraz częściej polegają na sekwencjonowaniu długich odczytów RNA w badaniach nad rakiem, zaburzeniami mózgu i innymi złożonymi chorobami, narzędzia takie jak DeepChopper będą niezbędne do przekształcania zaszumionych surowych odczytów w rzetelne wnioski biologiczne.
Cytowanie: Li, Y., Wang, TY., Guo, Q. et al. Genomic language model mitigates chimera artifacts in nanopore direct RNA sequencing. Nat Commun 17, 1864 (2026). https://doi.org/10.1038/s41467-026-68571-5
Słowa kluczowe: sekwencjonowanie RNA metodą nanopore, odczyty chimeryczne, artefakty fuzji genów, model języka genomowego, DeepChopper