Clear Sky Science · pl
Modyfikacja DNA przez fosforotioe w systemach BREX typu 4 w mikrobiomie jelitowym człowieka
Ukryte chemiczne poprawki w naszych bakteriach jelitowych
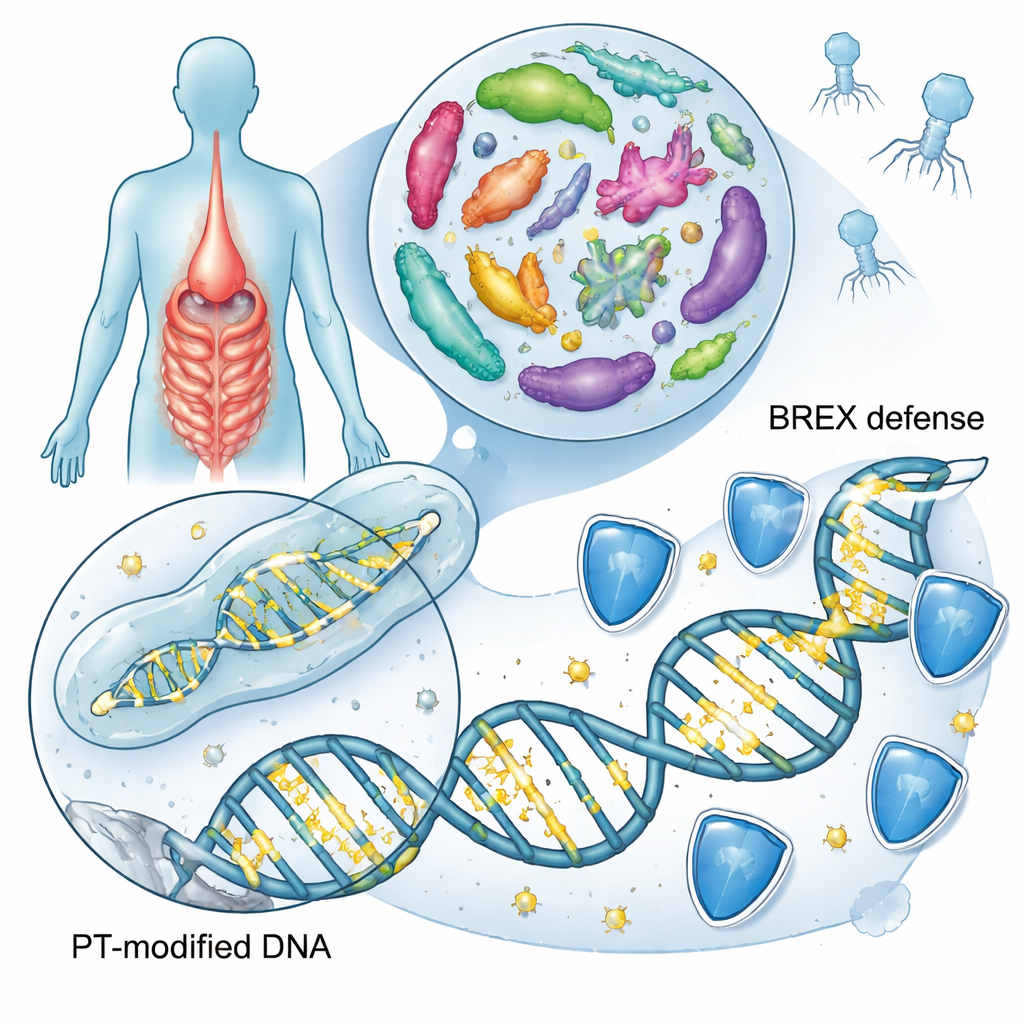
Głęboko w ludzkim jelicie biliony bakterii nieustannie wymieniają geny, walczą z wirusami i reagują na chemię tego, co jemy. To badanie ujawnia, że wiele z tych mikrobów cicho przepisuje szkielet własnego DNA, podstawiając atomy siarki i tworząc specjalne oznaczenie zwane fosforotioatem. Praca identyfikuje nową odmianę tego systemu, powiązaną z bakteryjnym zestawem obronnym BREX typu 4, i bada, jak powszechne są te siarkowe znaki w bakteriach jelitowych, które mogą wpływać na zdrowie i choroby.
Inny rodzaj oznaczenia w DNA
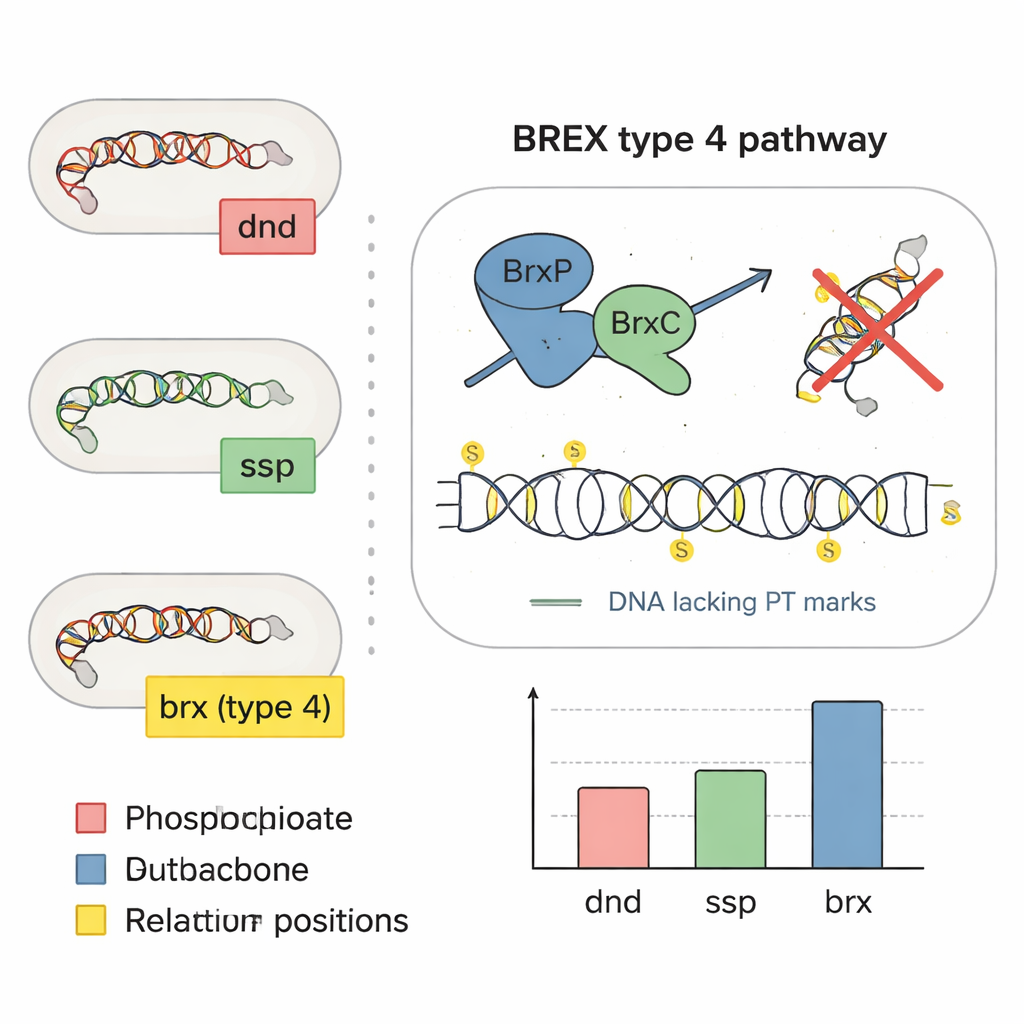
Wiele osób słyszało o „literach” DNA — A, T, C i G — modyfikowanych przez drobne grupy chemiczne, takie jak grupy metylowe, co jest kluczowym elementem epigenetyki. Tutaj uwaga skupia się na czymś znacznie bardziej radykalnym: niektóre bakterie zastępują jeden z atomów tlenu w szkielecie DNA siarką. Ta edycja szkieletonu, znana jako fosforotioacja, zmienia zachowanie DNA bez zmiany kodu genetycznego. Wcześniejsze badania wykazały dwa główne rodziny genów, określane jako dnd i ssp, które instalują te siarkowe znaczniki w około jednej na dziesięć gatunków bakterii i archeonów. Znaki te pomagają bakteriom rozpoznawać własne DNA, odpierać ataki wirusów zwanych fagami oraz potencjalnie reagować na stres oksydacyjny i zapalenie.
Przeszukiwanie tysięcy genomów jelitowych
Aby sprawdzić, jak powszechne jest siarkowane DNA w naszych jelitach, badacze przeskanowali 13 663 genomów bakteryjnych pochodzących z trzech dużych zbiorów mikroorganizmów człowieka. Szukali kluczowych sygnatur genetycznych wystarczających do wytworzenia siarkowych znaków: zestawów dnd, ssp lub nowego kandydującego zestawu genów nazwanego brx, które są częścią BREX, znanego systemu przeciwfagowego. Około 6,3% genomów jelitowych nosiło przynajmniej jeden z tych systemów, głównie w powszechnych grupach jelitowych Bacteroidota, Bacillota i Pseudomonadota. W porównaniu z szerszym katalogiem bakterii z różnych środowisk, jelito wykazywało wyraźne wzbogacenie wersji BREX typu 4, co sugeruje, że ta siarkowa forma obrony jest szczególnie preferowana w ekosystemie jelitowym.
Nowy siarkowy system obronny
Analizując, jak geny układają się obok siebie na chromosomach bakteryjnych, zespół zauważył geny podobne do dnd osadzone wśród genów obronnych BREX, co sugeruje, że niektóre systemy BREX mogą bezpośrednio instalować siarkowe znaczniki. Skoncentrowali się na zestawie czterech rdzeniowych genów: brxP, brxC, brxZ i brxL, i przy użyciu analizy sekwencji wykazali, że BrxP i BrxC przypominają białka obsługujące siarkę z systemów ssp. Eksperymenty w bakterii jelitowej Bacteroides salyersiae potwierdziły przypuszczenia: gdy badacze usunęli gen brxC, zmodyfikowane siarką DNA zniknęło; gdy przywrócili brxC na plazmidzie, znaki siarkowe powróciły. Przeniesienie kluczowych genów BREX do innej bakterii jelitowej, która normalnie tych systemów nie posiada, spowodowało, że zaczęła ona wytwarzać to samo siarkowe wzorcowane DNA, demonstrując, że maszyny BREX typu 4 same w sobie potrafią tworzyć oznaczenia fosforotioatowe.
Mapowanie miejsc, gdzie siarka trafia na genom
Odnalezienie siarkowych znaków to tylko połowa historii; kluczowe dla zrozumienia ich funkcji jest poznanie dokładnych miejsc, w których pojawiają się wzdłuż DNA. Badacze połączyli czułą spektrometrię mas z niestandardową metodą sekwencjonowania nazwaną PT-seq, która selektywnie przecina DNA w miejscach zmodyfikowanych siarką, a następnie odczytuje otaczającą sekwencję. Wśród 226 izolatów bakteryjnych z jelita zidentyfikowali osiem odrębnych dinukleotydowych „cegiełek” zawierających siarkę i na podstawie reprezentatywnych szczepów opracowali krótkie motywy sekwencyjne, w których siarka ma tendencję do osadzania się. Co ciekawie, bakterie z systemami dnd, ssp lub BREX wytwarzały różne zestawy siarkowych wzorców, jak odmienne dialekty tego samego chemicznego języka. Znaki nie były rozrzucone losowo: były wzbogacone w genach rRNA i generalnie unikały początków i końców genów kodujących białka, co sugeruje, że bakterie mogą kierować siarkę z dala od wrażliwych regionów kontrolnych.
Co to oznacza dla naszego zdrowia
Dla osoby niebędącej specjalistą te odkrycia pokazują, że bakterie jelitowe robią więcej niż tylko żywią się naszym jedzeniem — aktywnie przepisują chemię własnego DNA w sposób, który kształtuje ich walkę z wirusami i reakcję na silnie utleniające warunki towarzyszące często zapaleniom. Identyfikując BREX typu 4 jako nowy system znakowania siarką i pokazując, że około jedna na trzynaście bakterii jelitowych nosi jakąś formę aparatu fosforotioatowego, ta praca tworzy podstawy do badania, jak te niezwykłe oznaczenia DNA wpływają na stabilność mikrobiomu, odporność na zakażenia i być może przebieg chorób, takich jak zapalne choroby jelit. W dłuższej perspektywie zrozumienie, a być może manipulowanie tymi siarkowymi systemami epigenetycznymi, może zaoferować nowe strategie modulowania mikrobiomu jelitowego na korzyść zdrowia człowieka.
Cytowanie: Yuan, Y., DeMott, M.S., Byrne, S.R. et al. Phosphorothioate DNA modification by BREX type 4 systems in the human gut microbiome. Nat Commun 17, 1717 (2026). https://doi.org/10.1038/s41467-026-68412-5
Słowa kluczowe: mikrobiom jelitowy, bakteriologia epigenetyczna, fosforotioacja DNA, system obronny BREX, bakteriofagi