Clear Sky Science · pl
Projektowanie wszechstronnych syntaz tryptofanu za pomocą generatywnej AI opartej na sekwencjach
Nauczanie enzymów nowych sztuczek za pomocą AI
Współczesne społeczeństwo opiera się na cząsteczkach — lekach, materiałach i chemikaliach specjalnych — które często powstają w procesach energochłonnych i zanieczyszczających środowisko. Naturalne katalizatory, czyli enzymy, mogą wykonywać podobne zadania w sposób czysty i wydajny, lecz znalezienie lub zbudowanie odpowiedniego enzymu do nowego zastosowania przemysłowego jest powolne i niepewne. To badanie pokazuje, że generatywna sztuczna inteligencja, ta sama klasa technologii stojąca za chatbotami piszącymi teksty, może projektować zupełnie nowe enzymy, które nie tylko działają dobrze w laboratorium, lecz czasami przewyższają najlepsze enzymy uzyskane przez ewolucję i wieloletnie inżynieryjne wysiłki.
Dlaczego enzymy mają znaczenie w życiu codziennym
Enzymy to mikroskopijne białkowe maszyny, które przyspieszają reakcje chemiczne w komórkach żywych. Chemicy nauczyli się wykorzystywać je do produkcji leków, składników żywności i innych wartościowych produktów, zużywając mniej energii i mniej toksycznych reagentów niż w tradycyjnej chemii. Problem w tym, że każde nowe zastosowanie zwykle wymaga enzymu o idealnych właściwościach — akceptującego określone substraty, odpornego na warunki przetwarzania i dającego wysokie wydajności. Konwencjonalna „ukierunkowana ewolucja” poprawia enzymy przez tworzenie i testowanie wielu zmutowanych wersji, pokolenie po pokoleniu. To działa dobrze, ale zależy od przyzwoitego punktu wyjścia i może trwać miesiące lub lata prób i błędów, pozostawiając wiele użytecznych reakcji nieodkrytych.
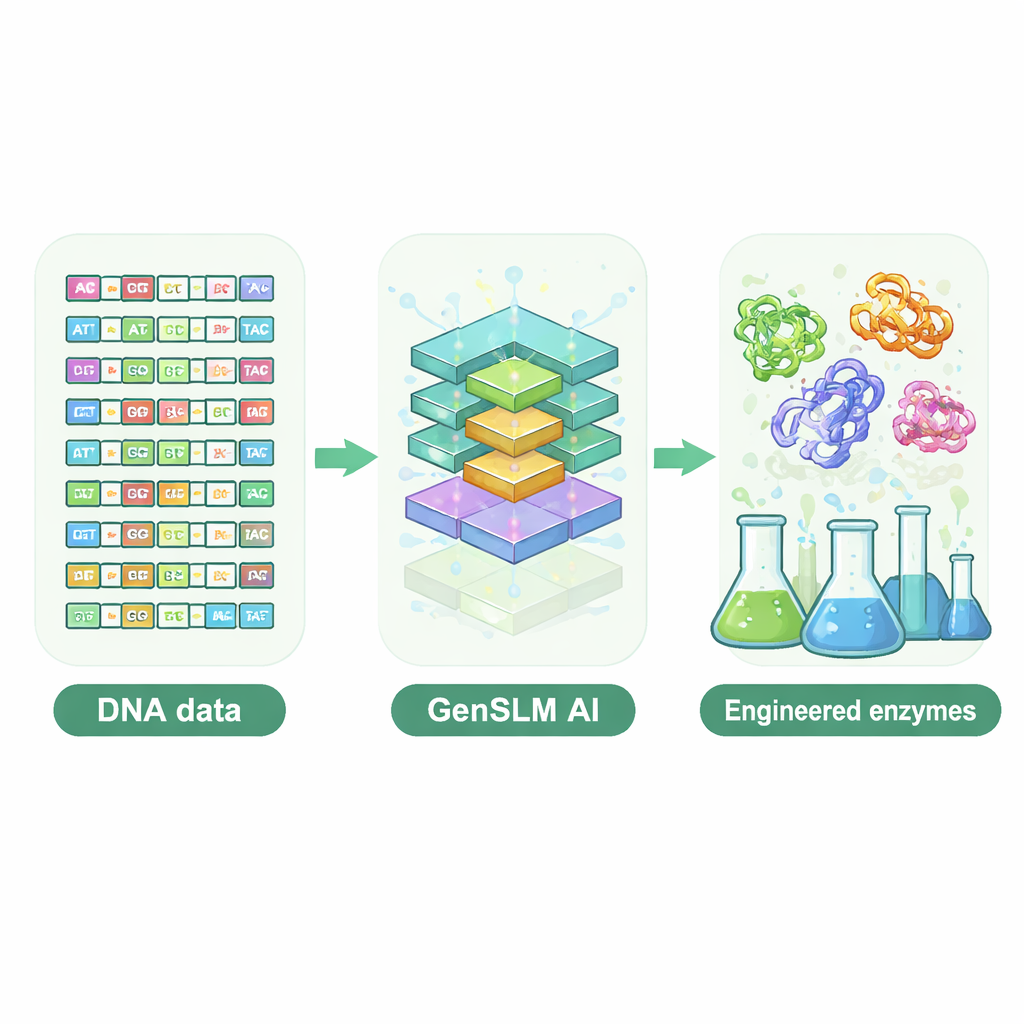
Pozwolić modelowi językowemu pisać DNA
Naukowcy sięgnęli po model językowy obejmujący całe genomy, nazwany GenSLM, który uczy się wzorców w DNA tak, jak model językowy uczy się gramatyki i stylu w tekście. Zamiast pracować z gotowymi sekwencjami białkowymi, GenSLM czyta i generuje DNA w trójliterowych kodonach, odwzorowując sposób, w jaki komórki tłumaczą geny na białka. Zespół najpierw dopracował (fine‑tuned) GenSLM na dziesiątkach tysięcy naturalnych genów dla jednej szczególnie złożonej podjednostki enzymu, zwanej TrpB, która pomaga w biosyntezie aminokwasu tryptofanu. Następnie poprosili model o wygenerowanie tysięcy całkowicie nowych genów trpB. Proste filtry obliczeniowe odrzuciły sekwencje zbyt krótkie lub zbyt długie, mało prawdopodobne do prawidłowego złożenia albo niemal identyczne z poznanymi naturalnymi enzymami, pozostawiając 105 różnorodnych kandydatów do testów eksperymentalnych w bakteriach.
Od projektów komputerowych do działających katalizatorów
Gdy tych 105 zaprojektowanych przez AI enzymów TrpB wyprodukowano w E. coli, wiele właściwie się złożyło i było wytwarzanych w dużych ilościach. Dziesiątki potrafiły wykonać swoją główną funkcję: przekształcać indol i naturalnego partnera, serynę, w tryptofan. Niektóre działały solidnie nawet w podwyższonych temperaturach, mimo że odporność na ciepło nie była explicitnie projektowana. W testach porównawczych część wariantów GenSLM‑TrpB dorównała lub przewyższyła enzym referencyjny, który przez lata był mozolnie ewoluowany w laboratorium, aby funkcjonować samodzielnie w 75 °C. Jeden wyróżniający się projekt, oznaczony jako 230, produkował więcej tryptofanu niż ten przemysłowo stosowany odnośnik zarówno w temperaturze pokojowej, jak i w wysokiej temperaturze, pokazując, że model trenowany wyłącznie na danych sekwencyjnych może bezpośrednio osiągnąć najwyższy poziom wydajności.
Nowa elastyczność wykraczająca poza to, co zbudowała natura
Zespół następnie poddał enzymy próbie z panelem nienaturalnych substratów — pochodnymi indolu, innym partnerem o charakterze alkoholowym oraz związkiem fluorowanym używanym w produkcji leków. Naturalne wersje TrpB są zwykle wybredne: silnie preferują swoje natywne substraty i wykazują niewielką aktywność wobec takich alternatyw. Co zaskakujące, enzymy wygenerowane przez AI były często bardziej „przedsiębiorcze”. Dla każdego testowanego nienaturalnego substratu przynajmniej jeden projekt GenSLM wykazał mierzalną aktywność, a wiele działało lepiej niż enzymy naturalne. Ponownie wariant 230 wyróżniał się, przekształcając wszystkie siedem alternatywnych substratów z wydajnościami od umiarkowanych do niemal całkowitych — zakres „promiskuity” wcześniej nieobserwowany w tej rodzinie enzymów. Jednak gdy badacze porównali 230 z jego najbliższym naturalnym krewnym — różniącym się zaledwie w 78 z 400 pozycji aminokwasowych — odkryli, że enzym naturalny nie miał tej wszechstronności, mimo że jego ogólna struktura i kluczowe reszty w miejscu aktywnym były niemal identyczne.
Co to oznacza dla przyszłej zielonej chemii
Dla osoby niespecjalizującej się kluczowy przekaz jest taki, że model AI trenowany wyłącznie na istniejących sekwencjach DNA może wyobrazić realistyczne nowe enzymy, których natura nigdy nie próbowała — niektóre z nich są lepszymi narzędziami dla chemii niż obecnie używane. Te zaprojektowane przez AI warianty TrpB zachowują zasadniczy kształt i funkcję swoich naturalnych krewnych, ale zyskują niezwykłą zdolność obsługi wielu różnych substratów. Taka elastyczność może drastycznie zmniejszyć ilość pracy laboratoryjnej potrzebnej do odkrywania enzymatycznych dróg prowadzących do nowych leków i innych produktów. W miarę jak projektowanie, synteza DNA i testowanie będą szybsze i tańsze, podobne modele generatywne mogą zmienić odkrywanie enzymów z powolnego poszukiwania skarbów w szybkie, rutynowe zadanie projektowe, pomagając przesunąć coraz więcej chemii przemysłowej w stronę czystszych procesów zasilanych przez enzymy.
Cytowanie: Lambert, T., Tavakoli, A., Dharuman, G. et al. Sequence-based generative AI design of versatile tryptophan synthases. Nat Commun 17, 1680 (2026). https://doi.org/10.1038/s41467-026-68384-6
Słowa kluczowe: inżynieria enzymów, generatywna AI, projektowanie białek, syntaza tryptofanu, biokataliza