Clear Sky Science · pl
Biochemiczne zasady rozpoznawania przez miRNA u muszek
Malutkie RNA, które kierują komórkami muszek
W każdej komórce muszki owocowej drobne cząsteczki zwane microRNA działają jak inspektorzy kontroli jakości, decydując, które komunikaty genetyczne zostaną zamienione na białko, a które zostaną wyciszone. W tym badaniu zadano pozornie proste pytanie: w jaki dokładnie sposób te microRNA rozpoznają swoje cele u muszek? Odpowiadając na nie, autorzy przybliżają nas do możliwości przewidywania wyłącznie na podstawie sekwencji, które geny zostaną podniesione lub przyciszone podczas rozwoju, zachowań czy chorób.
Jak małe RNA osłabiają ekspresję genów
MicroRNA to krótkie fragmenty RNA, długości około 22 nukleotydów, które w muszkach łączą się z białkiem zwanym Argonaute 1 (Ago1). Razem przeszukują znacznie dłuższe mRNA, niosące instrukcje do produkcji białek. Gdy microRNA znajdzie częściowo pasujący odcinek na mRNA, kompleks Ago1 może albo przeciąć mRNA, albo zablokować jego translację na białko, zmniejszając w ten sposób produkcję genu. U ssaków zasady rozpoznawania zostały zmapowane w dużym szczególe, ujawniając zaskakującą różnorodność sposobów, w jakie microRNA przyczepiają się do swoich celów. W przeciwieństwie do tego, reguły u muszek były mniej jasne, mimo że microRNA kontrolują tam kluczowe procesy, takie jak wzrost, timing rozwoju i dobowe cykle snu i czuwania.
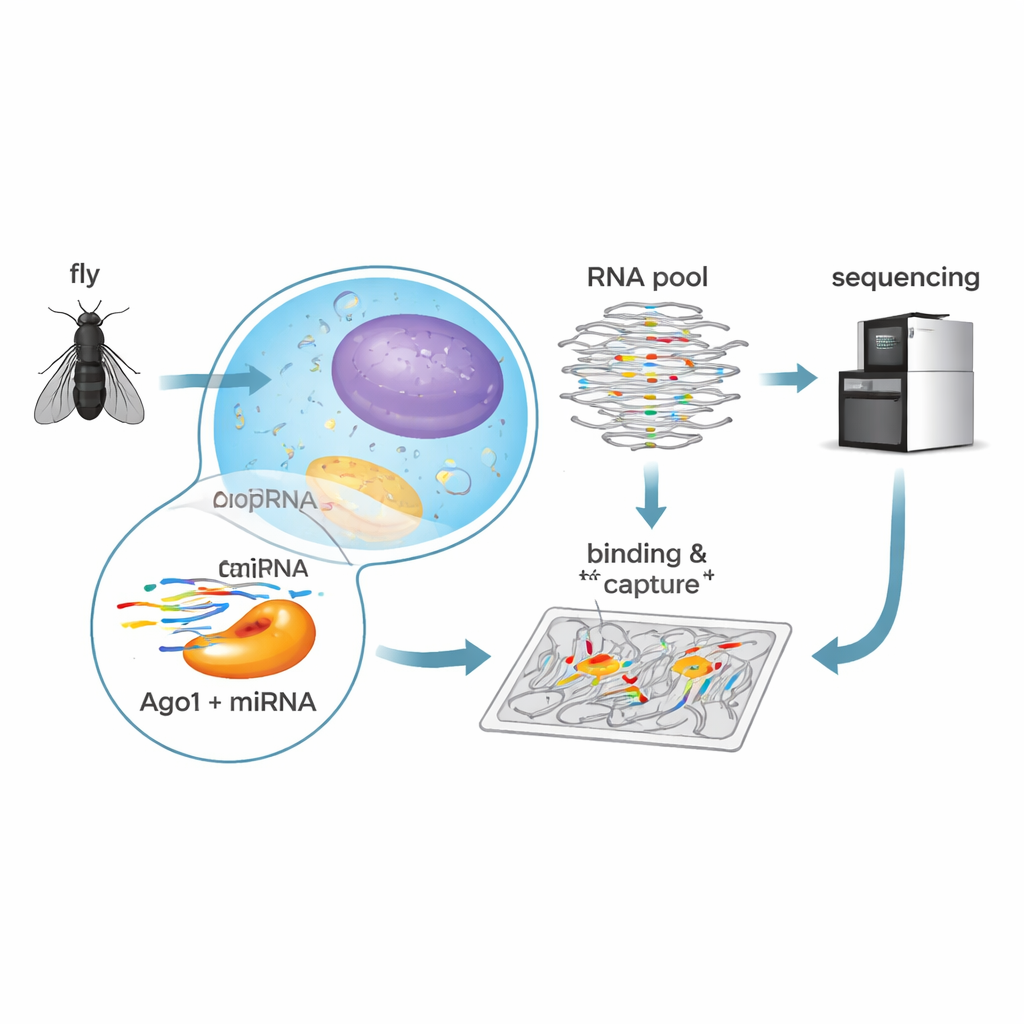
Wysokoprzepustowy test wiązania
Aby rozszyfrować te zasady u muszek, badacze zastosowali biochemiczną metodę nazwaną RNA Bind-n-Seq. Załadowali oczyszczone Ago1 muszki jednym z pięciu obfitych microRNA — let-7, bantam, miR-184, miR-11 lub miR-124 — z których każdy ma udokumentowane role w rozwoju i funkcjonowaniu mózgu muszek. Następnie wymieszali każdy kompleks Ago1–microRNA z ogromną biblioteką syntetycznych RNA zawierających losowe sekwencje. Po umożliwieniu zajścia wiązaniu oddzielili związane od niezwiązanych RNA, zsekwencjonowali związane cząsteczki i użyli modelowania statystycznego, by obliczyć, jak silnie rozpoznawany jest każdy typ sekwencji. Takie podejście dostarczyło ilościowych miar siły wiązania dla setek różnych wzorców celów w jednym zestawie eksperymentów.
Proste reguły z kilkoma sprytnymi wyjątkami
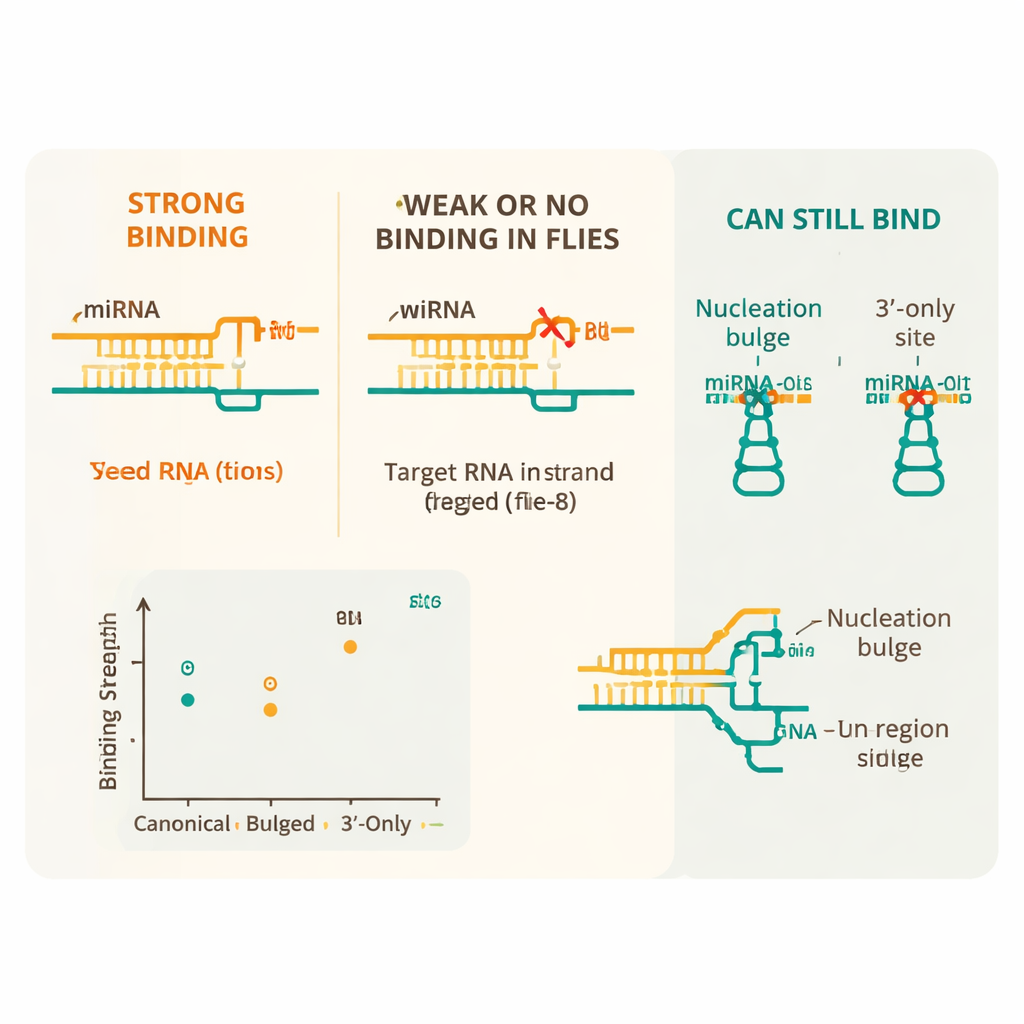
Wyniki pokazują, że microRNA u muszek przestrzegają bardziej rygorystycznego zestawu zasad niż ich odpowiedniki u ssaków. Najważniejszym elementem jest region „ziarna” (seed) — pozycje 2 do 8 microRNA — który musi niemal idealnie parować z mRNA, by wystąpiło silne wiązanie. Kanoniczne miejsca dopasowane do seeda, zwłaszcza te z ośmioma dopasowanymi nukleotydami i pewnym sąsiednim nukleotydem, wiązały się z najwyższą afinnością. Natomiast nawet pojedyncze niestandardowe parowanie niewłaściwego typu (tzw. para G:U) w obrębie seeda znacznie osłabiało wiązanie, a dwie lub więcej takich niedoskonałości powodowały, że interakcja była nieodróżnialna od tła. Niedopasowania pośrodku seeda były szczególnie szkodliwe, podkreślając, jak czułe jest Ago1 na odczytanie tego kluczowego segmentu.
Ukryta elastyczność poza jądrem dopasowania
Mimo tej ogólnej sztywności badanie ujawniło kilka ważnych „zaworów bezpieczeństwa”, które pozwalają niektórym niedoskonałym miejscom być nadal rozpoznawanym. Dodatkowe parowanie między końcem ogonowym microRNA a mRNA mogło zrekompensować pojedynczą wadę w seedzie, przywracając silne wiązanie. Pewne specjalne układy, zwane nucleation bulges — gdzie dodatkowy nukleotyd wystaje w pobliżu seeda — również wiązały się prawie tak dobrze jak standardowe miejsca. Zespół pokazał ponadto, że Ago1 potrafi wiązać „tylko 3′” miejsca, w których seed nie bierze udziału, ale ogon microRNA paruje silnie, oraz że może efektywnie przecinać cele z długimi centralnymi dopasowaniami. Wreszcie wykazali, że kontekst sekwencji ma znaczenie: miejsca otoczone regionami bogatymi w A i U, które zwykle utrzymują RNA w stanie mniej zstrukturakowanym i bardziej dostępnym, wiązały się silniej niż te same miejsca zanurzone w bardziej sztywnym kontekście sekwencji.
Dlaczego te zasady mają znaczenie dla biologii muszek
Podsumowując, wyniki pokazują, że microRNA u muszek zwykle wymagają niemal doskonałego dopasowania w regionie seeda, z jedynie ograniczonym zestawem tolerowanych wyjątków. Ten prostszy i bardziej restrykcyjny zestaw reguł kontrastuje z szerszą elastycznością obserwowaną u ssaków. Dostarczając twardych danych na temat siły wiązania różnych wzorców celów, praca tworzy podstawy pod narzędzia komputerowe nowej generacji, które będą mogły dokładniej przewidywać, które geny muszek będą kontrolowane przez które microRNA. Dla laików kluczowy wniosek jest taki, że regulacja genów u muszek, choć kierowana przez malutkie RNA, opiera się na klarownych zasadach biochemicznych — zasadach, które teraz można wykorzystać do zrozumienia i ostatecznie manipulowania złożonymi cechami, takimi jak rozwój, zachowanie i odporność na choroby.
Cytowanie: Vega-Badillo, J., Zamore, P.D. & Jouravleva, K. Biochemical principles of miRNA targeting in flies. Nat Commun 17, 1641 (2026). https://doi.org/10.1038/s41467-026-68360-0
Słowa kluczowe: microRNA, Drosophila, Argonaute, RNA binding, gene regulation