Clear Sky Science · pl
Zintegrowany atlas multi-omiczny ujawnia hierarchię czasoprzestrzennych sieci regulacyjnych podczas gastrulacji myszy
Jak zarodek buduje plan ciała
Każdy ssak, łącznie z człowiekiem, zaczyna życie jako maleńka kula komórek, która musi szybko zorganizować się w złożone ciało z głową, ogonem, grzbietem, brzuchem i narządami wewnętrznymi. Ta dramatyczna przebudowa zachodzi w krótkim oknie zwanym gastrulacją. Artykuł podsumowany tutaj tworzy szczegółową, wielowarstwową mapę tego procesu w zarodkach myszy, pokazując, jak geny, elementy przełącznikowe DNA i sygnały chemiczne współdziałają w przestrzeni i czasie, kierując komórki ku ich przyszłym losom.
Obserwowanie tysięcy komórek dokonujących wyborów
Aby śledzić gastrulację in statu nascendi, badacze przeanalizowali ponad 35 000 pojedynczych komórek z zarodków myszy obejmujących pięć blisko osadzonych stadiów, od wczesnej do późnej gastrulacji. Dla każdej komórki zmierzono nie tylko, które geny są aktywne, ale także, które fragmenty DNA są otwarte i dostępne — co świadczy, że mogą pełnić funkcję przełączników regulacyjnych. Na podstawie tych danych zidentyfikowano 31 odrębnych typów komórek i odtworzono, jak wczesne, plastyczne komórki stopniowo rozgałęziają się na trzy główne listki zarodkowe — ektodermę, mezodermę i endodermę — które ostatecznie tworzą wszystkie tkanki i narządy. Opracowano też nową metodę obliczeniową, BioCRE, pozwalającą precyzyjniej łączyć geny z ich kontrolującymi elementami DNA, co ujawniło, że wiele ważnych przełączników znajduje się daleko od genów, które regulują.
Budowanie trójwymiarowego atlasu molekularnego w rzeczywistej przestrzeni zarodka
Większość metod single-cell traci pierwotne położenie każdej komórki w zarodku, a lokalizacja jest kluczowa dla zrozumienia patterningu. Zespół przezwyciężył to, dopasowując swoje dane pojedynczych komórek do istniejącej trójwymiarowej mapy aktywności genów w zarodkach myszy. Wynikiem jest ST-MAGIC — „cyfrowy zarodek”, w którym każdemu małemu punktowi przypisano prawdopodobne typy komórek, geny, które one wyrażają, oraz dostępność otaczającego DNA. Ten atlas pokazuje na przykład, jak różne podtypy mezodermy — przyszłe serce, mięśnie i tkanki podporowe — wyłaniają się w odrębnych regionach oraz jak szeroko wyrażane geny, takie jak Otx2, wykorzystują różne elementy regulacyjne na zewnętrznej (epiblast) i wewnętrznej (endoderma trzewna) powierzchni zarodka.
Gdy symetria pęka i lewa strona różni się od prawej
Jedną z uderzających cech planów ciała jest to, że strony lewe i prawe nie są identyczne — pomyśl o sercu osadzonym nieco po lewej stronie. Autorzy wykorzystali swój atlas przestrzenny, aby przyjrzeć się mezodermie bocznej, gdzie po raz pierwszy pojawiają się różnice lewo‑prawo. Stwierdzili subtelne, lecz spójne asymetrie w tym, które typy komórek są wzbogacone po której stronie oraz w tym, które regiony DNA są bardziej otwarte. Po prawej stronie bardziej dostępne były regiony związane ze ścieżką sygnałową wzrostu zwaną BMP; po lewej dominowały regiony powiązane z genami potrzebnymi do formowania segmentów i struktur serca. Niektóre z tych elementów DNA, w tym nowo odkryte regulatory genu Lefty2, stają się otwarte zanim pojawią się widoczne różnice w ekspresji genów, co sugeruje, że wczesne „priming” krajobrazu chromatyny przygotowuje każdą stronę zarodka do odmiennej interpretacji sygnałów.
Sztafeta czynników kieruje osią ciała
Badanie następnie skupia się na mezendodermie osiowej, populacji komórek, które utworzą notochord — prętowatą strukturę biegnącą wzdłuż linii środkowej, pomagającą organizować kręgosłup i układ nerwowy. Korzystając ze swoich zintegrowanych narzędzi (ST-MAGIC oraz rozszerzonej wersji ST-MAGIC (+)), autorzy śledzili, jak te komórki powstają z przedniej prymitywnej szczeliny (anterior primitive streak) i dzielą się na dwa odgałęzienia: komórki węzła, które tworzą rzęskową strukturę ważną dla wykrywania lewo‑prawo, oraz przednią mezendodermę, która wnosi wkład do tkanek linii środkowej. Odkryli hierarchiczną sztafetę czynników transkrypcyjnych — białek kontrolujących aktywność genów. Wczesne czynniki, takie jak EOMES, oraz czynniki pośrednie, w tym FOXA2 i LHX1, najpierw otwierają kluczowe regiony DNA i ustanawiają podatność na główne sygnały jak WNT i NODAL. Później „końcowe” czynniki, takie jak NOTO, SOX9 i nowo powiązany czynnik POU6F1, uruchamiają wyspecjalizowane programy genowe, na przykład te potrzebne do tworzenia rzęsek czy macierzy zewnątrzkomórkowej.
Sygnały, chromatyna i specjaliści działający późno
Integrując publiczne zestawy danych o tym, gdzie efektory sygnałów WNT i NODAL wiążą DNA, autorzy pokazali, że podatność zarodka na te sygnały przesuwa się w przestrzeni zanim same źródła sygnałów się przemieści. W regionie przygotowanym do zostania mezendodermą osiową miejsca DNA reagujące na NODAL i WNT otwierają się wcześnie, a wiele z nich zawiera motywy dla FOXA2, Zfp281 i innych regulatorów, co sugeruje kontrolę kooperatywną. Eksperymentalne usunięcie czynników działających późno — NOTO i POU6F1 — u myszy zaburzyło ekspresję genów specyficznych dla węzła i związanych z rzęskami oraz skróciło rzęski węzła, lecz podstawowy, otwarty krajobraz DNA pozostał w dużej mierze niezmieniony. Wskazuje to, że wcześniejsze czynniki ustanawiają epigenetyczne podłoże, podczas gdy czynniki późne głównie doprecyzowują ekspresję genów bez gruntownej przebudowy chromatyny.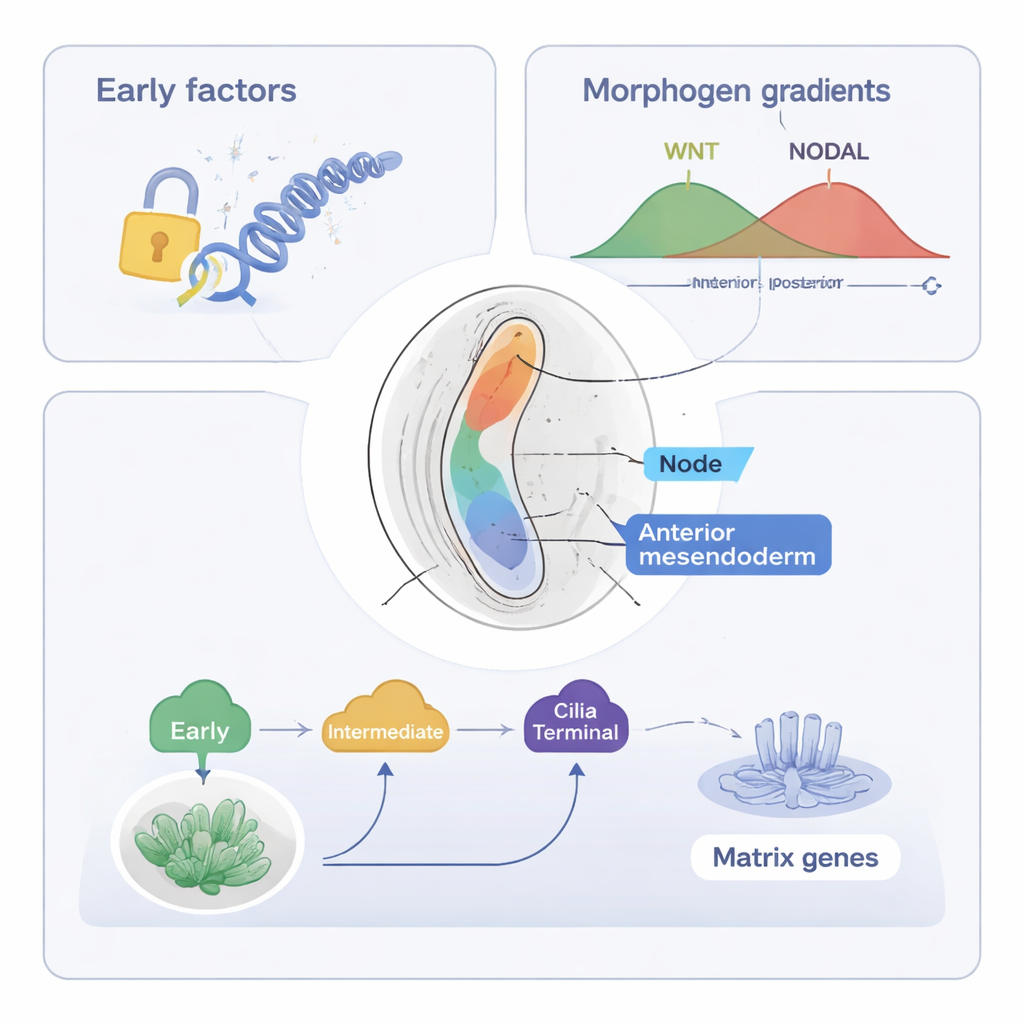
Dlaczego to ważne dla zrozumienia rozwoju
Dla niespecjalisty tę pracę można uznać za budowę wysokorozdzielczego „diagramu okablowania” pokazującego, jak zarodek rozkłada plan ciała. Autorzy pokazują, że decyzje losu komórkowego podczas gastrulacji są rządzone nie tylko przez obecność sygnałów, lecz także przez to, kiedy i gdzie przełączniki DNA są otwierane oraz które czynniki transkrypcyjne działają sekwencyjnie. Ich atlasy ST-MAGIC i ST-MAGIC (+) stanowią zasób do badania tych relacji w przestrzeni i czasie, oferując ramę, która może wspierać badania wad wrodzonych, modeli zarodków opartych na komórkach macierzystych oraz, w przyszłości, aspekty rozwoju człowieka.
Cytowanie: Yang, X., Xie, B., Shen, P. et al. Integrated multi-omic atlas reveals the hierarchy of spatiotemporal regulatory networks of mouse gastrulation. Nat Commun 17, 1572 (2026). https://doi.org/10.1038/s41467-026-68291-w
Słowa kluczowe: gastrulacja, genowe sieci regulacyjne, single-cell multi-omics, patternowanie zarodka, rozwój myszy