Clear Sky Science · pl
Długa droga do wiarygodnych i kompletnych genomów roślin leczniczych
Dlaczego mapy DNA roślin mają znaczenie dla zdrowia ludzi
Wiele z obecnie najsilniejszych leków — od leków przeciwnowotworowych, takich jak paklitaksel, po środki przeciwbólowe, jak morfina, oraz przeciwmalaryczne artemizynę — pochodzi z roślin. Tymczasem dla większości roślin leczniczych naukowcy wciąż nie dysponują kompletnym „manualem instrukcji” ich DNA. Niniejszy przegląd wyjaśnia, jak nowe technologie sekwencjonowania genomu zmieniają naszą zdolność do czytania tych instrukcji, dlaczego istniejące genomy roślin często są wciąż niekompletne lub wadliwe oraz jak naprawdę dokładne genomy mogą odblokować lepsze leki, bardziej zrównoważoną produkcję i lepszą ochronę cennych gatunków.
Obietnica odczytania planów roślin leczniczych
Od tysiącleci ludzie polegają na środkach ziołowych, a współczesna farmakologia nadal czerpie obficie z produktów naturalnych roślin. Te specjalistyczne cząsteczki — alkaloidy, terpenoidy, związki fenolowe i wiele innych — powstają dzięki złożonym szlakom metabolicznym kodowanym w DNA roślin. Jeszcze niedawno naukowcy musieli składać te szlaki przy użyciu powolnych, pracochłonnych metod, takich jak śledzenie izotopów czy klonowanie gen po genie. Pojawienie się przystępnego, wysokowydajnego sekwencjonowania DNA zmieniło sytuację. Do lutego 2025 r. zsekwencjonowano genomy 431 roślin leczniczych (w ramach 203 gatunków), dając badaczom systematyczny sposób wyszukiwania genów szlaków, rozumienia regulacji cennych związków i badania ewolucji tych chemii.
Boom sekwencjonowania, ale wiele niedoskonałych genomów
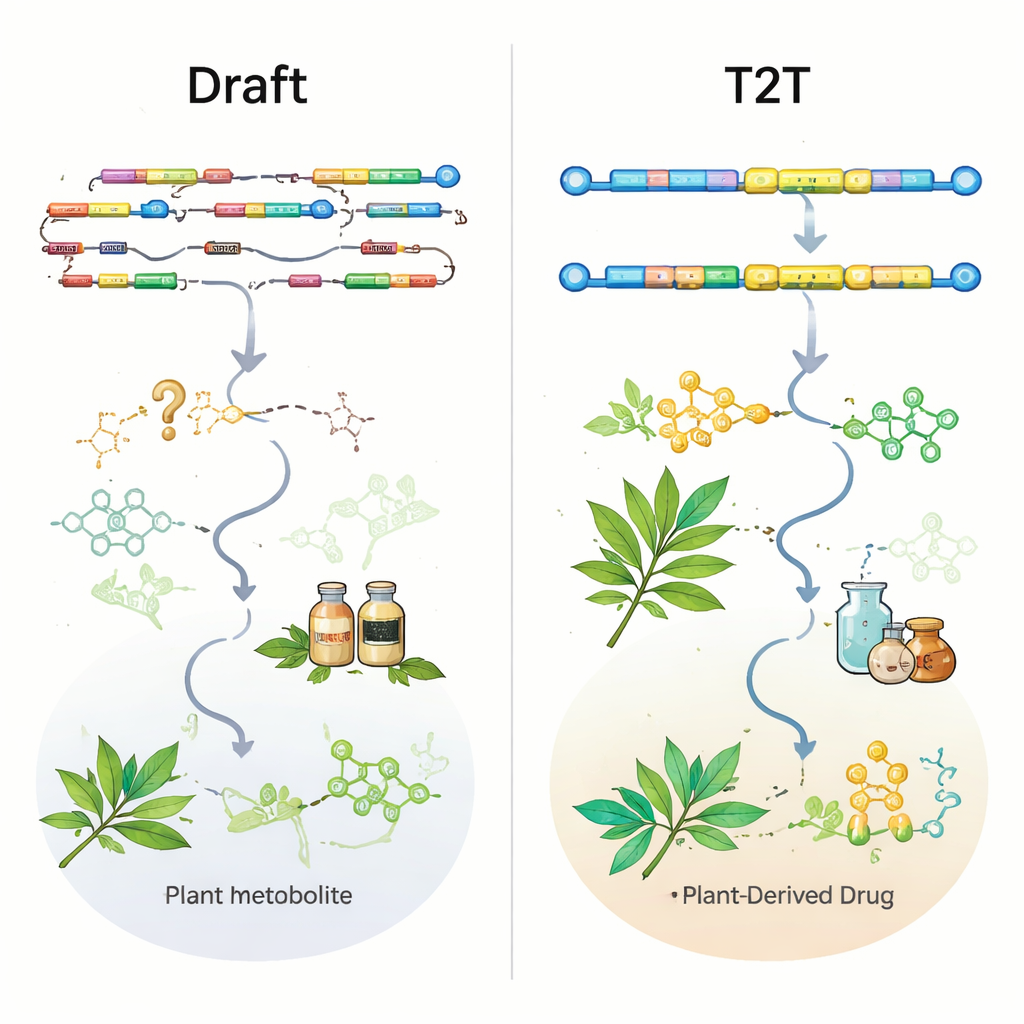
Technologie sekwencjonowania długich odczytów od PacBio i Oxford Nanopore, łączone z danymi krótkich odczytów Illumina i metodami mapowania na poziomie chromosomów, takimi jak Hi‑C, znacząco poprawiły jakość genomów roślin. Niemal połowa wszystkich złożeń genomów roślin leczniczych ukazała się w ciągu zaledwie ostatnich trzech lat, a większość nowszych genomów jest już budowana w skali chromosomowej. Jednak przegląd pokazuje, że liczba przewyższa jakość. Ponad połowa genomów istnieje jedynie jako wersja początkowa, wiele pozostaje na poziomie szkicu, a tylko 11 roślin leczniczych ma bezszwowe złożenia „od telomeru do telomeru” (T2T) obejmujące centromery i inne regiony powtarzalne. Standardowe metryki, takie jak N50 (miara ciągłości) i wyniki BUSCO (miara zachowanych genów), ogólnie wyglądają obiecująco, ale mogą maskować krytyczne luki dokładnie tam, gdzie znajdują się kluczowe geny biosyntetyczne.
Ukryte luki tam, gdzie powinny być geny lekotwórcze
Aby sprawdzić, jak użyteczne są obecne genomy, autorzy przeanalizowali znane, eksperymentalnie zweryfikowane geny szlaków w dziewięciu dobrze zbadanych roślinach leczniczych. Nawet w niektórych złożeniach na poziomie chromosomów ważne enzymy dla związków takich jak ginsenozydy w żeń‑szeniu czy artemizyna w Artemisia annua były albo całkowicie brakujące, albo tylko częściowo uchwycone. W innych przypadkach geny były obecne w surowej sekwencji genomu, ale brakowało ich lub były skrócone w oficjalnych adnotacjach genów, co utrudniało ich odnalezienie. Uderzający przykład pochodzi od zioła produkującego kumaryny, Peucedanum praeruptorum: starszy genom na poziomie chromosomów złamał jeden kluczowy gen i przegapił dwa inne; nowsze złożenie T2T przywróciło te geny i dodatkowo ujawniło, że kilka z nich siedzi razem w ciasno upakowanym skupisku genów biosyntetycznych. Tego rodzaju mapa skupiska jest dokładnie tym, czego potrzebują badacze, aby inżynierować rośliny lub mikroby do bardziej efektywnej produkcji leków.
Dlaczego genomy roślin są tak trudne do złożenia
Rośliny lecznicze stawiają szczególne wyzwania wykraczające poza problemy wielu gatunków uprawnych. Ich genomy często cechują się wysokim poziomem heterozygotyczności (wiele różnic DNA między dwiema kopiami każdego chromosomu), częstą poliploidią (wiele zestawów chromosomów) oraz dużymi frakcjami DNA powtarzalnego — cechami, które mylą algorytmy składania i prowadzą do przerw lub błędnych połączeń. Około jedna trzecia zsekwencjonowanych roślin leczniczych ma genom z ponad 70% zawartością elementów powtarzalnych, a ponad jedna czwarta wykazuje bardzo wysoką heterozygotyczność. Hodowanie silnie inbredowanych linii lub izolowanie tkanki haploidalnej może pomóc, ale jest to wolne, kosztowne lub biologicznie trudne dla wielu gatunków. Nowe strategie składające oddzielnie haplotypy rodzicielskie oraz potężniejsze algorytmy dostrojone do genomów bogatych w powtórzenia i poliploidalnych zaczynają zmniejszać te przeszkody, ale nie są jeszcze rutyną.
Od genomów do nowych leków i kierunków na przyszłość
Kiedy genomy są wystarczająco dobre, stają się potężnymi silnikami odkryć. Badacze mogą łączyć dane całogenomowe z transkryptomiką, metabolomiką i biologią syntetyczną, by precyzyjnie lokalizować enzymy, geny regulacyjne i skupiska genów biosyntetycznych kontrolujących produkcję wysoko wartościowych związków. Te wnioski już umożliwiły rekonstrukcję złożonych ścieżek roślinnych — takich jak dla winblastyny, paklitakselu i wielu innych leków — w drożdżach lub roślinach modelowych, otwierając drogę do stabilnej, dużej skali bioprodukcji. Patrząc w przyszłość, autorzy postulują przesunięcie od „jednego zgrubnego genomu na gatunek” do wielu, wysokiej jakości, T2T i rozdzielonych haplotypowo złożeń, które uchwycą różnorodność wewnątrzgatunkową, podobnie jak pangenomy w badaniach roślin uprawnych. Połączenie tych genomów referencyjnych z szeroko zakrojonym resekwencjonowaniem, zaawansowanym fenotypowaniem oraz pojawiającą się transkryptomiką jednokomórkową i przestrzenną powinno rozświetlić, jak środowisko, typ komórki i sieci genowe współdziałają, kształtując chemię leczniczą.
Co to oznacza dla pacjentów i planety
Główny przekaz przeglądu jest taki, że wiarygodne, kompletne genomy roślin leczniczych nie są luksusem; są fundamentem przekształcenia wielowiekowej wiedzy ziołowej w precyzyjne, nowoczesne terapie. Lepsze genomy pomogą naukowcom odnaleźć brakujące etapy w ścieżkach lekotwórczych, zaprojektować bezpieczniejsze i obfitsze źródła krytycznych leków oraz zidentyfikować alternatywne gatunki zdolne do produkcji tych samych związków. Poprowadzą też działania ochronne i zrównoważonego wykorzystania zagrożonych roślin leczniczych, z których większość wciąż nie ma żadnych zasobów genomowych. Krótko mówiąc, dokończenie pracy polegającej na dokładnym mapowaniu tych genomów może przyspieszyć odkrywanie leków, ustabilizować łańcuchy dostaw i zachować różnorodność botaniczną — a to wszystko ostatecznie przynosi korzyści zdrowiu ludzi.
Cytowanie: Cheng, LT., Wang, ZL., Zhu, QH. et al. A long road ahead to reliable and complete medicinal plant genomes. Nat Commun 16, 2150 (2025). https://doi.org/10.1038/s41467-025-57448-8
Słowa kluczowe: genomika roślin leczniczych, skupiska genów biosyntetycznych, genomy od telomeru do telomeru, biosynteza produktów naturalnych, biologia syntetyczna