Clear Sky Science · pl
Funkcjonalne ślady niedoboru homologicznej rekombinacji w raku prostaty ujawnione przez fragmentację ctDNA i dostępność czynników transkrypcyjnych
Dlaczego to ma znaczenie dla pacjentów z rakiem
Wielu mężczyzn z zaawansowanym rakiem prostaty mogłoby odnieść korzyść z leków wykorzystujących słabości w mechanizmach naprawy DNA ich nowotworów. Dziś jednak lekarze często nie rozpoznają dobrze, kto zareaguje, ponieważ badania zwykle wymagają trudnych biopsji tkankowych i koncentrują się tylko na kilku genach. To badanie pokazuje, jak proste pobranie krwi można przekształcić w bogaty, wielowarstwowy odczyt tych defektów naprawy DNA, co może prowadzić do precyzyjniejszych i łagodniejszych wyborów terapeutycznych.
Nowy sposób czytania sygnałów nowotworowych z krwi
Naukowcy skupili się na konkretnym problemie naprawy, zwanym niedoborem homologicznej rekombinacji (HRD), który czyni guzy szczególnie wrażliwymi na leki takie jak inhibitory PARP i na niektóre chemioterapie. Zamiast polegać na próbkach guza pobieranych z kości lub tkanki prostaty, analizowali fragmenty DNA guza unoszące się we krwi, znane jako krążące DNA nowotworowe. Spośród 375 mężczyzn z przerzutowym rakiem prostaty wybrali 106, których krew zawierała wystarczająco dużo takiego DNA, by przeprowadzić dogłębne analizy, i zastosowali kilka komplementarnych testów do tych samych próbek osocza.
Wyjście poza pojedyncze mutacje genowe
Pierwotnie zsekwencjonowali panel kluczowych genów naprawy DNA, w tym dobrze znane BRCA2, BRCA1 i PALB2, wraz z innymi genami kształtującymi agresywność raka prostaty. BRCA2 okazał się najczęściej zmienionym genem naprawy i często współwystępował z utratą innych ważnych strażników, takich jak PTEN i RB1. Zespół zbadał również duże zmiany struktury chromosomów w całym genomie, wykorzystując niskozagęszczoną sekwencjonowanie całego genomu do obliczenia wskaźnika niestabilności genomu. Guzy z uszkodzonymi genami BRCA lub z wysokimi wynikami miały silnie zrestrukturyzowane genomy i wiązały się z gorszym przeżyciem ogólnym, co podkreśla, że duże zmiany strukturalne mogą być równie informatywne co konkretne mutacje.
Ślady porażki naprawy w wzorcach mutacji
W podgrupie pacjentów naukowcy pogłębili analizę, sekwencjonując wszystkie regiony kodujące białka, aby odczytać szczegółowy wzór mutacji narastających w czasie. Pewne kombinacje zmian zasad azotowych oraz małych insercji i delecji działają jak odciski palców procesów, które je wygenerowały. Stwierdzili, że klasyczne sygnatury powiązane z HRD, takie jak SBS3 czy wzorzec indeli znany jako ID6, były wzbogacone w guzach z defektami genów naprawy i wysoką niestabilnością genomu. Inne sygnatury wskazywały na odrębne problemy, jak brak działania mechanizmu naprawy niedopasowań (MMR) lub wyraźny podtyp napędzany przez CDK12, podkreślając, że różne załamania naprawy DNA zostawiają rozpoznawalnie różne ślady w genomie.
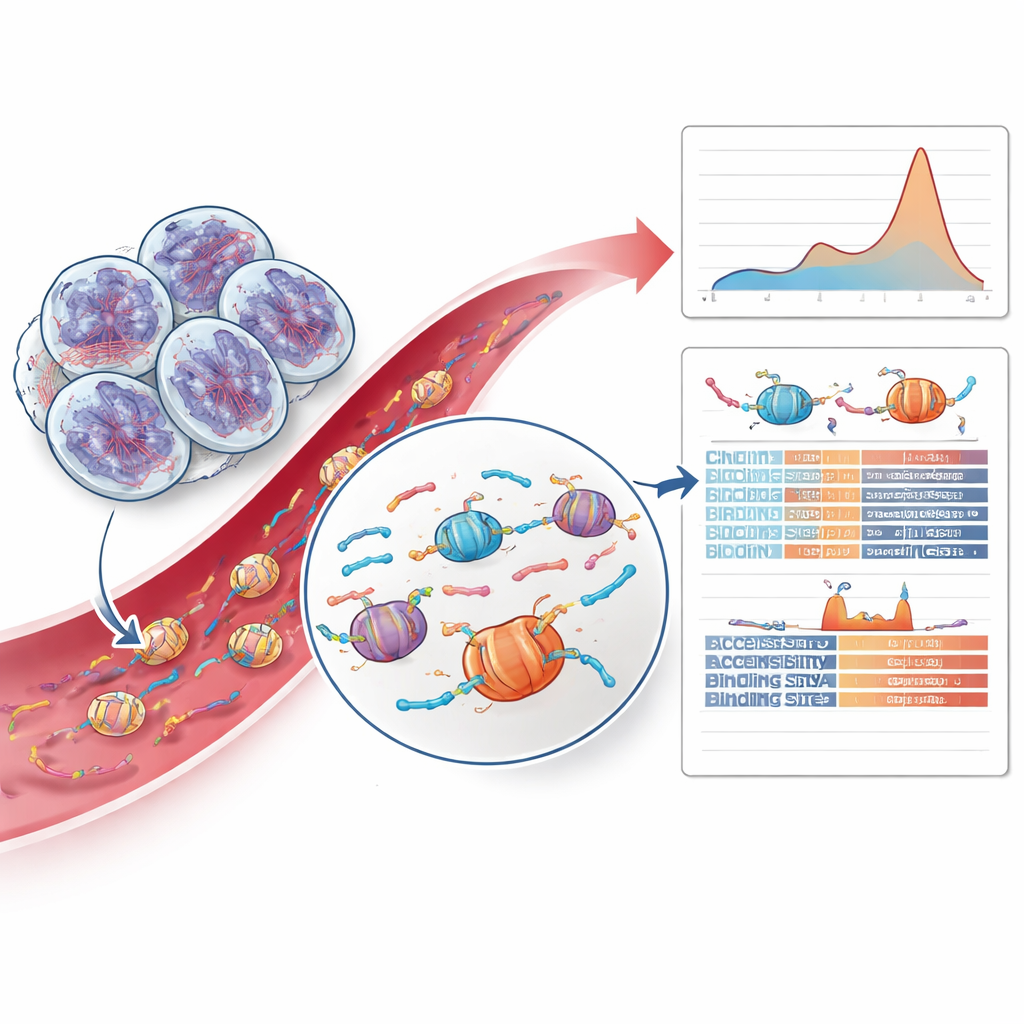
Odczytywanie wzorców fragmentów DNA i wskazówek chromatynowych
Najbardziej innowacyjna część pracy poszła poza analizę mutacji i zbadała, jak fragmenty DNA nowotwora są cięte. Gdy komórki obumierają, ich DNA jest cięte wokół białkowych pakietów zwanych nukleosomami, tworząc fragmenty o charakterystycznych długościach i wzorcach końcowych. Zespół odkrył, że guzy z HRD wykazywały względny nadmiar nieco dłuższych fragmentów odpowiadających dwóm nukleosomom — przesunięcie nieobserwowane w innych rakach prostaty ani u zdrowych kontrolnych osób. Trenując ostrożny model uczenia maszynowego na długościach fragmentów i cechach końców fragmentów, byli w stanie wyodrębnić przypadki HRD z samej krwi z obiecującą dokładnością. Badali także dostępność różnych regionów genomu wokół miejsc wiązania czynników transkrypcyjnych — białek kontrolujących aktywność genów — i odkryli, że niektóre miejsca wiązania palca cynkowego były mniej dostępne w guzach HRD, sugerując głębsze, związane z naprawą zmiany w organizacji chromatyny.
Co to może oznaczać dla pacjentów
Razem te warstwy informacji — od konkretnych mutacji genowych i dużych przetasowań chromosomów po subtelne przesunięcia w rozmiarze fragmentów DNA i dostępności chromatyny — tworzą pełniejszy obraz słabości mechanizmów naprawy DNA w raku prostaty. Dla osoby postronnej kluczowe przesłanie jest takie, że dokładnie przeanalizowana próbka krwi może ujawnić nie tylko, czy znany gen jak BRCA2 jest zmutowany, ale także czy guz zachowuje się jak taki z poważnym defektem naprawy, nawet gdy standardowe testy wypadają normalnie. Jeśli podejście to zostanie potwierdzone w większych i bardziej zróżnicowanych grupach pacjentów, wielomodalny test oparty na krwi mógłby pomóc lekarzom bardziej niezawodnie identyfikować osoby, które prawdopodobnie skorzystają z inhibitorów PARP lub leków platynowych, monitorować zmiany w czasie i ostatecznie personalizować terapię za pomocą prostego, powtarzalnego badania.
Cytowanie: Vlachos, G., Moser, T., Lazzeri, I. et al. Functional footprints of homologous recombination deficiency in prostate cancer revealed by ctDNA fragmentation and transcription factor accessibility. Br J Cancer 134, 949–960 (2026). https://doi.org/10.1038/s41416-025-03301-0
Słowa kluczowe: rak prostaty, biopsja płynna, naprawa DNA, krążące DNA nowotworowe, inhibitory PARP