Clear Sky Science · nl
Genomisch landschap van antimicrobiële resistentie in India: bevindingen uit een multispecies surveillancestudie
Waarom superbugs in India ons allemaal aangaan
Antibioticaresistente “superbugs” vormen een groeiende wereldwijde zorg, maar we weten nog verrassend weinig over hoe deze ziekteverwekkers evolueren en zich verspreiden in veel delen van de wereld. Deze studie onderzoekt nauwkeurig gevaarlijke bacteriën uit Indiase ziekenhuizen en leest hun volledige DNA om te begrijpen hoe ze onze krachtigste geneesmiddelen te slim af zijn. De resultaten onthullen niet alleen wat deze microben zo moeilijk te doden maakt, maar toetsen ook of snelle DNA-gebaseerde methoden betrouwbaar langzamere labtesten kunnen vervangen — een kwestie die van invloed kan zijn op de behandeling van infecties overal.
Nader onderzoek naar ziekenhuisinfecties
Onderzoekers verzamelden 266 bacteriële monsters van ernstig zieke patiënten in grote ziekenhuizen in Noord- en West-India tussen 2022 en 2024. De meeste monsters kwamen uit bloed, maar ook uit urine en longinfecties; de meerderheid was afkomstig van intensivecareafdelingen, waar patiënten het meest kwetsbaar zijn. Het team richtte zich op bekende probleemverwekkers — zoals Escherichia coli, Klebsiella pneumoniae, Acinetobacter baumannii, Pseudomonas aeruginosa, methicilline‑resistente Staphylococcus aureus (MRSA) en vancomycine‑resistente Enterococcus (VRE). Voor elk monster hadden artsen al standaard antibioticasusceptibiliteitstests uitgevoerd, waarbij bacteriën in het laboratorium aan geneesmiddelen worden blootgesteld om te zien welke middelen nog werken. De wetenschappers sequentieerden vervolgens de genomen van de bacteriën om het volledige assortiment resistentiegenen in kaart te brengen en vergeleken wat het DNA “voorspelde” met wat daadwerkelijk in de proefbuizen gebeurde.
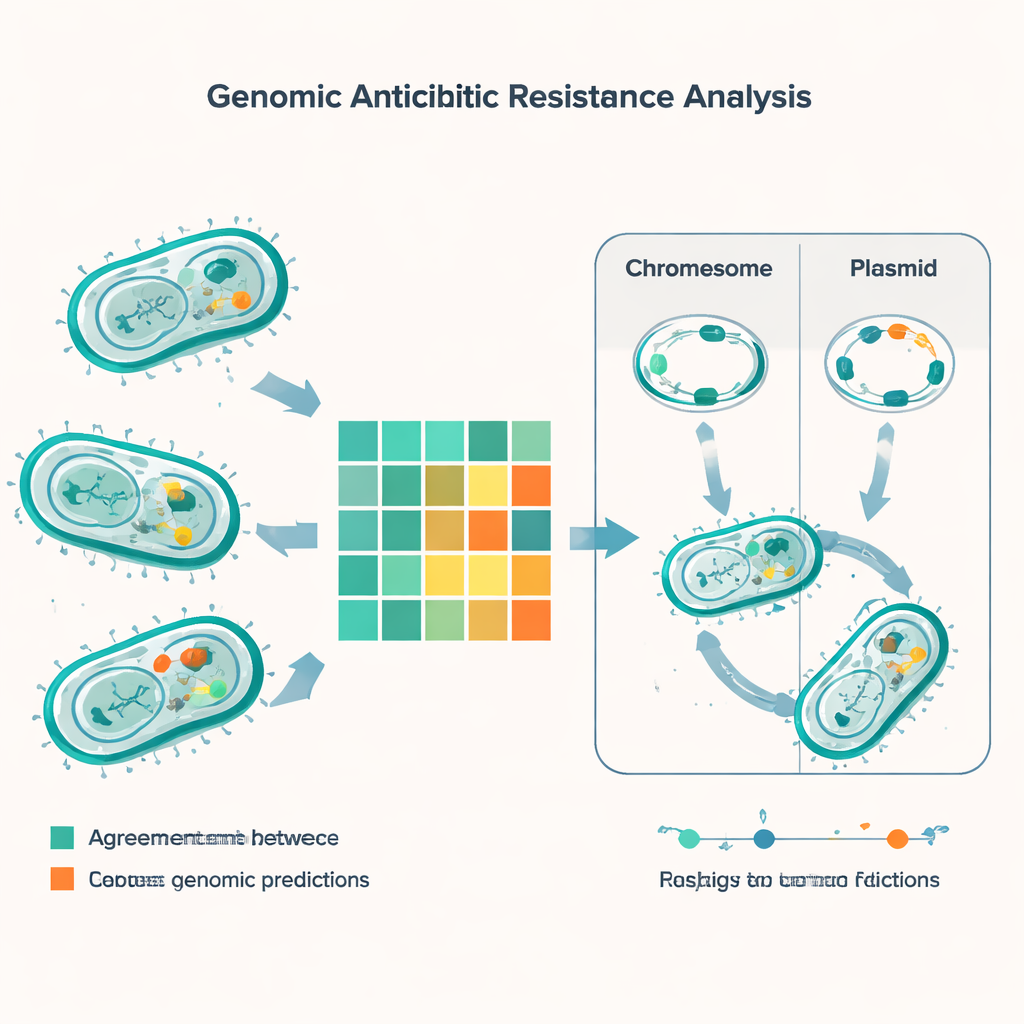
Wanneer genen en proefbuizen het oneens zijn
Door genetische voorspellingen te vergelijken met labresultaten voor 56 verschillende antibiotica voerde de studie meer dan 5.000 vergelijkingen uit. In de meeste gevallen kwamen de DNA‑gebaseerde methode en de traditionele tests overeen, maar bijna 600 discrepanties vielen op. De meest voorkomende fout was dat het genomische instrument voorspelde dat een bacterie resistent zou zijn terwijl de labtest aangaf dat ze nog behandelbaar was. Dit gebeurde vaak voor geneesmiddelen zoals minocycline, colistine en gentamicine, vooral bij E. coli. Het tegenovergestelde — waarbij de labtest resistentie constateerde maar de genen dit niet duidelijk verklaarden — kwam minder vaak voor maar is zorgwekkender, omdat dit risico geeft op gemiste resistentie. Deze “zeer belangrijke” afwijkingen traden opvallend op bij darmgerelateerde bacteriën genaamd enterokokken, met name voor veelgebruikte penicilline-achtige middelen en voor de combinatie trimethoprim‑sulfamethoxazol.
Verborgen arsenaal in bacterieel DNA
De genomische enquête onthulde een dicht arsenaal aan resistentiegenen over de belangrijkste soorten. Elk van de veelvoorkomende gramnegatieve pathogenen droeg ten minste één beta‑lactamasegen, dat penicilline en verwante middelen kan afbreken, en veel stammen hadden meerdere van zulke genen tegelijk. Beruchte boosdoeners zoals NDM‑type carbapenemases — die laatste redmiddelantibiotica neutraliseren — waren wijdverspreid in E. coli, Klebsiella, Acinetobacter en Pseudomonas. De studie vond ook genen die bacteriën helpen te overleven tegen krachtige “peptide” antibiotica zoals colistine, samen met het klassieke mecA-gen dat MRSA resistent maakt tegen methicilline en vancomycineresistentieclusters in enterokokken. Door DNA‑vingerafdrukken die sequentietypes worden genoemd te vergelijken, koppelde het team sommige van deze resistentiegenen aan bekende risicolinies van bacteriën die zich al in India en wereldwijd verspreiden.
Gendeling via mobiel DNA
Een cruciaal onderdeel van het verhaal is niet alleen welke genen bacteriën dragen, maar waar die genen zich bevinden. Veel resistentiegenen zitten op kleine DNA‑cirkelletjes genaamd plasmiden, die bacteriën kunnen uitwisselen als ruilkaartjes. Met gespecialiseerde software voorspelden de onderzoekers ongeveer 1.400 plasmiden in de monsters, met bijzonder hoge diversiteit in E. coli en Klebsiella. In deze soorten bevond zich een groot aandeel van de resistentiegenen — inclusief meerdere kritieke beta‑lactamases — op plasmiden, waardoor ze gemakkelijker tussen stammen en zelfs tussen soorten kunnen worden doorgegeven. Andere resistentietraits waren ingebakken in bacteriële chromosomen, wat betekent dat ze kunnen blijven bestaan zelfs als plasmiden verloren gaan. Het team bracht ook mobiele genetische elementen in kaart — korte DNA‑segmenten die kunnen springen en resistentiegenen met zich mee kunnen dragen — wat nog een route voor snelle verspreiding benadrukt.
Wat dit betekent voor toekomstige behandelingen
Voor niet‑specialisten is de centrale boodschap dat het lezen van bacterieel DNA de strijd tegen superbugs sterk kan ondersteunen, maar dat de technologie nog niet perfect is. De genomische tools neigden ertoe resistentie te “overvoorspellen”, wat veiliger is dan het missen van een gevaarlijke stam maar artsen ertoe kan aanzetten zwaardere middelen te gebruiken dan nodig. Tegelijk lieten een kleiner aantal gevallen zien dat labtesten resistentie detecteerden die de huidige genencatalogi niet volledig konden verklaren, wat belangrijke blinde vlekken in onze kennis onderstreept. Door een gedetailleerde kaart van resistentiegenen, plasmiden en mobiele elementen in Indiase ziekenhuizen op te bouwen, legt deze studie de basis voor betere, snellere DNA‑gebaseerde diagnostiek en meer geïnformeerd antibioticagebruik — niet alleen in India, maar in elke omgeving waar superbugs de moderne geneeskunde bedreigen.
Bronvermelding: Gheewalla, N., Karthikeyan, V., Jadhav, Y. et al. Genomic landscape of antimicrobial resistance in India: findings from a multi-species surveillance study. npj Antimicrob Resist 4, 13 (2026). https://doi.org/10.1038/s44259-026-00185-9
Trefwoorden: antimicrobiële resistentie, genoomsequencing, ziekenhuisinfecties, medicatie-resistente bacteriën, plasmidegemedieerde resistentie