Clear Sky Science · nl
IdentifiHR voorspelt homologe recombinatietekorten bij hooggradig serieuze ovariumcarcinoom via genexpressie
Waarom dit onderzoek belangrijk is voor patiënten met eierstokkanker
Voor mensen met hooggradig serieuze eierstokkanker, een van de dodelijkste vormen van deze ziekte, kunnen behandelingskeuzes van levensbelang zijn. Ongeveer de helft van deze tumoren heeft een zwakte in hoe ze beschadigd DNA herstellen, waardoor ze bijzonder gevoelig zijn voor bepaalde medicijnen die PARP-remmers worden genoemd. De uitdaging is per patiënt vast te stellen of hun tumor deze zwakte heeft. Deze studie introduceert IdentifiHR, een nieuw hulpmiddel dat patronen van genactiviteit leest — in plaats van alleen DNA-mutaties — om te voorspellen welke tumoren gebrekkige DNA-reparatie hebben en het meest van deze gerichte behandelingen kunnen profiteren.
Van DNA-littekens naar genactiviteitspatronen
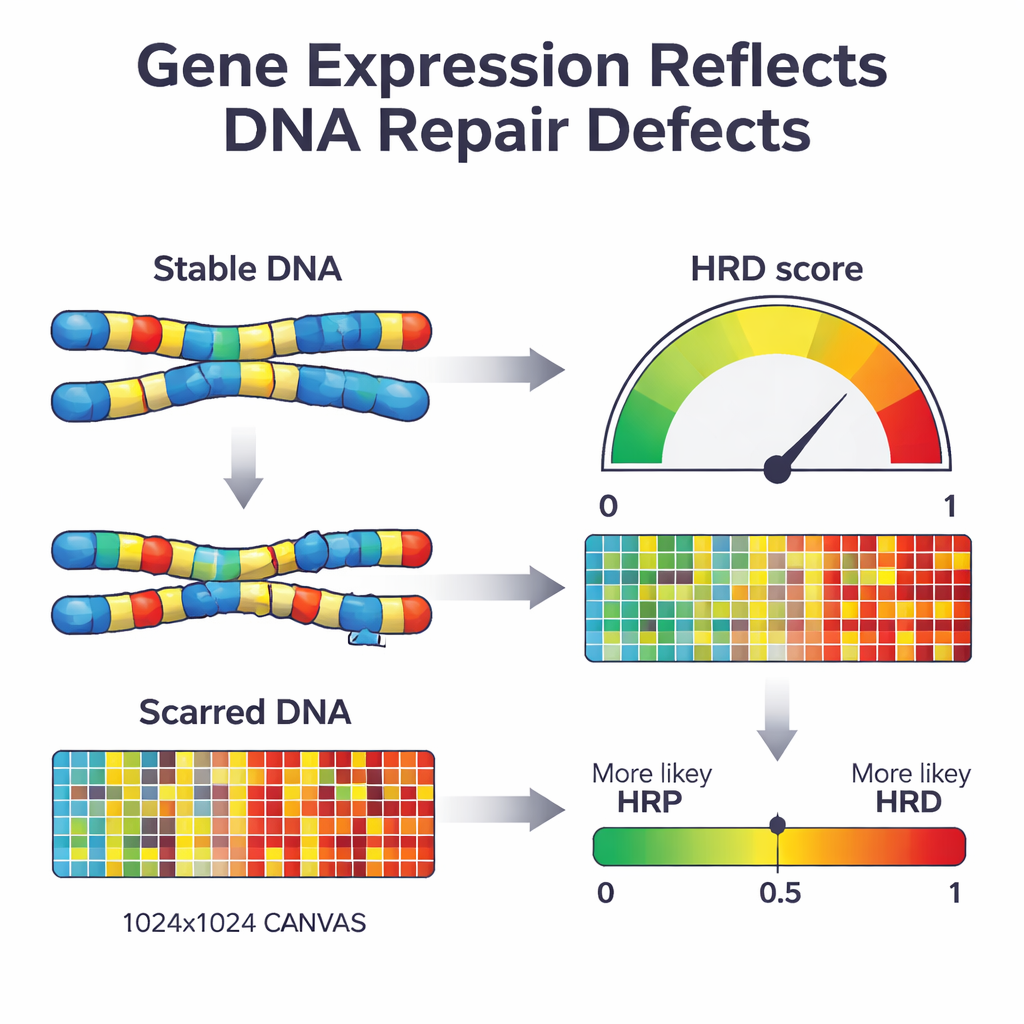
Wanneer een cel een belangrijk reparatiepad verliest dat homologe recombinatie heet, begint ze DNA te herstellen met meer foutgevoelige methoden. Na verloop van tijd laat dit een karakteristiek patroon van "littekens" in het genoom achter — ontbrekende regio’s, extra kopieën en gebroken chromosoomsegmenten. Bestaande klinische tests zoeken deze littekens direct in het DNA of naar specifieke mutaties in sleutelgenen zoals BRCA1 en BRCA2. Hoewel krachtig, vereisen deze tests uitgebreide DNA-sequencing en vangen ze niet altijd de huidige reparatiestatus van de tumor. De auteurs vroegen zich af of een andere biologische laag — het patroon van genen die aan of uit staan in de tumor — als een actuele weergave van deze schade kon dienen en gebruikt kon worden om tumoren als reparatie-deficiënt of reparatie-proficient te classificeren.
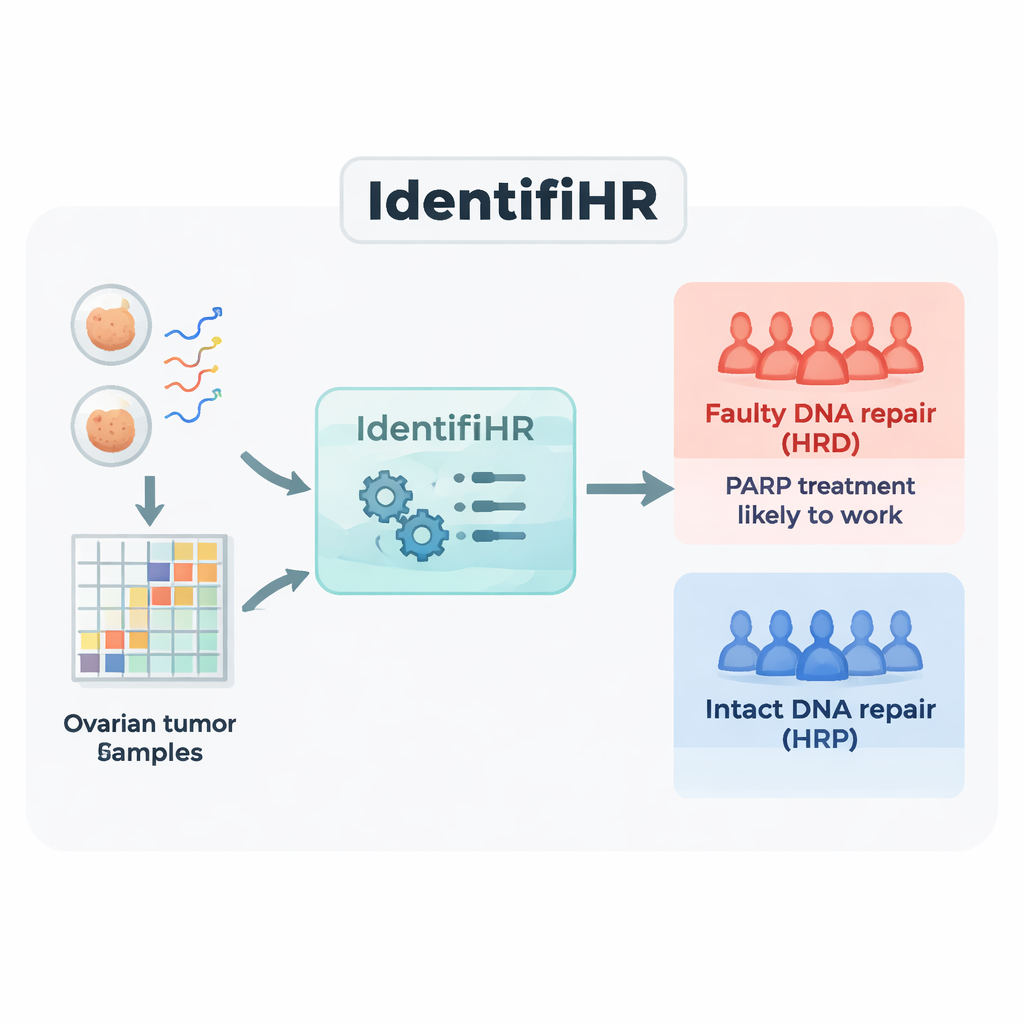
Het bouwen van een gengebaseerde voorspeller, IdentifiHR
Het team begon met RNA-sequencinggegevens van 361 ovariumtumoren uit een grote openbare bron, The Cancer Genome Atlas. RNA-sequencing meet welke genen actief zijn, en in welke mate, in elk monster. Ze verdeelden de tumoren in een trainingsgroep en een testgroep, en labelden elk geval als ofwel reparatie-deficiënt (HRD) of reparatie-proficient (HRP) met gebruik van de huidige DNA-gebaseerde standaard die meerdere maten van genomische littekens combineert. In de trainingsmonsters identificeerden ze 2.604 genen waarvan de activiteit consequent verschilde tussen HRD- en HRP-kankers. Veel van deze genen lagen in regio’s van het genoom die al bekend stonden als herhaaldelijk verloren of gewonnen in reparatiedefecte tumoren, wat laat zien dat het signaal van genactiviteit het onderliggende DNA-schadepatroon weerspiegelde.
Een signatuur van 209 genen die reparatiestatus volgt
Vervolgens gebruikten de onderzoekers een machine-learningbenadering bekend als gepenaliseerde logistische regressie om deze lijst van 2.604 genen terug te brengen tot de meest informatieve set. Het resulterende model, dat zij IdentifiHR noemden, vertrouwt op de activiteit van slechts 209 genen om te schatten hoe waarschijnlijk het is dat een tumor reparatie-deficiënt is. Interessant genoeg is slechts één van deze genen een klassiek DNA-reparatiegen; de meeste zijn gewone genen waarvan de activiteit verandert door bredere veranderingen in chromosoomstructuur. IdentifiHR geeft niet simpelweg een ja-of-nee-label — het produceert een waarschijnlijkheidsscore die vloeiend samenhangt met de onderliggende DNA-gebaseerde schadesscore, wat het idee weerspiegelt dat reparatietekort meer een continuüm is dan een strikt aan/uit-toestand.
Het hulpmiddel testen in meerdere patiëntcohorten
De auteurs testten IdentifiHR rigoureus in drie onafhankelijke datasets die nooit in de training waren gebruikt. In de achtergehouden subset van The Cancer Genome Atlas onderscheidde het model HRD van HRP tumoren correct in ongeveer 85% van de gevallen. Het presteerde net zo goed — rond 86% nauwkeurigheid — in een afzonderlijke Australische studie die niet alleen primaire tumoren omvatte maar ook monsters verkregen bij autopsie, uit vocht in de buikholte (ascites) en uit normale eileiders, de waarschijnlijke locatie waar veel van deze kankers beginnen. In elk normaal eileidermonster voorspelde IdentifiHR correct intacte DNA-reparatie. Het hulpmiddel werkte ook op "pseudobulked" single-cell gegevens, waarbij duizenden individuele kankercellen computationeel werden samengevoegd om een bulkmonster te simuleren, en behaalde opnieuw ongeveer 84% nauwkeurigheid. Over deze tests heen evenaarde of overtrof IdentifiHR de prestaties van verschillende bestaande gengebaseerde methoden die oorspronkelijk voor andere kankers of voor het voorspellen van gerelateerde schadesscores waren ontwikkeld.
Hoe dit onderzoek onderzoek en zorg kan veranderen
Omdat IdentifiHR op RNA-gegevens draait, die vaak goedkoper en gemakkelijker te verzamelen zijn dan whole-genome DNA-profielen, biedt het een praktische manier voor onderzoekers — en mogelijk in de toekomst clinici — om de DNA-reparatiestatus te schatten wanneer alleen genexpressiegegevens beschikbaar zijn. Het model is vrijgegeven als een open-source R-pakket, zodat elke groep met geschikte sequencinggegevens het kan toepassen. Hoewel het nog niet de gouden standaard DNA-tests vervangt en het vermogen om subtielere veranderingen zoals herstel van reparatie vast te leggen nog bestudeerd moet worden, levert IdentifiHR een krachtig nieuw perspectief op welke ovariumtumoren het meest waarschijnlijk reageren op PARP-remmers en vergelijkbare middelen. Voor patiënten brengt dit werk het veld dichter bij meer precieze, biologie-gedreven behandelingskeuzes die zijn afgestemd op het werkelijke gedrag van hun kankercellen.
Bronvermelding: Weir, A.L., Lee, S.C., Li, M. et al. IdentifiHR predicts homologous recombination deficiency in high-grade serous ovarian carcinoma using gene expression. Commun Med 6, 119 (2026). https://doi.org/10.1038/s43856-026-01387-y
Trefwoorden: eierstokkanker, DNA-reparatie, tekort in homologe recombinatie, genexpressie, machine learning