Clear Sky Science · nl
Analyse van gastheer-genexpressie bij de detectie van bacteriële en virale etiologie bij kinderen opgenomen met een vermoede ernstige infectie
Waarom dit onderzoek belangrijk is voor kinderen met ernstige infecties
Wanneer een kind met hoge koorts en er erg ziek uitziet op de spoedeisende hulp arriveert, moeten artsen snel beslissen of de oorzaak een bacteriële infectie is, die meestal antibiotica vereist, of een virale infectie, die vaak vanzelf verbetert. De huidige tests zijn verre van perfect en veel kinderen krijgen uit voorzorg antibiotica. Deze studie onderzocht of het aflezen van de eigen signalen in het bloed — specifiek patronen van genactiviteit — bacteriële en virale infecties bij kinderen met vermoedelijke ernstige ziekte nauwkeuriger van elkaar kan onderscheiden.
Kijken naar het alarmsysteem van het lichaam in plaats van naar het micro-organisme
Traditionele tests proberen het micro-organisme direct te vinden, bijvoorbeeld door bacteriën uit bloed te kweken of viraal genetisch materiaal met PCR aan te tonen. Deze benaderingen kunnen traag zijn, de werkelijke veroorzaker missen en vaak onschuldige ‘bystander’-virussen detecteren, vooral bij jonge kinderen die vaak respiratoire virussen dragen. De onderzoekers concentreerden zich in plaats daarvan op de gastheerrespons: welke genen in de bloedcellen van een kind aan- of uitstaan tijdens infectie. Omdat het immuunsysteem anders reageert op bacteriën en virussen, kan het patroon van actieve genen fungeren als een vingerafdruk van het infectietype, zelfs wanneer het moeilijk is het micro-organisme zelf te vinden of te interpreteren.
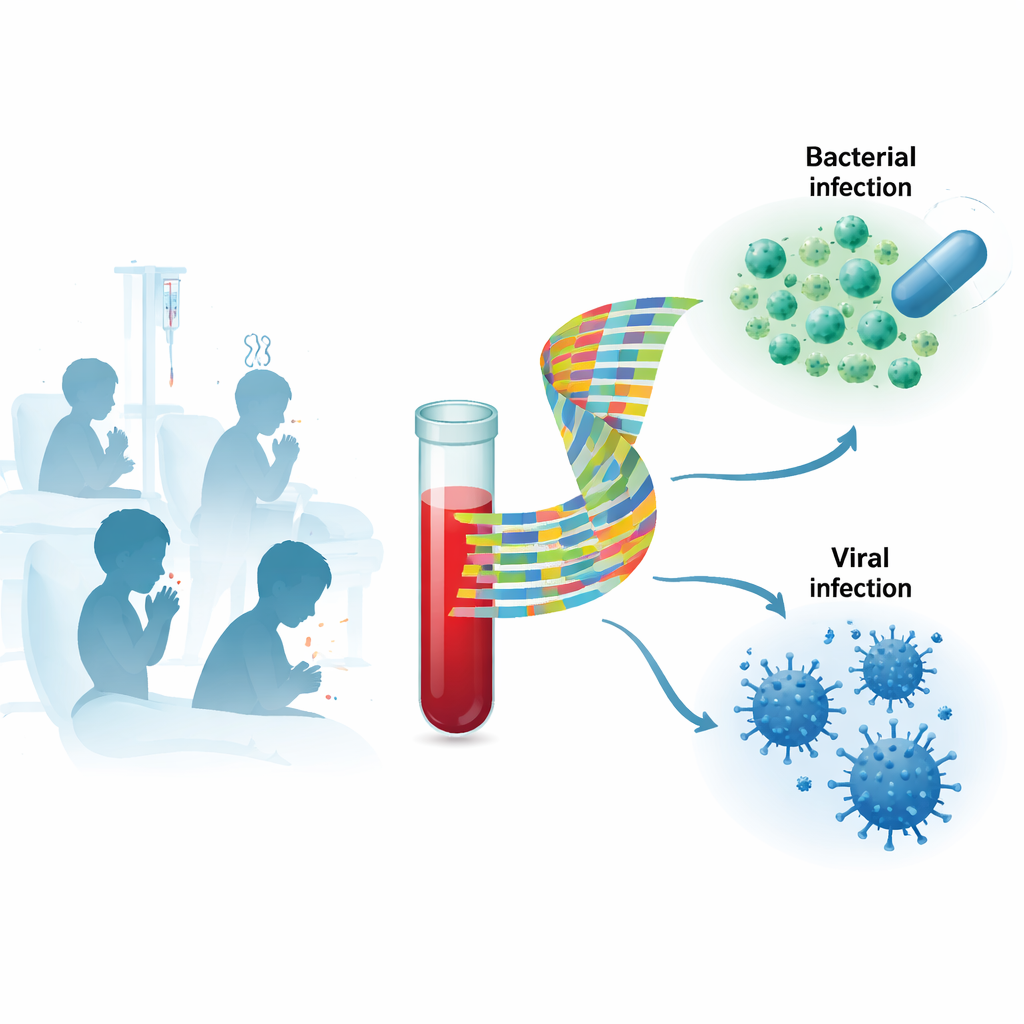
Onderzoek in een realistische mix van zieke kinderen
Het team nam 268 kinderen in de leeftijd van 4 weken tot 16 jaar op in Finland. De meeste waren opgenomen met vermoedelijke ernstige infecties; een kleinere groep had mildere, bevestigde virale infecties die poliklinisch werden behandeld, en enkele waren gezonde controles. Artsen verzamelden gedetailleerde klinische gegevens, standaard laboratoriumtesten zoals C-reactief proteïne en procalcitonine, en neuswatjes voor respiratoire virussen. Bloedmonsters werden gebruikt om de activiteit van duizenden genen te meten met RNA-sequencing. De ziekte van elk kind werd zorgvuldig geclassificeerd als bacterieel, viraal, gemengd bacterieel–viraal, onduidelijk of niet-infectieus, en voor belangrijke analyses ook eenvoudiger gegroepeerd als “bacterieel” of “viraal”.
Het vinden van een eenvoudige twee-genen-signal
Toen de wetenschappers eerst breed naar genactiviteit in bloed over alle kinderen keken, zagen ze dat de monsters in meerdere clusters groepeerden, maar deze clusters kwamen niet netjes overeen met de labels “bacterieel” versus “viraal”. Gezonde kinderen verschilden duidelijk van kinderen met een definitieve bacteriële infectie, terwijl genpatronen bij bevestigde virale infecties meer variatie lieten zien. Om deze complexiteit te doorbreken, splitsten de onderzoekers de patiënten in twee sets: een ontdekkingsgroep van kinderen met respiratoire infecties en een validatiegroep met andere typen infecties, zoals nier- of huidinfecties. In de ontdekkingsgroep zochten ze naar zeer kleine combinaties van genen die bacteriële van virale ziekte het beste konden onderscheiden, en testten vervolgens hoe goed diezelfde combinaties in de validatiegroep werkten.
Ze identificeerden één bijzonder veelbelovend paar genen, genoemd TSPO en SECISBP2. Samen konden de activiteitsniveaus van slechts deze twee genen bacteriële (inclusief gemengde bacterieel–viraal) infecties scheiden van louter virale infecties met hoge nauwkeurigheid. Gemeten als de oppervlakte onder de receiver operating characteristic-curve bereikte dit twee-genensignaal 0,93 in de ontdekkingsset en 0,81 in de validatieset; over beide groepen samen was het 0,87, met een sensitiviteit van ongeveer 77% en een specificiteit van ongeveer 87%. Met andere woorden, het signaal herkende de meeste bacteriële gevallen correct, terwijl het zelden virale infecties foutief als bacterieel bestempelde. Het presteerde ook beter dan veelgebruikte bloedmerkers zoals C-reactief proteïne en procalcitonine in deze studiepopulatie.

Wat deze twee genen mogelijk doen
TSPO is betrokken bij hoe mitochondriën — de energiecentrales van de cel — omgaan met stress en helpen ontsteking te reguleren. Eerder onderzoek heeft hogere TSPO-activiteit in verband gebracht met ernstigere bacteriële infecties en sepsis, en experimenten suggereren dat stimulatie van immuuncellen met bacteriële componenten TSPO kan verhogen en de afgifte van ontstekingsmoleculen kan aanwakkeren die helpen microben te doden. In deze studie neigde TSPO naar hogere activiteit bij bacteriële infecties en lagere activiteit bij virale infecties. SECISBP2 daarentegen helpt het lichaam bij de productie van seleniumhoudende eiwitten die antioxidant-, immuun- en antivirale functies hebben. Selenium ondersteunt immuuncellen en kan de ernst van sommige virale ziekten verminderen. Hier was de SECISBP2-activiteit over het algemeen hoger bij virale infecties, wat past bij het idee dat het lichaam selenium-gerelateerde verdedigingen opvoert bij de bestrijding van virussen.
Wat dit kan betekenen voor toekomstige zorg
De auteurs benadrukken dat hun bevindingen vroeg maar veelbelovend zijn. Een eenvoudige test die slechts deze twee genen uit een kleine bloedafname leest, zou op een dag spoedteams kunnen helpen met meer vertrouwen beslissen of een ernstig ziek kind antibiotica nodig heeft. Omdat het twee-genensignaal niet alleen bij longinfecties werkte maar ook bij andere ernstige infecties, kan het bruikbaar zijn in een breed spectrum van reële gevallen, inclusief situaties waarin bacteriële en virale micro-organismen samen worden aangetroffen. De studie werd echter in één land uitgevoerd en steunde op de best beschikbare maar onvolmaakte definities van bacteriële versus virale ziekte. Grotere studies in verschillende ziekenhuizen en snelle, kliniekklare versies van de test zijn nodig voordat het routinematig beslissingen kan sturen. Toch laat dit werk zien dat de eigen genactiviteit van het lichaam wel eens de sleutel kan zijn tot slimmer antibioticagebruik en betere zorg voor kinderen met ernstige infecties.
Bronvermelding: Piri, R., Valta, M., Lempainen, J. et al. Host gene expression analysis in the detection of bacterial and viral etiology in children hospitalized with a suspected severe infection. Commun Med 6, 204 (2026). https://doi.org/10.1038/s43856-025-01370-z
Trefwoorden: pediatrische infecties, genexpressie, bacterieel versus viraal, antibioticabeleid, diagnostiek van gastheerrespons