Clear Sky Science · nl
Wiskunde-geïnformeerd deep learning maakt snelle ultrahoge-resolutie kernspinresonantiespectroscopie mogelijk
Moleculen helderder zien
Kernspinresonantiespectroscopie (NMR) is een van de krachtigste microscopen in de chemie voor het bestuderen van moleculen, maar de meest gedetailleerde modi kunnen pijnlijk traag zijn. Dit artikel introduceert een manier om kunstmatige intelligentie te gebruiken om een bijzonder scherpe vorm van NMR, genaamd pure shift NMR, drastisch te versnellen zonder de fijne details op te geven die wetenschappers nodig hebben. Snellere, scherpere spectra kunnen chemici helpen complexe reacties in real time te volgen, betere geneesmiddelen en katalysatoren te ontwerpen en te begrijpen hoe moleculen zich gedragen in drukbezette, realistische mengsels.
Waarom gewone NMR soms tekortschiet
Conventionele NMR zet subtiele magnetische signalen van atoomkernen om in grafieken met pieken die de structuur en omgeving van een molecuul onthullen. In drukbezette monsters met veel vergelijkbare moleculen overlappen deze pieken vaak en splijten in ingewikkelde patronen, waardoor interpretatie lastig wordt. Pure shift NMR vereenvoudigt dit beeld door die meervoudige piekpatronen samen te trekken tot enkele, scherpe lijnen, en levert zo "ultrahoge-resolutie"-weergaven van drukbezette protonenspectra. Het nadeel is dat pure shift-methoden extra tijdpunten moeten opnemen en veel kleine datablokjes aan elkaar moeten plakken. Dat kan experimenten tien keer langer of meer laten duren, zeker voor twee- of driedimensionale technieken die de instrumenttijd al flink belasten.
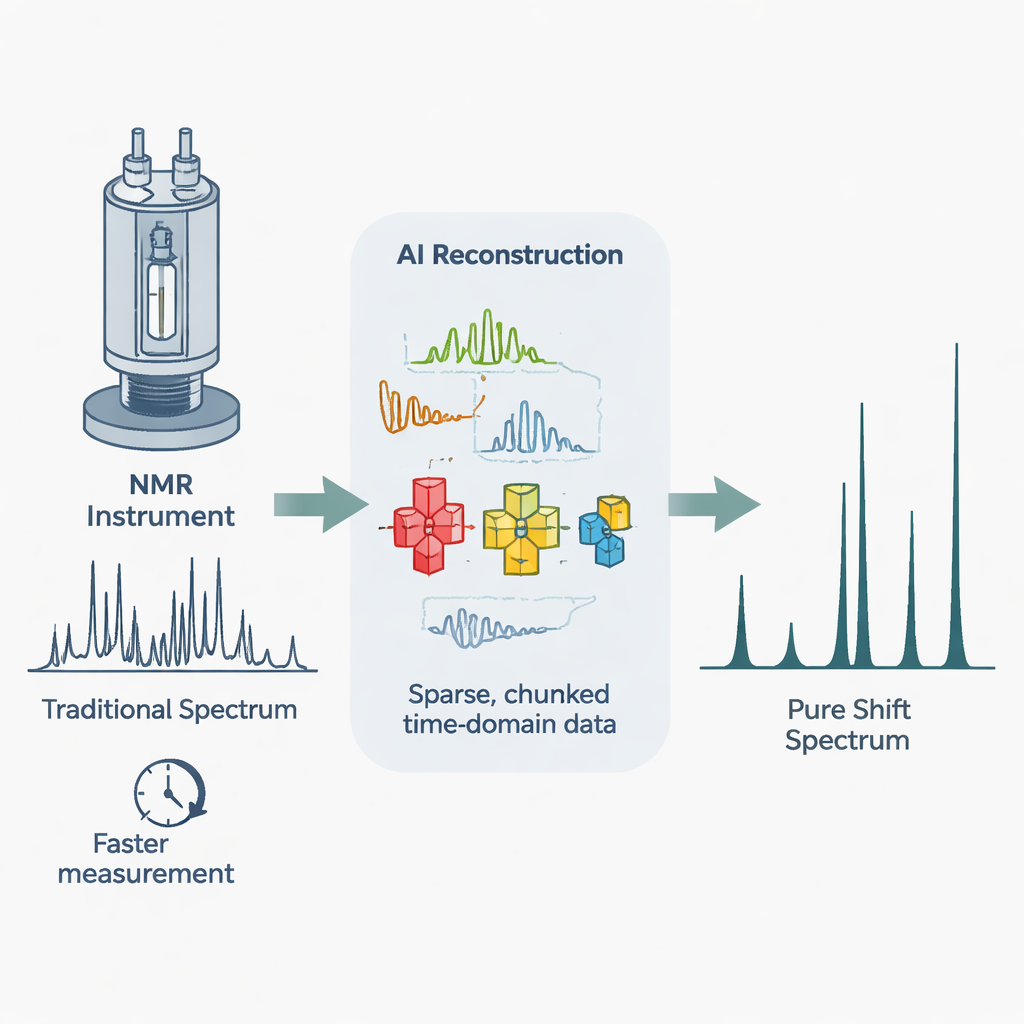
Tijd besparen zonder in te leveren op kwaliteit
Een manier om experimenten te verkorten is slechts een fractie van de data vast te leggen en later te proberen de ontbrekende delen te reconstrueren. Eerdere benaderingen leenden ideeën uit compressed sensing, maar die vereisten nauwkeurige afstemming en faalden vaak bij het terugwinnen van zwakke signalen of juiste piekhoogtes. De auteurs presenteren een nieuw deep learning-kader, DA-PSNet genoemd, dat rechtstreeks uit voorbeelden leert hoe hoogwaardige pure shift-spectra uit schaars bemonsterde metingen kunnen worden herbouwd. Het netwerk is "physics-informed": het werkt zowel in het frequentiedomein, waarin spectra gewoonlijk worden bekeken, als in het tijdsdomein, waar het consistentie afdwingt met de data die daadwerkelijk werden gemeten. Het gebruikt ook attentiemechanismen om zich te concentreren op subtiele kenmerken zoals zwakke pieken verborgen nabij sterke.
Scherpere spectra in één en twee dimensies
Het team test DA-PSNet eerst op eendimensionale pure shift-spectra van mengsels zoals 1-butanol en boterzuur, waarin sleutelpieken sterk overlappen in standaard NMR. Met slechts ongeveer 5% van de gebruikelijke pure shift-data is het ruwe schaarse spectrum sterk vervormd. Traditionele reconstructie heeft moeite met het herstellen van signalen bij lage concentraties en vervormt piekintensiteiten. Daarentegen herstelt DA-PSNet dichtbije pieken, behoudt hun relatieve hoogtes en onderdrukt kunstmatige kenmerken, terwijl het ook ongeveer honderd keer sneller draait dan de oudere methode. Bij iets hogere bemonsteringsniveaus wordt de reconstructie nauwkeurig genoeg voor veeleisend kwantitatief werk, en levert nog steeds een meervoudige verkorting van de experimenteertijd op.
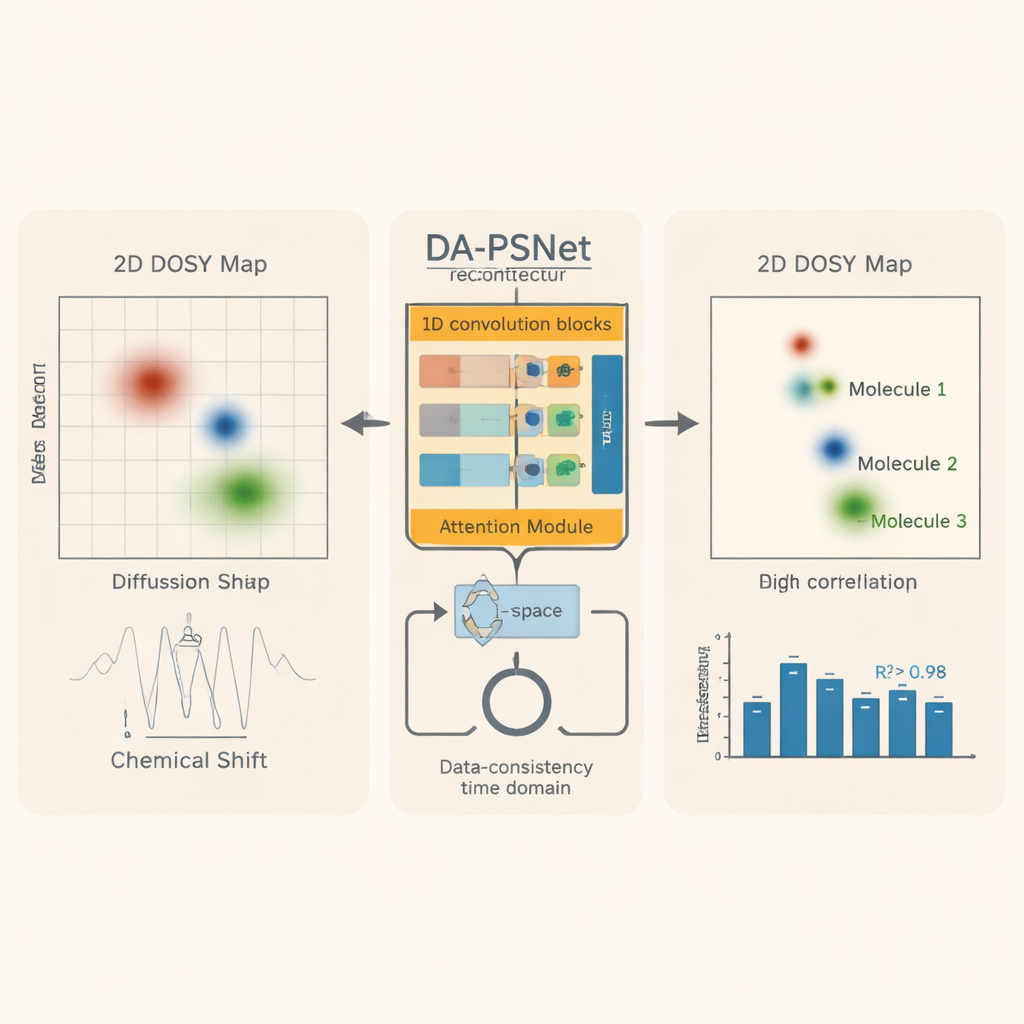
Reacties volgen en complexe mengsels scheiden
Vervolgens tonen de auteurs aan dat hetzelfde getrainde model complexere, multidimensionale experimenten kan versnellen zonder opnieuw te hoeven trainen. In tweedimensionale pure shift DOSY-metingen—which aanvullende informatie geven over hoe snel moleculen in oplossing diffunderen—reconstrueert DA-PSNet hoogresolutie-datasets voor mengsels van drie vergelijkbare organische verbindingen uit slechts 40% van de gebruikelijke data. De resulterende kaarten scheiden de componenten duidelijk en komen dicht in de buurt van volledig bemonsterde referentiespectra, met statistische overeenstemming beter dan 98%. De methode bewijst ook haar waarde in real-time elektrochemische experimenten: door pure shift NMR te combineren met DA-PSNet-reconstructie kunnen de onderzoekers signalen van een brandstofmolecuul (1-butanol) en het oxidatieproduct (boterzuur) helder onderscheiden terwijl ze in de tijd evolueren op verschillende katalysatoren, wat onthult welke katalysator de brandstof efficiënter omzet.
Wat dit betekent voor toekomstige moleculaire studies
Kort gezegd toont dit werk aan dat een zorgvuldig ontworpen, natuurkundig-bewust neuraal netwerk ontbrekende NMR-data kan "invullen" op een manier die zwakke pieken en nauwkeurige intensiteiten behoudt terwijl de experimenteertijd drastisch wordt verkort. Er blijven grenzen bestaan—als er te weinig data worden verzameld, kan zelfs het beste model het spectrum niet volledig herstellen, en de training moet het bereik van monsters en condities van belang weerspiegelen. Maar binnen realistische bemonsteringsniveaus verandert DA-PSNet eerder trage, hoge-resolutie pure shift-methoden in praktische hulpmiddelen voor routinematige en tijdgevoelige studies. Voor niet-specialisten is de conclusie dat AI NMR helpt transformeren van een trage, hogeprecisielabtechniek naar een snellere, flexibelere instrument om structuur en reactiviteit in complexe chemische en biologische systemen te onderzoeken.
Bronvermelding: Bao, J., Ni, Y., Hu, L. et al. Physics-informed deep learning enables fast ultrahigh-resolution nuclear magnetic resonance spectroscopy. Commun Chem 9, 103 (2026). https://doi.org/10.1038/s42004-026-01912-z
Trefwoorden: kernspinresonantie, pure shift NMR, deep learning, spectrale reconstructie, reactiemonitoring