Clear Sky Science · nl
Het optimaliseren van CRISPR-nauwkeurigheid in muizembryo’s via microhomology-gemedieerde end-joining-dominante targeting
Waarom nauwkeuriger genetisch bewerkte muizen belangrijk zijn
Genbewerkingstools zoals CRISPR hebben het opmerkelijk eenvoudig gemaakt om muizen te creëren die menselijke ziekten nabootsen, maar er is een verborgen probleem: de genetische veranderingen in de allereerste generatie dieren zijn vaak rommelig en gemengd. Dat maakt experimenten trager, minder betrouwbaar en vereist meer dieren. Deze studie introduceert een manier om CRISPR-knipsels in muizembryo’s te sturen naar goed voorspelbare uitkomsten, zodat de meeste founder-muizen met dezelfde, goed gedefinieerde mutatie worden geboren — wat schonere biologie en betere ethiek in genbewerkingonderzoek brengt.
De uitdaging van rommelig DNA-herstel
Wanneer CRISPR DNA knipt, moet de cel de breuk herstellen met haar eigen herstelmechanismen. De meest voorkomende route, non-homologous end joining, is snel maar onnauwkeurig en leidt tot een wirwar van kleine inserties en deleties op de knipplaats. Een andere route, microhomology-mediated end joining, neigt ertoe stukken DNA op gestereotypeerde wijze te verwijderen door korte, overeenkomende sequenties als gids te gebruiken. Beide zijn veel efficiënter dan de precieze maar trage homology-directed route. In standaard CRISPR-experimenten concentreren wetenschappers zich grotendeels op hoe sterk een gids-RNA kan knippen en hoeveel off-targets het heeft, en besteden ze veel minder aandacht aan welke herstelroute zal worden bevoordeeld of welke exacte mutatie zal ontstaan. Het resultaat is dat veel founder-muizen een lappendeken van verschillende mutaties in verschillende cellen dragen, waardoor onderzoekers moeten fokken naar de volgende generatie voordat ze met een zuiver, uniform genotype kunnen werken.
Een slimmer manier om CRISPR-gidsen te kiezen
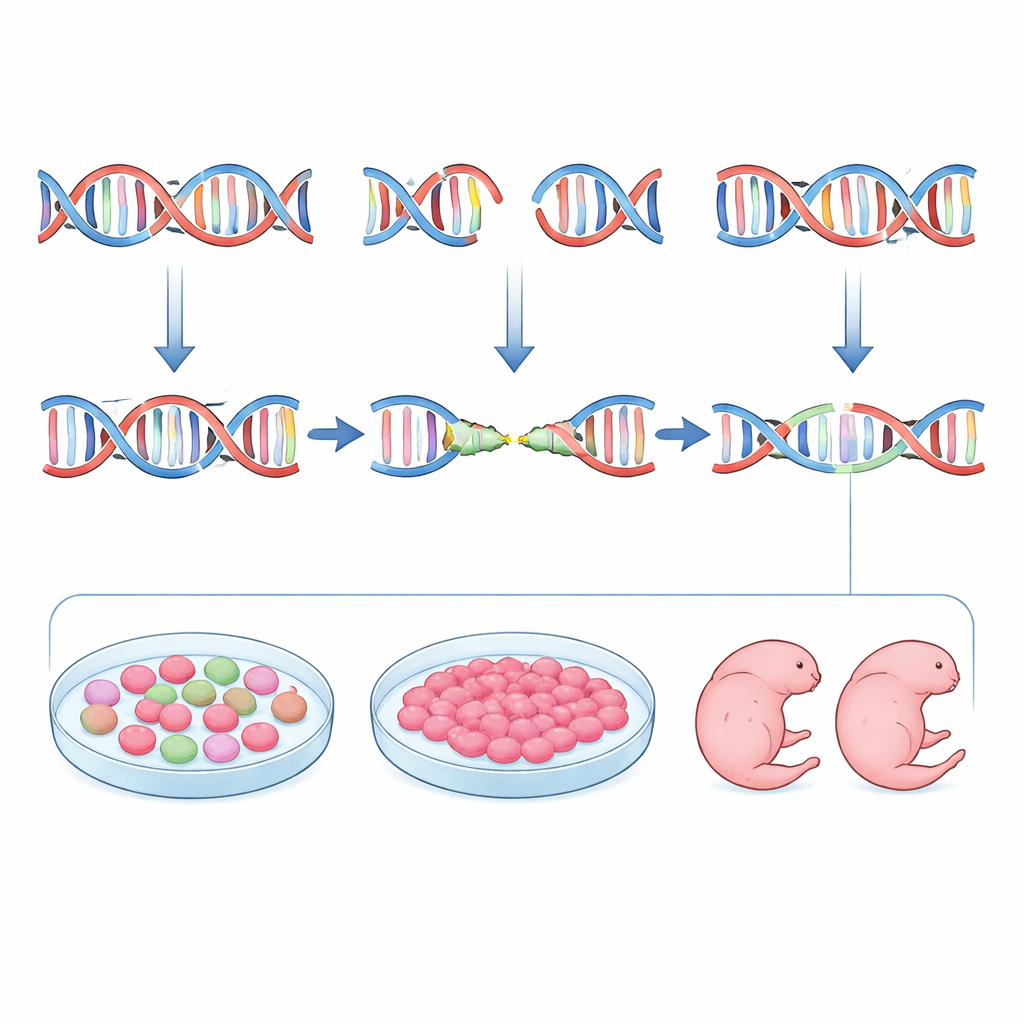
De auteurs wilden dit omdraaien door gidsen te ontwerpen niet alleen op kracht en veiligheid, maar ook op voorspelbaarheid. Ze begonnen met inDelphi, een machine-learningtool getraind op enorme datasets van CRISPR-geïnduceerde mutaties in gekweekte cellen. inDelphi zegt niet alleen hoe vaak een site wordt bewerkt; het voorspelt het volledige menu van mogelijke inserties en deleties en hoe frequent elk ervan zal voorkomen, met speciale aandacht voor microhomology-gedreven gebeurtenissen. Het team doorzocht het muizengene Tyr (tyrosinase), waarbij functieverlies dieren albino maakt, en selecteerde gids-RNA’s waarvan voorspeld werd dat ze sterke, herhaalbare microhomology-gemedieerde deleties zouden bevorderen, terwijl de off-targetrisico’s laag blijven. Vervolgens bewerkten ze muizembryo’s en bepaalden de resulterende mutaties met diepe sequencing. Over het geheel genomen verscheen inDelphi’s favoriete genotype voor elke gids in embryo’s met vergelijkbare frequenties als voorspeld, en gidsen met sterkere microhomology-kenmerken produceerden inderdaad meer uniforme mutatiepatronen.
Stamcellen gebruiken als generale repetitie
Toch was voorspelling alleen niet voldoende. Toen het team inDelphi-voorspellingen vergeleek met daadwerkelijke bewerkingspatronen, vonden ze slechts matige overeenstemming. Om deze kloof te overbruggen introduceerden ze een praktisch tussenschot: het testen van elke gids in muizeneurale embryonale stamcellen die veel kenmerken delen met zeer vroege embryo’s. Nadat ze deze cellen hadden getransfecteerd met CRISPR-componenten, sorteerden ze bewerkte cellen en seqeunceerden de doellocaties. De mutatiepatronen in stamcellen kwamen veel beter overeen met die in embryo’s dan het computermodel deed. Gidsen die in stamcellen één dominante deletie produceerden, deden dat doorgaans ook in blastocysten en later stadium embryo’s. Door inDelphi’s rangschikking te combineren met deze stamcel-‘generalerepetitie’, konden de onderzoekers betrouwbaar gidsen kiezen die microhomology-gemedieerd herstel sturen en de diversiteit aan mutante allelen minimaliseren.
Van oogkleur tot ontbrekende ledematen
De auteurs zetten hun pijplijn op de proef in levende dieren. Voor het Tyr-gen kozen ze drie gidsen die hoge, middelmatige en lage voorspelde precisie vertegenwoordigen en implementeerden bewerkte embryo’s bij pleegmoeders. Op dag 11,5 van de embryonale ontwikkeling onderzochten ze de oogpigmentatie en sekveneerden ze elk embryo individueel. De gids die sterk microhomology bevoordeelde produceerde embryo’s die grotendeels albino waren en één dominante kleine deletie droegen, vaak in beide kopieën van het gen, met zeer weinig variatie. Een minder geoptimaliseerde gids gaf een mengeling van pigmentverlies en gedeeltelijke pigmentatie, gekoppeld aan een complexer geheel van mutaties. Ze pasten dezelfde benadering toe op het Fgf10-gen, waarbij functieverlies leidt tot embryo’s zonder ledematen. Door een gids te kiezen die voorspeld werd — en bevestigd in stamcellen — een specifieke deletie van vier basen te geven met een hoge kans op het verstoren van het gen, genereerden ze embryo’s op dag 15,5 die uniform ledemaatloos waren en een sterk verrijkte set van de verwachte deleties droegen. Voor beide genen domineerden dezelfde paar mutatietypen in inDelphi-voorspellingen, stamcellen, vroege embryo’s en later stadium embryo’s.
Schonere genetica met minder dieren
In praktische termen biedt de studie een nieuw sjabloon voor het ontwerpen van CRISPR-experimenten in muizen. In plaats van meteen van een computergestuurde gids naar embryo-bewerking te haasten, pleiten de auteurs voor een geïntegreerde pijplijn: gebruik inDelphi en off-targettools om gidsen te kiezen die waarschijnlijk microhomology-gemedieerde deleties en frameshifts bevoordelen, test die gidsen in embryonale stamcellen om zowel efficiëntie als uniformiteit van mutaties te bevestigen, en breng alleen de beste kandidaten naar embryowerk. Deze strategie levert founder-muizen op waarvan de cellen overwegend hetzelfde, goed gekarakteriseerde mutatie delen, waardoor ze direct bruikbaar zijn voor het modelleren van menselijke ziekten — vooral die veroorzaakt door terugkerende deletietypen — terwijl het aantal dieren dat gefokt en gescreend moet worden vermindert. Het resultaat is scherpere, beter reproduceerbare genetica en een ethischer pad naar krachtige ziektemodellen.
Bronvermelding: Lkhagvadorj, K., Okamura, E., Taki, T. et al. Optimizing CRISPR precision in mouse embryos via microhomology-mediated end joining-dominant targeting. Commun Biol 9, 371 (2026). https://doi.org/10.1038/s42003-026-09771-z
Trefwoorden: CRISPR, muismodellen, genoombewerking, DNA-herstel, ziektemodellering