Clear Sky Science · nl
Arromatisch plekje in whiB-achtige transcriptiefactoren vergemakkelijkt interactie met de primaire sigmafactor in Mycobacterium tuberculosis
Hoe bacteriën gevaar waarnemen
Mycobacterium tuberculosis, de kiem die tuberculose veroorzaakt, overleeft in het menselijk lichaam door snel te herprogrammeren welke genen aan- of uitgezet worden wanneer de omstandigheden veranderen, bijvoorbeeld bij blootstelling aan antibiotica of immuunaanval. Deze studie onthult een klein structureel kenmerk — een "aromatisch plekje" — in een familie bacteriële eiwitten dat hen helpt zich vast te grijpen aan het belangrijkste schakelmechanisme voor genexpressie van de cel. Het begrijpen van deze microscopische handdruk legt bloot hoe tuberculoseverwekkers en verwante bacteriën zich aanpassen en kan wijzen op nieuwe manieren om dit pathogeen te verzwakken.
Een speciale familie bacteriële schakelaars
Het werk richt zich op WhiB-achtige (Wbl) eiwitten, een groep die alleen voorkomt bij actinobacteriën en hun virussen, inclusief Mycobacterium tuberculosis. Deze eiwitten dragen een klein ijzer–zwavel-cluster, een metaalgebaseerde cofactor die hen in staat stelt veranderingen in zuurstof en andere stressfactoren te detecteren. Wbl-eiwitten reguleren bekende processen zoals celdeling, reacties op oxidatieve en nutriëntstress en resistentie tegen antibiotica. Toch missen de meeste van hen de klassieke structuren waarmee veel regulerende eiwitten direct aan DNA binden, wat een langbestaand mysterie opliep: hoe regelen ze eigenlijk genactiviteit?
Vastpakken van het hoofdmechanisme voor genlezing
Eerder werk toonde dat meerdere Wbl-eiwitten genen activeren door te binden aan een geconserveerde regio, genoemd regio 4, van de primaire sigmafactor. De sigmafactor is het deel van RNA-polymerase — het enzym dat DNA leest — dat herkent waar met het kopiëren van genen begonnen moet worden. In Mycobacterium tuberculosis gebruikt deze primaire sigmafactor dezelfde regio 4 om vele verschillende regulatoren te rekruteren. De auteurs combineerden röntgendiffractie, biochemische pull-downs en calorimetrie en lieten zien dat nagenoeg alle onderzochte Wbl-eiwitten uit deze bacterie (met één bijzondere uitzondering) zich aan precies dezelfde plek op sigmafactor regio 4 hechten en dat dit zeer sterke bindingen oplevert.
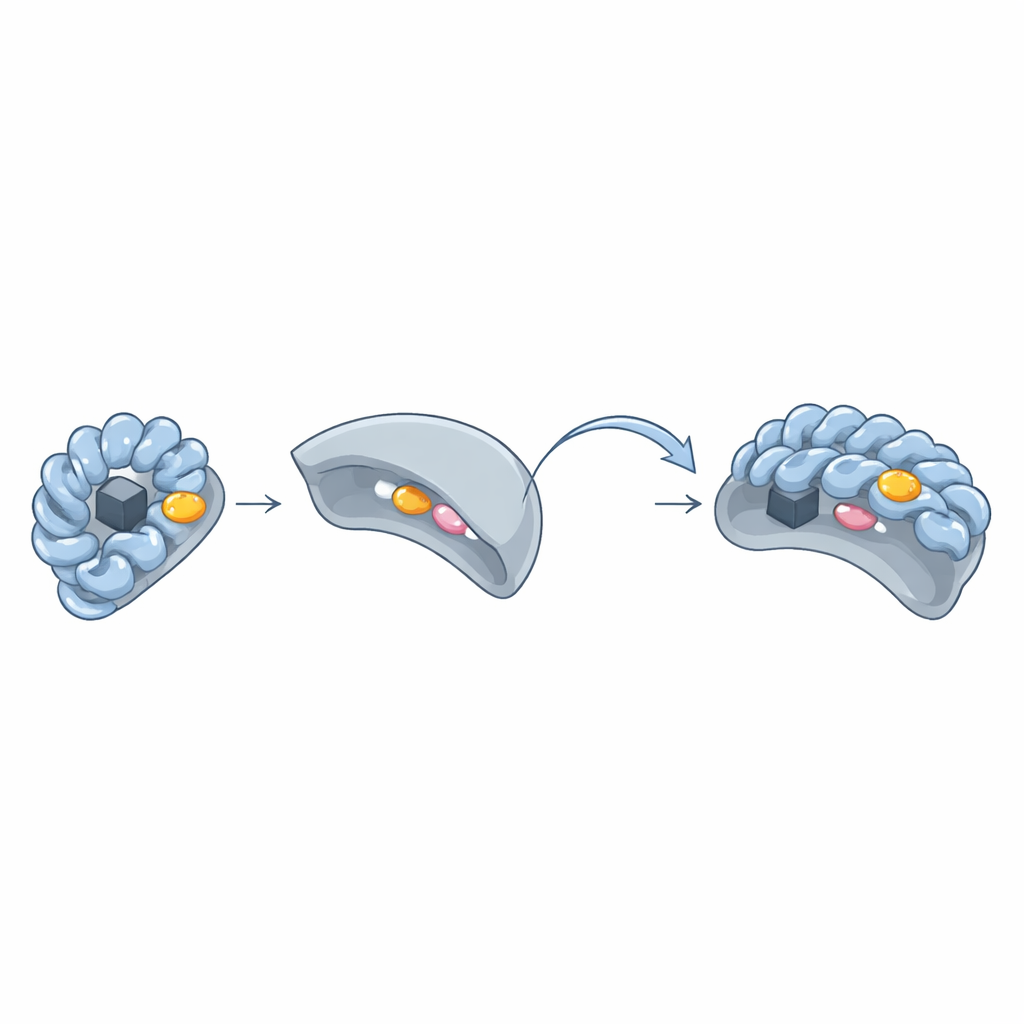
De verborgen "aromatische patch" sleutel-slot
Door drie-dimensionale structuren van Wbl–sigma-paren te vergelijken, ontdekte het team een terugkerende cluster van lompe ringvormige aminozuren — tryptofaan, fenylalanine, tyrosine of histidine — die een "aromatisch plekje" vormen op het oppervlak van Wbl-eiwitten. Dit plekje ligt rond het ijzer–zwavel-cluster en drukt direct tegen twee sleutelaminozuren in sigma regio 4. Wanneer de onderzoekers deze aromatische residuen vervingen door eenvoudigere aminozuren, konden de Wbl-eiwitten geen stabiele complexen met sigma meer vormen en werden hun ijzer–zwavel-clusters vaak instabiel. Zelfs bij Wbl-varianten die ongebruikelijk leken — zoals WhiB6 of WhiB5 — compenseerden alternatieve residuen of nabije aromatische zijketens om hetzelfde type interactie te behouden.
Een gedeeld ontwerp over bacteriën en hun virussen
Om te onderzoeken hoe wijdverbreid dit kenmerk is, analyseerden de auteurs 995 Wbl-eiwitsequenties uit vele actinobacteriële soorten en hun infecterende virussen (actinobacteriofagen). Ze groepeerden deze eiwitten in 29 subfamilies en vonden dat vijf grote takken, vertegenwoordigd door vijf Mycobacterium tuberculosis Wbl-eiwitten, ongeveer 80% van alle sequenties omvatten. Structurele modellering met AlphaFold toonde aan dat bijna alle Wbls — meer dan 98% — ten minste twee aromatische residuen dragen op posities die overeenkomen met het aromatische plekje, en bijna alle hebben ten minste één in de cruciale centrale posities. Experimenten met meerdere door fagen gecodeerde Wbl-eiwitten bevestigden dat deze virale varianten ook aan dezelfde sigmaregio binden op een plekje-afhankelijke manier, wat aangeeft dat hetzelfde moleculaire ontwerp wordt hergebruikt bij zowel bacteriën als hun fagen.
Een evolutionair touwtrekken om controle
De fylogenetische boom opgebouwd uit deze 995 sequenties toont fage- en bacteriële Wbl-eiwitten door elkaar, met duidelijke aanwijzingen voor horizontale genoverdracht in beide richtingen. Sommige virale Wbls zitten aan de basis van grote bacteriële takken, wat suggereert dat fagen deze regulatoren aan vroege bacteriën hebben geschonken, die ze daarna voor eigen doeleinden aanpasten. Andere virale Wbls lijken ingebed in grotendeels bacteriële clusters, wat wijst op latere overdrachten terug naar fagen. Omdat Wbl-eiwitten stressreacties, celontwikkeling en medicijnresistentie strak reguleren via hun sigma-bindende aromatische plekjes, hebben deze heen-en-weer uitwisselingen waarschijnlijk vormgegeven hoe zowel bacteriën als hun virussen het transcriptiemechanisme van de gastheer manipuleren.
Wat dit betekent voor tuberculose en verder
Kort gezegd toont deze studie aan dat veel actinobacteriële regulatoren een klein maar cruciaal kleverig plekje delen — het aromatische plekje — dat hen in staat stelt aan dezelfde plaats van het genleesmotor te dokken en fijnmazig te regelen welke genen actief zijn onder stress. In Mycobacterium tuberculosis helpt dit gedeelde dockingmechanisme reacties te coördineren die persistentie, virulentie en antibioticumresistentie ondersteunen. Door bloot te leggen hoe dit microscopische interface werkt en hoe wijdverspreid het geconserveerd is, benadrukt het werk een potentiële zwakke plek die op termijn aangegrepen zou kunnen worden om het aanpassings- en overlevingsvermogen van het pathogeen in zijn gastheer te verstoren.
Bronvermelding: Guiza Beltran, D., Wan, T., Seravalli, J. et al. Aromatic patch in whiB-like transcription factors facilitates primary sigma factor interaction in mycobacterium tuberculosis. Commun Biol 9, 424 (2026). https://doi.org/10.1038/s42003-026-09698-5
Trefwoorden: Mycobacterium tuberculosis, transcriptiefactoren, sigmafactor, ijzer-zwavel-eiwitten, bacteriofaag-evolutie