Clear Sky Science · nl
DANST maakt cel-type-deconvolutie mogelijk in ruimtelijke transcriptomica met behulp van diepe domein-adversariële neurale netwerken
Cellen zien in hun omgeving
Menselijk weefsel is een drukke stad van vele verschillende celtypen, elk met een eigen rol. Nieuwe “ruimtelijke transcriptomica”-technologieën kunnen meten welke genen actief zijn over een weefselsnede, maar elke meting bevat vaak signalen van meerdere naburige cellen door elkaar. Dit artikel introduceert DANST, een slimme computationele methode die die mengsels uit elkaar haalt. Door ons te vertellen welke celtypen aanwezig zijn en waar ze zich bevinden in organen en tumoren, helpt het wetenschappers beter te begrijpen hoe weefsels zijn opgebouwd, hoe ziekten zich verspreiden en waar behandelingen het beste gericht kunnen worden. 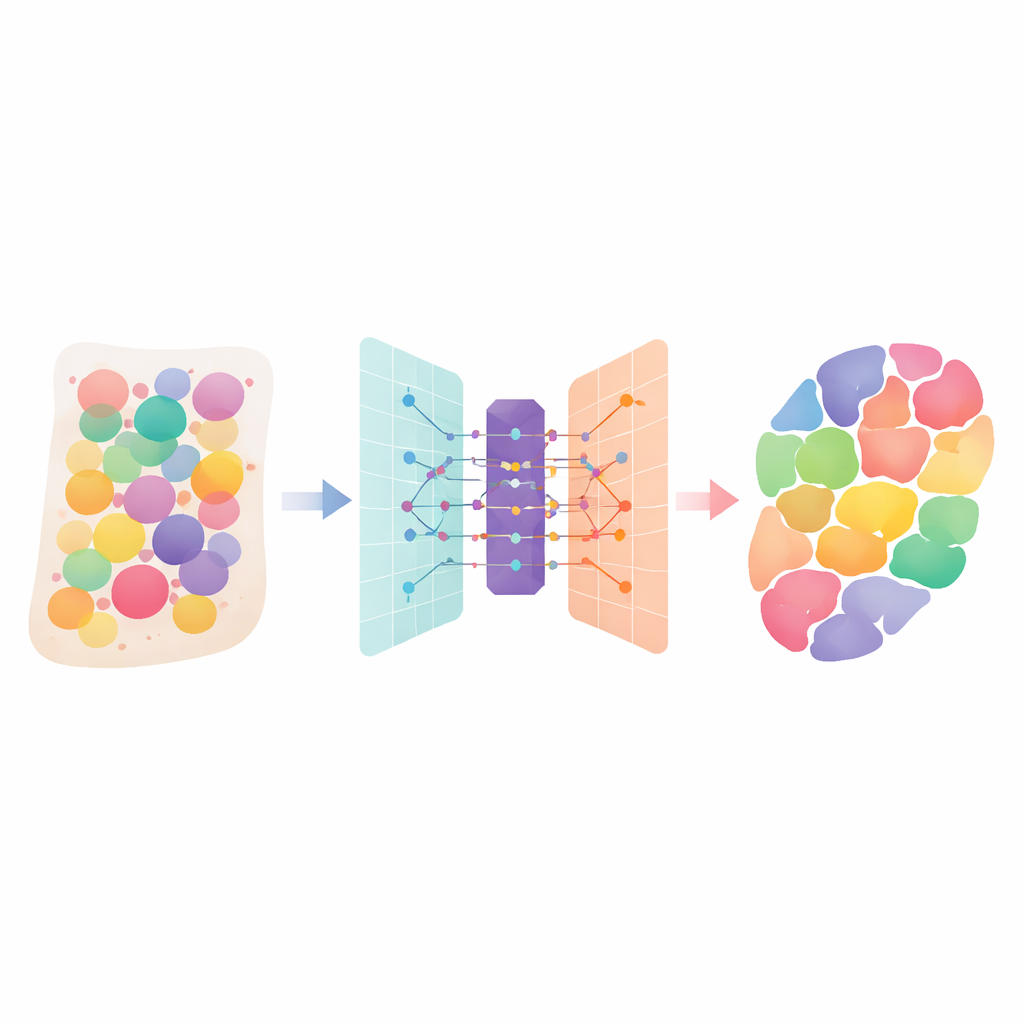
De uitdaging van het ontwarren van celmenigten
Moderne genlezers kunnen ofwel heel precies naar individuele cellen kijken of het volledige weefsel in kaart brengen, maar zelden beide tegelijk. Populaire ruimtelijke technologieën registreren genactiviteit in relatief grote “spots” die meerdere cellen kunnen omvatten. Het resultaat is alsof je een koor hoort zonder te kunnen zeggen wie welke noten zingt. Om dit te begrijpen hebben onderzoekers “deconvolutie”-methoden nodig die inschatten welk aandeel elk celtype levert aan elke spot. Veel bestaande benaderingen gebruiken single-cell gegevens als referentie, maar ze hebben moeite omdat de twee datatypes in verschillende experimenten zijn verzameld en niet perfect overeenkomen in kwaliteit, ruis of resolutie.
Een brug bouwen tussen datawerelden
DANST pakt deze mismatch aan door een brug te creëren tussen single-cell-gegevens en ruimtelijke gegevens. Eerst gebruikt het de gedetailleerde single-cell-profielen om vele kunstmatige gemengde spots met bekende celtypeverhoudingen te simuleren. Tegelijkertijd groepeert het de echte ruimtelijke spots op basis van zowel hun locatie in het weefsel als hun genpatronen, en gebruikt de afstanden tot deze groepen om elke gesimuleerde spot een “pseudo”-positie toe te wijzen. Deze stap creëert een gekoppelde kaart waarin kunstmatige en echte spots een gemeenschappelijk ruimtelijk kader delen, waardoor de methode kan leren hoe gemengde signalen eruit zouden moeten zien in specifieke buurten van het weefsel. 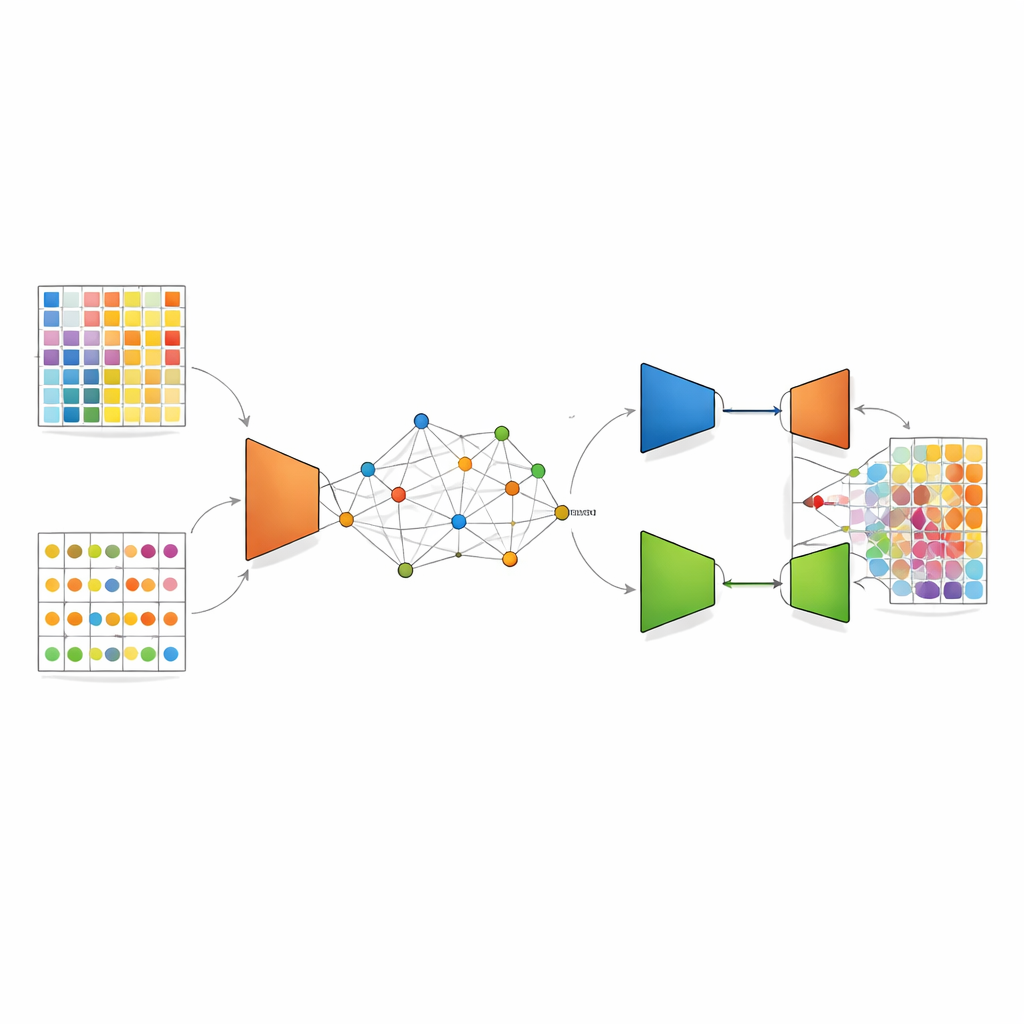
Signaleren schonen en domeinen uitlijnen
Zodra deze gezamenlijke kaart is opgesteld, past DANST een vorm van diepe leertechniek toe die bekend staat als een variational autoencoder. Dit netwerk comprimeert genpatronen van zowel echte als gesimuleerde spots tot een verfijnde interne representatie en probeert ze vervolgens te reconstrueren, waardoor het de data effectief ontruischt en belangrijke kenmerken benadrukt. Daarbovenop voegen de auteurs een adversariële component toe: een tweede netwerk probeert te achterhalen of een verfijnd patroon afkomstig is van echte ruimtelijke data of van gesimuleerde data, terwijl de feature-extractor leert het te misleiden. Deze “touwtrek” duwt het model richting kenmerken die voor beide databronnen goed werken, zodat kennis verkregen uit gesimuleerde spots met bekende celtypefracties betrouwbaar kan worden overgedragen naar echte weefselspots waarvan de samenstelling onbekend is.
Testen op harten, hersenen en tumoren
Het team testte DANST zowel op kunstmatige benchmarks als op echte biologische monsters van muizen en mensen. In vergelijking met verschillende toonaangevende methoden herstelde DANST nauwkeuriger de verhoudingen van celtypen in synthetische datasets en behield het zijn voordeel over zeer verschillende weefsels en platformen. In een muizen-hersendataset reconstrueerde het duidelijk de gelaagde organisatie van de cortex en kwam het overeen met door experts gedefinieerde anatomische gebieden. In een aparte muizen-hersensnede ving het fijne patronen op in gebieden zoals de hippocampus. Meest opvallend, in menselijk borsttumorweefsel traceerde DANST hoe verschillende immuuncellen, ondersteunende cellen en hormoongevoelige luminale cellen zijn gerangschikt binnen en rond tumorregio's. Deze kaarten kwamen overeen met bekende biologische kennis en suggereerden klinisch relevante kenmerken, zoals hormoonafhankelijkheid en mogelijk slechtere prognose waar bepaalde immuuncellen schaars waren.
Wat dit betekent voor biologie en geneeskunde
Voor een niet-specialist kan DANST worden gezien als een krachtige vertaler die vage, overlappende signalen omzet in een helder beeld van welke cellen waar in een weefsel leven. Door celtypen betrouwbaar ruimtelijk te scheiden, geeft het onderzoekers een scherper beeld van hoe gezonde organen zijn georganiseerd en hoe ziekte die organisatie verandert. Bij kanker kan dit onthullen hoe tumorcellen en immuuncellen in specifieke regio's met elkaar interageren, wat gerichte therapieën kan sturen en kan helpen patiëntuitkomsten te voorspellen. Naarmate er meer ruimtelijke en single-cell-datasets beschikbaar komen, liggen tools zoals DANST klaar om essentieel te worden voor het decoderen van de cellulaire buurten die ten grondslag liggen aan gezondheid en ziekte.
Bronvermelding: Zhang, X., Wu, Z., Wang, T. et al. DANST enables cell-type deconvolution in spatial transcriptomics using deep domain adversarial neural networks. Commun Biol 9, 388 (2026). https://doi.org/10.1038/s42003-026-09659-y
Trefwoorden: ruimtelijke transcriptomica, celtype-deconvolutie, diepe leertechnieken, tumormicroomgeving, single-cell RNA-sequencing