Clear Sky Science · nl
Moleculaire QTL zijn verrijkt voor structurele varianten in een runderen long-read cohort
Waarom runderdna ons iets kan leren over complexe eigenschappen
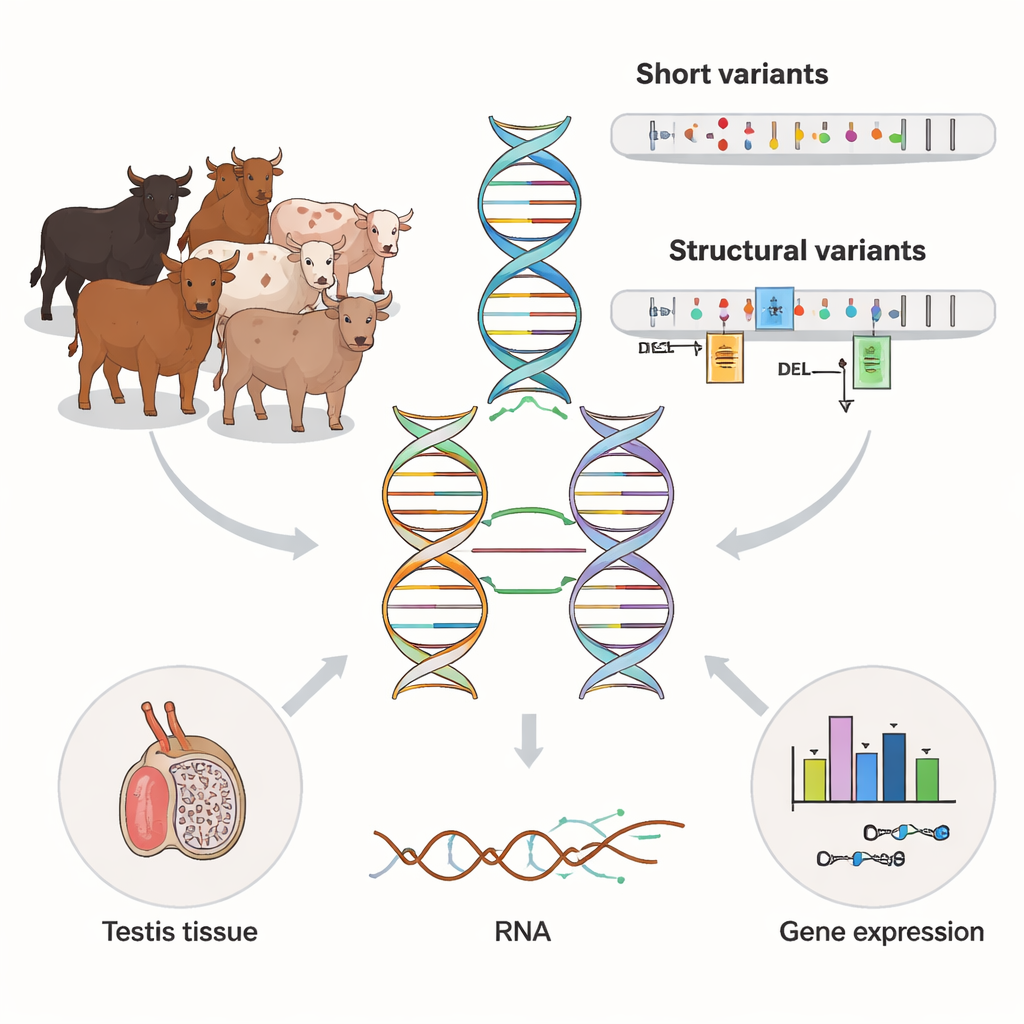
Boeren, dierenartsen en genetici willen allemaal begrijpen waarom sommige dieren sneller groeien, beter bestand zijn tegen ziekten of meer melk produceren dan andere. Een groot deel van het antwoord ligt in DNA, maar onze gebruikelijke technieken richten zich meestal op kleine veranderingen in individuele "letters" van het genoom. Deze studie laat zien dat veel grotere DNA-veranderingen — structurele varianten — op subtiele wijze bepalen hoe genen werken bij runderen, en dat nieuwe long-read sequencingtechnologieën ons eindelijk in staat stellen hun volledige impact te zien.
Het genoom bekijken met een scherpere lens
De meeste genetische studies vertrouwen op korte DNA-fragmenten, die goedkoop en nauwkeurig zijn maar moeite hebben in repetitieve of complexe gebieden van het genoom. De auteurs gebruikten een nieuwere techniek, long-read sequencing, op 120 stieren van een zuivelgerelateerd runderras. Deze lange reads overspannen veel grotere stukken DNA, waardoor het gemakkelijker wordt om grote inserties, deleties en herschikkingen te detecteren die bekendstaan als structurele varianten. Het team vergeleek deze long reads met bestaande short-read data van dezelfde dieren en ontdekte dat long reads in het algemeen meer varianten onthulden en de dekking van moeilijke regio’s, zoals de X- en Y-chromosomen, dramatisch verbeterden.
Duizenden verborgen DNA-herschikkingen aan het licht brengen
Met de long-read data catalogueerden de onderzoekers ongeveer 24 miljoen kleine DNA-veranderingen en meer dan 79.000 structurele varianten over de stieren heen. Veel van deze grotere veranderingen waren gekoppeld aan repetitieve DNA-elementen die zichzelf kopiëren en elders in het genoom invoegen. Ongeveer één op de tien structurele varianten kwam slechts in één of twee dieren voor, wat een rijke bron van zeldzame variatie onthult. Vergeleken met een eerder runderen “pangenoom” opgebouwd uit hoogkwalitatieve assemblages, voegde de nieuwe dataset tienduizenden extra structurele varianten toe, vooral inserties en complexe duplicaties die moeilijk te detecteren zijn met oudere methoden. Dit suggereert dat long-read studies nog steeds voorheen onzichtbare lagen van genetische diversiteit in veehouderij blootleggen.
DNA-veranderingen koppelen aan genactiviteit
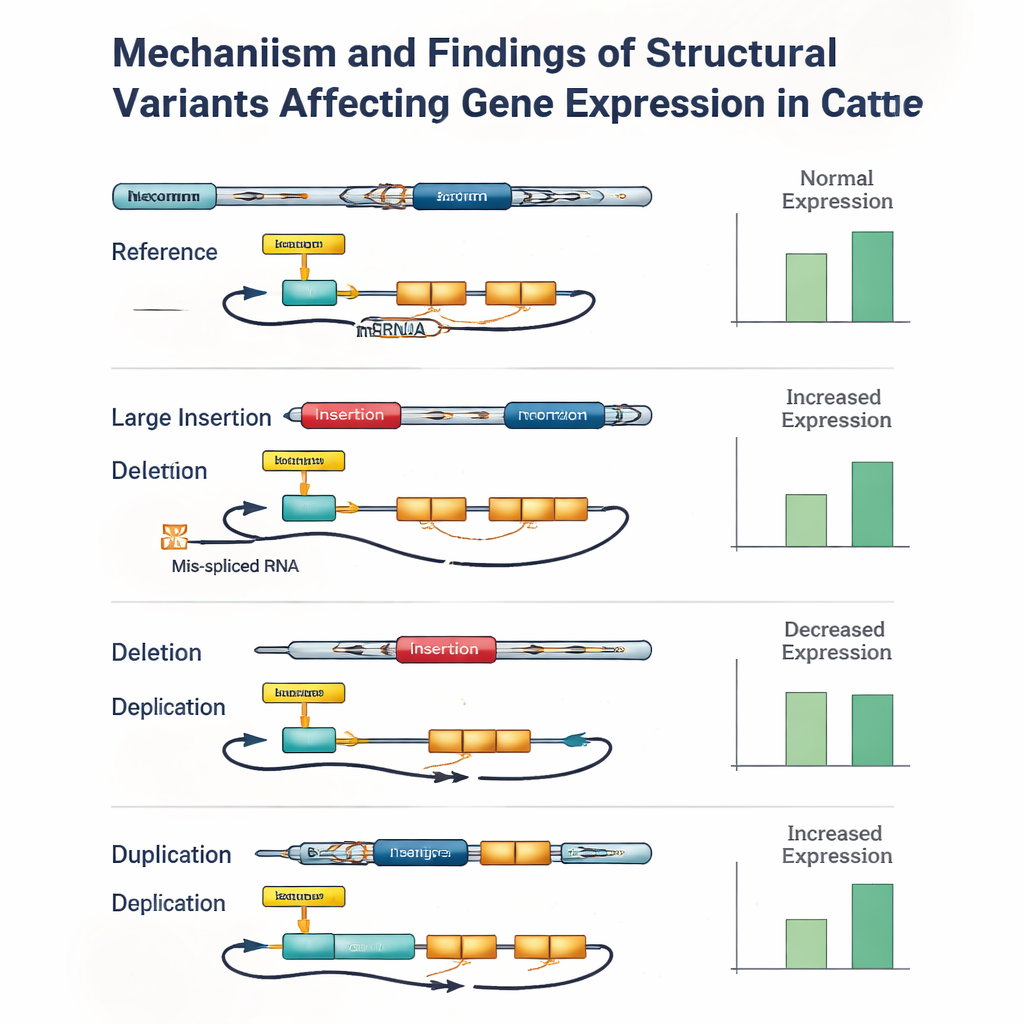
Om te zien hoe deze DNA-verschillen de biologie daadwerkelijk beïnvloeden, richtte het team zich op weefsel dat belangrijk is voor mannelijke vruchtbaarheid: de testis. Voor 117 van de stieren hadden ze diepe RNA-sequencingdata die laten zien welke genen actief zijn en hoe hun boodschappers (RNA) worden gespliced. Door genetische varianten in de nabijheid van elk gen statistisch te koppelen aan diens activiteit, identificeerden ze meer dan 27.000 "moleculaire QTLs" — genomische locaties die ofwel de hoeveelheid genexpressie veranderen ofwel hoe het RNA wordt samengevoegd. Structurele varianten kwamen naar voren als belangrijke spelers: ze waren meer dan twee keer zo vaak aanwezig bij de belangrijkste expressiesignalen en meer dan vijf keer zo vaak bij de belangrijkste splicingssignalen als verwacht op basis van toeval. In veel gevallen was de meest invloedrijke variant een grote insertie, deletie of duplicatie die zich bevond in een promotor, enhancer, exon of splice-site in plaats van een enkel-letter verandering.
Wanneer genotypeerfouten belangrijke signalen verbergen
De studie bracht echter ook de beperkingen van huidige hulpmiddelen aan het licht. Zelfs met hoogwaardige long reads was het nauwkeurig toewijzen van genotypen voor structurele varianten aan elk dier uitdagend, vooral voor grote inserties en lange duplicaties. Kleine fouten — soms slechts bij één of twee stieren — konden een structurele variant net iets minder statistisch significant laten lijken dan een nabijgelegen kleine variant die er genetisch perfect mee in lockstep liep. Toen de auteurs sommige van de sterkste signalen handmatig controleerden, vonden ze herhaaldelijk gevallen waarin een structurele variant binnen een gen of een belangrijke regulerende regio de meest waarschijnlijke oorzaak van het effect was, maar genotypeerfouten of ontbrekende data ervoor zorgden dat een gekoppelde kleine variant bovenaan de ranglijst kwam te staan.
Wat dit betekent voor veeteelt en daarbuiten
Voor niet-specialisten is de belangrijkste conclusie dat “grote” DNA-veranderingen veel uitmaken. Deze long-read inventarisatie bij runderen toont aan dat structurele varianten sterk verrijkt zijn onder genetische locaties die bepalen hoe genen worden aangezet en gespliced, met name in reproductief weefsel. Tegelijk waarschuwt de studie dat de huidige analysemethoden nog steeds veel van deze varianten missen of verkeerd labelen, vooral wanneer de sequencingdiepte bescheiden is. Naarmate long-read sequencing goedkoper en nauwkeuriger wordt en betere software beschikbaar komt, zullen fokkers en onderzoekers in staat zijn economisch belangrijke eigenschappen — zoals vruchtbaarheid, ziekteweerstand en melkproductie — terug te voeren op specifieke structurele varianten. Dezelfde principes gelden voor de menselijke gezondheidszorg en plantenveredeling: om complexe eigenschappen volledig te begrijpen, moeten we verder kijken dan enkel-letterveranderingen en de grotere herschikkingen omarmen die genomen hervormen.
Bronvermelding: Mapel, X.M., Leonard, A.S. & Pausch, H. Molecular QTL are enriched for structural variants in a cattle long-read cohort. Commun Biol 9, 290 (2026). https://doi.org/10.1038/s42003-026-09596-w
Trefwoorden: structurele varianten, long-read sequencing, rundergenomics, genexpressie, moleculaire QTL