Clear Sky Science · nl
Kwaliteitsbeoordeling van RNA 3D-structuurmodellen met diepe leertechnieken en tussentijdse 2D-kaarten
Waarom het beoordelen van RNA-vormen belangrijk is
In elke cel vouwen RNA-moleculen zich tot ingewikkelde driedimensionale vormen die helpen bepalen welke genen actief zijn, chemische reacties sturen en zelfs virussen bestrijden. Tegenwoordig kunnen krachtige computers veel van deze vormen voorspellen, maar wetenschappers hebben nog een fundamenteel probleem: wanneer de computer tientallen of honderden kandidaatvormen voor hetzelfde RNA oplevert, welke daarvan komt echt in de buurt van de werkelijkheid? Dit artikel introduceert RNArank, een kunstmatig-intelligentiehulpmiddel dat die vraag aanpakt door RNA 3D-modellen te beoordelen, als een structurele kwaliteitsinspecteur, zodat onderzoekers zich kunnen concentreren op de meest betrouwbare voorspellingen.
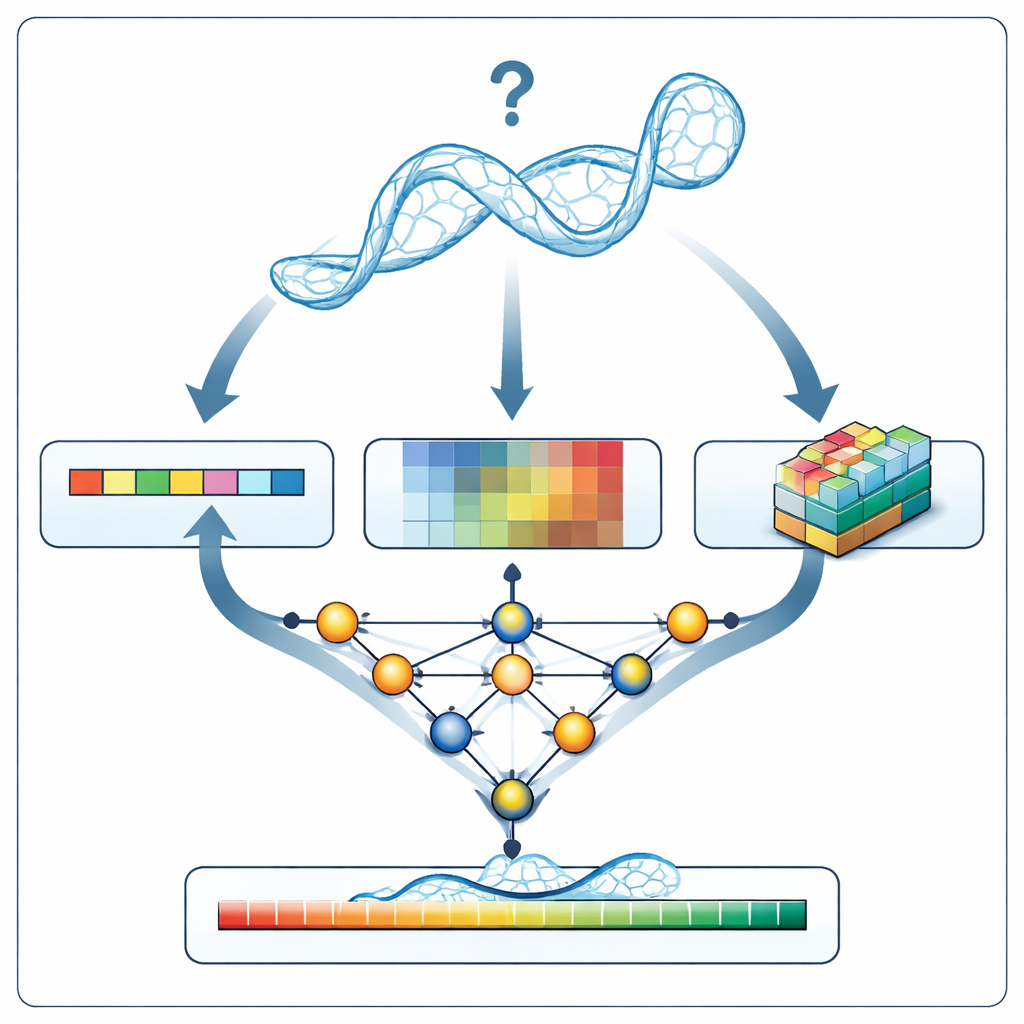
Een nieuwe inspecteur voor RNA-modellen
RNArank is ontwikkeld om de kwaliteit van een voorgestelde RNA-vorm te beoordelen zonder te hoeven weten hoe die vorm tot stand is gekomen. Of het model nu afkomstig is van een deep-learning-systeem, een op fysica gebaseerde simulatie of een menselijke expert, RNArank kijkt alleen naar de uiteindelijke 3D-coördinaten. Het stelt dan in feite de vraag: “Ziet deze structuur eruit als een realistisch RNA?” Dit soort onafhankelijke kwaliteitsbeoordeling is essentieel omdat RNA-voorspelling, in tegenstelling tot het eiwitveld waar tools zoals AlphaFold vaak direct zeer betrouwbare resultaten leveren, nog steeds profiteert van het combineren van meerdere methoden en menselijke inzichten — en van een slimme manier om de resulterende modellen te rangschikken.
De AI leren wat goed RNA is
Om RNArank te trainen, verzamelden de auteurs zo’n 200.000 RNA-structuren, die een breed spectrum bestrijken van duidelijk fout tot bijna perfect. Deze werden opgebouwd uit bekende experimentele structuren met gebruik van uiteenlopende benaderingen, waaronder moderne deep-learning-voorspellers, moleculaire dynamicasimulaties die atomaire beweging nabootsen, en opzettelijke vervormingen van nauwkeurige structuren om “decoys” te creëren. Voor elk model berekende het team hoe nauwkeurig het overeenkwam met het echte, experimenteel bepaalde RNA, met behulp van een verfijnde nauwkeurigheidsscore toegespitst op RNA, genaamd lDDT_RNA. Deze score focust op hoe goed de afstanden tussen paren nucleotiden worden gereproduceerd, en legt zowel de algemene vouwing als lokale details vast zonder overdreven gevoelig te zijn voor molecuullengte.
Hoe RNArank een RNA leest en scoort
Wanneer RNArank een nieuw RNA-model onderzoekt, vertaalt het eerst de structuur naar drie soorten informatie: een 1D-beschrijving van de sequentie en de ruggegraatgeometrie langs de keten, 2D-beschrijvingen van hoe elk paar nucleotiden zich tot elkaar verhoudt (hun afstanden, geschatte interactie-energieën en mogelijke atomaire botsingen), en 3D “voxel”-momentopnamen, kleine rasters die de lokale atoomwolken rond elk nucleotide vastleggen. Een meerledig neuraal netwerk weeft deze aanwijzingen samen tot een verenigd beeld en voorspelt vervolgens twee tussentijdse 2D-kaarten: welke nucleotiden waarschijnlijk in contact staan en hoe ver elke gemodelleerde afstand waarschijnlijk afwijkt van de onbekende ware structuur. Uit deze kaarten reconstrueert RNArank zowel een per-nucleotide betrouwbaarheidscore als een totaalscore voor het gehele RNA-model.
De methode op de proef stellen
Het team beoordeelde RNArank op drie veeleisende datasets: een set van 24 recent opgeloste RNA’s uit de Protein Data Bank, en de RNA-doelwitten uit twee internationale blinde voorspellingswedstrijden, CASP15 en CASP16, waar veel groepen modellen indienen zonder de antwoorden van tevoren te kennen. Over duizenden kandidaatstructuren volgden RNArank’s scores de werkelijke modelkwaliteit nauwer dan verschillende gevestigde energie-gebaseerde scoremethoden en andere deep-learningbenaderingen. Het was bijzonder sterk in het selecteren van de beste of bijna beste modellen uit een pool en in het identificeren welke delen van een structuur waarschijnlijk onbetrouwbaar waren. De auteurs toonden ook aan dat RNArank zijn prestaties behield, zelfs voor RNA’s die sequentieel duidelijk verschilden van die in de trainingsset, wat wijst op echte generalisatie in plaats van memorisatie.
Beperkingen nu en vooruitzichten voor de toekomst
RNArank is niet perfect: het heeft nog moeite met bijzonder flexibele RNA’s die vele vormen aannemen, en met RNA’s die van vorm veranderen wanneer ze worden geklemd door eiwitten in grote moleculaire machines. Toch is het snel genoeg om vele modellen van RNA’s van enkele honderden nucleotiden in slechts seconden te verwerken, en het helpt al geautomatiseerde servers hogere-kwaliteitvoorspellingen te kiezen in community-brede tests. Door een methode-agnostische, alleen-structuur gebaseerde beoordelaar van RNA-modellen te bieden, geeft RNArank biologen een scherper filter om ruwe computeruitvoer om te zetten in betrouwbare structurele hypothesen, en brengt het veld een stap dichter bij routinematige, betrouwbare voorspelling van RNA-vormen en daarmee diepere inzichten in hoe deze veelzijdige moleculen werken.
Bronvermelding: Liu, X., Wang, W., Du, Z. et al. Quality assessment of RNA 3D structure models using deep learning and intermediate 2D maps. Commun Biol 9, 293 (2026). https://doi.org/10.1038/s42003-026-09582-2
Trefwoorden: RNA 3D-structuur, diepe leertechniek, beoordeling van modelkwaliteit, structurele bioinformatica, RNArank