Clear Sky Science · nl
Onderzoek naar interacties tussen het Escherichia coli Colicine E9-immuniteitsproteïne en DNA-gyrase van Pseudomonas aeruginosa: geavanceerde computationele benadering voor de ontwikkeling van nieuwe antimicrobiële strategieën
Bacteriële wapens omzetten in nieuwe geneesmiddelen
Nu antibioticaresistentie om zich heen grijpt, raken artsen steeds meer zonder opties om gevaarlijke infecties te bestrijden. Sommige van de hardnekkigste veroorzakers, zoals Pseudomonas aeruginosa, zijn bestand tegen veel middelen. Deze studie zoekt nieuwe ideeën juist bij bacteriën zelf en onderzoekt of het ingebouwde beschermingsproteïne van de ene microbe kan worden hergebruikt om een essentieel enzym in een andere microbe uit te schakelen. Met geavanceerde computersimulaties laten de onderzoekers zien hoe een klein "immuniteits"-proteïne zich stevig kan vasthechten aan een sleutelenzym van bacteriën, wat wijst op een nieuwe route voor toekomstige antimicrobiële middelen.
Een klein schild tegen een dodelijk toxine
Bepaalde stammen van Escherichia coli produceren krachtige proteïnetoxinen, colicinen genaamd, die naburige bacteriën kunnen doden. Om zichzelf te beschermen tegen vergiftiging maken deze bacteriën ook bijbehorende immuniteitsproteïnen. Een van die beschermers, bekend als het Colicine E9-immuniteitsproteïne (vaak Im9 genoemd), klemt zich vast aan het snijdende domein van het toxine en voorkomt dat het het DNA van de gastheer beschadigt. Omdat dit partnerschap zo specifiek en sterk is, vermoeden wetenschappers al lang dat gedetailleerd begrip ervan nieuwe manieren zou kunnen onthullen om schadelijke bacteriën te beheersen. In dit werk vragen de auteurs zich af of Im9 zich ook aan DNA-gyrase kan hechten, een essentieel enzym in Pseudomonas aeruginosa dat reguleert hoe het DNA wordt gekronkeld en gekopieerd.
Een kwetsbaar enzym mikken in een moeilijk behandelbare kiem
Pseudomonas aeruginosa is een belangrijke ziekenhuispathogeen, in staat te overleven in vijandige omgevingen en resistent tegen veel geneesmiddelen. DNA-gyrase is een van zijn belangrijkste enzymen en zorgt ervoor dat de lange DNA-strengen van de bacterie goed gedraaid blijven zodat ze gerepliceerd kunnen worden. Omdat het blokkeren van dit enzym de bacteriegroei kan stilleggen, is het al een bewezen doelwit voor sommige antibiotica. De auteurs gebruikten een deep-learningtool om de driedimensionale structuur van Pseudomonas DNA-gyrase te scannen en waarschijnlijke "hotspots" aan te wijzen — clusters van aminozuren op het oppervlak die het belangrijkst zijn voor het binden van partners. Deze regio’s vormen de actieve pocket van het enzym, waar de normale DNA-verwerking plaatsvindt en waar een potentiële remmer idealiter zou aanhechten.
Het simuleren van een moleculaire handdruk
Om te onderzoeken of Im9 deze hotspots kon vastpakken, gebruikten de onderzoekers moleculaire dockingprogramma’s die eiwitten virtueel als 3D-puzzels in elkaar laten passen. Ze hebben eerst de beschikbare structuren van zowel Im9 als DNA-gyrase opgeschoond en aangevuld, een ontbrekende lus in het enzym gerepareerd en korte simulaties gedraaid om gespannen regio’s te laten ontspannen. Vervolgens gebruikten ze twee complementaire dockingtools, ClusPro en LightDock, om veel kandidaatcomplexen te genereren. Uit deze set selecteerden ze de meest veelbelovende arrangementen en onderwierpen die aan lange moleculaire dynamicasimulaties van honderden nanoseconden. Deze tijdsafhankelijke ‘films’ stelden hen in staat te observeren hoe de twee eiwitten zich aanpasten, buigden en in stabielere vormen zakten wanneer ze gebonden waren.
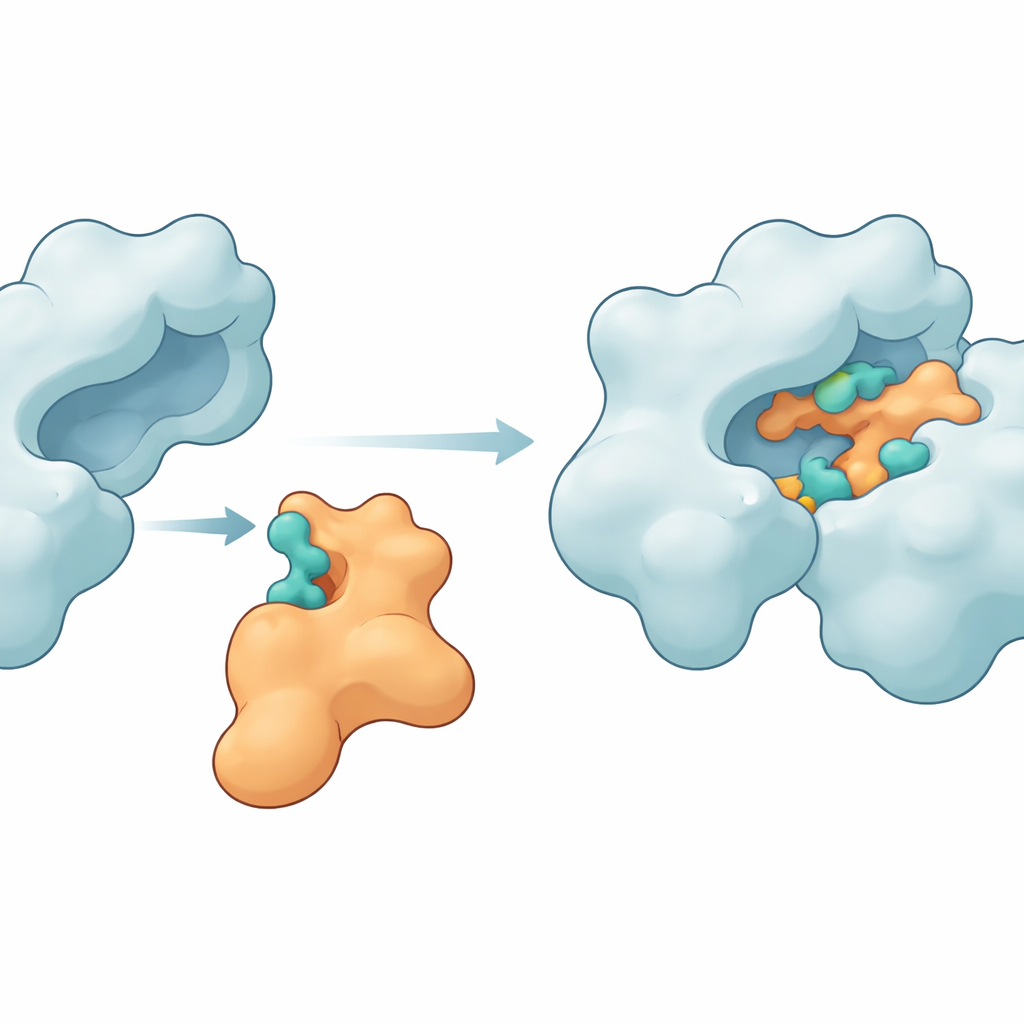
Sleutelcontactpunten die de eiwitten bij elkaar houden
De simulaties toonden aan dat Im9 inderdaad een nauwe en duurzame complexvorming met DNA-gyrase kan aangaan. Verschillende aminozuren op het enzym — zoals MET27, ASP47, LYS105, LEU198, ASN199, ARG191 en GLU194 — vormden herhaaldelijk waterstofbruggen en andere aantrekkingskrachten met corresponderende plaatsen op Im9. In één leidend model behielden de twee partners gedurende het grootste deel van de simulatie tussen de zes en tien waterstofbruggen, een teken van een sterke en goed georganiseerde interface. Andere structurele maten, waaronder hoe compact de eiwitten bleven en hoeveel hun vormen fluctueerden, lieten zien dat het enzym intact bleef terwijl het immuniteitsproteïne net genoeg flexibiliteit toonde om zich naar het gyrase-oppervlak te vormen. Energieberekeningen met de MM-GBSA-methode ondersteunden verder het idee dat deze contacten een gunstige, zij het bescheiden, bindingsvrije energie opleveren, gedomineerd door elektrostatica en van der Waals-bijdragen.
Van computermodellen naar toekomstige antimicrobiële middelen
Gezamenlijk suggereren de resultaten dat het Colicine E9-immuniteitsproteïne zich stabiel kan binden aan het actieve gebied van Pseudomonas DNA-gyrase en zo een langdurig complex kan vormen dat in principe de normale rol van het enzym bij DNA-hantering zou kunnen blokkeren. Hoewel deze bevindingen volledig op computermodellen zijn gebaseerd en nog experimenteel moeten worden bevestigd, bieden ze een gedetailleerd blauwdruk van waar en hoe een eiwitgebaseerde remmer zou kunnen aanhechten. Voor niet-specialisten is de kernboodschap dat de wapens en schilden uit de natuur zelf nieuwe strategieën kunnen inspireren tegen moeilijk behandelbare infecties. Door deze microscopische handdruk op atomair niveau te begrijpen, komen wetenschappers een stap dichter bij het ontwerpen van nieuwe antimicrobiële middelen die cruciale bacteriële enzymen uitschakelen zonder menselijke cellen te schaden.
Bronvermelding: Alfaraj, R., Alkathiri, F. & Chikhale, R. Investigating Escherichia coli Colicin E9 immunity protein interactions with DNA gyrase of Pseudomonas aeruginosa: advanced computational approach for developing novel antimicrobial strategies. Sci Rep 16, 10786 (2026). https://doi.org/10.1038/s41598-026-44427-2
Trefwoorden: antibioticaresistentie, DNA-gyrase, eiwit-eiwitinteracties, computationeel medicijnontwerp, Pseudomonas aeruginosa