Clear Sky Science · nl
Morpho-biochemische en moleculaire identificatie van Bacillus licheniformis en Bacillus cereus-isolaten uit de rhizosfeer van sorghum (Sorghum bicolor L.)
Vriendelijke microben bij de wortel van een taaie gewas
Sorghum is een robuust graan dat miljoenen mensen voedt, vooral op plaatsen waar hitte en droogte landbouw lastig maken. Maar sorghum staat niet alleen in arme bodems: de wortels worden omringd door kleine bodembewonende partners die kunnen helpen bij het vinden van voedingsstoffen, het bestrijden van ziekte en het omgaan met stress. Deze studie onderzoekt welke bacteriën rond sorghumwortels voorkomen in oostelijk India en neemt twee belangrijke hulpverleners uit het geslacht Bacillus nader onder de loep, en laat zien hoe zorgvuldig speurwerk in het laboratorium onthult wie ze zijn en hoe ze verwant zijn aan hun vele verwanten.

Graven in het leven rond de wortels
De onderzoekers verzamelden aan de wortels klevende grond van verschillende sorghumvariëteiten die op drie locaties rond Bhubaneswar, India, werden geteeld, waaronder een stadspark, een landbouwstation en een universiteitscampus. Uit deze wortelzone- (rhizosfeer) bodems gebruikten ze standaard kweektechnieken om bacteriën op voedingsrijke platen te laten groeien, en kozen vervolgens kolonies die verschilden in kleur, vorm en textuur. Een eerste kijkje onder de microscoop en met Gramkleuring toonde dat de meeste van de 13 isolaten staafvormige bacteriën met dikke celwanden waren, een kenmerk van Bacillus en nauwe verwanten, naast enkele bolvormige types en één dunnerwandige, Gram-negatieve stam.
Testen wat de microben kunnen
Om verder te gaan dan uiterlijk voerde het team eenvoudige biochemische tests uit die laten zien hoe elk microbe met zuurstof omgaat, bepaalde moleculen afbreekt en suikers fermenteert. Bijvoorbeeld, het toevoegen van waterstofperoxide toont aan of cellen catalase maken, een enzym dat hen beschermt tegen reactieve zuurstof, terwijl andere tests zuurvorming of het vermogen om het aminozuur tryptofaan af te breken detecteren. Patronen in deze reacties hielpen bij het beperken van de waarschijnlijke identiteit van elk isolaat. Twee staafvormige stammen, aangeduid als AG3 en AG11, vielen op: beide tolereerden zuurstof goed, gingen efficiënt om met schadelijke bijproducten en toonden een vergelijkbare fermentatiestijl die typisch is voor Bacillus-soorten die goed gedijen rond plantenwortels.
Het genetische streepjescode van bacteriën lezen
Aangezien veel Bacillus-soorten er hetzelfde uitzien en zich vergelijkbaar gedragen, wendden de wetenschappers zich tot hun DNA voor een nauwkeuriger antwoord. Ze concentreerden zich op het 16S rRNA-gen, een veelgebruikte genetische "streepjescode" voor bacteriën. Na DNA-extractie uit AG3 en AG11 kopieerden ze dit gen met de polymerasekettingreactie en bevestigden, op een gel, dat de fragmenten de verwachte lengte hadden. Het team las daarna de genvolgordes met Sanger-sequencing en vergeleek ze met duizenden bekende sequenties in de openbare NCBI-database. De overeenkomsten waren opvallend: AG3 kwam bijna perfect overeen met Bacillus licheniformis, terwijl AG11 een exacte match was met Bacillus cereus. Beide komen veel voor in landbouwbodems en staan bekend om sterke interacties met planten, soms met groeibevorderende effecten en soms, in het geval van B. cereus, met gezondheidsrisico’s in andere contexten.
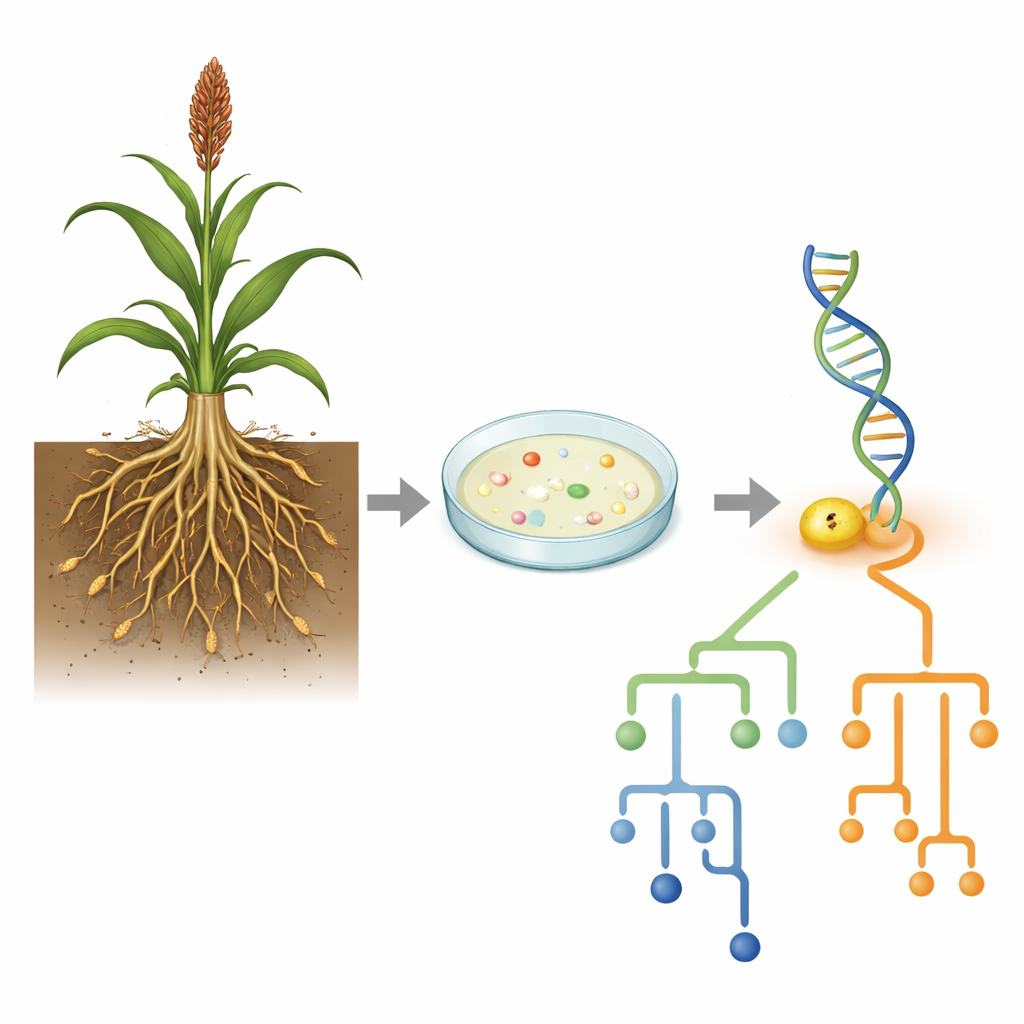
De nieuwe vondsten plaatsen in de levensboom
Weten wat de dichtstbijzijnde match is, is slechts een deel van het verhaal; de auteurs wilden ook zien waar deze isolaten op de bredere bacteriële stamboom staan. Ze bouwden evolutionaire bomen door de 16S-sequenties van AG3 en AG11 op één lijn te zetten met tientallen verwante stammen en statistische modellen te gebruiken om te schatten hoe snel verschillende posities in het gen in de loop van de tijd zijn veranderd. Bacillus licheniformis AG3 groepeerde zich nauw met een grote groep vergelijkbare stammen, maar toonde sterke variatie in hoe snel verschillende delen van het gen zijn geëvolueerd, wat wijst op regio’s onder verschillende evolutionaire druk. Daarentegen viel Bacillus cereus AG11 in een afzonderlijke subgroep binnen het B. cereus-complex, met meer gelijkmatig veranderende genposities. Deze patronen suggereren dat, zelfs binnen één geslacht, verschillende lijnen verschillende evolutionaire paden kunnen volgen terwijl ze toch vergelijkbare bodemniches bezetten.
Wat dit betekent voor toekomstige landbouw
De studie toont aan dat sorghumwortels in één regio een diverse groep bacteriën herbergen en dat het combineren van eenvoudige microscopische en chemische tests met DNA-sequencing een krachtig middel is om sleutelspelers zoals B. licheniformis en B. cereus te identificeren. Voor niet‑specialisten is de belangrijkste boodschap dat de gezondheid en opbrengst van gewassen niet alleen afhangen van zaden en bodem, maar ook van deze verborgen microbiële partners. Hoewel dit werk nog niet direct heeft getest hoe de geïdentificeerde stammen sorghumgroei beïnvloeden, brengt het in kaart welke microben aanwezig zijn en hoe ze verwant zijn—cruciale stappen richting het ontwerpen van veilige, gerichte microbieel-inoculanten die boeren kunnen helpen veerkrachtiger sorghum te telen met minder chemische input.
Bronvermelding: Jurry, A.G., Sahoo, J.P., Sharma, S.S. et al. Morpho-biochemical and molecular identification of Bacillus licheniformis and Bacillus cereus isolates from sorghum (Sorghum bicolor L.) rhizosphere. Sci Rep 16, 8983 (2026). https://doi.org/10.1038/s41598-026-42932-y
Trefwoorden: sorghum, rhizosfeerbacteriën, Bacillus licheniformis, Bacillus cereus, plantenstimulatie