Clear Sky Science · nl
Eerste inzichten in kenmerken en voorspelling van geneesmiddelresistentie bij Mycobacterium tuberculosis door whole genome sequencing in de provincie Fujian, China
Waarom dit onderzoek belangrijk is voor alledaagse gezondheid
Tuberculose (tbc) is een oude luchtwegaandoening die nog steeds elk jaar miljoenen mensen infecteert. De grootste hedendaagse bedreiging is niet alleen tbc zelf, maar tbc‑kiemen die onze beste geneesmiddelen kunnen omzeilen. Deze studie uit de provincie Fujian in zuidoostelijk China stelt een eenvoudig maar cruciaal vraagstuk: kan het uitlezen van de volledige genetische code van tbc‑kiemen artsen snel vertellen welke medicijnen werken, lang voordat traditionele testen klaar zijn? Het antwoord kan bepalen hoe landen patiënten en gemeenschappen beschermen tegen moeilijk behandelbare tbc.
Oude testen zijn traag, maar de tijd dringt
Om de juiste behandeling te kiezen, moeten artsen weten tegen welke antibiotica de tbc‑stam van een patiënt resistent is. De lang gebruikte methode is het kweken van de bacterie in het laboratorium met en zonder medicijnen en kijken welke middelen de groei remmen. Hoewel betrouwbaar, kan dit proces tot twee maanden duren, waarin patiënten mogelijk onvoldoende behandeling krijgen en resistente kiemen blijven verspreiden. In Fujian, waar tbc nog een belangrijk volksgezondheidsprobleem is, werd het totale resistentiepercentage eerder geschat op ongeveer één op de vijf tbc‑gevallen. Volksgezondheidsfunctionarissen hebben dus een snellere manier nodig om patiënten de juiste medicijnen te geven en om te volgen hoe resistente stammen zich verspreiden.
Het instructieboekje van de tbc‑kiem lezen
In deze studie onderzochten de onderzoekers 150 tbc‑monsters, verzameld bij patiënten in Fujian tussen 2021 en 2022. Voor elk monster gebruikten ze zowel de klassieke groeigebaseerde test als een nieuwere methode, whole‑genome sequencing. In plaats van te observeren hoe kiemen zich gedragen bij verschillende medicijnen, leest sequencing elke letter van het bacteriële DNA en onthult kleine veranderingen — mutaties — die bekendstaan om specifieke geneesmiddelen minder effectief te maken. Door deze genetische aanwijzingen te vergelijken met de traditionele laboratoriumresultaten, kon het team beoordelen hoe goed DNA‑data op zichzelf voorspellen tegen welke medicijnen een bepaalde tbc‑stam resistent is.
Welke tbc‑families verspreiden zich en hoe resistent zijn ze?
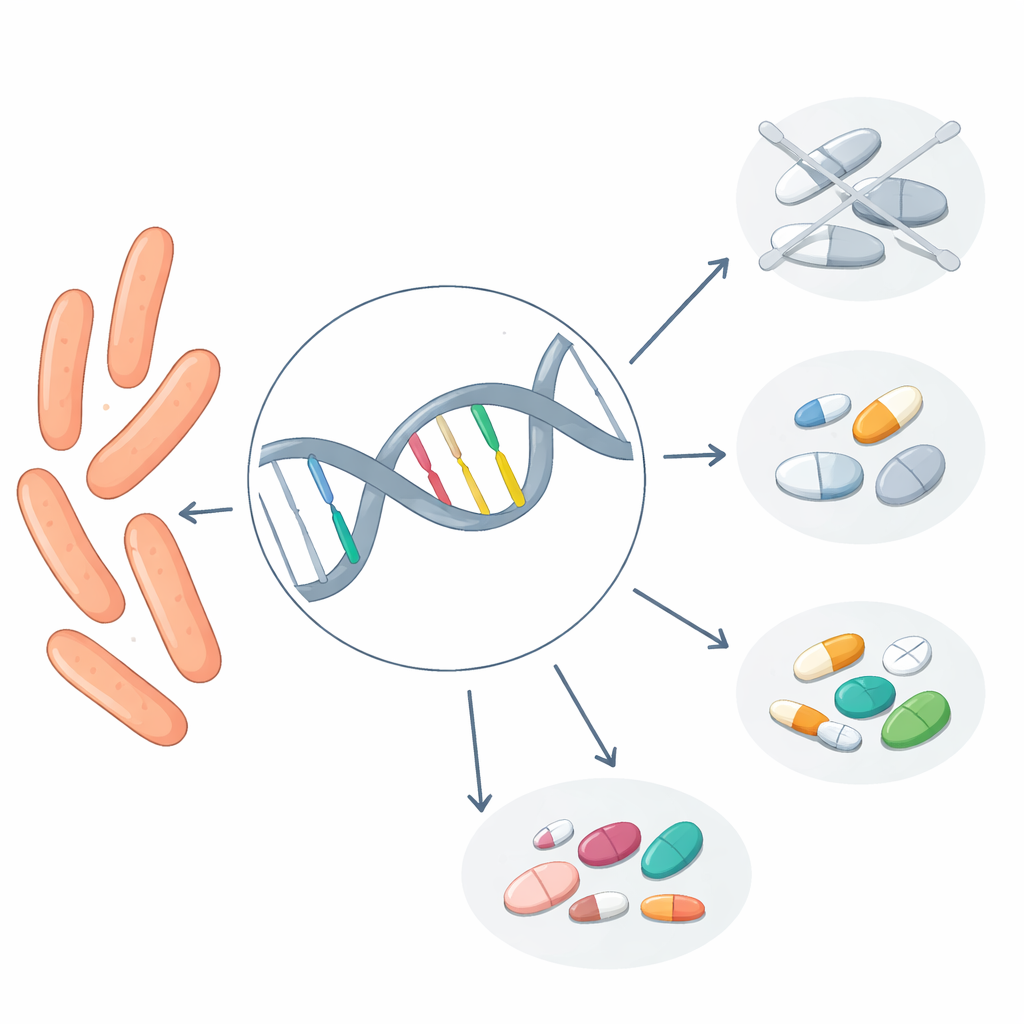
De genetische gegevens stelden het team ook in staat om elke tbc‑stam op een soort stamboom te plaatsen. In Fujian domineerden twee hoofdgroepen: één bekend als Lineage 2 en een andere als Lineage 4. Samen vormden zij bijna alle monsters. Opmerkelijk was dat resistentie veel voorkwam maar over deze groepen verspreid was, in plaats van beperkt te zijn tot één tak. Meer dan tweederde van de stammen droeg ten minste één mutatie die met resistentie geassocieerd wordt. Bepaalde genetische veranderingen keerden steeds terug en waren telkens gekoppeld aan een specifiek medicijn. Zo ging één mutatie vaak samen met resistentie tegen isoniazide, een basismedicijn tegen tbc, terwijl een andere sterk geassocieerd was met resistentie tegen rifampicine, een belangrijk onderdeel van de standaardbehandeling. Vergelijkbare patronen werden gezien voor andere middelen zoals fluoroquinolonen en ethambutol.
Hoe goed komt DNA‑voorspelling overeen met praktijkresultaten?
De cruciale toets was of deze DNA‑aanwijzingen overeenkwamen met wat de langzamere groeigebaseerde testen aantoonden. Voor drie van de belangrijkste geneesmiddelen — isoniazide, rifampicine en de groep fluoroquinolonen — was de overeenstemming sterk. De sequencing wees resistentie correct aan in ruwweg drie van de vier gevallen en misclassificeerde bijna nooit een werkelijk gevoelige stam als resistent. Met andere woorden, wanneer het DNA aangaf dat een stam gevoelig zou zijn, was dat meestal het geval. Voor twee oudere middelen, streptomycine en ethambutol, waren de genetische voorspellingen minder betrouwbaar, waarschijnlijk omdat er nog hiaten zijn in de kennis over alle mutaties die resistentie veroorzaken. De methode had ook moeite met het inschatten van resistentie tegen verschillende tweede‑lijnsmiddelen, simpelweg omdat in deze studie slechts heel weinig stammen resistent waren tegen die medicijnen.
Wat dit betekent voor patiënten en de volksgezondheid
Voor mensen met tbc en de zorgverleners die hen behandelen, is de conclusie bemoedigend. Dit onderzoek laat zien dat een enkele DNA‑test snel zowel de familieachtergrond van een tbc‑stam kan onthullen als, voor meerdere sleutelmedicijnen, of die stam waarschijnlijk resistent is tegen behandeling. Hoewel traditionele groeigebaseerde testen nog steeds nodig zijn, vooral voor sommige medicijnen, kan whole‑genome sequencing artsen een vroeg en redelijk accuraat beeld geven van welke middelen waarschijnlijk effectief zullen zijn. Op plaatsen zoals Fujian, en mogelijk wereldwijd, kan het combineren van deze benaderingen leiden tot snellere, preciezere behandelingen, minder kans op verspreiding en een sterker verweer tegen de toename van geneesmiddelresistente tbc.
Bronvermelding: Wei, S., Zhao, Y., Lin, J. et al. First insight of characteristics and prediction of Mycobacterium tuberculosis drug resistance by whole genome sequencing in Fujian Province, China. Sci Rep 16, 9266 (2026). https://doi.org/10.1038/s41598-026-40398-6
Trefwoorden: tuberculose, geneesmiddelresistentie, whole genome sequencing, Fujian China, infectieziekte‑surveillance