Clear Sky Science · nl
Moleculaire evolutie en diversiteit van het RNA-afhankelijke RNA-polymerase van norovirus
Waarom maag-darmvirussen ons blijven verrassen
Norovirus is het beruchte 'maaggriep'-virus dat binnen enkele dagen cruiseschepen, scholen en ziekenhuizen lam kan leggen. Het verspreidt zich gemakkelijk, maakt jaarlijks honderden miljoenen mensen ziek en brengt voortdurend nieuwe varianten voort. Deze studie kijkt onder de motorkap van die evolutie, met de nadruk op één viraal enzym — een interne "kopieermachine" genaamd RNA-polymerase — om te onderzoeken hoe het in de loop van de tijd verandert en hoe stabiel het werkelijk is. Inzicht in deze verborgen motor van verandering kan helpen verklaren waarom sommige norovirusstammen wereldwijd domineren en kan de ontwikkeling van toekomstige antivirale middelen sturen.
De interne kopieermachine van het virus
Norovirus draagt zijn genetisch materiaal als RNA en is afhankelijk van een enzym genaamd RNA-afhankelijk RNA-polymerase om dat RNA in geïnfecteerde cellen te kopiëren. Dit enzym, ongeveer 510 bouwstenen lang, lijkt op een gekromde hand met vingers, palm en duim, die een kanaal vormt waar RNA en nieuwe bouwstenen doorheen gaan. Binnen deze structuur bevinden zich zeven kleine "hitzones" die bijna identiek zijn tussen stammen; deze regio’s voeren de kernchemie van het kopiëren van het genoom uit. Omdat het polymerase essentieel is voor de reproductie van het virus, kunnen zelfs kleine verstoringen in deze hitzones desastreus zijn voor het virus, waardoor de evolutie deze regio’s uiterst zorgvuldig lijkt te bewaren.
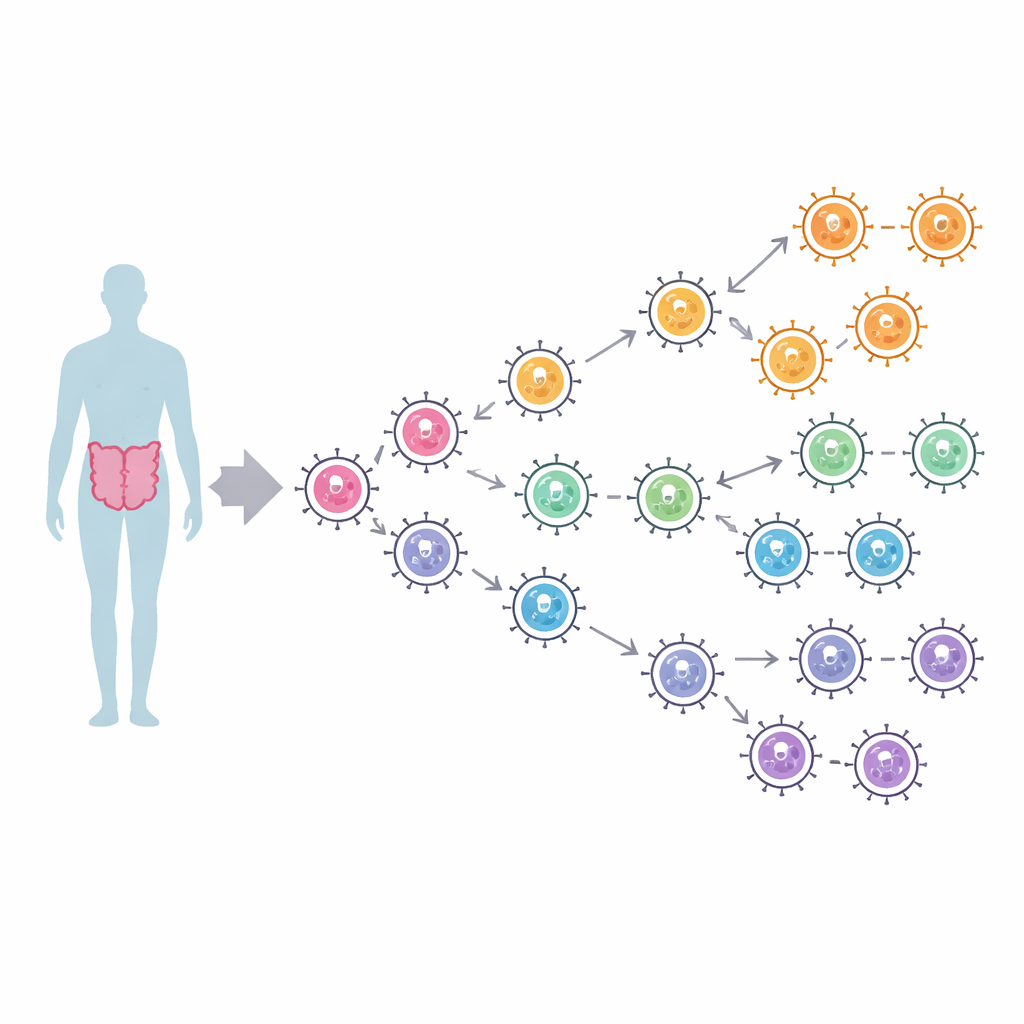
Honderden stammen, een paar sleutelgroepen
De onderzoekers verzamelden 1.094 volledige polymerase-sequenties van twee grote humane norovirusgroepen, GI en GII, verzameld wereldwijd tussen 1972 en 2024. Met behulp van computationele stambomen die zowel bemonsteringsdata als locaties incorporeerden, volgden zij hoe deze enzymen zich vertakten over bijna vier eeuwen. GI-polymerases vielen in drie hoofdlijnen uiteen die waarschijnlijk begonnen te splitsen rond de 1600s, terwijl GII-polymerases vier lijnen vormden, inclusief een aparte tak voor een type dat bekendstaat als P16. Moderne infecties worden gedomineerd door twee GII-polymerasetypes, P16 en P31, beide historisch gekoppeld aan het lang heersende pandemische capsid-genotype GII.4. Ondanks de wereldwijde verspreiding toonden de stambomen weinig geografische clustering — stammen van verschillende continenten mengen zich — wat suggereert dat norovirus zich snel over de wereld verplaatst zonder in bepaalde regio’s gevangen te blijven.
Langzame, gestage veranderingen met goed beschermde kernen
Door de aminozuurbouwstenen op elke positie in het polymerase te vergelijken, stelde het team duizenden veranderingen over de types heen vast. Ze vonden veel minder veranderingen in GI dan in GII, deels een weerspiegeling van minder beschikbare sequenties, maar er ontstond een duidelijk patroon: de zeven geconserveerde hitzones en de nabijgelegen RNA-bindingsplaats bleven vrijwel onaangetast. Wanneer daar substituties optraden, waren het meestal milde wissels tussen chemisch vergelijkbare bouwstenen, wat aangeeft dat het enzym alleen zeer zachte aanpassingen in deze cruciale zones tolereert. De meeste frequente veranderingen concentreerden zich in de 'vingers' en andere buitenste regio’s van het enzym, weg van de centrale chemie. Sommige posities lieten zelfs omkeerbare heen-en-weer veranderingen zien tussen verschillende polymerasetypes, een teken van convergente evolutie waarbij niet-verwante stammen op soortgelijke oplossingen stuiten.
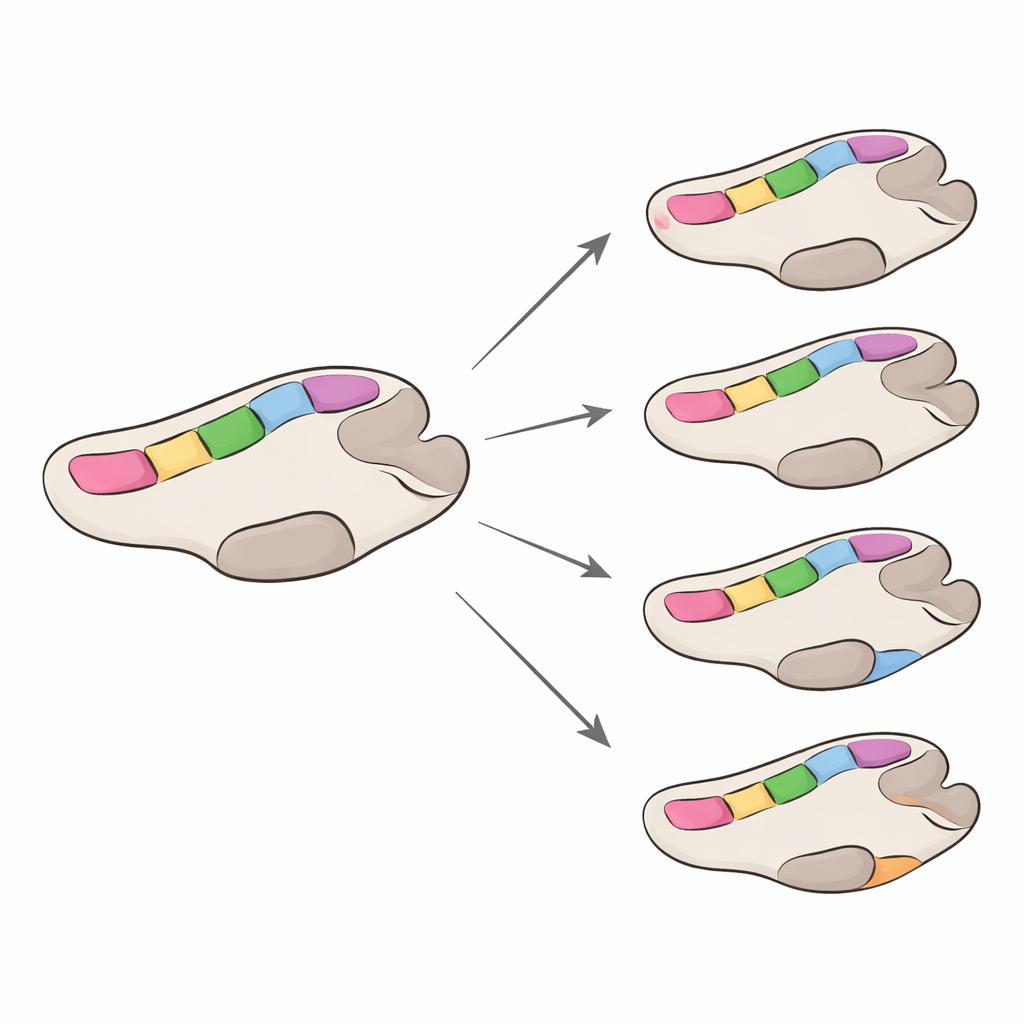
Verschillende snelheden voor verschillende virusfamilies
Het team schatte vervolgens hoe snel het polymerase evolueert, met de focus op veranderingen die aminozuren veranderen, omdat die waarschijnlijker de functie beïnvloeden. Over het geheel genomen veranderden GII-polymerases ongeveer vier keer zo snel als GI-polymerases, hoewel beide langzamer evolueerden dan het buitenste schildeiwit van norovirus, dat bekendstaat om snel te schuiven om aan immuniteit te ontsnappen. Binnen elke groep evolueerden sommige polymerasetypes iets sneller dan andere, maar de verschillen waren bescheiden. Belangrijk is dat de meeste posities in het enzym onder sterke 'zuiverende' druk stonden — mutaties die de functie verstoorden werden uitgeselect — terwijl slechts een handvol sites tekenen van positieve selectie vertoonde. Toen deze positief geselecteerde sites op driedimensionale modellen van het enzym werden geplaatst, zaten ze bijna altijd buiten de meest geconserveerde hitzones, hoewel enkelen dicht genoeg lagen om mogelijk de wijze waarop het polymerase RNA bindt of beweegt tijdens het kopiëren bij te stellen.
Wat dit betekent voor toekomstige uitbraken en behandelingen
Samen schetsen deze bevindingen het noroviruspolymerase als een verrassend stabiele kern omgeven door meer flexibele regio’s die geleidelijke aanpassing mogelijk maken. GII-polymerases, vooral die geassocieerd met historisch pandemische stammen, evolueren enigszins sneller, wat die virussen kan helpen gelijke tred te houden met veranderende gastheerders en concurrerende varianten. Toch suggereert de diepe conservatie van sleutelfunctionele regio’s over eeuwen dat dit enzym een veelbelovend vast doelwit is voor antivirale middelen: verstoor de kern van de kopieermachine en het virus heeft weinig speelruimte om te ontsnappen zonder zichzelf te verlammen. Voor niet-specialisten is de conclusie dat hoewel de buitenkanten van norovirus blijven verschuiven, waardoor nieuwe uitbraken onvermijdelijk zijn, de binnenmotor die deze veranderingen aandrijft zowel sterk begrensd als wetenschappelijk benaderbaar is — en daarmee een stabiel mikpunt biedt voor toekomstige therapieën.
Bronvermelding: Flint, A., Jawad, M. & Nasheri, N. Molecular evolution and diversity of the norovirus RNA-dependent RNA polymerase. Sci Rep 16, 9042 (2026). https://doi.org/10.1038/s41598-026-40248-5
Trefwoorden: norovirus, virale evolutie, RNA-polymerase, antivirale doelwitten, moleculaire epidemiologie