Clear Sky Science · nl
Klinisch interpreteerbaar extracellulair vesikel-genmodel voor niet-invasieve leverkankerdetectie
Waarom een bloedtest voor leverkanker ertoe doet
Leverkanker behoort wereldwijd tot de dodelijkste vormen van kanker, grotendeels omdat de ziekte vaak te laat wordt ontdekt voor genezende behandeling. De huidige middelen om vroege detectie te bereiken—beeldvorming en leverbiopten—zijn duur, soms riskant en niet altijd nauwkeurig. Deze studie onderzoekt een ander idee: of een eenvoudig bloedmonster, geanalyseerd met slimme computermodellen, vroege signalen van leverkanker kan onthullen door heel kleine genetische boodschappen te lezen die zieke cellen in de bloedbaan uitsturen.
Kleine boodschappers drijven in ons bloed
Alle cellen in ons lichaam geven regelmatig microscopische blaasjes, zogeheten extracellulaire vesikels, af in het bloed en andere lichaamsvloeistoffen. Deze vesikels bevatten eiwitten, vetten en fragmenten genetisch materiaal die de toestand van de oorsprongscellen weerspiegelen. Kankercellen stoten ook zulke vesikels uit, maar hun lading verschilt van die van gezonde cellen. Omdat vesikels in de circulatie rondreizen, kunnen ze worden verzameld via een eenvoudige bloedafname in plaats van een naald in de lever. De auteurs gebruikten een grote openbare database, exoRBase 3.0, die gedetailleerde metingen bevat van genetisch materiaal in vesikels van honderden personen met en zonder leverkanker.
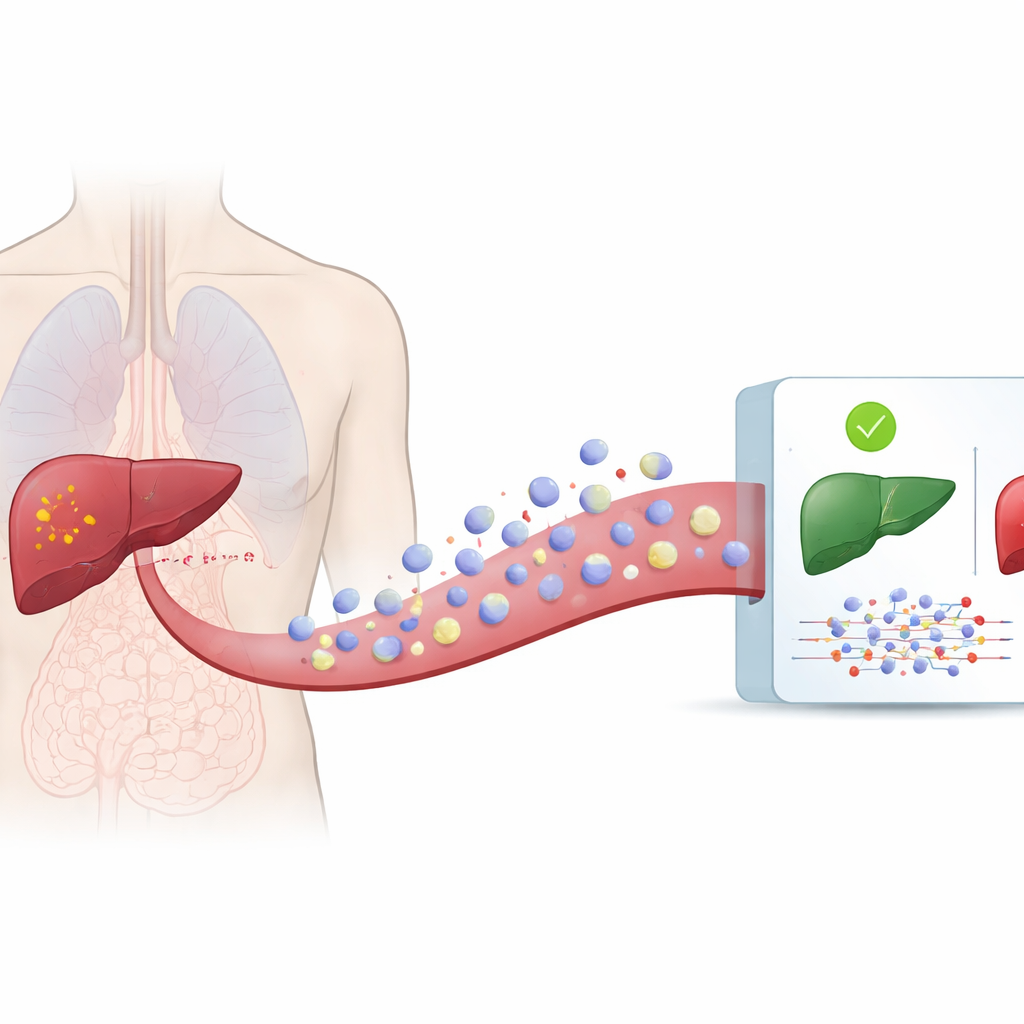
Computers leren vesikelsignalen te lezen
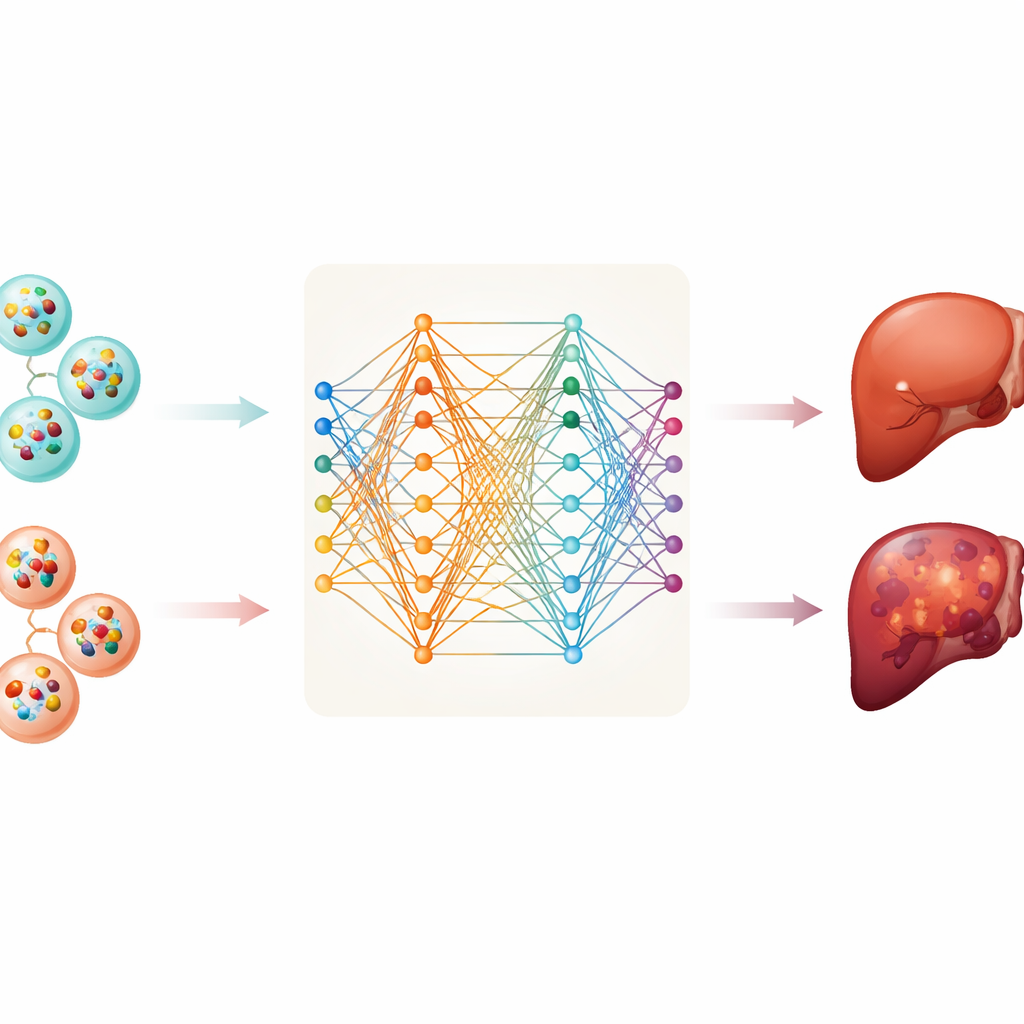
Uit deze database verzamelde het team gegevens over twee typen RNA-moleculen—messenger-RNA, dat instructies draagt voor het maken van eiwitten, en lange niet-coderende RNA’s, die helpen het celgedrag te reguleren. Ze analyseerden monsters van 112 patiënten met leverkanker en 118 gezonde individuen. Na het opschonen en standaardiseren van de data trainden ze zes verschillende computermodellen om kankermonsters van niet-kankermonsters te onderscheiden op basis van patronen in vesikel-RNA. Deze methoden varieerden van traditionele statistische instrumenten tot flexibelere diepe neurale netwerken die complexe patronen kunnen ontdekken.
Het vinden van een klein maar krachtig genpanel
Het diepe neurale netwerk behaalde de beste prestaties binnen deze dataset en kon veelal kanker van gezonde bloedmonsters scheiden. Een model dat op duizenden metingen berust is echter moeilijk te doorgronden en onpraktisch voor routinematig gebruik. Om dit op te lossen pasten de onderzoekers een methode toe genaamd SHAP, die helpt te identificeren welke invoervariabelen het meest van belang zijn voor de beslissingen van een model. Daarmee konden ze het signatuur terugbrengen tot slechts tien specifieke messenger-RNA’s die door vesikels worden gedragen. Eén daarvan, MTRNR2L8, viel op als de grootste bijdrager aan de voorspellingen van het model, met andere genen zoals HBB, PF4, FTL en S100A9 die ook belangrijke rollen speelden. Zelfs met slechts deze tien RNA’s presteerde het model nog goed, wat suggereert dat een relatief klein, gericht panel mogelijk voldoende kan zijn voor een bloedtest.
De ‘zwarte doos’ van kunstmatige intelligentie openen
Artsen zijn vaak terughoudend bij computermodellen die uitspraken doen zonder duidelijke onderbouwing. Om vertrouwen te bouwen legde het team de nadruk op transparantie. SHAP werd niet alleen gebruikt om het belang van elk gen in het geheel te rangschikken, maar ook om, voor een bepaalde patiënt, te laten zien hoe elk gen de voorspelling naar “kanker” of “gezond” duwde. De onderzoekers probeerden ook een nieuwere netwerksoort, het Kolmogorov–Arnold-netwerk, dat relaties tussen invoer en uitvoer met expliciete wiskundige krommen weergeeft. Deze aanpak bevestigde dat dezelfde tien genen sterke signalen dragen en illustreerde hoe hun gecombineerde gedrag de uiteindelijke beslissing vormt, wat een beter interpreteerbaar beeld oplevert van wat het model heeft geleerd.
Van laboratoriumconcept naar mogelijke klinische tool
Als proof of concept bouwden de auteurs een online demonstratieplatform waar gebruikers vesikel-genmetingen kunnen invoeren en de door het model voorspelde kans op leverkanker kunnen zien, samen met een visuele uitsplitsing welke genen het resultaat beïnvloedden. Ze benadrukken echter dat het werk nog experimenteel van aard is. Het model is tot nu toe alleen getest op gegevens uit dezelfde openbare database, en patiënten in de echte wereld hebben vaak gemengde leverziekten, uiteenlopende behandelingen en technische verschillen in hoe monsters worden verzameld. Grotere, zorgvuldig ontworpen studies in onafhankelijke patiëntengroepen—met gestandaardiseerde methoden—zullen nodig zijn voordat zo’n test in ziekenhuizen of screeningsprogramma’s kan worden ingezet.
Wat dit betekent voor patiënten
Deze studie toont aan dat een kleine set genetische markers, gedragen door kleine deeltjes in het bloed, in principe kan helpen leverkanker te detecteren zonder invasieve procedures. Door deze markers te combineren met computermodellen die artsen kunnen begrijpen en inspecteren, wijst het werk in de richting van toekomstige bloedtests die zowel nauwkeurig als betrouwbaar zijn. Hoewel er nog aanzienlijke obstakels zijn voordat klinisch gebruik mogelijk is—zoals het bevestigen van de uitkomsten in verschillende populaties en het waarborgen dat de test praktisch en betaalbaar is—biedt dit onderzoek een voorproefje van hoe liquid biopsies en interpreteerbare kunstmatige intelligentie op termijn een vroegere, veiligere diagnose van leverkanker zouden kunnen mogelijk maken.
Bronvermelding: Zhang, Y., Mo, Z., Zhang, L. et al. Clinically interpretable extracellular vesicle gene model for Non-Invasive liver cancer diagnosis. Sci Rep 16, 9054 (2026). https://doi.org/10.1038/s41598-026-40020-9
Trefwoorden: leverkanker, liquid biopsy, extracellulaire vesikels, machine learning, vroege diagnose