Clear Sky Science · nl
CiCLoDS: Gezamenlijke celclustering en genselectie voor single-cell ruimtelijke transcriptomica
Buurtwijken vinden in de stad van cellen
Moderne microscopen kunnen nu aflezen welke genen actief zijn in honderdduizenden cellen terwijl elke cel op zijn oorspronkelijke plaats in het weefsel blijft. Deze "ruimtelijke transcriptomica"-revolutie is alsof je een vage stadskaart verandert in een straatbeeld van elk huis. Er is echter een probleem: deze kaarten bevatten metingen voor duizenden genen per cel, veel meer dan wetenschappers gemakkelijk kunnen interpreteren of betaalbaar kunnen meten in vervolgexperimenten. Deze studie introduceert CiCLoDS, een nieuwe methode die betekenisvolle cellulaire buurten vindt en tegelijkertijd een kleine, interpreteerbare lijst genen selecteert die die buurten definiëren.
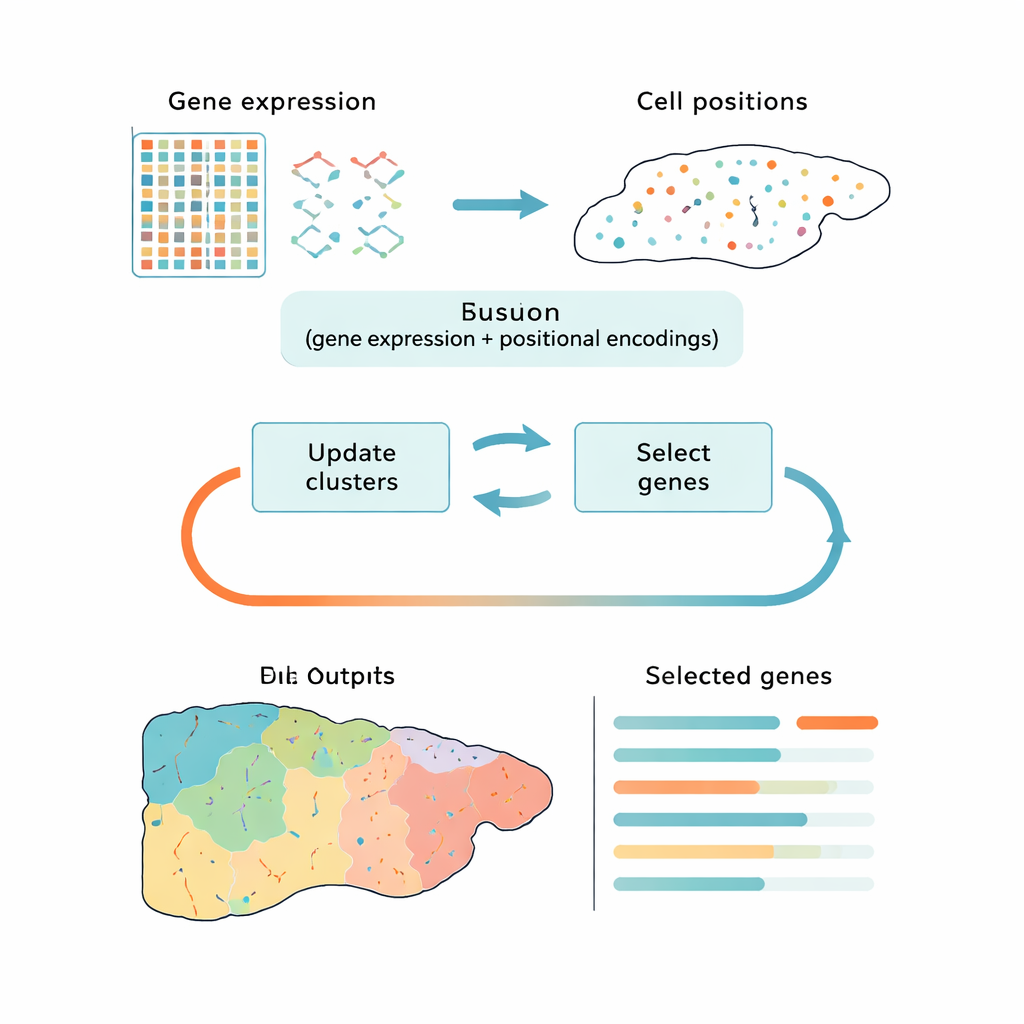
Een slimmer manier om big data te verkleinen
De meeste huidige tools pakken deze uitdaging in twee losgekoppelde stappen aan: eerst reduceren ze de data naar een eenvoudiger vorm, daarna groeperen ze cellen in clusters. Populaire benaderingen zoals principal component analysis (PCA) behouden de algemene variatie maar kunnen zich richten op technische ruis of generieke celdelingssignalen in plaats van op de biologische verschillen die ertoe doen. Andere methoden gebruiken deep learning om patronen te vinden, maar werken als black boxes en geven niet duidelijk aan welke genen het belangrijkst zijn. CiCLoDS kiest een andere route. Het behandelt genselectie en clustering als één gezamenlijk probleem binnen een door de gebruiker gedefinieerd "budget" voor hoeveel genen bewaard mogen blijven. In wezen vraagt het: welke beperkte set genen verklaart het beste hoe cellen in verschillende groepen vallen, gegeven zowel hun genactiviteit en, indien beschikbaar, hun fysieke positie in het weefsel?
Van wiskunde naar kaarten van echte weefsels
De auteurs passen een familie van wiskundig transparante technieken genaamd subspace clustering aan aan de realiteit van ruimtelijke transcriptomica, waar datasets meer dan een miljoen cellen kunnen bevatten. CiCLoDS werkt op een eenvoudige cel‑bij‑gen tabel, wijst cellen toe aan clusters en scoort elk gen op hoeveel het helpt die clusters te scheiden. Het kan ook ruimtelijke informatie verwerken door positionele "encoderingen" toe te voegen die beschrijven waar elke cel zich in het weefsel bevindt, zonder de kernoptimalisatie te veranderen. Op grote muislever- en menselijk colon-datasets gegenereerd door hoogresolutie-imagingplatforms draait CiCLoDS binnen enkele minuten op standaardcomputers en produceert compacte genpanels—van enkele tientallen tot een paar honderd genen—die toch de rijke structuur van de oorspronkelijke data vastleggen.
Verborgen zones en bloedvaten onthullen
Bij toepassing van CiCLoDS op muislever vroeg het team zich af of de methode bekende "zonatie"-patronen kon terugvinden—geleidelijke verschuivingen in hepatocytenfunctie van de ene kant van het lobulus naar de andere. In vergelijking met PCA en een toonaangevende genselectietool genaamd geneBasis produceerde CiCLoDS schonere ruimtelijke zones met scherpere grenzen en veel minder verkeerd toegewezen regio's, zoals te zien is in kwantitatieve maatstaven die overeenstemming met een referentiekaart meten. Opmerkelijk genoeg herontdekte CiCLoDS, wanneer het meer genen mocht gebruiken, peri‑portaal‑achtige en peri‑centraal‑achtige hepatocytengroepen die nauw overeenkwamen met door experts gedefinieerde referentieclusters, ondanks dat het niet geïnformeerd was over het belangrijke biomerkergen AXIN2 of expliciete ruimtelijke coördinaten kreeg. Toen ruimtelijke encoderingen werden toegevoegd, leerde CiCLoDS ook genpanels die verrijkt waren voor celoppervlak- en vatgerelateerde functies en kon het echte bloedvaten nauwkeurig onderscheiden van beeldartefacten—iets waar eenvoudigere methoden in faalden of alleen bereikten met meer ad-hoc aanpassingen.
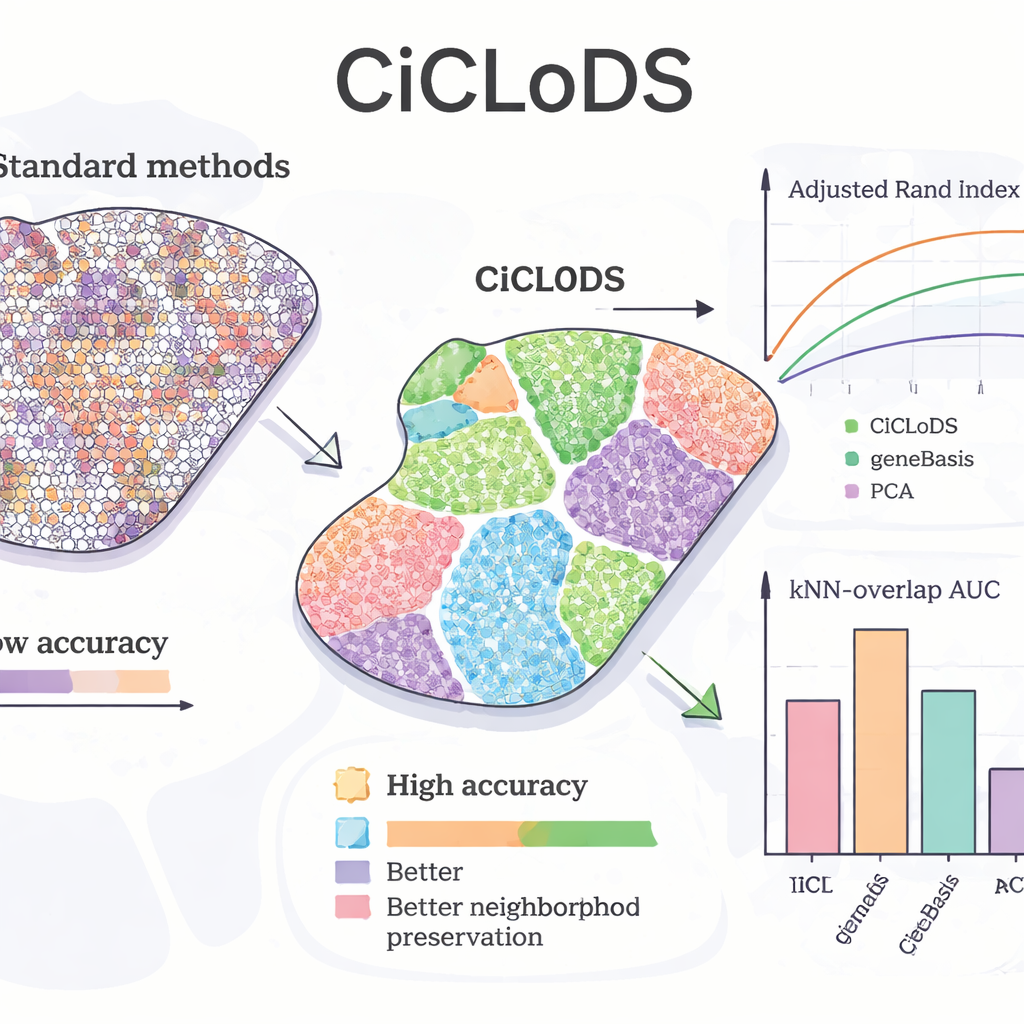
Generaliseerbaar over hersenen en het verbeteren van andere methoden
Om te testen of CiCLoDS standhoudt over zeer verschillende weefsels en individuen, analyseerden de auteurs menselijke dorsolaterale prefrontale cortexmonsters van drie donoren. Hier presteerde CiCLoDS gelijk aan of beter dan gespecialiseerde ruimtelijke methoden zoals BayesCafe en BayesSpace, vooral op een lastiger monster waar de andere tools moeite mee hadden. De studie benadrukt ook een "hybride" gebruik: eerst CiCLoDS laten draaien om stabiele clusters te krijgen, en die vervolgens in BayesSpace invoeren. Deze warm-startstrategie verhoogde de algehele nauwkeurigheid en produceerde hersenlaagpatronen die het beste overeenkwamen met deskundige annotaties, wat laat zien dat CiCLoDS zowel op zichzelf kan staan als downstream probabilistische modellen betrouwbaarder kan maken.
Waarom dit belangrijk is voor biologie en geneeskunde
Voor niet‑specialisten is de belangrijkste conclusie dat CiCLoDS overweldigende cellulaire kaarten omvormt tot beknopte, biologisch betekenisvolle samenvattingen. In plaats van te werken met duizenden lawaaierige metingen krijgen onderzoekers een hanteerbare lijst genen en duidelijke ruimtelijke clusters die echte weefselorganisatie weerspiegelen—metabole zones in de lever, bloedvaten en hun niches, en gelaagde structuren in de hersenen. Omdat het genbudget door de gebruiker wordt beheerd en de berekeningen lichtgewicht zijn, kan CiCLoDS helpen bij het ontwerpen van gerichte genpanels voor toekomstige experimenten, het begeleiden van de interpretatie van complexe ruimtelijke datasets en het bieden van robuuste startpunten voor meer uitgebreide modellering. In een tijdperk waarin de bottleneck niet langer dataverzameling maar begrip is, beloven tools als CiCLoDS hoge-dimensionale weefselkaarten zowel praktisch als inzichtgevend te maken.
Bronvermelding: Wang, N., He, Y., Ray, E. et al. CiCLoDS: Joint cell clustering and gene selection for single-cell spatial transcriptomics. Sci Rep 16, 5356 (2026). https://doi.org/10.1038/s41598-026-39168-1
Trefwoorden: ruimtelijke transcriptomica, celclustering, selectie van genpanel, weefselarchitectuur, single-cell analyse