Clear Sky Science · nl
Nieuwe markergenen voor gelijktijdige detectie van Salmonella, EHEC O157:H7 en Cronobacter
Waarom dit van belang is voor alledaagse voedselveiligheid
Van sla en hamburgers tot zuigelingenvoeding: het voedsel waarop we vertrouwen kan soms gevaarlijke ziekteverwekkers bevatten. Drie van de meest zorgwekkende boosdoeners — bepaalde stammen van E. coli, Salmonella en een minder bekend type bacterie genaamd Cronobacter — kunnen ernstige ziekten veroorzaken, vooral bij jonge kinderen en kwetsbare volwassenen. Deze studie laat zien hoe wetenschappers enorme DNA-databanken en slimme laboratoriumtests gebruiken om alledrie deze bedreigingen tegelijk, snel en nauwkeurig op te sporen voordat besmet voedsel uw tafel bereikt.
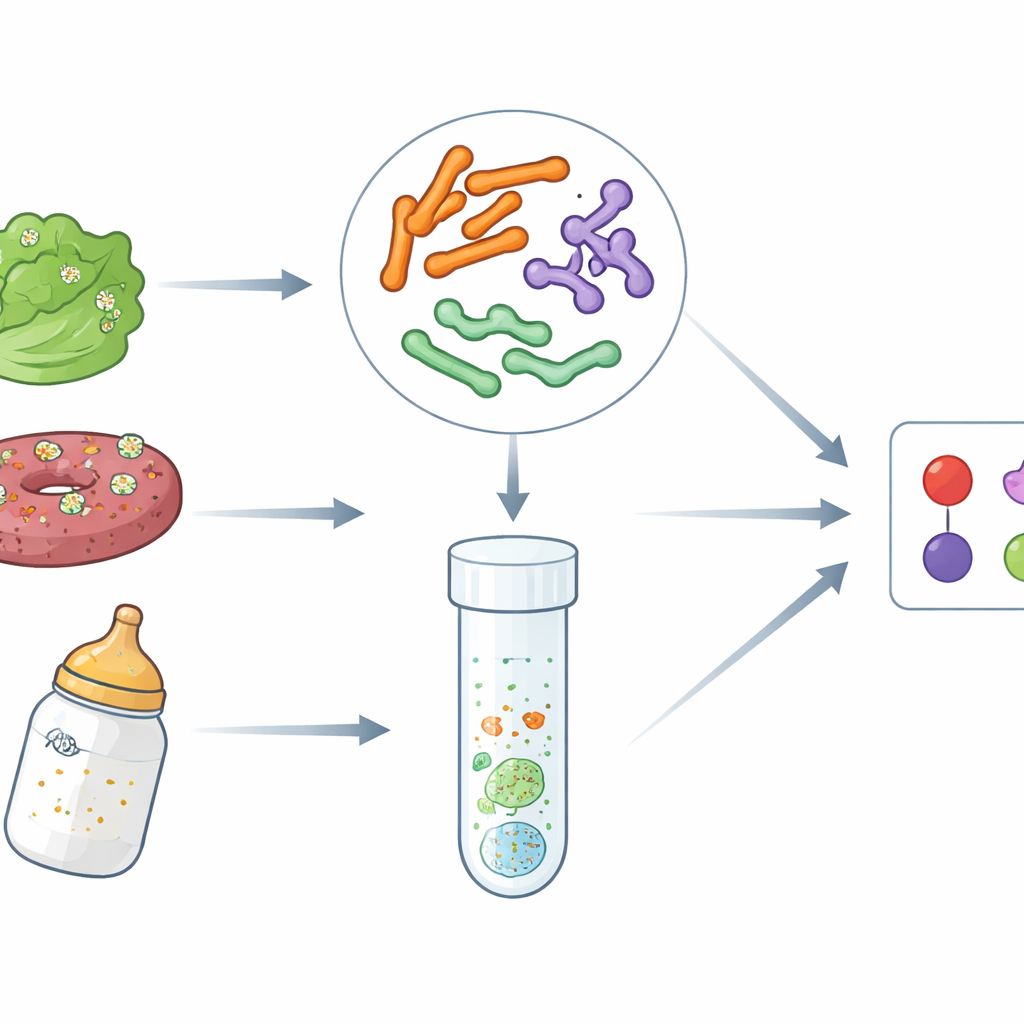
Verborgen gevaren in alledaagse voedingsmiddelen
Voedselgerelateerde ziekten zijn in het afgelopen decennium toegenomen, deels door wereldwijde toeleveringsketens en het grote volume aan bewerkte en kant-en-klare voedingsmiddelen. EHEC O157:H7, een zeer toxische vorm van E. coli, kan bloedige diarree en nierfalen veroorzaken. Salmonella zorgt jaarlijks voor miljoenen gevallen van voedselvergiftiging, en Cronobacter, hoewel minder bekend, kan dodelijk zijn voor pasgeborenen, met name in verband met poedervoeding voor zuigelingen. Traditionele laboratoriummethoden richten zich vaak op één micro-organisme per keer en vereisen dagen van kweek, wat onderzoek naar uitbraken en routinematige screening vertraagt. De auteurs wilden snellere DNA-gebaseerde tests ontwikkelen die deze drie ziekteverwekkers samen in één gestroomlijnd procedure kunnen signaleren.
“Barcodes” vinden in een zee van DNA
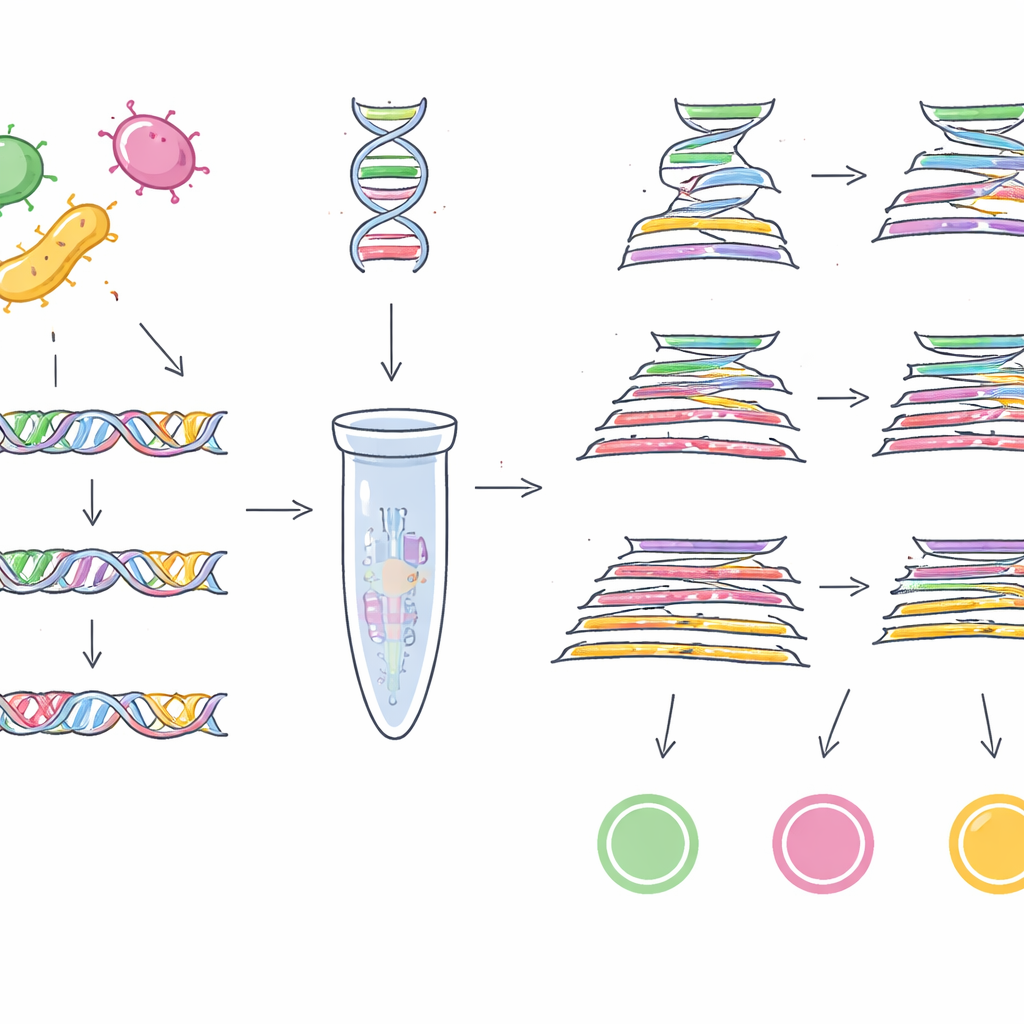
Hiervoor had het team eerst betrouwbare genetische “barcodes” nodig — korte DNA-stukken die in bijna alle stammen van een doelmicrobe aanwezig zijn maar afwezig in andere. In plaats van een handvol genomen te doorzoeken, maakten ze gebruik van een enorme openbare verzameling van 1,46 miljoen bacteriële genomen uit 50 verschillende geslachten. Voor EHEC O157:H7 vergeleken ze duizenden E. coli-genomen en probeerden meer dan 100.000 accessoire genfamilies om DNA-sequenties te vinden die uniek zijn voor deze gevaarlijke subtype. Na meerdere filtratierondes en kruiscontroles tegen meer dan een miljoen niet-E. coli-genomen, kwamen ze uit op een gen genaamd z0340 als een zeer specifieke marker voor EHEC O157:H7. Met een vergelijkbare strategie op meer dan een half miljoen Salmonella-genomen en bijna een miljoen andere bacteriële genomen, identificeerden ze een ander gen, sbcC, als een betrouwbare marker voor de Salmonella-groep als geheel.
Markers omzetten in praktijktests
Met deze twee nieuwe barcodes — plus een Cronobacter-specifiek gen, ygcB, dat de groep eerder had ontdekt — ontwierpen de onderzoekers laboratoriumtests die alle drie de pathogenen in één keer kunnen detecteren. Ze bouwden multiplex PCR-assays, die fungeren als moleculaire kopieerapparaten gericht op specifieke DNA-stukken, en een meer gevoelige TaqMan kwantitatieve PCR-versie die in realtime meet hoeveel doel-DNA aanwezig is. Wanneer deze tests werden uitgedaagd met 23 stammen van de drie pathogenen en 100 stammen van andere veelvoorkomende bacteriën, selecteerden ze telkens correct alleen de bedoelde doelwitten, wat 100% specificiteit toonde. De basis multiplex PCR kon detecteren tot 1 picogram DNA per microliter, terwijl de TaqMan-versie ging tot 0,5 picogram, wat wijst op hoge gevoeligheid.
De methoden op voedsel testen
Laboratoriumnauwkeurigheid is alleen nuttig als de tests ook werken in rommelige, realistische monsters. Om dit te controleren besmetten de wetenschappers sla, rundergehakt en zuigelingenpoeder opzettelijk met bekende hoeveelheden EHEC O157:H7, Salmonella of Cronobacter. Na standaard verrijkingsstappen om aanwezige bacteriën te laten vermenigvuldigen, pasten ze hun multiplex PCR- en TaqMan qPCR-assays toe. In alle gevallen detecteerden de methoden correct de geïntroduceerde pathogeen en gaven geen valse alarmen bij negatieve controles. De prestaties waren consistent over alle drie voedseltypen, wat suggereert dat vetten, plantaardige componenten of complexe ingrediënten de detectie niet merkbaar verstoorden.
Beperkingen en toekomstige verbeteringen
Ondanks de sterke resultaten merken de auteurs op dat hun validatiepaneel nog steeds slechts een klein deel vertegenwoordigt van de microbiële diversiteit in de natuur. Zo testten ze in het laboratorium slechts één EHEC O157:H7-stam, hoewel hun genoomgebaseerde screening tienduizenden van dergelijke stammen omvatte. Ze werkten ook met relatief hoge besmettingsniveaus vergeleken met de extreem lage aantallen bacteriën die nog ziekte kunnen veroorzaken. Toekomstig werk zal veel meer real-world isolaten moeten testen, natuurlijk besmet voedsel moeten onderzoeken en interne controles moeten toevoegen om te beschermen tegen stoffen in voedsel die DNA-amplificatie kunnen remmen.
Wat dit betekent voor consumenten
In gewone bewoordingen toont deze studie aan dat zorgvuldig gekozen DNA-barcodes voedselveiligheidslaboratoria in staat kunnen stellen om meerdere hoogrisico-pathogenen tegelijk te screenen, met hoge nauwkeurigheid en in minder tijd dan traditionele kweekgebaseerde methoden. Door miljoenen genomen te analyseren identificeerden de onderzoekers drie genetische signaturen — één voor EHEC O157:H7, één voor Salmonella en één voor Cronobacter — die zowel zeer specifiek als stabiel lijken te zijn. De resulterende tests zouden routinemonitoring van voedingsmiddelen zoals bladgroenten, vlees en zuigelingenvoeding kunnen versterken, waardoor besmetting eerder en betrouwbaarder wordt opgespoord. Buiten deze drie pathogenen kan dezelfde genoom-eerste benadering worden gebruikt om snelle tests voor vele andere gevaarlijke microben te ontwerpen, wat een krachtig nieuw instrument biedt om de wereldwijde voedselvoorziening veiliger te maken.
Bronvermelding: Zhang, H., Xiong, P., Lu, Z. et al. Novel marker genes for simultaneous detection of Salmonella, EHEC O157:H7, and Cronobacter. Sci Rep 16, 9362 (2026). https://doi.org/10.1038/s41598-026-38990-x
Trefwoorden: voedselgerelateerde ziekteverwekkers, multiplex PCR, genomische markers, Salmonella en EHEC, detectie van Cronobacter